Clear Sky Science · sv
Telomer-till-telomer komplett genometssammansättning av Opsariichthys evolans (Cypriniformes: Cyprinidae)
En bäckfisk med en genomisk berättelse
Forsande bergsbäckar i sydöstra Kina och Taiwan hyser en liten, färgstark fisk kallad Opsariichthys evolans. Trots att den är relativt okänd utanför regionen är arten en ekologisk hörnsten och ett naturens konstverk, med klara ränder och iögonfallande lekt färgskiftningar. I mer än ett sekel har forskare diskuterat hur den ska klassificeras och hur den passar in i sötvattensfiskarnas släktträd. Denna studie levererar en viktig pusselbit: det första kompletta, gapfria genomet för O. evolans, läst från ena kromosomänden till den andra.
Varför denna fisk spelar roll
O. evolans lever i klara, strömmande bäckar där den hjälper till att hålla näringsvävarna i balans och fungerar som en känslig indikator på vattenkvalitet. Hanarna utvecklar under lektiden livfulla sidostrimmor och korniga knölar på huvudet och runt ögonen, tillsammans med en mörk, svartviolett nos. Dessa iögonfallande drag, kombinerat med fiskens preferens för snabbflytande vatten, gör den idealisk för studier av hur djur anpassar sig till sina miljöer. Samtidigt minskar människodrivna förändringar — föroreningar, fragmentering av livsmiljöer och invasiva arter — dess populationer, vilket gör det viktigt att förstå dess biologi för bevarandeinsatser.
En långdragen namnförvirring
I årtionden har biologer haft svårt att avgöra om O. evolans hör hemma i släktet Opsariichthys eller i Zacco. Tidiga taxonomer beskrev arten som Zacco evolans, och baserade sitt beslut till stor del på yttre kännetecken som fenornas form och kroppsstrimmor. Senare, mer detaljerade studier visade att dess randmönster och lekknölar skiljer sig från den liknande Zacco platypus. Studier av mitokondrie-DNA föreslog att O. evolans passar bäst inom Opsariichthys, men vissa nukleära gendata antydde en närmare koppling till Zacco. Utan ett komplett genom förblev den evolutionära bilden otydlig och debatten om dess rätta plats i fiskarnas familjeträd fortsatte.

Att läsa varje bokstav i genomet
För att lösa dessa frågor samlade forskarna in en vild hane från en flod i Anhui-provinsen, Kina, och bevarade noggrant nio olika vävnader. De kombinerade sedan flera avancerade DNA-sekvenseringstekniker, var och en med sina styrkor, för att avläsa djurets genetiska kod. Korta, mycket exakta fragment användes för att polera sekvensen, medan långa och ultralånga läsningar från PacBio och Oxford Nanopore-plattformar spände över svåråtkomliga regioner och sömmande samman kromosomer från ända till ända. Hi-C-teknik, som fångar hur DNA viks inne i cellen, användes för att ordna bitarna till fullängdskromosomer. Slutresultatet är ett telomer-till-telomer, gapfritt genom på cirka 0,89 miljarder baspar, prydligt organiserat i 39 kromosomer med en kontinuerlig DNA-bit för var och en.
Vad genomet avslöjar
Det färdiga genomet klarade strikta kvalitetskontroller, fångade mer än 99 % av förväntade bevarade gener och alignerade nära kända DNA-sekvenser från närbesläktade fiskar. Nästan hälften av genomet består av upprepade sekvenser, många av dem ”hoppargener” som kan förflytta sig och omforma genomet över evolutionär tid. Teamet identifierade nästan 30 000 protein-kodande gener och tusentals icke-kodande RNA, varav de flesta kunde kopplas till kända funktioner med hjälp av större biologiska databaser. Genom att jämföra detta nya genom med dem från två nära släktingar — Opsariichthys bidens och Zacco platypus — fann forskarna att den övergripande kromosomstrukturen är mycket lik, vilket bekräftar täta evolutionära band. Inom denna struktur pekade de ut kandidatgener och signalvägar som sannolikt är involverade i fiskens kroppsrandsfärgning och anpassningar för att leva i snabba strömmar, vilket ger ledtrådar till hur dess karakteristiska utseende och livsstil utvecklats.
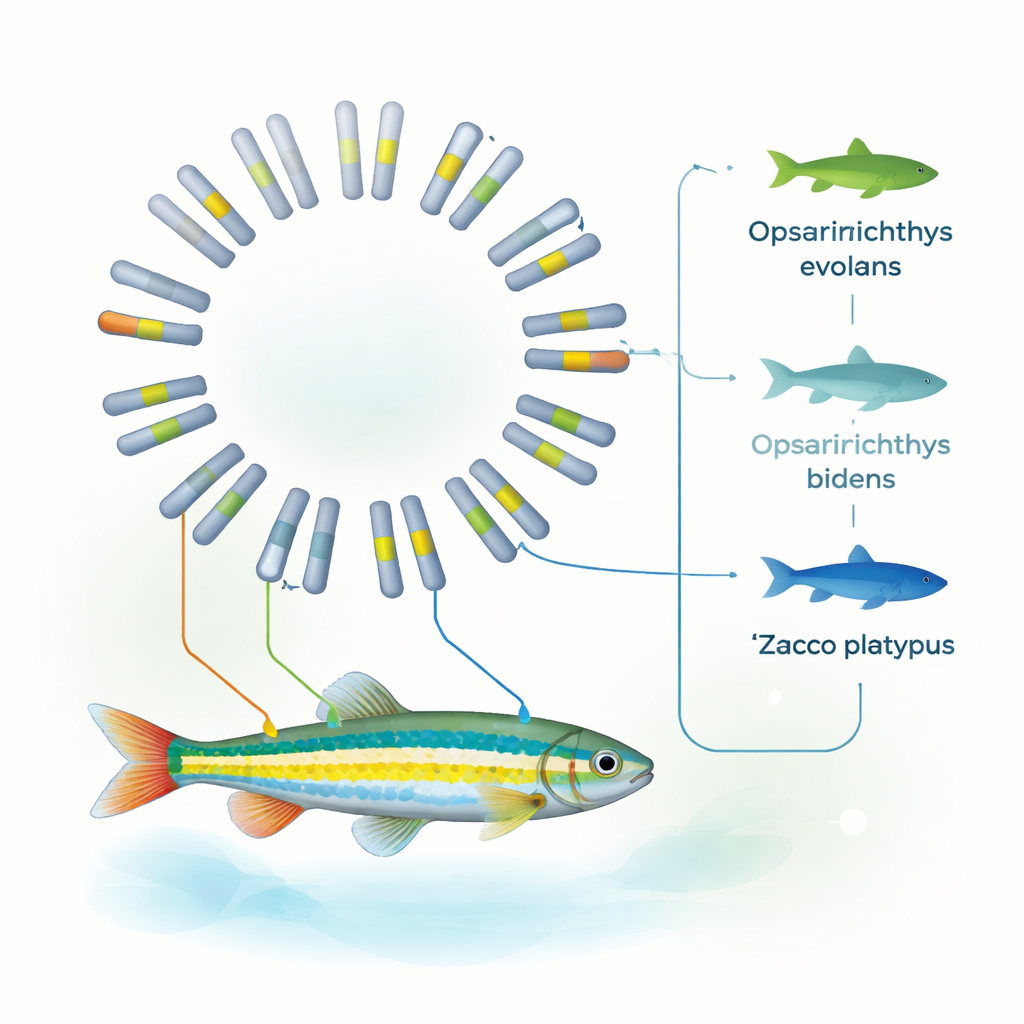
Att klargöra dess plats i fiskarnas familjeträd
Med hjälp av genfamiljer som delas över tio olika fiskarter rekonstruerade teamet ett detaljerat evolutionärt träd. Deras analys indikerar att O. evolans skilde sig från Z. platypus för ungefär 8 till 19 miljoner år sedan och att dess genomstruktur är särskilt nära den hos O. bidens. Tillsammans med tidigare mitokondriebevis stöder dessa mönster att placera O. evolans tydligt i släktet Opsariichthys, inte i Zacco. Med andra ord stärker det fullständiga genomet nu vad noggranna observationer av ränder, nosfärg och lekstrukturer antytt: utseenden kan lura, men när morfologi och ett komplett genom är överens blir taxonomiska gränser mycket klarare.
Varför ett komplett genom förändrar spelplanen
För icke-specialister är prestationen här som att gå från en suddig, sliten karta till en skarp, högupplöst atlas över en art. Med ett komplett, gapfritt genom kan forskare nu spåra ursprunget till O. evolans’s iögonfallande färger, dess strömlinjeformade form för livet i stark ström och dess relationer till andra östasiatiska småfiskar med en hittills oöverträffad precision. Denna resurs kommer att hjälpa till att förfina fiskklassificeringar, vägleda bevarandeinsatser för utsatta bäckekosystem och fördjupa vår förståelse av hur små skillnader i DNA kan skapa den rika mångfald som ses hos sötvattensfiskar.
Citering: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Nyckelord: genomsammansättning, sötvattensfisk, telomer-till-telomer, fiskevolution, jämförande genomik