Clear Sky Science · sv
En generaliserbar grundmodell för analys av mänsklig hjärn‑MRI
Att lära datorer att läsa hjärnskanningar
Magnetresonansavbildning (MRI) låter läkare se in i den levande hjärnan utan operation, men tolkningen av bilderna förlitar sig fortfarande i hög grad på mänskliga experter och stora märka dataset. Denna studie presenterar BrainIAC, en sorts "allmän hjärnmotor" som lär sig från tiotusentals omärkta hjärnskanningar och som därefter snabbt kan anpassas till många medicinska uppgifter – från att uppskatta hjärnans ålder till att avgränsa tumörer – ofta med endast några få exempel. För patienter kan sådan teknik på sikt innebära snabbare diagnoser, bättre behandlingsplanering och tillgång till avancerade avbildningsverktyg även på sjukhus med begränsad specialistkompetens.
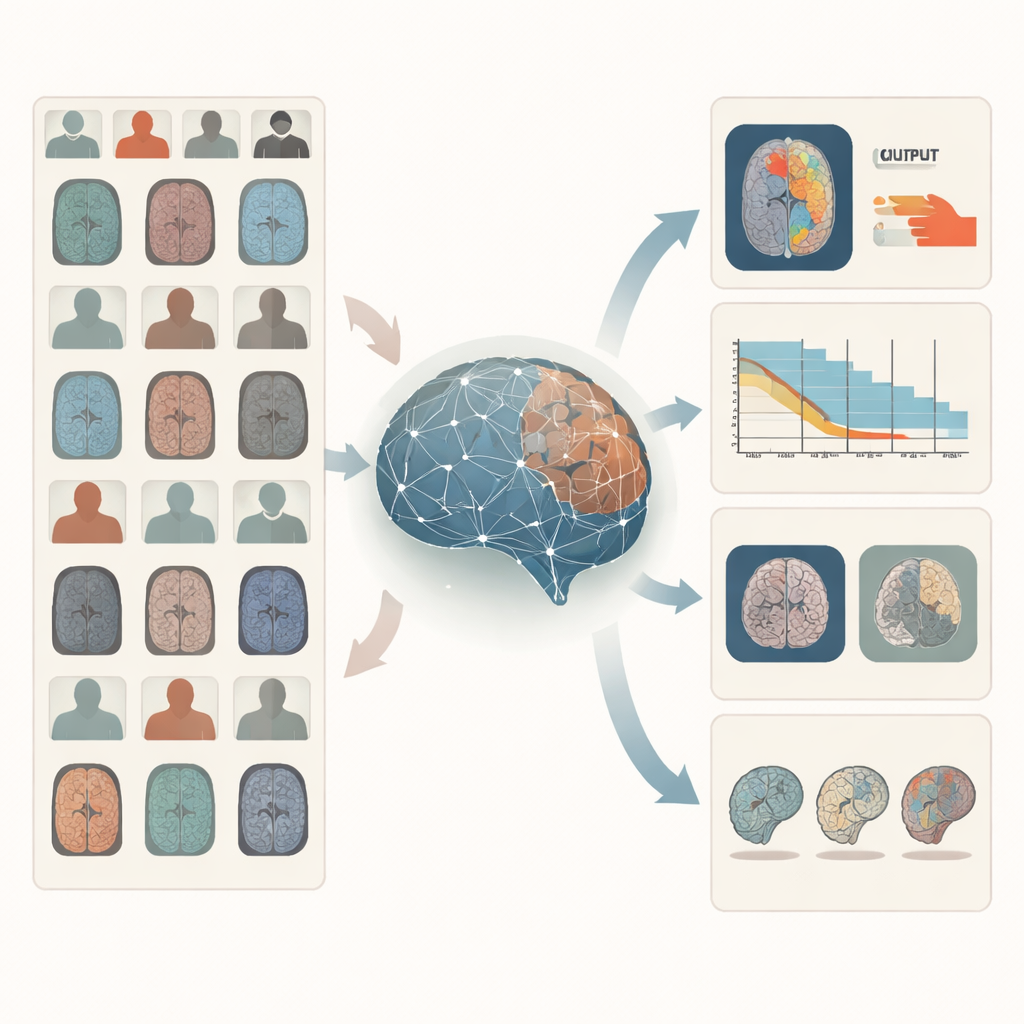
Varför hjärnskanningar är svåra för datorer
Hjärn‑MRI är informationsrikt men rörigt. En och samma person kan skannas med flera olika inställningar, där varje inställning framhäver olika vävnader eller sjukdomsdrag. Sjukhus använder en mängd olika skannrar och protokoll, så bilder kan se mycket olika ut från plats till plats. Utöver det är detaljerade expertdelar—till exempel att rita exakta tumörgränser eller följa långsiktig överlevnad—dyrt och sällsynt. Traditionella artificiella intelligenssystem tränas oftast för en smal uppgift på ett kuraterat dataset. De har svårt när de ombeds arbeta på nya sjukhus, sällsynta sjukdomar eller frågor de inte specifikt byggts för.
En enda kärnmodell för många hjärnuppgifter
BrainIAC väljer en annan väg: istället för att lära en uppgift i taget lär den först det generella "språket" för hjärnstruktur och sjukdom från 32 015 MR‑skanningar hämtade från 34 dataset och tio neurologiska tillstånd, med nästan 49 000 skanningar i hela poolen. Modellen tränas självövervakat, vilket betyder att den inte behöver mänskliga etiketter. Den betraktar många små tredimensionella patchar utskurna från helhjärnsbilder och lär sig avgöra när två olika augmenterade versioner kommer från samma plats respektive från olika hjärnor. Genom att dra ihop matchande patchar och trycka isär orelaterade i sitt interna representationsrum bygger BrainIAC en flexibel avbildning av hur friska och sjuka hjärnor vanligtvis ser ut över åldrar, skannrar och sjukhus.
Sätta hjärnmotorn i arbete
När denna kärnrepresentation väl är inlärd testar forskarna BrainIAC på sju konkreta uppgifter som speglar verkliga kliniska problem. Dessa inkluderar att sortera skanningar efter MRI‑sekvenstyp, uppskatta hur gammal en persons hjärna verkar, förutsäga om en hjärntumör bär på en viktig genetisk mutation, prognostisera överlevnad för patienter med aggressiva tumörer, särskilja tidiga minnesproblem från normal åldrande, uppskatta hur länge sedan en stroke inträffade, samt avgränsa tumörer på bilder. För varje uppgift jämförs tre strategier: träna en modell från grunden på just den uppgiften, starta från tidigare medicinska bildmodeller byggda för andra ändamål, eller finjustera BrainIAC:s redan inlärda hjärnfunktioner. I samtliga fall matchar eller överträffar BrainIAC alternativen, särskilt när endast begränsade märkta data finns tillgängliga.
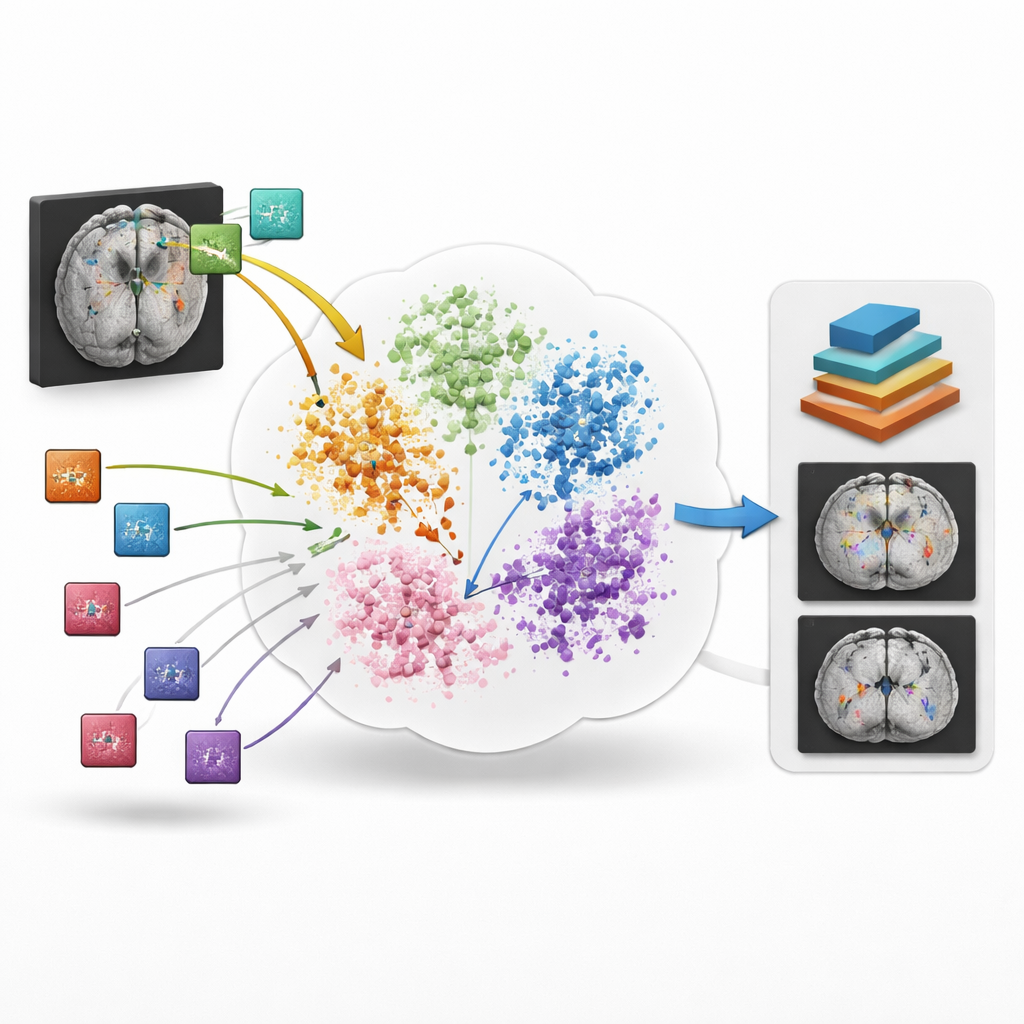
Fungerar bra när data är knappa
Ett huvudtest är hur systemet beter sig när märkta data är extremt få, vilket ofta händer vid sällsynta sjukdomar eller dyra avbildningsstudier. Teamet undersöker scenarier där endast 10 % av de vanliga träningsskanningarna används och ännu tuffare "fåskotts"‑inställningar där det bara finns ett eller fem märkta exempel per klass. Under dessa snäva villkor ger BrainIAC konsekvent mer precisa förutsägelser än modeller som tränats från scratch eller andra tillgängliga grundmodeller. Till exempel skiljer den bättre mellan subtila MRI‑sekvenstyper, förutsäger tumörgenetik och överlevnad mer exakt och ritar renare tumörkonturer med betydligt färre annoterade bilder. Modellen visar sig också mer stabil när vanliga MRI‑artefakter, såsom kontrastförskjutningar eller skannerrelaterade distorsioner, konstgjort läggs till, vilket tyder på att den lärt sig robusta funktioner snarare än bräckliga genvägar.
Vad detta kan innebära för patienter och kliniker
För att förstå om BrainIAC fokuserar på kliniskt meningsfulla regioner genererar författarna visuella "uppmärksamhetskartor" som visar var modellen tittar när den fattar beslut. Dessa kartor framhäver strukturer såsom hippocampus vid tidiga minnessvårigheter, vit substans‑regioner vid åldersbedömning och tumörkärnan för genetiska och överlevnadsrelaterade prognoser – områden som ligger i linje med mänsklig expertintuiton. Eftersom BrainIAC kan kopplas in i olika analysflöden och anpassas med minimal extra träning erbjuder den en flexibel ryggrad för framtida avbildningsverktyg, inklusive möjliga kombinationer med journaldata eller genetisk information.
Ett steg mot smartare och mer tillgänglig hjärnavbildning
Sammanfattningsvis visar studien att en enda, noggrant tränad grundmodell kan fungera som en stark utgångspunkt för många olika hjärn‑MRI‑uppgifter, och ofta överträffa specialiserade system som måste byggas om från grunden varje gång. För icke‑specialister är huvudsaken att BrainIAC fungerar som en brett utbildad "hjärnläsare" som snabbt kan plocka upp nya färdigheter med bara några få exempel. Medan den inte ersätter skräddarsydda modeller eller medicinskt omdöme lägger den viktig grund för att göra avancerade bildbaserade förutsägelser mer precisa, mer robusta och mer allmänt tillgängliga, även i situationer där insamling av stora märkta dataset annars skulle vara omöjlig.
Citering: Tak, D., Garomsa, B.A., Zapaishchykova, A. et al. A generalizable foundation model for analysis of human brain MRI. Nat Neurosci 29, 945–956 (2026). https://doi.org/10.1038/s41593-026-02202-6
Nyckelord: hjärn‑MRI, medicinsk AI, grundmodeller, självövervakad inlärning, neuroavbildning