Clear Sky Science · sv
Simulationsbaserad inferens av cellernas migrationsdynamik i komplexa rumsliga miljöer
Hur immunceller hittar fram i trånga vävnader
Våra immunceller måste ofta pressa sig igenom täta, labyrintliknande vävnader för att nå infektionsställen eller lymfknutor. Denna studie ställer en förenklat formulerad men betydelsefull fråga: hur navigerar cellerna i sådana röriga miljöer, och hur kan vi pålitligt sluta oss till deras beteenden från brusiga mikroskopdata? Genom att kombinera precist konstruerade laboratorie"labyrinter" med avancerade datasimuleringar och moderna maskininlärningsverktyg visar författarna ett nytt sätt att avkoda de regler som styr cellrörelser i komplexa omgivningar.
Bygga en liten labyrint för immunceller
För att undersöka hur miljön formar rörelsen fokuserade forskarna på dendritiska celler—immunsystemets vakter som måste förflytta sig från perifera vävnader till lymfknutor, styrda av kemiska attraktanter kallade kemoattractanter. De konstruerade en mikrofabricerad chip: en platt "pelarskog" av regelbundet placerade pelare gjorda av silikon (PDMS), med smala 10-mikrometers springor som efterliknar de trånga utrymmena i verkliga vävnader. Ena sidan av chippet fylldes med tiotusentals dendritiska celler; motsatt sida innehöll en källa för kemoattractanten CCL19, som skapar en stabil gradient över pelarna. Med tidsförloppsmikroskopi följde de cellkärnornas positioner var 30:e sekund när cellerna försökte röra sig mot kemoattractanten. 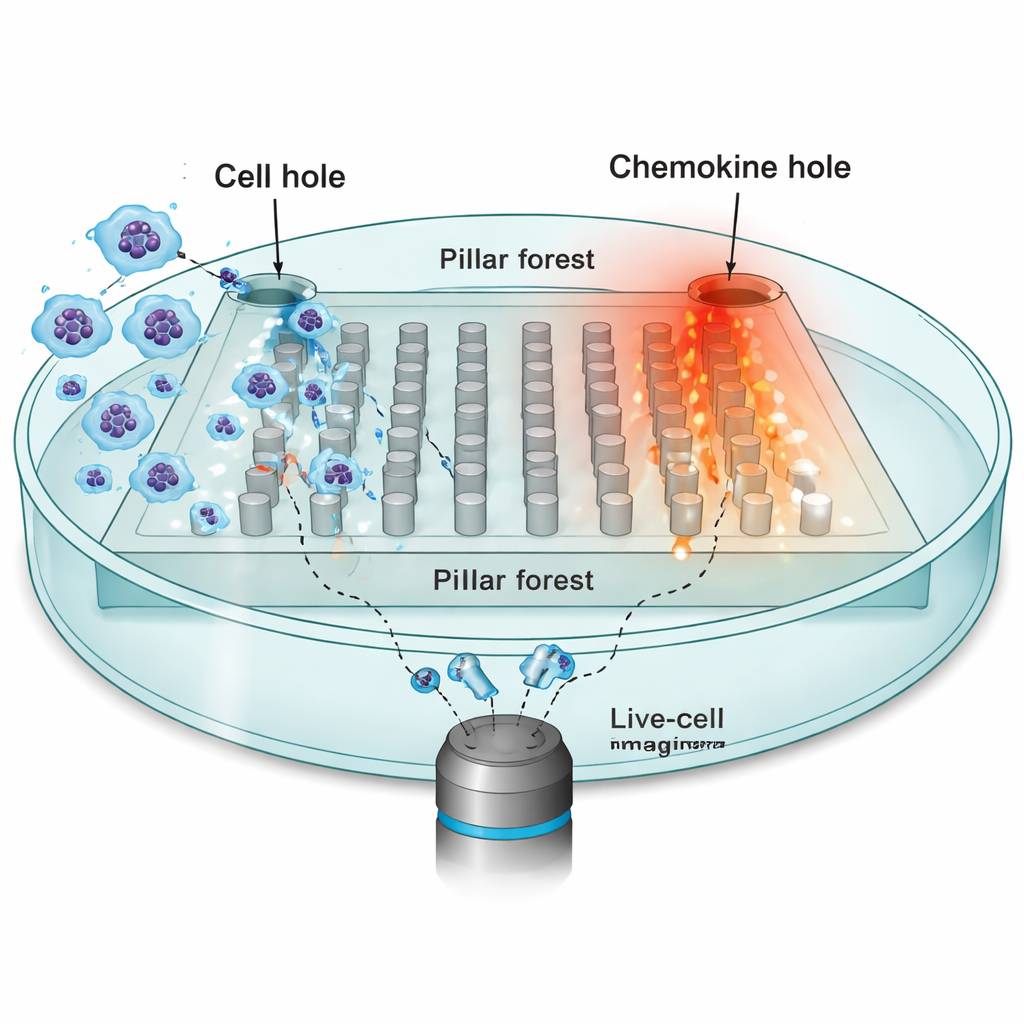
Göra biologi till ett virtuellt experiment
För att förstå denna mångfald byggde teamet en detaljerad datormodell av cellmigration med en ram kallad Cellular Potts-modellen. Istället för att behandla en cell som en enkel punkt representerar detta tillvägagångssätt varje cell som en utsträckt yta på ett gitter, vilket tillåter formförändring, att pressas mellan pelare och att reagera på kemiska signaler. Modellen innehåller fyra nyckelingredienser: hur starkt en cell dras av kemoattractantgradienten (mdir), hur mycket den tenderar att bibehålla sin nuvarande rörelseriktning (mrand), hur ofta den omorienterar sig (fångat av en hastighet λ) och dess effektiva storlek (a). Genom att justera dessa parametrar och köra simuleringar producerar modellen syntetiska spår som kan jämföras direkt med de inspelade cellbanorna i pelarskogen.
Varför handplockade mått inte räcker
Traditionellt sammanfattar forskare sådana rörelsedata med ett fåtal välkända statistiska mått—hur långt en cell förflyttar sig (förskjutning), hur snabbt den rör sig (hastighet) och hur dess riktning ändras över tid (svängningsvinklar). Författarna använde först dessa handgjorda mått inom en metod kallad approximerad Bayesiansk beräkning (ABC), som söker parametrar som gör att simulerade spår liknar de experimentella. De fann att medan dessa sammanfattningar fångar breda trender missar de mycket av den finmaskiga strukturen i data. Som en följd förblev vissa modellparametrar, särskilt de som styr slumpmässig persistens och omorienteringstidpunkter, dåligt begränsade eller till och med snedvridna. Dessutom krävde ABC hundratusentals simuleringar och många timmars beräkningstid för att nå acceptabla anpassningar.
Låta neurala nätverk lära sig vad som är viktigt
För att övervinna dessa begränsningar vände sig studien till en nyare familj metoder kallad neural posteriorestimering (NPE). Här tränas ett neuralt nätverk direkt på många par av simulerade data och underliggande parametrar. En del av nätverket lär automatiskt en kompakt uppsättning "sammanfattande funktioner" från hela samlingar av cellspår; en annan del lär sig hur dessa funktioner kartlägger tillbaka till sannolika parametervärden. Avgörande är att dessa lärda funktioner optimeras uttryckligen för noggrann parameterslutsats, inte för mänsklig tolkbarhet. Författarna återanvände sedan de lärda sammanfattningarna inom ett ABC-ramverk och skapade en hybridpipeline som kombinerar ABC:s robusthet med neurala nätverks flexibilitet. 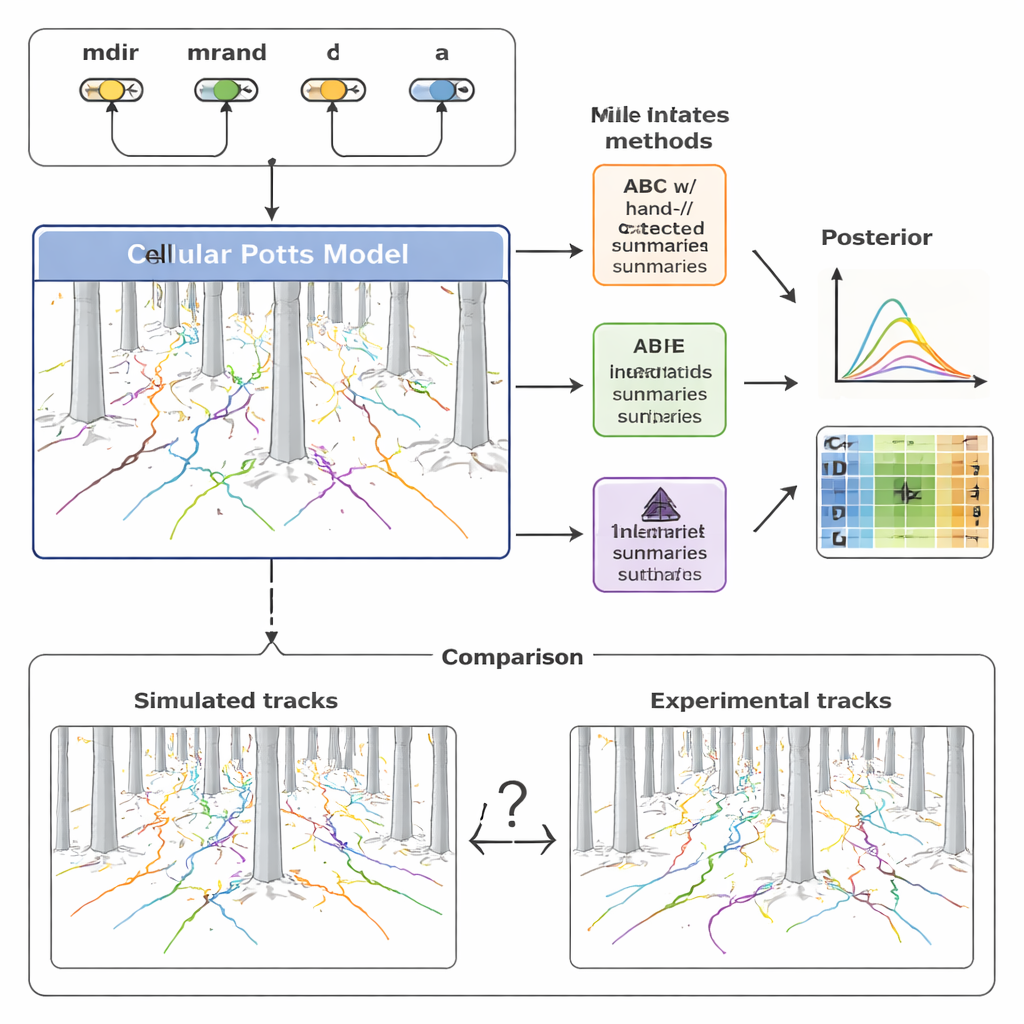
Vad den nya metoden avslöjar om cellnavigation
Med denna kalibrerade modell undersökte forskarna hur kemoattractantsignaler och fysiska hinder gemensamt formar migrationen. Den uppskattade cellstorleken indikerade att dendritiska celler effektivt krymper och deformeras för att komma igenom 10-mikrometersspringorna, i linje med deras kända flexibilitet. Simuleringarna indikerade att persistent slumpmässig rörelse är en huvudorsak till hur brett celler sprider sig, även utan kemoattractantstyrning, och att pelarskogen kan fånga celler när starka riktade signaler och persistens verkar tillsammans. Förvånande nog förutspår modellen att en kemoattractantsignal som är kortvarigt aktiv tidigt i processen i vissa fall kan hjälpa fler celler att nå målet än en konstant signal, eftersom långvarig attraktion kan hålla celler cirklandes inom hinder istället för att låta dem ta sig ut.
Varför detta spelar roll för biologi och modellering
För icke-specialister är huvudbudskapet dubbelt. För det första handlar immuncellernas migration i vävnader inte bara om att följa ett kemiskt spår; den uppstår ur ett subtilt samspel mellan vägledande signaler, cellernas egna rörelsetendenser och den fysiska utformningen av deras omgivning. För det andra kräver det att man härleder dessa regler från bilddata att datorn får lära sig vilka mönster i data som är mest informativa, snarare än att enbart förlita sig på enkla, människodesignade mått. Genom att integrera mikroengineerade experiment, formupplösande simuleringar och neurala nätverksbaserad inferens erbjuder detta arbete en kraftfull mall för att studera hur celler av många typer rör sig i komplexa miljöer, med potentiella tillämpningar från att förstå immunövervakning till att utforma bättre cancerterapier.
Citering: Arruda, J., Alamoudi, E., Mueller, R. et al. Simulation-based inference of cell migration dynamics in complex spatial environments. npj Syst Biol Appl 12, 20 (2026). https://doi.org/10.1038/s41540-026-00648-9
Nyckelord: cellmigration, dendritiska celler, kemoattraktantgradienter, simulationsbaserad inferens, mikrofluidiska pelarskogar