Clear Sky Science · sv
SMART: spatial multi-omic aggregation using graph neural networks and metric learning
Att se vävnader som kvarterkartor
Våra kroppar består av livliga cellulära kvarter där gener, proteiner och DNA-packning samverkar på precisa platser. Nya mikroskop och sekvenseringsverktyg kan nu läsa många av dessa molekylära lager direkt i tunna vävnadsskivor, men att omvandla denna flod av flerskiktiga, rumsliga data till tydliga bilder av hur organ är organiserade är en stor beräkningsutmaning. Denna studie presenterar SMART, en datormetod som hjälper forskare att förena dessa komplexa signaler till detaljerade kartor över var olika cellgemenskaper finns och hur de är ordnade.
Varför det är svårt att kartlägga cellkvarter
Moderna "spatial multi-omics"-tekniker kan mäta flera typer av molekylär information samtidigt — såsom RNA, proteiner på cellytan och hur öppet eller stängt DNA är — samtidigt som varje mätning behåller sin exakta position i en vävnadsskiva. Varje typ, eller "omik", ger en annan bild av cellernas beteende, men de är brusiga, högdimensionella och stämmer inte naturligt överens med varandra. Dessutom är celler av samma typ inte alltid klustrade; de kan förekomma som utspridda öar i ett organ. Befintliga programverktyg förbiser ofta den rumsliga layouten, förenklar hur olika omics förhåller sig till varandra eller har svårt att skala till de mycket stora dataset som nya instrument kan generera.
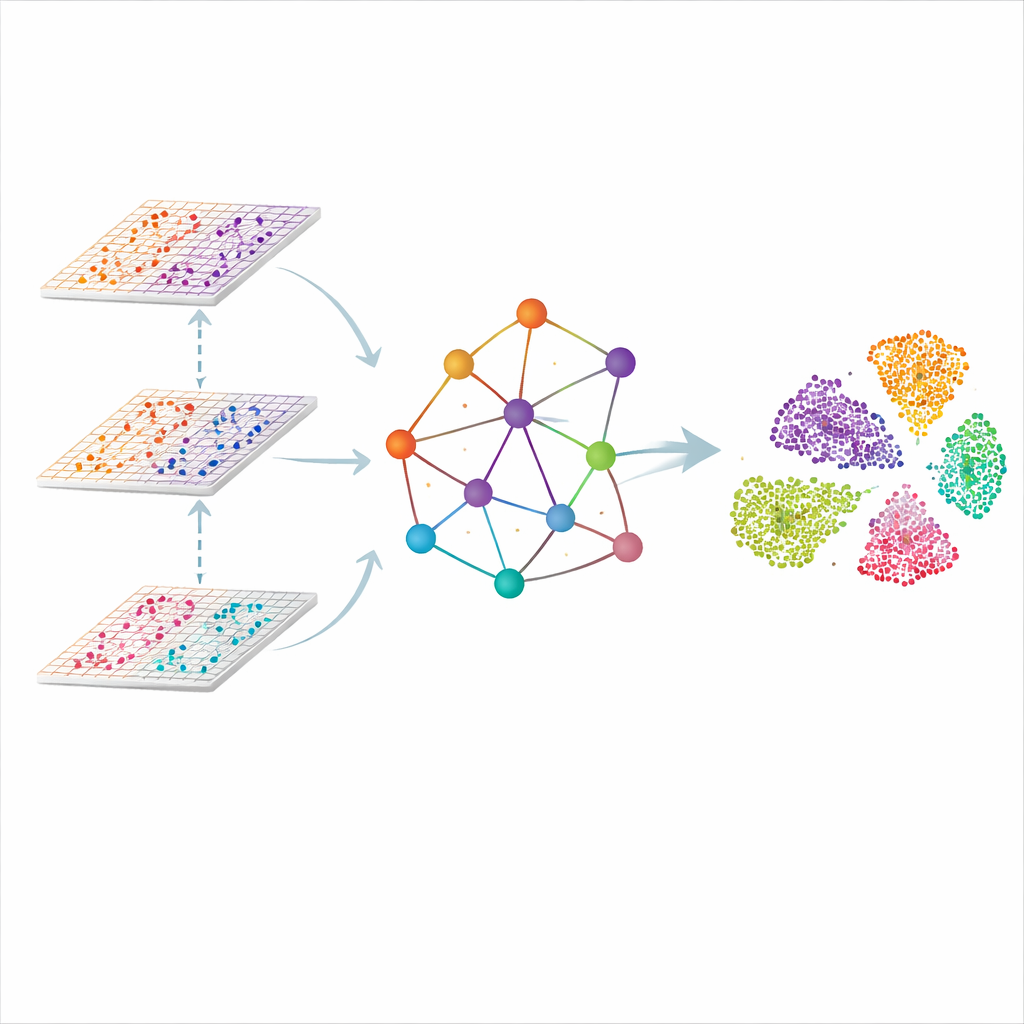
En graf över vävnaden, inte bara en lista över celler
SMART angriper problemet genom att behandla varje mätpunkt i vävnaden som en nod i ett nätverk. Närliggande punkter länkas ihop för att bilda en rumslig graf, och de molekylära avläsningarna från varje omik komprimeras först till ett mindre antal samordnade funktioner som fångar övergripande mönster snarare än enskilda gener. En typ av neuralt nätverk designat för grafer skickar sedan information längs länkarna, vilket låter varje punkt "lyssna" på sina grannar samtidigt som det håller reda på hur varje omik bidrar. Resultatet är en gemensam, lågdynamisk representation där liknande regioner i vävnaden — såsom distinkta hjärnlager eller zoner i en lymfknuta — naturligt grupperar sig tillsammans.
Att lära modellen vad som bör vara likt
Att bara följa fysiska grannar räcker inte, eftersom celler av samma typ kan ligga långt ifrån varandra. SMART lägger till en andra ingrediens hämtad från ansiktsigenkänningssystem: metric learning med tripletter. För varje punkt hittar metoden automatiskt en annan punkt med mycket liknande molekylära mönster (en "positiv") och en som är tydligt olik (en "negativ"). Den justerar sedan den interna representationen så att positiva punkter dras närmare och negativa skjuts längre bort, även om de ligger långt ifrån varandra på vävnadsskivan. Denna dragkamp körs parallellt med ett rekonstruktionssteg som tvingar SMART att bevara de viktigaste detaljerna i varje omiklager, och balanserar rumslig kontinuitet med molekylär specificitet.
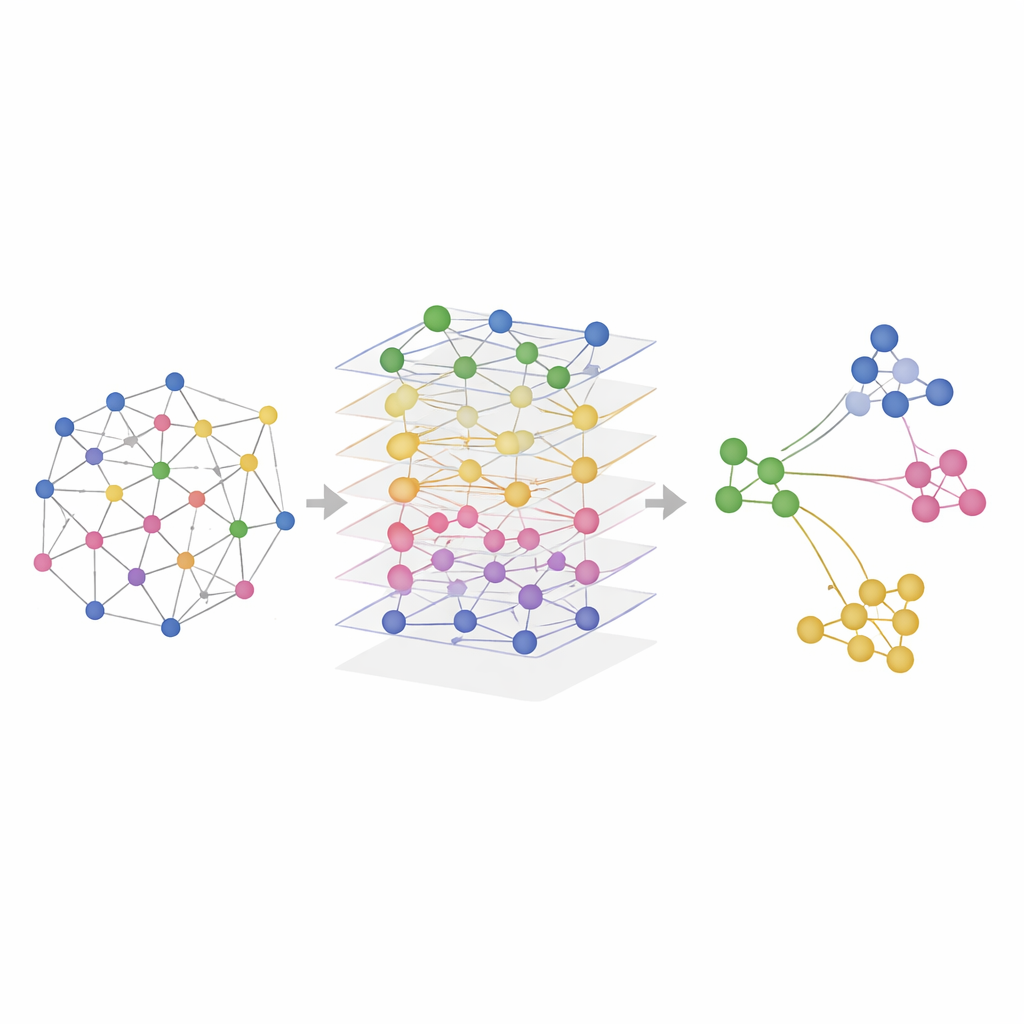
Att testa SMART i verkliga vävnader
Forskarna testade SMART både på simulerade data och på verkliga experiment som mätte kombinationer av RNA, proteiner och kromatinåtkomlighet i mössens hjärnor, mjältar, samt i mänskliga lymfknutor och tonsiller. I kontrollerade simuleringar där de sanna rumsliga regionerna var kända återfann SMART mest exakt grundmönstren och bevarade relationerna som fanns i varje omiklager. I verkliga dataset identifierade SMART konsekvent fina anatomiska strukturer — såsom specifika hjärnregioner eller immuncellzoner i lymfoida organ — skarpare än konkurrerande metoder, samtidigt som beräkningsbehovet hölls lågt. En relaterad version, kallad SMART-MS, utvidgar samma idéer över flera vävnadsskivor, alignerar sektioner från samma organ och korrigerar för tekniska skillnader mellan experiment.
Snabba kartor för nästa våg av rumslig biologi
Enkelt uttryckt är SMART en kartläggningsmotor för nästa generationens molekylatlaser. Genom att kombinera nätverksbaserad modellering av vävnadslayout med en inbyggd känsla för vad som bör räknas som "likt", kan den omvandla stora, röriga samlingar av rumsliga multi-omics-mätningar till sammanhängande kvarterkartor över organ. Det gör det lättare för forskare att upptäcka var särskilda celltyper och mikromiljöer finns, hur de förändras under utveckling eller sjukdom, och hur nya experimentella teknologier passar ihop. Allteftersom rumsliga data fortsätter att växa i storlek och komplexitet kommer verktyg som SMART och SMART-MS vara avgörande för att omvandla råa mätningar till biologisk insikt.
Citering: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Nyckelord: rumslig multi-omik, grafneurala nätverk, vävnadens mikromiljö, dataintegration, encellsbiologi