Clear Sky Science · sv
Systematisk identifiering av variant-specifika RNA-struktur–småmolekylinteraktioner exemplifierat av RNA G-quadruplex
Varför små förändringar i RNA spelar roll för framtida läkemedel
De flesta av oss ärver små skillnader i vårt DNA som gör oss unika. Dessa små förändringar kan subtilt omforma veckningen av RNA-molekyler i våra celler. Den nya studien introducerar ett sätt att se hur sådana genetiska finjusteringar ändrar greppet hos experimentella läkemedel som riktar sig mot RNA. Det är viktigt eftersom samma medicin kan bete sig mycket olika från en person till en annan, särskilt vid cancer eller genetiska sjukdomar.
Nytt sätt att se var läkemedel berör RNA
Många läkemedelsutvecklare tittar nu på RNA, inte bara proteiner, som mål för terapi. Små molekyler kan fästa vid speciella RNA-strukturer och påverka hur gener läses, men hittills har de flesta metoder bara fungerat på en enda ”referens” RNA-sekvens. De har i stor utsträckning ignorerat de otaliga enkelbokstavsförändringarna som finns hos verkliga patienter. Författarna skapade en höggenomströmningsmetod kallad BIVID-MaP som samtidigt kan testa tusentals RNA-varianter och peka ut var en småmolekyl binder varje variant, ända ner till enkel-nukleotidupplösning. 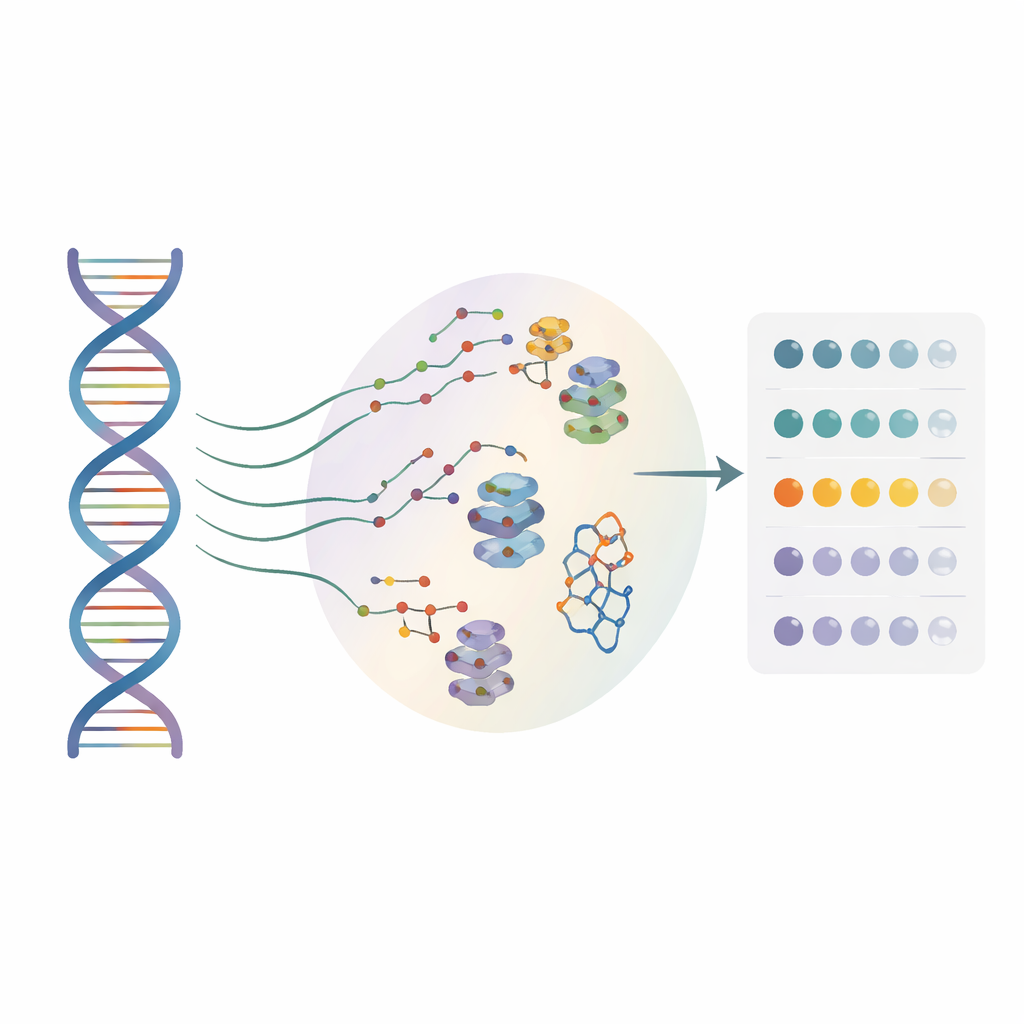
Att omvandla kemiska märken till en läsbar signal
BIVID-MaP fungerar i tre huvudsteg. Först fäster teamet en reaktiv markör på en RNA-bindande småmolekyl. När den märkta föreningen lägger sig i sin föredragna RNA-struktur, till exempel en kompakt G-quadruplex som bildas av guaninrika sekvenser, bildar markören en permanent kemisk bindning med en närliggande RNA-bas. För det andra kopierar ett särskilt enzym det modifierade RNA:t till DNA. När det stöter på ett av dessa kemiska märken tenderar det att ”hoppa över” en bas, vilket skapar en liten deletion i kopian. För det tredje läser djupsekvensering ut dessa deletionssignaturer över miljontals molekyler. Eftersom nästan hela den omgivande sekvensen bevaras kan deletionerna noggrant kopplas till specifika genetiska varianter i en blandad pool.
Bevisar metoden i ett kontrollerat testfall
För att bekräfta att BIVID-MaP verkligen upptäcker variant-specifik bindning studerade forskarna ett RNA-segment från CD44-genen som normalt bildar en G-quadruplex. En enda G-till-A-förändring stör denna struktur. I en blandning som innehöll båda versionerna visade endast den intakta formen starka deletionssignaler nära det vikta området när den utsattes för en berberinbaserad probe, och oberoende analyser verifierade starkare bindning där. Mutanten, som inte kan bilda samma form, gav avsevärt färre deletioner och svagare bindning. Andra vanliga kartläggningstekniker missade antingen denna skillnad eller gav förvirrande bakgrund, vilket understryker den förbättrade känsligheten och specificiteten hos det nya tillvägagångssättet.
Skanning av cancerkopplade mutationer över många gener
Teamet skalar sedan upp arbetet. De byggde ett RNA-bibliotek av 5′ okodade regioner (5′ UTR) från 283 cancerrelaterade gener, vardera ihopkopplad med verkliga somatiska mutationer rapporterade i tumörer. Med hjälp av en probe som känner igen G-quadruplex-liknande strukturer upptäckte BIVID-MaP många mutationer som antingen stärkte eller försvagade bindningen av småmolekyler. I gener såsom DAXX och ING2 förändrade enkelbokstavsbyten i guaninrika sträckor bindningen markant, i linje med oberoende biofysiska tester av G-quadruplexbildning och direkta bindningsmätningar med masspektrometri. I vissa fall påverkade mutationer utanför de uppenbara G-sekvenserna ändå bindningen genom att subtilt ändra hur sannolikt närliggande baser parade sig, och omformade den strukturella ”ensemblen” utan att grovt förändra den förutsagda övergripande vikningen. 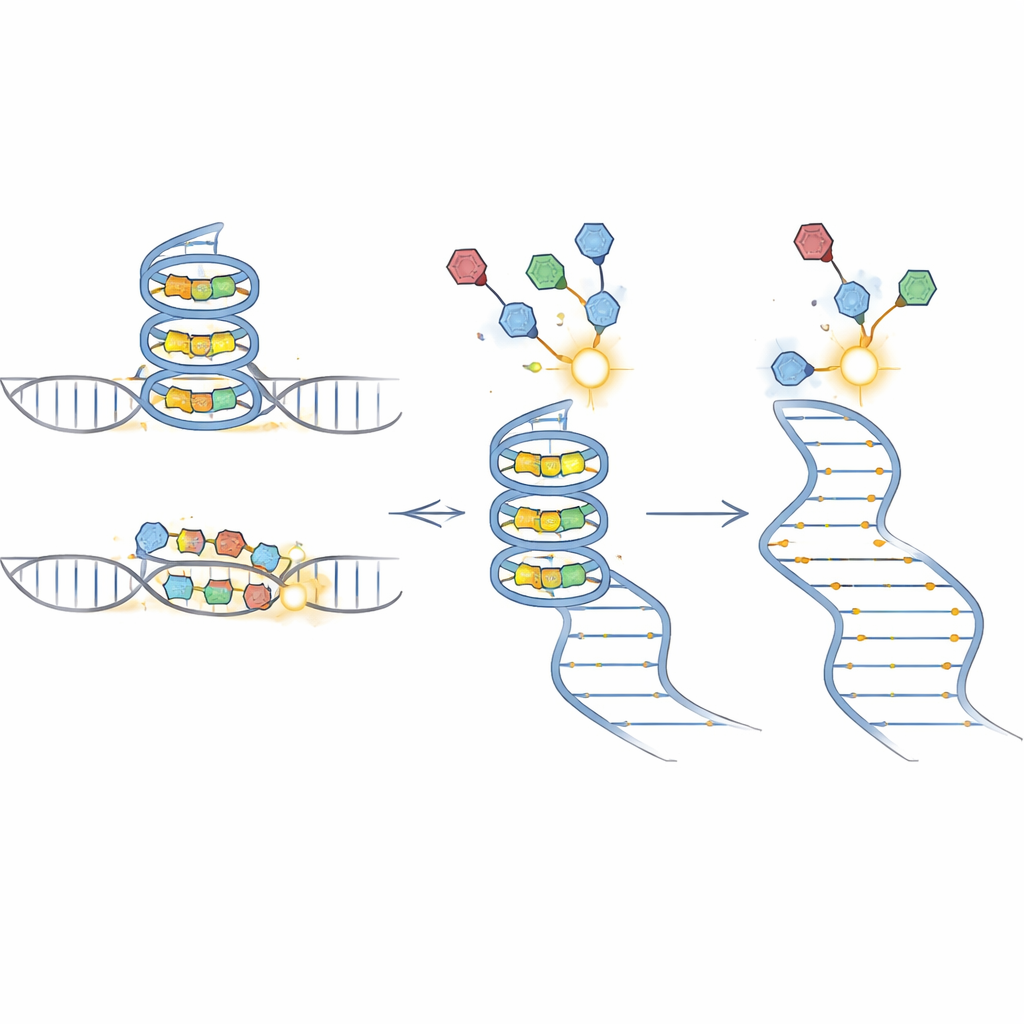
Det datorn förutspår men ändå missar
Viktigt är att befintliga verktyg för förutsägelse av RNA-struktur och G-quadruplex ofta misslyckades med att förutse de förändringar som BIVID-MaP avslöjade. Vissa varianter som nästan inte ändrade de beräknade poängen gav i verkligheten stora skillnader i bindning. Andra verkade påverka bindning över en familj av G-quadruplex-riktade föreningar, medan vissa mutationer hade läkemedelsspecifika effekter. Detta visar att enkel-nukleotidvarianter kan finjustera landskapet av RNA-veck och läkemedelskontakter på sätt som är svåra att härleda bara från sekvensen.
Vad detta betyder för personliga RNA-läkemedel
Författarna drar slutsatsen att BIVID-MaP erbjuder en kraftfull väg för att kartlägga hur individuella genetiska skillnader omformar RNA-strukturer och deras interaktioner med småmolekylära läkemedel. Genom att omvandla lokala kemiska modifieringar till precisa deletionssignaturer kan metoden undersöka tusentals varianter parallellt och lyfta fram dem som väsentligt ändrar läkemedelsbindning. På längre sikt kan sådana kartor vägleda designen av RNA-riktade läkemedel som är effektivare och säkrare över en mångfald av patienter, och avslöja tidigare dolda RNA-strukturer som kan fungera som nya läkemedelsmål.
Citering: Miyashita, E., Onizuka, K., Chen, Y. et al. Systematic identification of variant-specific RNA structure-small molecule interactions exemplified by RNA G-quadruplexes. Nat Commun 17, 2243 (2026). https://doi.org/10.1038/s41467-026-70097-9
Nyckelord: Läkemedel som riktar sig mot RNA, G-quadruplex, genetiska varianter, bindning av småmolekyler, cancermutationer