Clear Sky Science · sv
XL-MSDigger: en djupinlärningsbaserad, mångsidig lösning för korsbindnings-masspektrometri
Att se hur proteiner hålls ihop
Alla processer i våra kroppar är beroende av att proteiner inte bara viks i rätt former utan också hittar rätt partners. Ändå är det notorisk svårt att iaktta dessa molekylära relationer i aktion. Denna studie presenterar XL-MSDigger, en mjukvaruplattform som använder modern artificiell intelligens för att plocka fram mycket tydligare signaler ur en bullrig experimentell metod kallad korsbindnings-masspektrometri, vilket hjälper forskare att kartlägga hur proteiner är arrangerade och vilka de interagerar med inne i cellerna.
Att reda ut en trång molekylär värld
För att förstå hur proteiner är uppbyggda och hur de kopplas samman använder forskare ofta korsbindnings-masspektrometri. I denna metod länkar små kemiska ”broar” närliggande delar av proteiner till varandra. De ihopkopplade bitarna klyvs sedan till peptider och vägs i en masspektrometer. I teorin avslöjar fragmentmönstret vilka proteinbitar som varit nära varandra i rummet, ungefär som att ta reda på vilka sidor i en bok som klämts ihop. I praktiken är dock de resulterande data extremt komplexa. Befintliga datorverktyg tittar mest på grundläggande massinformation och har svårt med det enorma antalet möjliga kombinationer, vilket leder till missade kopplingar och felaktiga träffar.
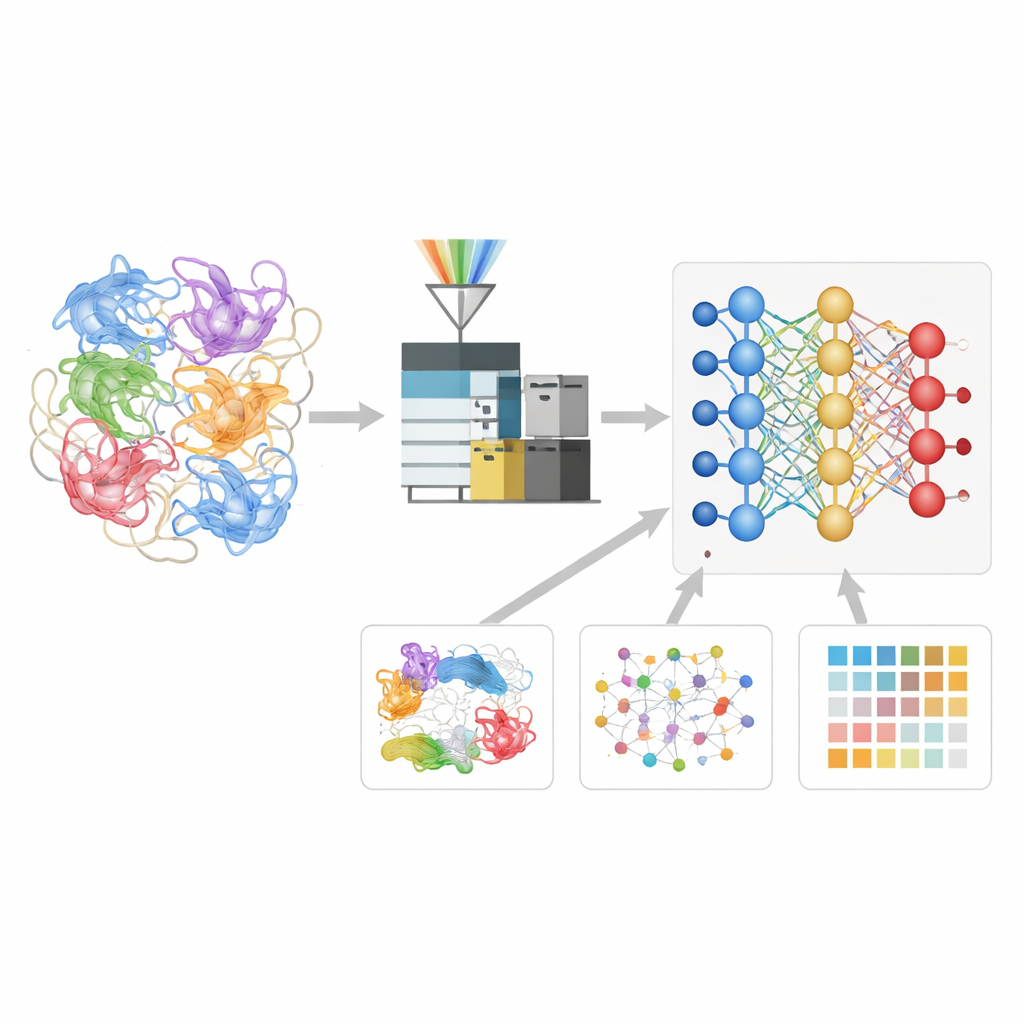
Att lära ett neuralt nätverk språket för proteinfragment
Författarna byggde en djupinlärningsmodell kallad Deep4D-XL för att bättre tolka dessa korsbindningsexperiment. De skapade först en stor referensuppsättning genom att korsbinda proteiner från humana celler, klyva dem till peptider och spela in inte bara deras massor utan också hur lång tid de tog att resa genom instrumentet och hur de rörde sig genom en jonmobilitetskammare. Varje korsbundet par kodades för modellen, som använder en tvilling-"Siamese"-arkitektur för att läsa båda peptidpartnerna och ett cross-attention-steg för att kombinera deras information. Utifrån detta lär sig nätverket att förutsäga tre nyckelegenskaper för varje nytt korsbundet peptid: när det bör dyka upp i experimentet, hur det bör röra sig och hur dess fragmenteringsmönster bör se ut.
Att omvandla förutsägelser till renare signaler
XL-MSDigger kapslar in denna prediktionsmotor i analysarbetsflöden för två stora datainsamlingsstilar. I den traditionella, riktade stilen spelar instrumentet selektivt in fragment från joner som väljs i farten. XL-MSDigger tar de initiala matchningarna från etablerad sökprogramvara och omvärderar dem med modellens förutsagda beteende för varje kandidat. Ett andra neuralt nätverk jämför förutsägelse och experiment över flera dimensioner och tilldelar förbättrade poäng. Detta ompoängsättningssteg fördubblar nästan antalet säkert detekterade länkar mellan olika proteiner i jäst- och humana prover samtidigt som felprocenten hålls låg, vilket avslöjar många fler protein–protein-interaktioner än tidigare.
Att göra mening av strömmar av obiaserade data
En nyare driftsättningsmetod, kallad dataoberoende förvärv, spelar in fragment för nästan allt i ett prov, vilket förbättrar täckningen men genererar överväldigande mängder data. Hittills har det inte funnits något bra sätt att uppskatta hur många av de resulterande korsbindningarna som verkligen var verkliga. XL-MSDigger använder Deep4D-XL för att bygga ett noggrant matchat "decoy"-bibliotek av falska korsbindningar och analyserar sedan både riktiga och decoy-poster tillsammans. Genom att se hur ofta decoys slinker igenom kan mjukvaran uppskatta felupptäcktsfrekvensen och träna ännu ett neuralt nätverk för att skilja sanna från falska träffar. Denna ompoängsättning ökar antalet pålitliga korsbundna signaler med ungefär fem gånger och ger en tydlig separation mellan verkliga och decoy-mönster.
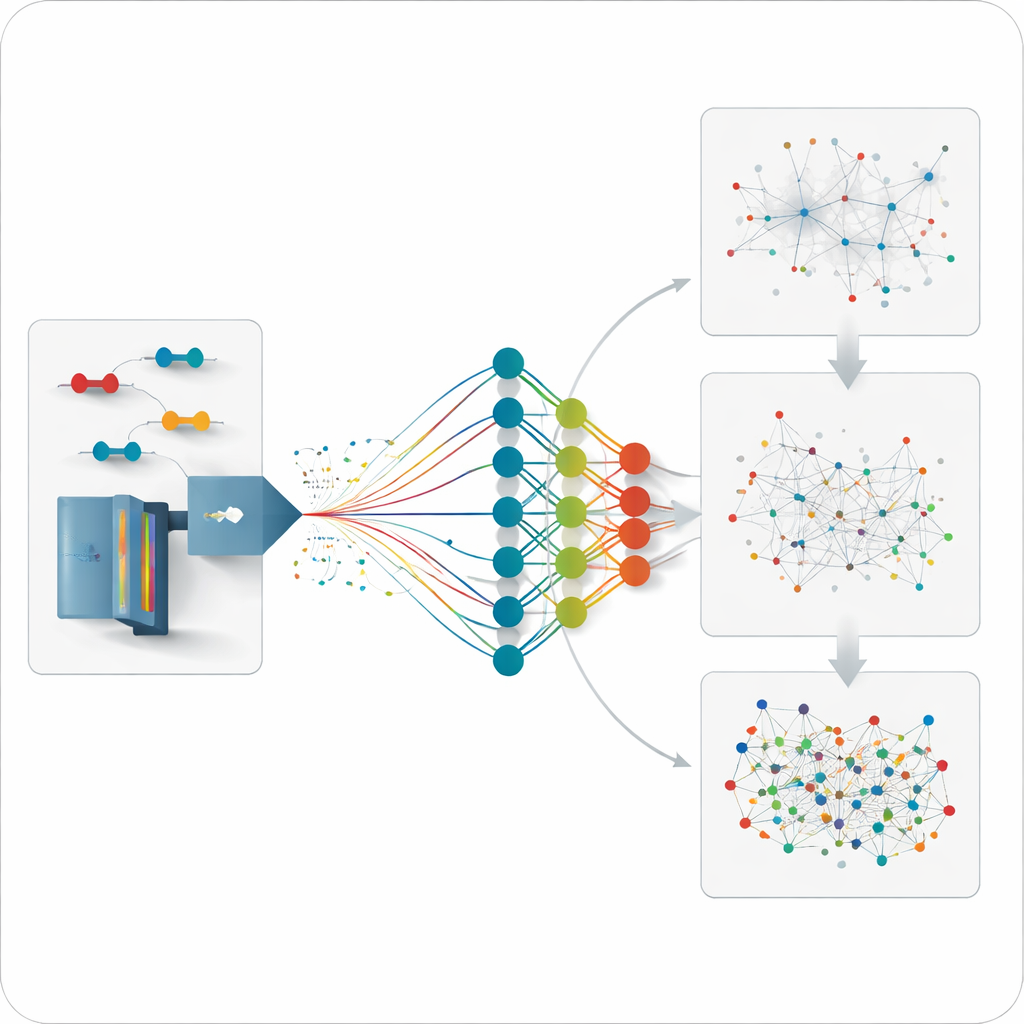
Att förutsäga det som ännu inte mätts
Eftersom modellen kan förutsäga hur vilken rimlig korsbunden peptid som helst bör bete sig kan teamet ta ett steg längre och analysera data för länkar som aldrig direkt mätts tidigare. De genererar måttligt stora förutsagda bibliotek med fokus på utvalda proteiner eller interaktionsnätverk och söker sedan i de obiaserade data mot dessa bibliotek. Denna strategi avslöjar ytterligare länkar inom enskilda proteiner och mellan partners till viktiga chaperonproteiner, med avstånd som stämmer väl överens med kända tredimensionella strukturer. Den återfinner också interaktioner som missades av de traditionella, mer begränsade experimentbiblioteken, särskilt för låg-abundanskopplingar.
Att öppna ett klarare fönster mot proteinpartnerskap
För icke-specialister är huvudbudskapet att XL-MSDigger fungerar som en högt tränad mönsterigenkännare lagd ovanpå en redan kraftfull experimentell metod. Genom att lära sig hur genuina korsbundna signaler bör se ut i flera dimensioner samtidigt kan den sålla igenom stora, röriga dataset, kasta bort sannolika bedragare och rädda verkliga men tidigare dolda proteinkopplingar. Även om fullskaliga hela-proteometillämpningar fortfarande kommer att kräva stora datorkapaciteter visar detta arbete att kombinera korsbindningsexperiment med djupinlärning avsevärt kan skärpa vår bild av hur proteiner är arrangerade och vilka de möter inne i cellen.
Citering: Chen, M., Hao, Y., Huang, X. et al. XL-MSDigger: a deep learning-based, versatile solution for cross-linking mass spectrometry. Nat Commun 17, 2554 (2026). https://doi.org/10.1038/s41467-026-69489-8
Nyckelord: proteinteraktioner, korsbindnings-masspektrometri, djupinlärning, proteomik, dataoberoende förvärv