Clear Sky Science · sv
TANGO: Analys och kurering av partiklar i kryo-elektrontomografi
Se celler i 3D och sedan förstå mängden
Kryo-elektrontomografi låter forskare frysa levande celler i arbete och fånga dem i tre dimensioner, nästan som att pausa en film på atomnivå. Men när tusentals små molekylära ”prickar” har kartlagts inne i en cell uppstår ett nytt problem: hur förstår vi vem som sitter bredvid vem, vilka som bildar lag och var de viktiga mönstren gömmer sig i denna trånga molekylstad? Denna studie presenterar TANGO, ett programvaruramverk som förvandlar råa 3D-partikelkartor till läsbara berättelser om hur molekylerna är ordnade och samverkar.
Från prickar i is till en karta över molekylära grannar
Kryo-elektrontomografi börjar med att luta ett fryst prov i mikroskopet för att ta många 2D-bilder. Dessa kombineras till ett 3D-volym, kallat en tomogram, där individuella molekylkomplex framträder som suddiga fläckar. Befintliga metoder använder redan dessa data för att förbättra molekylers former genom medelvärdesbildning av många kopior, men de bortser till stor del från en lika rik skatt: de exakta positionerna och orienteringarna för varje partikel. TANGO är byggt för att utnyttja denna förbisedd information. Det behandlar alla dessa partiklar som punkter i rummet, var och en med en riktning, och analyserar hur de är positionerade och orienterade i förhållande till varandra. Genom att göra detta går det bortom att endast fråga ”hur ser denna molekyl ut?” till att fråga ”hur är dessa molekyler organiserade tillsammans i cellen?” 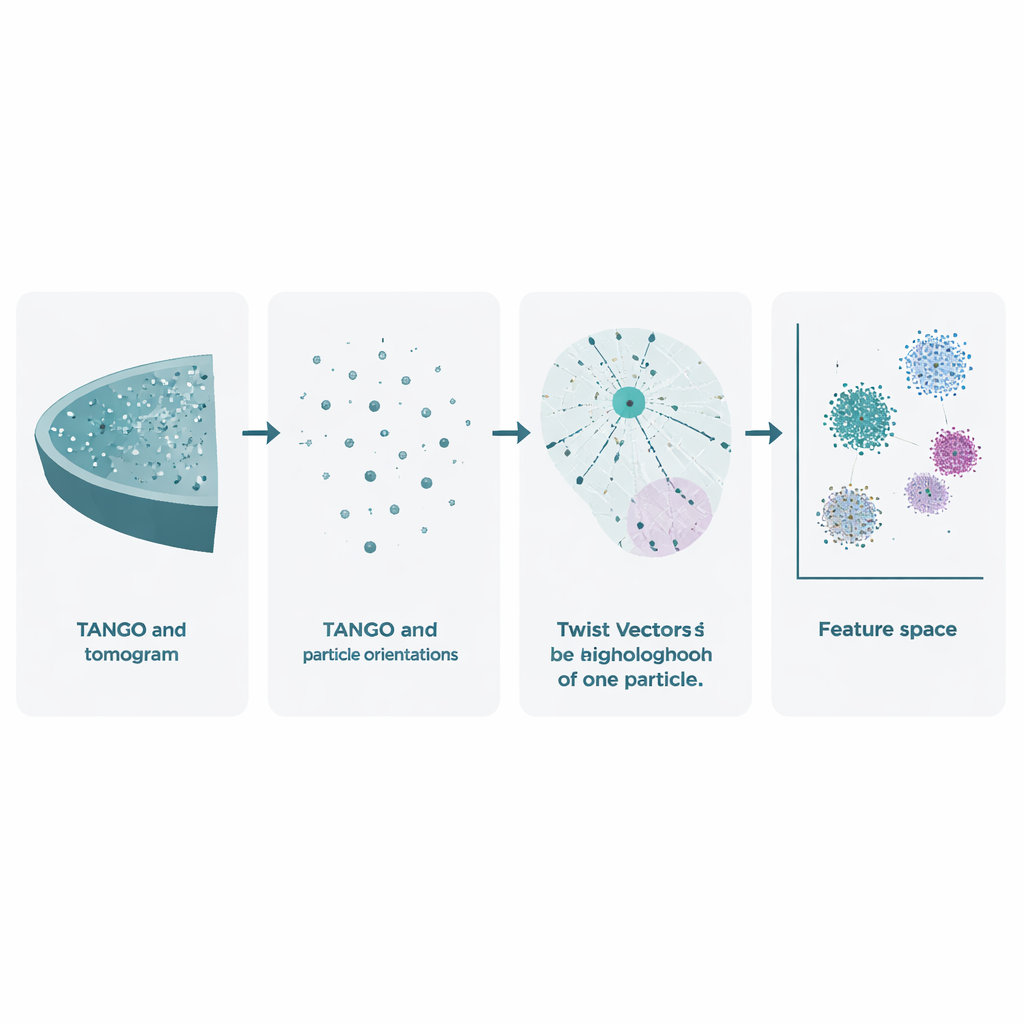
Fånga vridningar och svängar med en ny beskrivare
I hjärtat av TANGO finns idén om ”twist-vektorer”. För en given partikel tittar programvaran på alla dess grannar inom en vald radie och registrerar två saker: var varje granne ligger i 3D-rummet och hur den är roterad i förhållande till partikeln i centrum. Dessa kombinerade positions- och vinkelrelationer kodas som koncisa numeriska beskrivningar kända som twist-deskriptorer. Eftersom TANGO alltid omorienterar områden till ett gemensamt referenssystem är dessa deskriptorer okänsliga för hur hela provet är roterat i mikroskopet. Detta gör det möjligt att jämföra lokala grannskap över olika tomogram och experiment på ett konsekvent sätt.
Rensa upp brusiga data och bygga om molekylära sammanställningar
Verkliga experimentdata är röriga: automatiska plockmetoder kan inkludera många falska partiklar och tappa reda på vilka små bitar som hör till vilken större struktur. TANGO hanterar detta genom att förvandla nätverket av twist-relationer till en graf, där partiklar är noder och grannskapskopplingar är kanter. Genom att analysera hur noderna kopplar samman kan TANGO gruppera partiklar tillbaka till sina korrekta moderförsamlingar och kasta bort avvikare som inte passar den förväntade geometrin. Författarna visar att detta tillvägagångssätt med precision återfinner den ringformade arkitekturen hos kärnporer i cellens kärnmembran, mikrofilamentens rörformiga arrangemang och de ungefär sfäriska skalen hos omogna HIV-liknande partiklar. I varje fall både städar TANGO partikelister och återställer vilka delar som hör ihop, ofta i nivå med eller bättre än noggrann manuell kurering.
Upptäcka subtila fel och mönster i gitter
Många virus och cellulära strukturer bildar upprepande gitter, som molekylär kakling på krökta ytor. TANGO använder sina twist-deskriptorer för att mäta hur regelbundna dessa mönster är och för att upptäcka platser där de böjer sig eller bryts. En nyckelingrediens är en ”vinkelpoäng” som jämför orienteringar samtidigt som inbyggda symmetrier, såsom sexfaldig symmetri hos hexamerer, beaktas. Tillämpat på mogna HIV-kapsider upptäcker TANGO pentamerer — femdelade enheter som behövs för att stänga den koniska skalen — gömda bland stora fält av hexamerer. I omogna HIV-gitter separerar det välordnade regioner från förvrängda och kopplar låga vinkelpoäng till oregelbundna, brutna områden av skalet. Liknande analyser på syntetisk kromatin och ribosomdata avslöjar staplade nukleosomer, helikala DNA–proteinarrangemang och återkommande par av ribosomer som liknar tidigare beskrivna translationsstater. 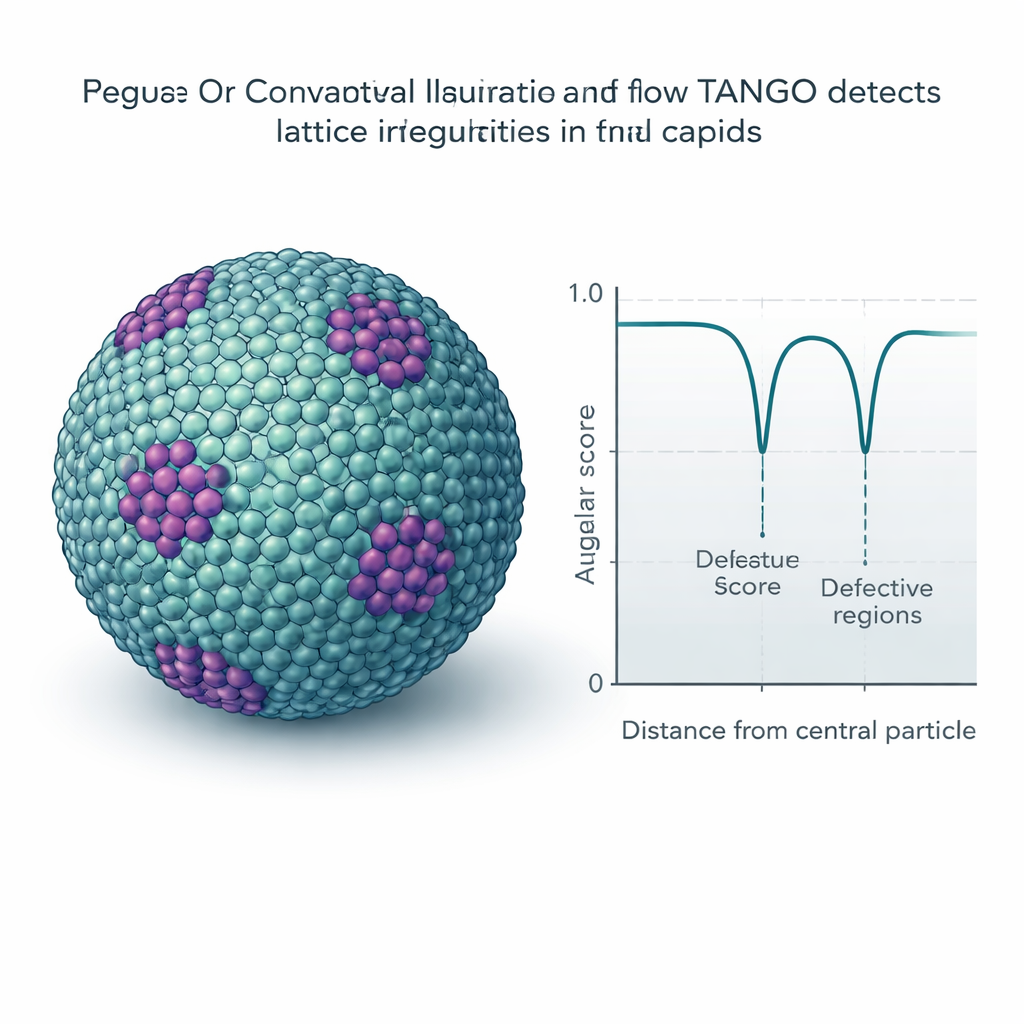
En flexibel verktygslåda för att utforska cellulär arkitektur
TANGO är implementerat som öppen källkod i Python och levereras med ett grafiskt gränssnitt så att användare kan testa olika grannskapsformer, filter och funktioner utan tung programmering. Eftersom det är modulärt kan forskare koppla in sina egna geometriska mått eller mönsterbeskrivare och omedelbart använda dem inom samma arbetsflöde. För nykomlingar sänker detta tröskeln för att utforska rumslig organisation; för experter ger det ett ramverk som kan växa med nya idéer och dataset.
Varför detta är viktigt för att förstå levande celler
Enkelt uttryckt ger detta arbete biologer ett sätt att gå från statiska bilder av enskilda molekyler till kartor över hur dessa molekyler är ordnade och samarbetar inne i celler. Genom att koda relationerna ”vem ligger nära vem” och ”hur de är orienterade” i robusta numeriska funktioner förvandlar TANGO brusiga 3D-mikroskopdata till mönster som kan klustras, jämföras och testas statistiskt. Detta kan avslöja dolda sammanställningar, peka ut defekter i virala skal och upptäcka sällsynta molekylära arrangemang kopplade till sjukdom eller läkemedelsverkan. När kryo-elektrontomografi blir mer utbrett kommer verktyg som TANGO att hjälpa till att omvandla täta partikelsmoln till tydliga insikter om livets inre koreografi.
Citering: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
Nyckelord: kryo-elektrontomografi, rumslig organisation, molekylära gitter, virala kapsider, ribosomer