Clear Sky Science · sv
PRICE: direkt och robust upptäckt av mikroRNA med enkelnukleotidupplösning
Varför små genetiska budskap spelar roll
Inuti varje cell finns en svärm av små RNA-molekyler kallade mikroRNA som hjälper till att finjustera vilka gener som slås på eller av. En förändring av bara en "bokstav" i dessa korta molekyler kan rubba balansen mot hälsa eller sjukdom, inklusive cancer. Läkare och forskare vill gärna läsa dessa små skillnader direkt från blod eller vävnad, men dagens metoder är ofta långsamma, kostsamma och inte tillräckligt precisa för att pålitligt upptäcka en enkel bokstavsförändring. Denna artikel presenterar en ny laboratorieteknik, kallad PRICE, som lovar att läsa dessa mikroskopiska fel i mikroRNA enklare och mer exakt, och därmed öppna möjligheter för tidigare cancerupptäckt och bättre spårning av tumörers beteende.
Ett nytt sätt att skilja lika molekyler åt
MikroRNA är extremt korta, vilket gör dem svåra att skilja åt när deras sekvenser skiljer sig med bara en byggsten. Många nuvarande verktyg, såsom PCR och RNA-sekvensering, gör ett bra jobb med att räkna mikroRNA överlag, men har svårt när två varianter är nästan identiska eller kräver komplex provberedning och dyra instrument. Författarna kombinerar två kraftfulla idéer för att övervinna detta: en programmerbar molekylär "sax" från CRISPR-familjen och syntetiska, DNA-liknande bitar kallade peptid‑nukleinsyror (PNA). CRISPR-enzymet Cas13a kan instrueras vilket RNA det ska känna igen, och när det hittar sitt mål börjar det klippa i närliggande rapportormolekyler, vilket ger en stark fluorescerande signal. PNAs, å andra sidan, är korta strängar som binder särskilt tätt till matchande RNA-sekvenser men tappar greppet tvärt om bara en bokstav är fel.
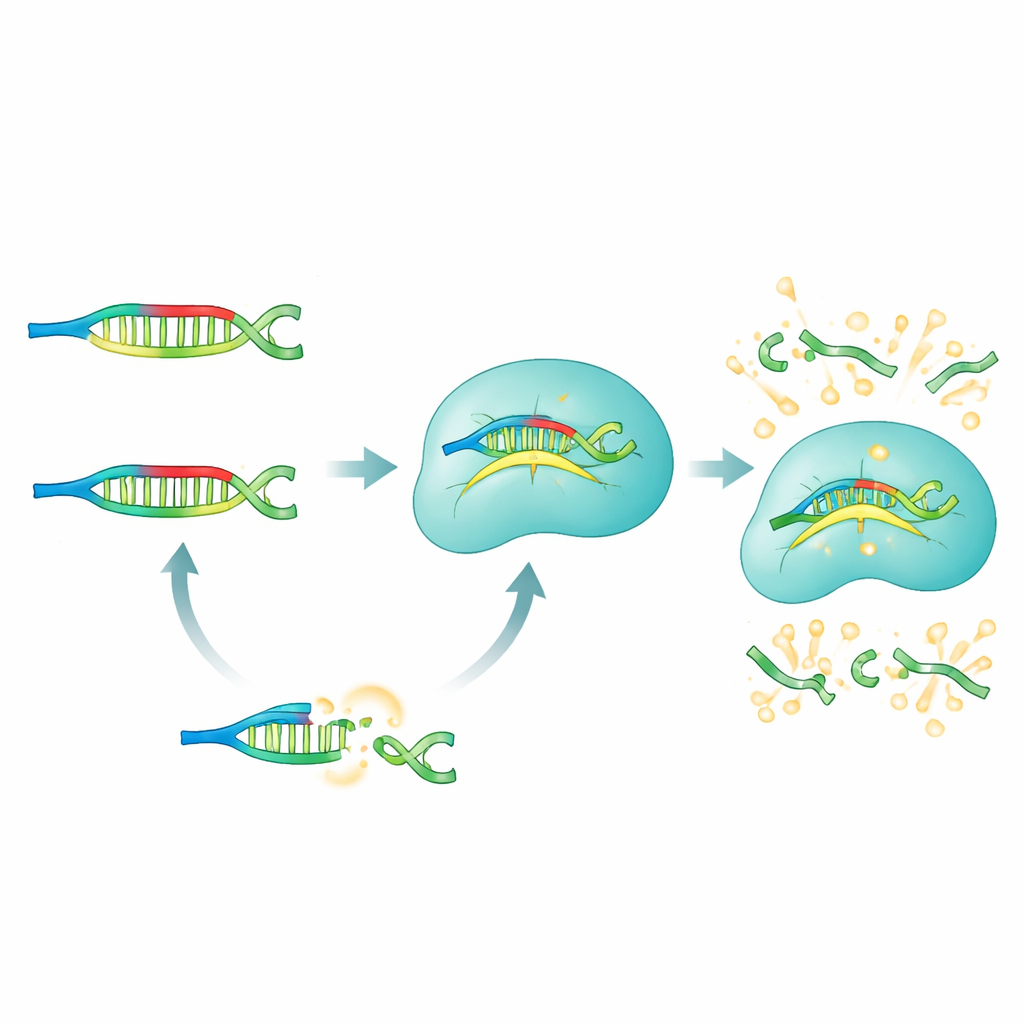
Hur PRICE-metoden fungerar
I PRICE-systemet fungerar PNAs som selektiva blockare som tystar allt forskarna inte vill se. För ett givet mikroRNA av intresse designar teamet en panel av PNA-blockare som perfekt matchar alla de "felaktiga" versionerna — de med oönskade enkla bokstavsändringar — samtidigt som de medvetet missmatchar det valda målet. När ett biologiskt prov (från serum, celler eller vävnad) blandas med dessa PNA binder de icke-målade mikroRNA:t hårt och maskeras effektivt. Det verkliga målet lämnas obundet och fritt att interagera med Cas13a-komplexet, som har förprogrammerats med ett guide-RNA som känner igen just det mikroRNA:t. Endast detta oblockerade mål kan växla Cas13a till dess aktiva klippningsläge, vilket i sin tur styckar fluorescerande rapportormolekyler och genererar ett starkt, lättmätt sken.
Finjustering för enkelnukleotidprecison
Författarna utforskade systematiskt hur man designar PNA-blockare som är starka nog att fånga det felaktiga mikroRNA:t, men ändå svaga nog att ignorera det önskade som skiljer sig med bara en bokstav. De fann att två temperatur‑lika designregler är avgörande: PNA:t bör bilda ett stabilt par med den oönskade mutanten vid eller över kroppstemperatur, men bilda ett mycket svagare par med målet som faller isär väl under den temperaturen. Med hjälp av dessa regler, stödda av en enkel prediktiv modell, byggde de PNAs som minskar falska signaler från mutanta mikroRNA med mer än 70 procent samtidigt som den sanna signalen nästan inte påverkas. Viktigt är att de tillsatta PNA:na inte minskade den övergripande känsligheten: PRICE kunde fortfarande upptäcka mikroRNA vid koncentrationer på endast några tiotals femtomolar, jämförbart med de bästa förstärkningsbaserade testerna men utan extra kopieringssteg.
Tillämpning av testet i cancersampel
För att visa att PRICE är mer än en teoretisk pryl fokuserade teamet på let‑7-familjen av mikroRNA, som spelar en stor roll i cancerbiologin. De visade att PRICE kan plocka ut mål‑mikroRNA ur blandningar som innehåller många närapå identiska familjemedlemmar och kan till och med upptäcka sällsynta varianter som utgör så lite som 5 procent av ett prov. Forskarna gick sedan vidare till verkligt kliniskt material: levercancercellinjer, vävnadsbiopsier och patientserum. I både tumörvävnad och blod upptäckte PRICE konsekvent lägre nivåer av specifika let‑7-mikroRNA hos patienter jämfört med icke‑cancerkontroller, i linje med tidigare studier. När det jämfördes direkt med standarden RT‑qPCR visade PRICE åtminstone likvärdig och ofta bättre förmåga att skilja cancer från icke‑cancerfall, särskilt i serumprov med låg förekomst där PCR-resultat blev brusiga.
Varför detta är viktigt för framtida diagnostik
I grunden visar detta arbete att det är möjligt att direkt läsa enkla bokstavsskillnader i små regulatoriska RNA på ett praktiskt, skalbart sätt. Genom att låta PNAs låsa fast oönskade snarlika sekvenser och överlämna slutlig avläsning till ett CRISPR‑enzym erbjuder PRICE en flexibel verktygslåda för att designa tester som enkelt kan riktas om genom att byta ut blockerarpanelen och guide‑RNA. Bortom levercancer och let‑7‑familjen kan samma strategi utvidgas till många andra sjukdomar där små RNA‑förändringar spelar roll, och till och med till DNA‑varianter när den paras med relaterade CRISPR‑enzymer. Författarna visar också en kompakt, flerkanelig läsare som kan köra PRICE‑tester utanför stora centrallabb, vilket antyder framtida punkt‑av‑vård‑tester. Om PRICE utvecklas vidare kan det bli ett praktiskt sätt att övervaka subtila genetiska skiftningar som signalerar cancer och andra sjukdomar långt innan symtom uppträder.
Citering: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Nyckelord: mikroRNA-diagnostik, CRISPR Cas13a, peptid–nukleinsyra, ens nukleotidvariant, biomarkörer för levercancer