Clear Sky Science · sv
Förbättrad upptäckt av enhancer–promotor-slingor via normaliseringsmetoder för kromatininteraktionsdata
Att se de dolda slingorna i vårt DNA
Inuti varje cell veckas och slingrar långa DNA-strängar i tre dimensioner, vilket för avlägsna delar av genomet i nära kontakt med varandra. Några av dessa slingor kopplar fysiskt på–av-reglage som kallas enhancers till de gener de styr, vilket formar hur celler utvecklas och hur sjukdomar som cancer uppstår. Denna artikel presenterar en ny beräkningsmetod, Raichu, som gör dessa subtila regulatoriska slingor mycket lättare att upptäcka i genometäckande experiment och öppnar ett skarpare fönster mot hur DNA-fällning och genaktivitet hänger ihop.
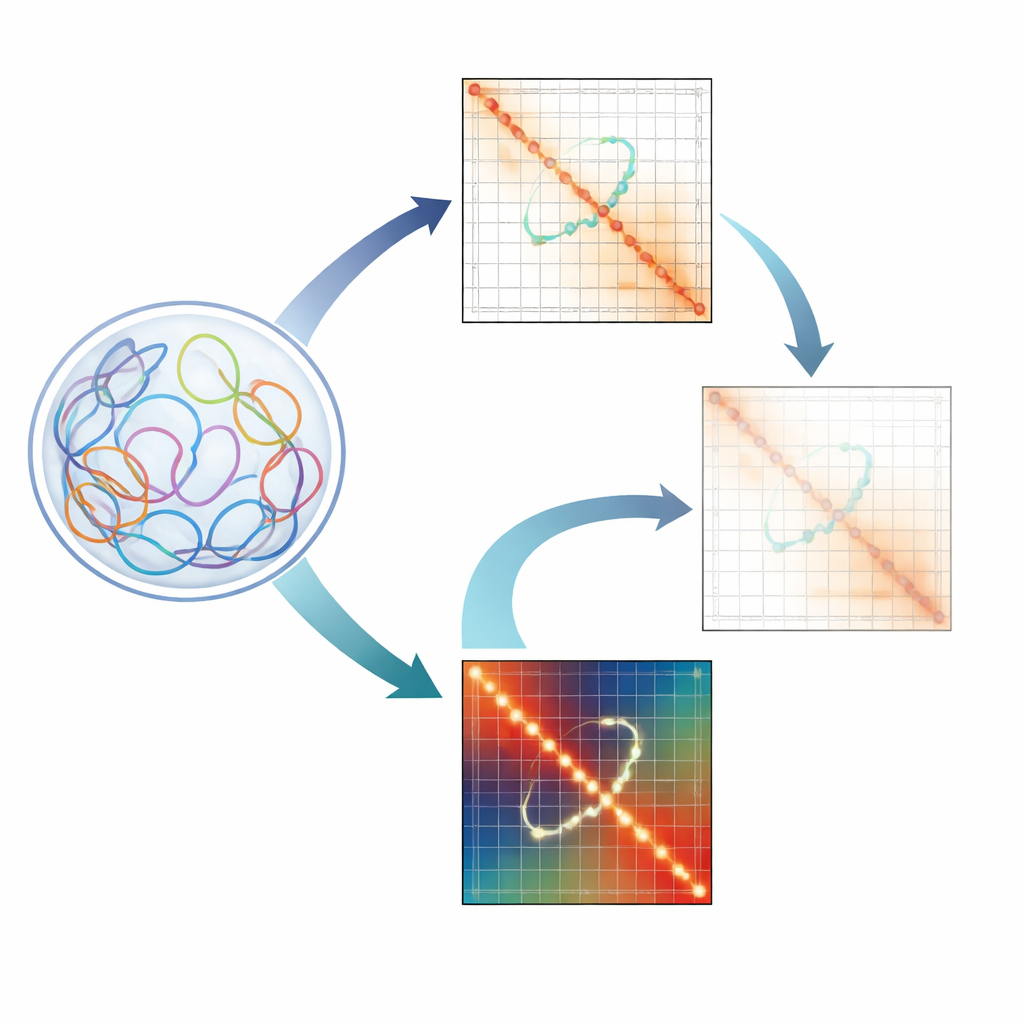
Varför små DNA-slingor spelar roll
Våra genom är inte ordnade som raka bokstavssträngar. Istället skrynklas de ihop till en komplex 3D-struktur inne i kärnan. I detta veckade tillstånd kan regioner som ligger långt ifrån varandra i linjär sekvens komma i kontakt och bilda kromatinslingor. Vissa slingor fungerar som stomme som hjälper till att organisera hela kvarter av genomet. Andra är regulatoriska slingor som kopplar genpromotorer till avlägsna enhancers som ökar deras aktivitet. Störningar i dessa regulatoriska slingor har kopplats till utvecklingsstörningar och cancer, så forskare är angelägna om att kartlägga dem i detalj.
Utmaningen med att läsa 3D-genomkartor
Tekniker som Hi-C och besläktade metoder fångar miljontals till miljarder DNA–DNA-kontakter och sammanfattar dem som värmekartor, där varje pixel speglar hur ofta två genomregioner möts. Men dessa kartor är fulla av tekniska finesser: vissa regioner är lättare att läsa än andra på grund av sekvensinnehåll, hur väl de kan aligneras eller hur de klipps i experimentet. För att städa upp använder forskare normaliseringsmetoder som ICE och KR som balanserar kartorna så att varje region ser ut att ha lika synlighet. Medan dessa verktyg skärper stora drag som breda domäner och starka strukturella slingor, visar författarna att de oavsiktligt jämnar ut de svagare men biologiskt avgörande enhancer–promotor-slingorna.
Ett nytt sätt att rena signalen
Raichu använder en annan strategi för att rengöra kromatinkontaktdata. Istället för att tvinga varje region i genomet att se lika synlig ut modellerar den varje interaktion som summan av tre delar: en allmän avtagande kontaktfrekvens med ökad linjär distans längs kromosomen, ett bias som är specifikt för varje plats, och en återstående signal som är specifik för just den kontakten. Med hjälp av en optimeringsalgoritm uppskattar Raichu det biasmönster som bäst förklarar de observerade data samtidigt som den övergripande distansberoende trenden hålls fast. Kontakterna justeras sedan genom att dividera bort dessa biasvärden. Detta bevarar den naturliga globala avtagningen av interaktioner samtidigt som tekniska distorsioner selektivt korrigeras, och lämnar tydligare signaler efter sig för verkliga, specifika DNA-kontakter.
Att avslöja tusentals förbisedda regulatoriska slingor
När författarna tillämpade Raichu på djupt sekvenserade mänskliga och musdata avslöjade metoden nästan dubbelt så många kromatinslingor som standardmetoderna, samtidigt som nästan alla tidigare kända slingor återfanns. De extra slingor som upptäcktes av Raichu var starkt berikade för biokemiska markörer för aktiva enhancers och promotorer och för bindning av transkriptionsfaktorer som styr genaktivitet. Många av dessa slingor stödjs oberoende av andra 3D-genomtekniker och till och med av högupplöst bilddiagnostik, vilket bekräftar att de speglar verklig fysisk närhet i kärnan. Viktigt är att Raichu bibehöll denna fördel även när data tunnades ut för att simulera lägre sekvenseringsdjup, vid studier med specialiserade kartläggningsmetoder som Micro-C och region-capture Micro-C, och även vid sammanslagning av ett litet antal enstaka celler.
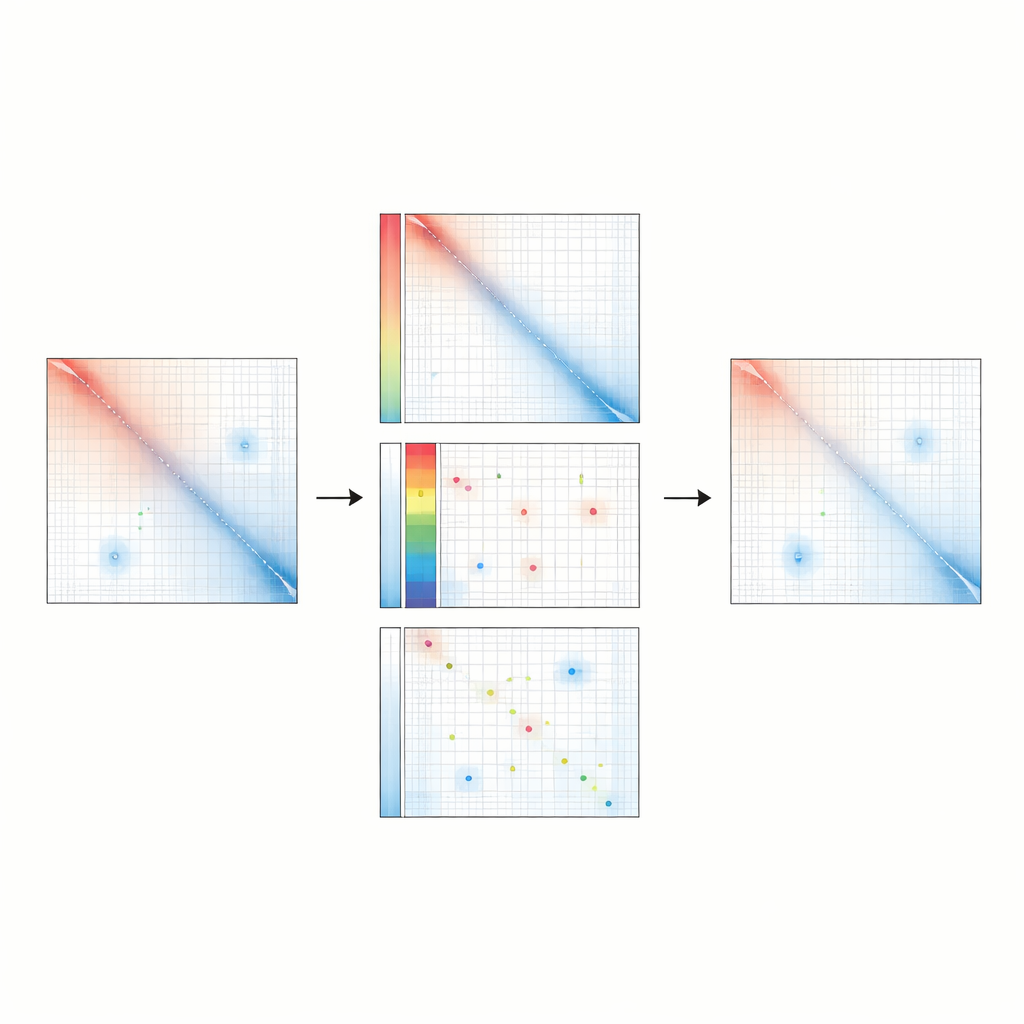
Att avslöja subtila förändringar och evolutionära mönster
Eftersom Raichu är särskilt känsligt för regulatoriska slingor är metoden bättre på att upptäcka meningsfulla skillnader mellan förhållanden som annars kan se lika ut. I en konstruerad mänsklig cellmodell som bar på en leukemirisksvariant avslöjade Raichu nya slingor som endast framträdde i risktillståndet, och kopplade nyckelgener till deras enhancers i linje med förändringar i genaktivitet. Över mus- och människans neurala progenitorceller upptäckte Raichu tusentals enhancer–promotor-slingor som var bevarade mellan arter och ofta kopplade avlägsna enhancers till gener involverade i hjärnans utveckling. Dessa fynd tyder på att många viktiga regulatoriska kontakter har legat uppenbara men dolda, maskerade av tidigare normaliseringsmetoder.
Vad detta betyder för framtida genomforskning
För en allmän läsare är kärnbudskapet att hur vi bearbetar stora genomiska dataset kan påverka dramatiskt vilken biologi vi ser. Genom att ompröva städetappen för 3D-genomkartor återställer Raichu svaga men viktiga signaler som länkar genreglage till deras mål. Det blir enklare att spåra hur DNA-fällning styr genaktivitet i hälsa och sjukdom, från enstaka celler till hela vävnader och över arter. När fler studier antar Raichu kan forskare förvänta sig rikare kartor över enhancer–promotor-kommunikation och en tydligare bild av hur förändringar i genomarkitektur bidrar till utveckling, cancer och andra komplexa tillstånd.
Citering: Wang, X., Shi, D., Xue, F. et al. Boosting the detection of enhancer-promoter loops via normalization methods for chromatin interaction data. Nat Commun 17, 2299 (2026). https://doi.org/10.1038/s41467-026-69082-z
Nyckelord: 3D-genomorganisation, enhancer-promotor-slingor, Hi-C-dataanalys, kromatinnormalisering, genreglering