Clear Sky Science · sv
Förlängda Shine‑Dalgarno‑motiv styr initiering av translation i Staphylococcus aureus
Hur en sjukhusbakterie finjusterar sina proteinfabriker
Staphylococcus aureus är en vanlig bakterie som kan orsaka allt från lindriga hudinfektioner till livshotande sjukdomar. För att överleva i kroppen och motstå behandling måste den ständigt omprogrammera vilka proteiner den producerar. Denna artikel avslöjar hur S. aureus kontrollerar det allra första steget i proteinproduktionen på ett sätt som skiljer sig från läroboksbakterier som Escherichia coli, och visar hur denna kontroll är kopplad till biofilmformation—en viktig bidragande orsak till kroniska och antibiotika‑toleranta infektioner.
En dold ”handskakning” mellan gen och ribosom
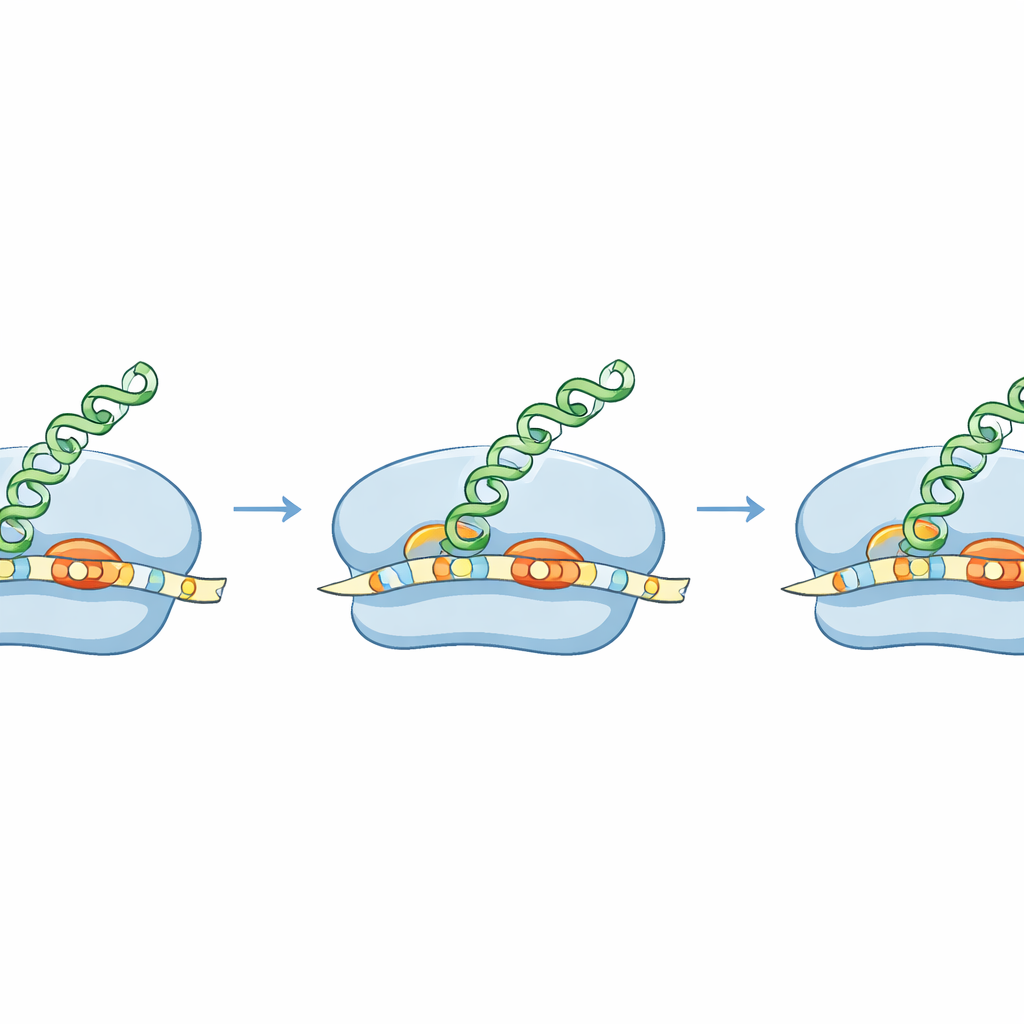
För att omvandla en gen till ett protein använder bakterier ribosomer, molekylära maskiner som skannar ett budbärar‑RNA (mRNA) för att hitta var läsningen ska börja. Många bakteriella mRNA innehåller en kort sekvens, länge känd som Shine–Dalgarno‑regionen, som hjälper ribosomen att lägga an på rätt plats. Genom att frysa ribosomer i det ögonblick då de inleder translation och sekvensbestämma de skyddade RNA‑fragmenten skapade författarna en högupplöst karta över startpunkter i S. aureus‑genomet. De upptäckte att S. aureus ofta använder en ovanligt lång version av denna anläggningssekvens, placerad mycket nära startsignalen, vilket bildar ett förlängt ”blixtlås” mellan mRNA och ribosomalt RNA. Denna förlängda parning är mycket tydligare än hos E. coli och verkar vara ett kännetecken för hur S. aureus väljer startplats.
Artspecifika regler för att starta proteinsyntes
Forskarteamet visade att detta förlängda anläggningshelix har verkliga konsekvenser. I flera naturliga S. aureus‑gener kan de första bokstäverna läsas på mer än ett sätt, vilket ger konkurrerande startpunkter för translation. Med hjälp av renade ribosomer, cellfria system och levande celler jämförde forskarna hur S. aureus och E. coli hanterar dessa tvetydiga starter. S. aureus‑ribosomer valde konsekvent samma ”korrekta” start som används i bakterien själv, vägledda av den långa anläggningshelixen och det föredragna avståndet mellan denna helix och startplatsen. E. coli‑ribosomer föredrog däremot en annan närliggande start som skulle ge ett alternativt protein. Det innebär att samma mRNA kan leda till olika proteiner i olika arter, vilket öppnar möjligheter att designa budskap som bara kan läsas av utvalda bakterier.
Nya små proteiner och svaga startsignaler
Där deras metod pekar ut exakt när ribosomer anländer till startplatser kunde författarna också avslöja många korta, tidigare förbisedda gener. De identifierade flera dussin små öppna läsramar, inklusive korta ”uppströms” sekvenser som ligger precis före större, kända gener. Några av dessa korta regioner kodar troligen för små proteiner med egna funktioner; andra verkar främst fungera som regulatorer. Studien visade vidare att S. aureus ibland påbörjar translation vid ”non‑kanoniska” starttripletter som vanligtvis betraktas som svaga signaler. I dessa fall tycks starka och förlängda anläggningsmotiv kompensera för den svaga starten, vilket dämpar proteinproduktionen så att vissa faktorer, inklusive metabola regulatorer, bara tillverkas sparsamt eller som svar på tillväxtförhållanden.
En molekylär sensor som kopplar näringstillgång till biofilmtillväxt
Ett kort uppströms‑element, kallat rbfL, framträdde som ett tydligt exempel på translational kontroll knuten till virulens. Det ligger precis före rbf, en gen som kodar för en transkriptionsfaktor som främjar biofilmformation. rbfL‑sekvensen kodar för en liten ”ledarpeptid” rik på arginin, inklusive mycket ovanliga argininkodon som avläses av sällsynta transfer‑RNA. När arginin är begränsat översätts dessa kodon långsamt och ribosomer fastnar över regionen som överlappar anläggningsplatsen för rbf själv, vilket fysiskt blockerar nya ribosomer från att initiera rbf‑translation. När arginin eller motsvarande transfer‑RNA är riktligt förekommer inte detta stopp och rbf produceras mer effektivt. I tillväxtexperiment ökade tillsatt arginin biofilmformationen, vilket binder denna molekylära sensor direkt till en samhällslivsstil som motstår antibiotika.
Varför dessa fynd är viktiga
Denna forskning visar att S. aureus har utvecklat förlängda anläggningsmotiv och små uppströms‑element för att finjustera var och när proteinsyntesen startar. Dessa egenskaper skiljer den inte bara från modellbakterier som E. coli utan kopplar också näringssensorik till kontrollen av biofilmregulatorer. För en lekmannaläsare är huvudpoängen att bakteriens ”startknappar” för proteinproduktion är mer invecklade än man tidigare trott—och att dessa specialiserade omkopplare hjälper avgöra när S. aureus blir farligare. Att förstå dessa unika initieringsregler kan vägleda designen av artspecifika antibiotika eller genetiska verktyg som selektivt stör skadliga bakterier samtidigt som nyttiga arter lämnas oskadade.
Citering: Kohl, M.P., Bahena-Ceron, R., Chane-Woon-Ming, B. et al. Extended Shine-Dalgarno motifs govern translation initiation in Staphylococcus aureus. Nat Commun 17, 2678 (2026). https://doi.org/10.1038/s41467-026-69079-8
Nyckelord: Staphylococcus aureus, translationsinitiering, Shine‑Dalgarno, små ORF:er, biofilmreglering