Clear Sky Science · sv
Konstruera plasmider med syntetiska replikationsorigin
Varför omskrivning av mikrobiellt DNA spelar roll
Många av verktygen bakom modern bioteknik, från insulinproduktion till avancerade gencirklar, förlitar sig på små DNA-cirklar som kallas plasmider. Dessa genetiska arbetsdjur för in konstruerade gener i bakterier, men deras grundläggande design har knappt ändrats på årtionden. Denna studie visar att plasmidernas innersta kärna — sekvenserna som talar om för celler när och hur ofta de ska kopiera dem — kan omformas helt. Genom att bygga om denna "kopieringsmotor" från grunden skapar författarna plasmider som är lättare att finjustera, kombinera och programmera, vilket öppnar dörren för mer flexibla diagnostikmetoder, biotillverkning och syntetisk biologi.
Gamla verktyg med dolda begränsningar
Plasmider utvecklades naturligt som mobilt DNA och hjälper bakterier att dela egenskaper som antibiotikaresistens eller nya sätt att bryta ner näringskällor. I laboratoriet lånar ingenjörer dessa plasmider för att bära användbara gener, men de flesta bygger på några klassiska konstruktioner som upptäcktes på 1980-talet. De gamla konstruktionerna döljer en härva av överlappande genetiska delar som styr hur många kopior av en plasmid som finns i varje cell och om olika plasmider kan samexistera utan konflikt. Eftersom dessa delar sitter hopfogade kan en förändring av en funktion oförutsägbart störa en annan. Som ett resultat sitter forskare fast med en begränsad meny av plasmider som har fasta kopieringsnummer och begränsad kompatibilitet, vilket inskränker hur komplexa konstruerade system kan bli.
Bygga om kopieringsmotorn från grunden
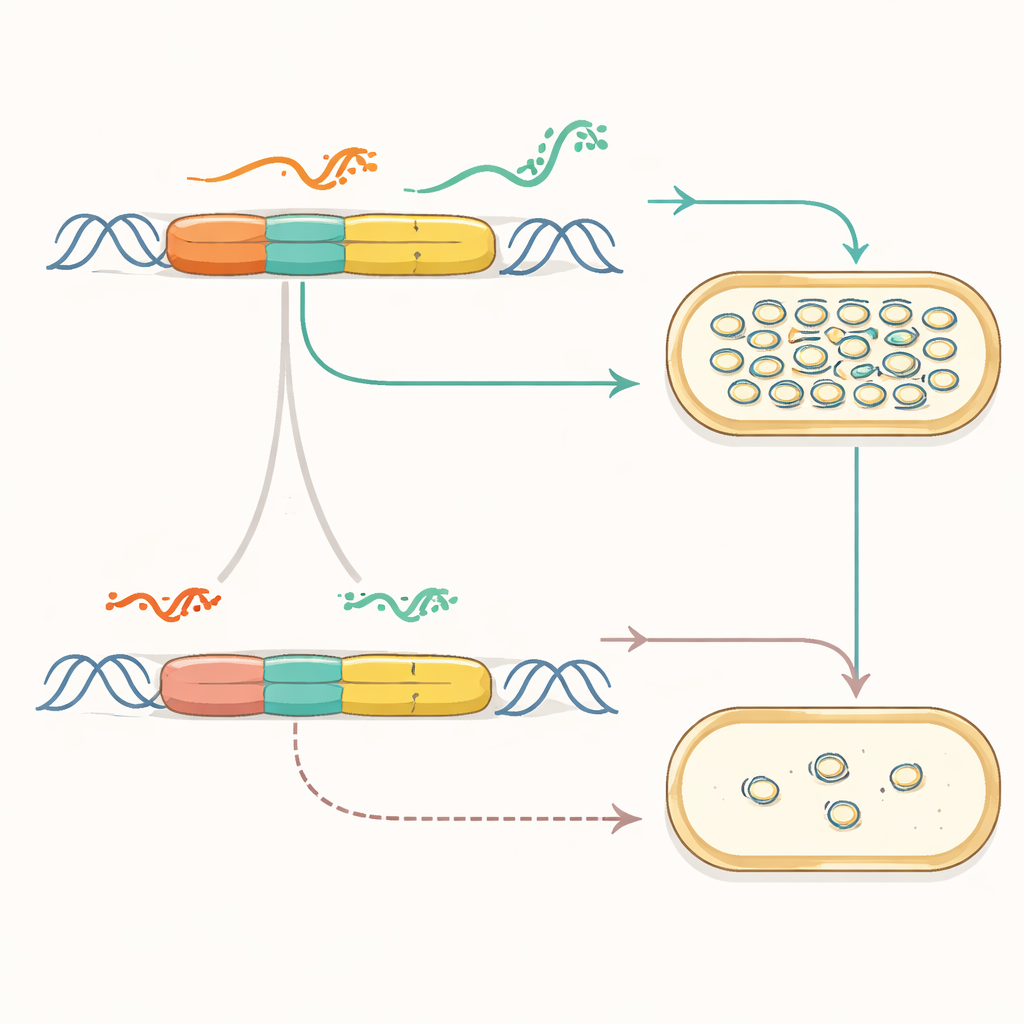
Forskarna fokuserade på ett allmänt använt replikationsorigin från pMB1-plasmidfamiljen. I dess naturliga form använder origin en finbalanserad dialog mellan två RNA — ett som startar DNA-kopieringen och ett annat som stänger av den — för att hålla plasmidantalet i schack. Teamet "refaktorerade" först detta system: de separerade överlappande gener, inaktiverade en dold promotor och placerade nyckeldelarna på separata, rena genetiska kassetter. Detta visade att originens kärnuppgift kunde bevaras samtidigt som upplägget förenklades, och förvandlade en rörig, evolutionärt formad del till något mer likt en modulär maskin med åtkomliga komponenter.
Byta in syntetiska reglage
När den ursprungliga styrlogiken blottlades ersatte författarna den med fullt syntetiska regulatorer. De kopplade replikationsprimern till konstruerade RNA-brytare som fungerar som dimmern: små kontrollerande RNA kan slå dessa brytare för att antingen tillåta eller blockera produktionen av primern och därigenom plasmidkopiering. Genom att välja olika brytarvarianter och kombinera dem med promotorer av varierande styrka ställde de in plasmidkopieringsnummer över mer än två storleksordningar. De utforskade också olika fysiska layoutalternativ för kontrollkassetterna på DNA:t, och upptäckte arrangemang som förbättrade stabiliteten och tillät dem att förminska replikationsregionen till en kompakt, funktionell kärna samtidigt som de lade till naturliga hjälpsystem som förhindrar problematiska plasmidtrassel.
Förvandla kemiska signaler till DNA-antal
När kopieringsmotorn blev modulär visade teamet att den kunde kopplas till att känna av omvärlden. De anslöt det syntetiska originet till inducerbara promotorer och RNA-strukturer kallade riboswitchar, som ändrar form som svar på små molekyler. I dessa nya plasmider fick tillsats av en kemikalie som IPTG eller cumat plasmidkopieringsnumret — och därmed en rapportersignal — att stiga eller falla. Flera signaler kunde kombineras så att en kemikalie drev på kopiering medan en annan bromsade den. Forskarna byggde till och med par av plasmider där varje plasmid svarade på en olika kemikalie, och följde deras förändrade kopieringsnummer i samma cell med DNA-sekvensering, vilket effektivt förvandlade plasmidantal till en streckkod av miljöhistoria.
Många skräddarsydda plasmider i en cell
Ett viktigt test för angreppssättet var om flera oberoende kontrollerade plasmider kunde samexistera. Genom att använda ett bibliotek av ortogonala RNA-regulatorer byggde teamet sex olika plasmider, var och en med sitt eget syntetiska origin och antibiotikamarkör, och introducerade alla sex samtidigt i E. coli. Helplasmidssekvensering över flera dagar bekräftade att alla sex förblev närvarande, även om deras relativa abundanser förändrades. Försök att göra samma sak med sex konventionella plasmider misslyckades, vilket understryker hur den refaktorerade designen och de tillagda stabilitetssystemen gör de nya plasmiderna mer kompatibla och robusta när de trängs ihop i en enda cell.
Vad detta betyder för framtidens bioteknik
För en icke-specialist är slutsatsen enkel: författarna har förvandlat plasmider från stela, universella verktyg till en anpassningsbar plattform. Deras syntetiska replikationsorigin fungerar som plug-and-play-motorer vars hastighet, känslighet och ingångar kan väljas efter behov. Det gör det möjligt att bygga bakterier som registrerar kemiska exponeringar som förändringar i DNA-kopieringsnummer, testa många genetiska vägar parallellt genom att fördela dem över flera plasmider, eller noggrant balansera tillväxt och produktion i industriella stammar. Trots att vissa stabilitetsoch kompromisser kvarstår visar detta arbete att plasmidreplikationens grundläggande mekanik inte längre är utom räckhåll för ingenjörskonst, vilket öppnar nytt utrymme för innovation inom syntetisk biologi.
Citering: Liu, B., Seet, Z.R.D., Peng, X. et al. Engineering plasmids with synthetic origins of replication. Nat Commun 17, 2255 (2026). https://doi.org/10.1038/s41467-026-68907-1
Nyckelord: syntetiska plasmider, replikationsorigin, RNA-regulatorer, kopieringsnummerkontroll, syntetisk biologi