Clear Sky Science · sv
En absolut kvantifieringsatlas för små icke-kodande RNA över olika däggdjursvävnader och cellinjer
Varför små RNA-molekyler spelar roll
Inne i varje cell hjälper flottor av små RNA-molekyler till att avgöra vilka gener som slås på eller av. Dessa små icke-kodande RNA fungerar som dimmers för våra genetiska program och formar utveckling, organfunktion och sjukdom. Trots kraftfulla sekvenseringstekniker har forskare haft svårt att mäta exakt hur många av dessa molekyler som finns i olika celler och vävnader. Denna studie presenterar ett mer exakt sätt att räkna dem och bygger en detaljerad atlas som visar deras verkliga abundans över många däggdjursvävnader och vanliga laboratorieceller.
En tydligare metod för att räkna små RNA
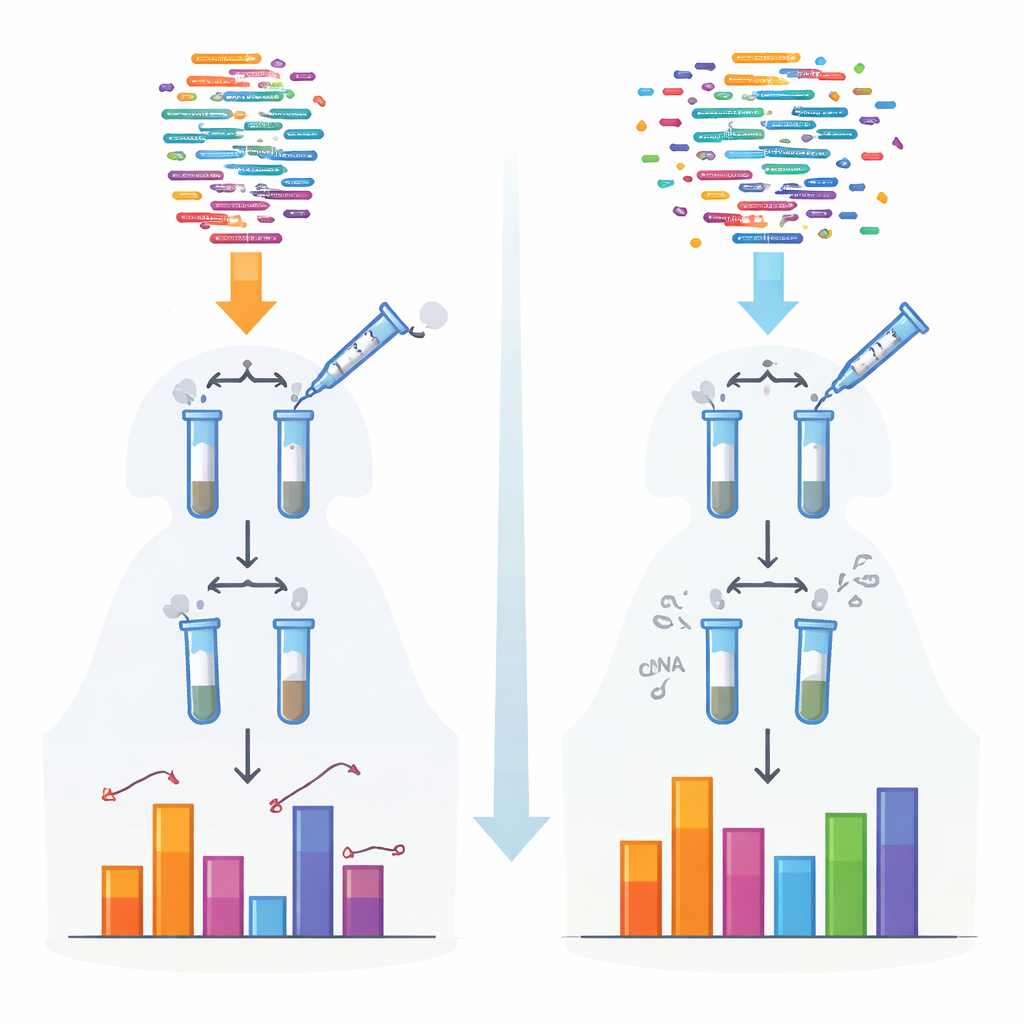
Traditionella metoder för att sekvensera små RNA förlitar sig på enzymer som fäster adapterstycken innan molekylerna läses. Dessa enzymer föredrar vissa former och kemiska ändar, så vissa RNA fångas upp effektivt medan andra missas eller underskattas. Denna bias är särskilt uttalad för vissa klasser som piRNA och växtens små RNA, som bär skyddande kemiska caps på ändarna. Författarna skapade ett nytt protokoll, kallat 4NBoost, som omdesignar adapterarna och reaktionsförhållandena för att utjämna dessa preferenser och lägger till inbyggda molekylära streckkoder för att skilja verkliga molekyler från kopior som skapats under amplifikation.
Att förvandla ett protokoll till ett mätverktyg
För att omvandla 4NBoost från en relativ avläsning till ett faktiskt mätverktyg lade teamet till noggrant designade syntetiska "spike-in"-RNA i kända koncentrationer över ett mycket brett spektrum. Genom att jämföra hur många gånger varje spike-in lästes av sekvenseraren med hur mycket som ursprungligen tillsattes byggde de standardkurvor som omvandlar läsantal till absoluta molekylantal. Tester med olika spike-in-blandningar och tillsatta kontroll-RNA visade att 4NBoost kunde följa abundans korrekt över flera storleksordningar, inklusive RNA med problematiska kemiska modifieringar. Även vid start från så lite som en nanogram totalt RNA fångade metoden fortfarande små-RNA-landskapet troget.
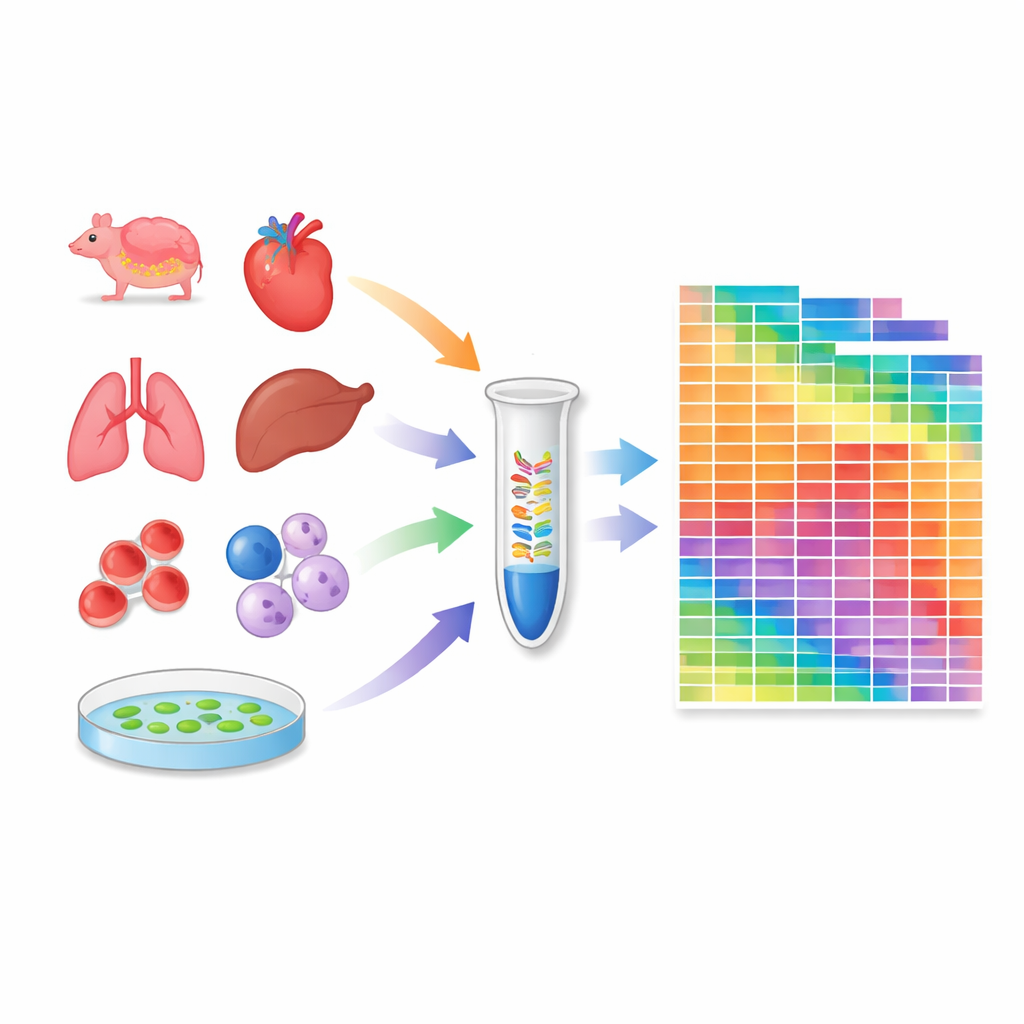
Bygga en atlas över vävnader och cellinjer
Utrustade med detta kalibrerade protokoll profilerade forskarna 259 prover: 20 vävnader från möss, 18 från krabbätande makaker, 24 allmänt använda humana och murina cellinjer, samt flera vävnader från modellväxten Arabidopsis. För varje prov uppskattade de det absoluta antalet molekyler för tusentals mikroRNA och piRNA. Detta avslöjade hur många olika mikroRNA‑arter som finns i varje kontext och hur deras totala mängder varierar mellan vävnader och arter. Vissa cellinjer och organ bär särskilt rika mikroRNA-repertoarer, medan andra, såsom blodceller, domineras av ett fåtal mycket abundanta arter. Atlasen exponerade också betydande skillnader mellan mus- och makakvävnader, vilket understryker att små-RNA-reglering kan vara art‑specifik.
Korrigera gammal data och revidera vanliga antaganden
När den nya atlasen jämfördes med populära små-RNA-databaser byggda med konventionella metoder uppstod markanta avvikelser. Flera viktiga mikroRNA-familjer—såsom miR-19 och miR-29—visade sig vara mycket mer abundanta än man tidigare trott, medan andra—som de välstuderade let-7- och miR-10-familjerna—ofta överskattats. Studien granskade också om vilken "arm" av varje prekursor-hårnål som faktiskt används i celler, och avslöjade fall där nuvarande annoteringar anger fel huvudsträng. För att rädda rikedomarna i befintliga biaserade dataset tränade författarna en maskininlärningsmodell som lär sig hur konventionella mätningar avviker från 4NBoost och sedan matematiskt korrigerar dem för att bättre återspegla verkliga abundanser.
En offentlig resurs för att utforska små RNA
Alla 4NBoost-mätningar och korrigeringsmodellen görs fritt tillgängliga via en onlineplattform kallad SmRNAQuant. Forskare kan bläddra eller ladda ner absoluta små-RNA-nivåer för specifika vävnader, cellinjer eller mikroRNA, och kan ladda upp sina egna data framställda med ett vanligt kit för att få bias-korrigerade värden. För icke-specialister är huvudbudskapet att räkning spelar roll: små skillnader i små-RNA-kopienummer kan vara skillnaden mellan aktiv genreglering och ingen effekt alls. Genom att erbjuda mer tillförlitliga siffror och ett sätt att åtgärda äldre data lägger detta arbete en starkare kvantitativ grund för att förstå hur små RNA formar normal biologi och sjukdom.
Citering: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
Nyckelord: mikroRNA-kvantifiering, små icke-kodande RNA, RNA-sekvenseringsbias, vävnadsuttrycksatlas, maskininlärningskorrigering