Clear Sky Science · sv
Högfarts blind strukturerad belysningsmikroskopi via osupervised algoritmupprullning
Skarpare filmer av livet inne i celler
Modern biologi är ofta beroende av att observera levande celler i arbete, men många centrala strukturer är helt enkelt för små och för snabba för att vanliga mikroskop ska kunna fånga dem tydligt. Denna artikel presenterar ett nytt sätt att förvandla suddiga, snabbt tagna bilder till skarpa, superdetaljerade filmer i realtid, utan att kräva perfekt justerad hårdvara. Metoden, kallad unrolled blind structured illumination microscopy (UBSIM), lovar att göra avancerad, högfrekvent cellavbildning mer tillgänglig för vanliga biologiska laboratorier.
Varför vanliga mikroskop räcker inte till
Traditionella ljusmikroskop begränsas av diffraktion, en grundläggande egenskap hos ljus som suddar ut fina detaljer mindre än några hundra nanometer. Strukturerad belysningsmikroskopi (SIM) tacklar detta genom att belysa provet med mönstrat ljus och använda det resulterande interferensmönstret för att utvinna extra information, vilket ungefär fördubblar upplösningen. Klassisk SIM kräver dock precist kända belysningsmönster och noggrann kalibrering, vilket kan vara kostsamt och känsligt. En nyare variant, blind‑SIM, slappnar av hårdvarukraven genom att tillåta slumpmässiga mönster och lösa både provet och belysningen utifrån datan. Nackdelen är att denna lösningsprocess är långsam och iterativ, ofta tar sekunder till minuter per bildruta — alldeles för segt för realtidsfilmer av levande celler.
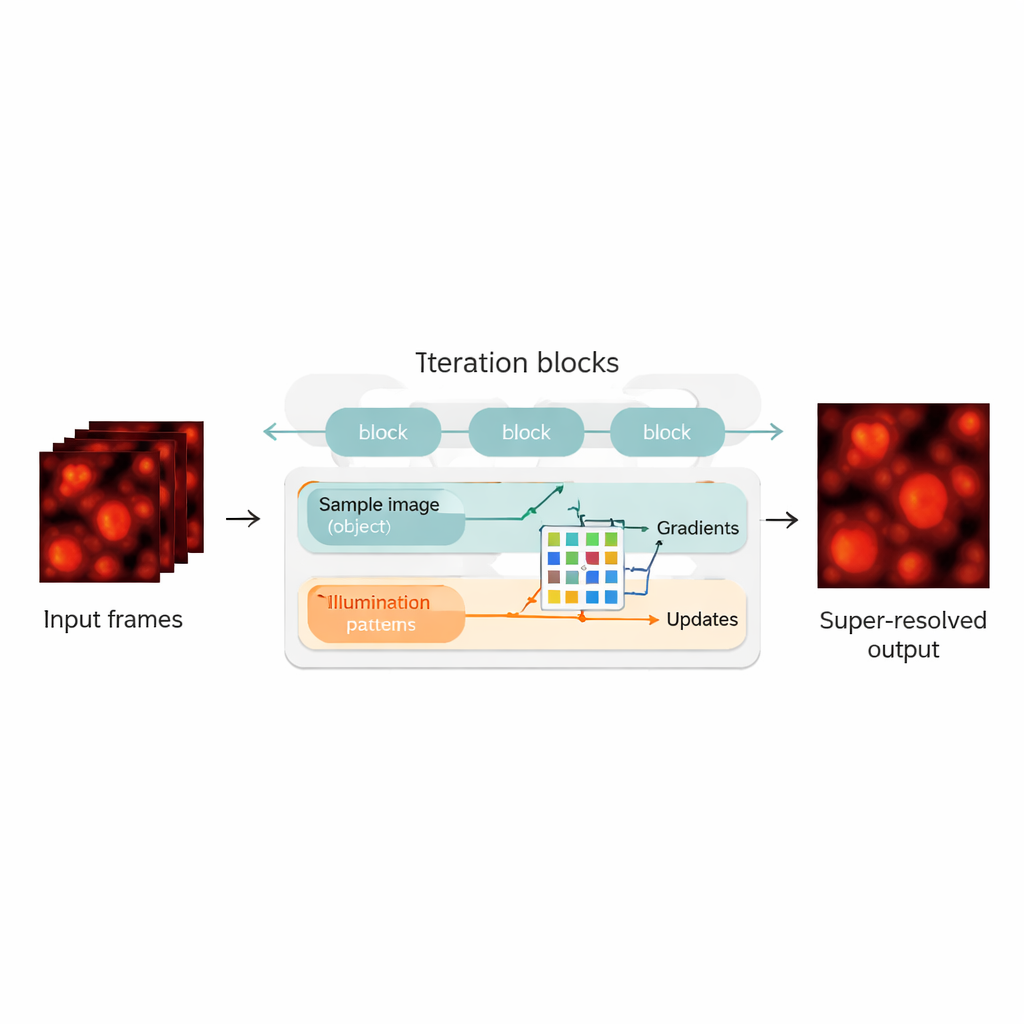
Att förena fysik med neurala nätverk
Författarna bygger en brygga genom att omforma blind‑SIM‑rekonstruktionen till en hybrid mellan en fysikbaserad modell och ett neuralt nätverk. De "rullar ut" den ursprungliga iterativa algoritmen — varje iteration blir ett lager i ett neuralt nätverk och bildar en kedja av uppdateringsblock. Inom varje block beräknar metoden hur väl den aktuella gissningen av provet och belysningen förklarar de uppmätta bilderna, beräknar gradienter (riktningar för förbättring) och matar dessa till ett kompakt konvolutionellt neuralt nätverk. Detta nätverk lär sig att göra smartare korrigeringssteg och fungerar som en automatiskt inställd accelerator för den ursprungliga algoritmen. Avgörande är att UBSIM tränas på ett osuperviserat sätt: istället för att behöva perfekta exempelbilder som sanningsreferens krävs endast den fysiska modellen för hur ljus passerar genom mikroskopet. Det minskar risken för att nätverket ”hallucinerar” plausibla men felaktiga strukturer.
Snabbt, korrekt och mindre benäget till gissningar
För att testa UBSIM använde teamet först simulerade mikroskopibilder där de sanna underliggande strukturerna är kända. De visade att UBSIM återvinner ungefär dubbla upplösningen jämfört med vanliga widefield‑bilder, i nivå med standard blind‑SIM, men kör två till tre storleksordningar snabbare — en 256×256‑bild kan rekonstrueras på cirka 10 millisekunder istället för sekunder. Bildkvalitetsmått, inklusive fel, likhet och signal‑till‑brus‑kvoter, förbättrades markant jämfört med konventionella bilder. UBSIM visade sig också mer pålitligt än populära djuplärningsnätverk för superupplösning när de ställdes inför okänd data. Medan standardnät som tränats på en typ av struktur tenderade att lägga sin karaktäristiska struktur även på nya, olika prover — och därigenom introducera subtila men vilseledande artefakter — bibehöll UBSIM konsekvent trohet, eftersom den är förankrad i den underliggande avbildningsfysiken snarare än enbart visuella exempel.
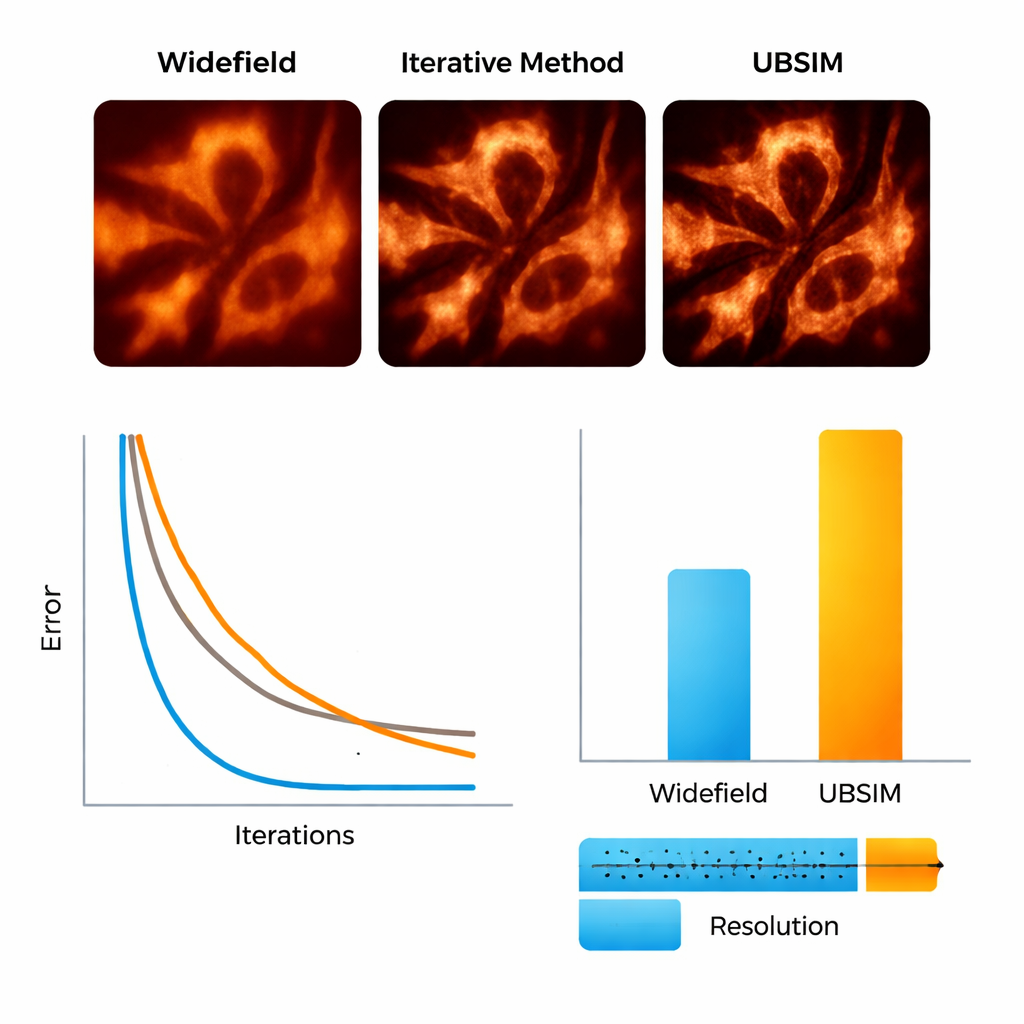
Se cellens skelett och membran i rörelse
Forskarna gick sedan vidare till verkliga biologiska prover. Med en flexibel uppställning som projicerar slumpmässiga specklemönster på levande celler avbildade de aktinfilament — proteinets ”stomverk” inne i celler — och det endoplasmatiska retiklet (ER), ett förgrenat membrannätverk som är involverat i proteintillverkning och cellens stressvar. Med UBSIM blev aktinfibrer som i vanliga bilder såg ut som suddiga band till skarpt separerade trådar, med upplösningsförbättring från ungefär 300 nanometer till cirka 150 nanometer. Mest slående var att UBSIM möjliggjorde video‑frekvens superupplösning: genom att fånga rådata med upp till 100 bilder per sekund och rekonstruera upp till 50 superupplösta bildrutor per sekund kunde teamet följa ER‑tubuli som växer, kollapsar och omorganiserar i realtid. Dessa dynamiker, som sker över fraktioner av en sekund till några sekunder, är normalt svåra att visualisera med tillräcklig detalj.
Vad detta innebär för framtidens cellavbildning
För icke‑specialister är huvudpoängen att UBSIM gör det betydligt mer praktiskt att i realtid följa små cellulära strukturer i rörelse, med klarhet bortom de vanliga gränserna för ljusmikroskop — allt utan att kräva perfekt hårdvarukalibrering eller massiva träningsdataset. Genom att kombinera pålitligheten hos fysikbaserade modeller med hastigheten hos moderna neurala nätverk förvandlar detta tillvägagångssätt högar av brusiga, mönstrade bilder till trovärdiga, ultraskarpa filmer tillräckligt snabbt för rutinexperiment. När metoden förfinas ytterligare och paras med bättre belysningsstrategier kan den hjälpa forskare att undersöka hur organeller som ER svarar på stress, hur cellens stomme omorganiserar sig under rörelse eller delning, och hur sjukdomar förändrar cellulär arkitektur på nanoskalan.
Citering: Burns, Z., Zhao, J., Sahan, A.Z. et al. High-speed blind structured illumination microscopy via unsupervised algorithm unrolling. Nat Commun 17, 1967 (2026). https://doi.org/10.1038/s41467-026-68693-w
Nyckelord: superupplösningsmikroskopi, strukturerad belysning, djuplärning, levande cellsavbildning, endoplasmatiskt retikel-dynamik