Clear Sky Science · sv
ProteoAutoNet: högkapacitets co-eluerad proteinanalys med robotik och maskininlärning
Varför förståelsen av proteinpartnerskap är viktig
Inuti varje cell arbetar proteiner sällan ensamma. De bildar skiftande allianser för att bygga strukturer, kopiera DNA, bryta ner skadade delar och driva tillväxt. Många cancerformer kapar dessa partnerskap, men att kartlägga dem i detalj har gått långsamt och krävt mödosamt arbete. Denna studie presenterar ProteoAutoNet, ett system som kombinerar robotik och maskininlärning för att avsevärt snabba upp hur forskare identifierar proteinpartnerskap i celler, och visar hur metoden kan avslöja dolda svagheter i thyreoideacancer.
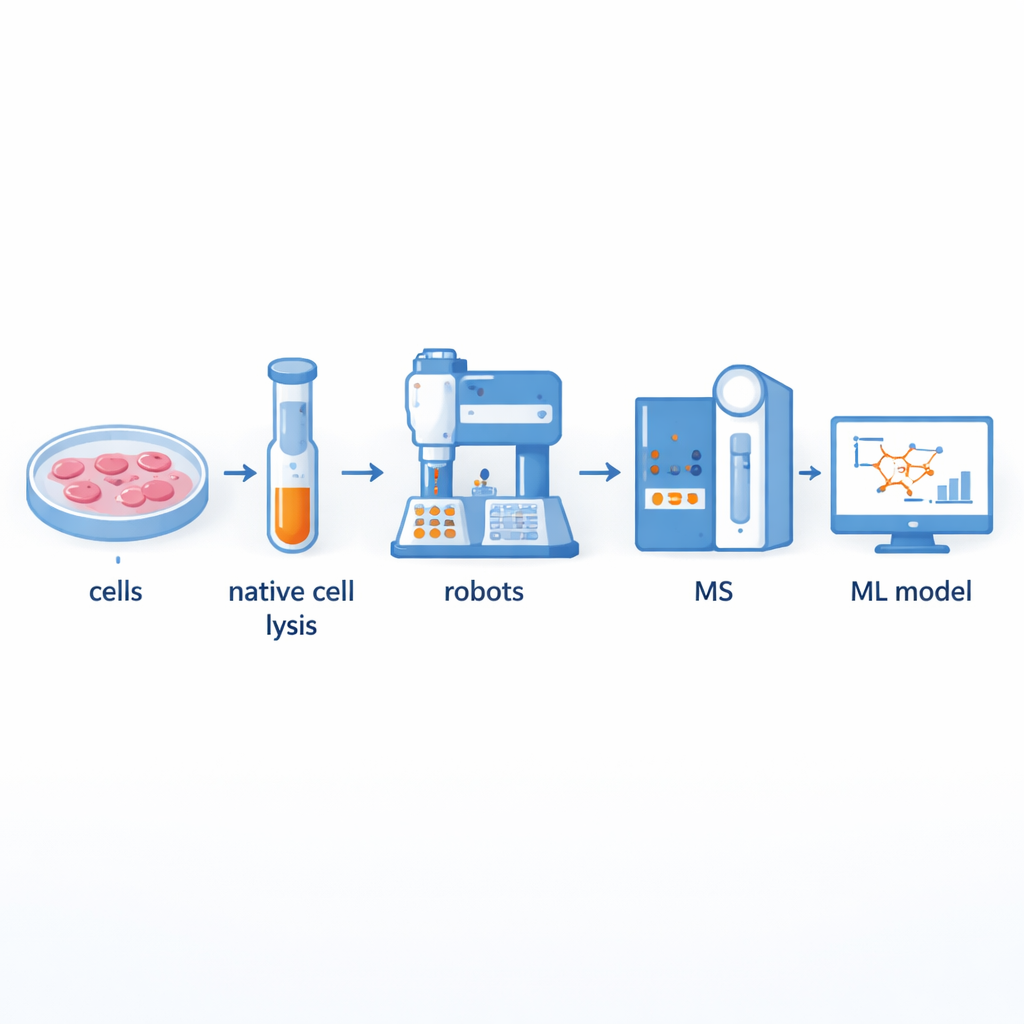
Bygga en snabbare fabrik för proteinpartnerskap
Traditionellt använder forskare en metod som kallas co-fraktionerings-masspektrometri för att separera stora proteinkomplex och sedan identifiera deras komponenter. Trots sin styrka är detta arbetssätt arbetsintensivt och har låg genomströmning: att manuellt förbereda hundratals fraktioner kan ta flera dagar. Författarna byggde en robotikstödd plattform som automatiserar större delen av detta arbetsflöde. Cellinnehållet bryts först försiktigt upp så att naturliga proteinkomplex förblir intakta, och passerar sedan genom storleksbaserade kolonner som delar upp dem i dussintals fraktioner. Vätskahanteringsrobotar och robotarmar tar därefter över, tillsätter kemikalier, klyver proteiner till mindre bitar, rengör proverna och levererar dem till en masspektrometer för mätning. Denna uppställning kan bearbeta upp till 540 fraktioner från flera thyreoideacellinjer på bara två till tre dagar, vilket ungefär fördubblar genomströmningen jämfört med tidigare semi-automatiserade system.
Robotar som inte bara är snabbare utan också mer tillförlitliga
Hastighet räcker inte om resultaten är brusiga eller inkonsekventa. Teamet kontrollerade noggrant om den automatiserade pipelinen matchade eller överträffade kvaliteten hos traditionell manuell bearbetning. Med hjälp av kvalitetskontrollprover visade de att det automatiserade systemet upprepade gånger identifierade nästan 3 000 proteiner per thyreoideacellinje med mycket hög överlappning mellan replikat och stark överensstämmelse i uppmätta proteinmängder. När de jämförde robot- och manuell bearbetning av samma prover upptäckte båda metoderna liknande antal proteiner, men den robotiska metoden gav något mindre variation i antalsräkningar och mer stabila proteinabundansmätningar. Det innebär att den nya plattformen inte bara sparar tid och arbetskraft utan också stöder mer reproducerbara experiment — ett avgörande krav för stora studier och kliniska tillämpningar.
Att lära datorer känna igen meningsfulla kopplingar
Även med snabba instrument kvarstår en central utmaning: att avgöra vilka proteiner som verkligen interagerar och vilka som bara förekommer tillsammans av en slump. För att tackla detta kombinerade författarna kurerade databaser över proteinkomplex med en maskininlärningsmodell baserad på XGBoost-algoritmen. De rengjorde och sammanslog först tre stora resurser för proteinkomplex och slutade med 96 635 kända protein–protein-interaktioner. De använde sedan profiler över hur proteiner förekom i fraktionerna som indatavariabler och märkta par som sannolika partners eller icke-partners utifrån databaserna. Eftersom verkliga, högkonfidensa partnerskap är relativt sällsynta använde de en riktad dataaugmenteringsstrategi: de skapade många lätt störda versioner av kända positiva exempel för att lära modellen att känna igen robusta mönster snarare än att memorera specifika spår. Tränad på tiotals miljoner sådana exempel från tre thyreoideacellinjer uppnådde modellen god prestanda och rankade korrekt sanna interaktioner långt över slump både i interna tester och i en oberoende valideringscellinje.
Nya perspektiv på cancercellernas maskineri
Med detta arbetsflöde kartlade forskarna interaktionsnätverk i en normal thyreoideacellinje och två cancerösa linjer: en papillära thyreoideakarcinomlinje och en follikulär karcinomlinje som kan sprida sig till lungorna. I dessa celler identifierade de över 25 000 sannolika proteininteraktioner och fann starka signaler från välkända cellulära maskiner såsom ribosomer (som bygger proteiner) och proteasomer (som bryter ner dem), vilket bekräftar att metoden återfångar etablerad biologi. Genom att jämföra cancerlinjerna med den normala linjen upptäckte de nätverk som var uppreglerade i sjukdomen. I de metastatiska follikulära karcinomcellerna var både proteasomkomponenter och ett chaperonkomplex kallat prefoldin tydligt mer sammankopplade och mer abundanta. Flera prefoldin-subenheter hade tidigare kopplats till andra cancerformer, men globala proteinskanningar hade missat deras samordnade beteende i thyreoideacancer, möjligen eftersom dessa proteiner är hårt kontrollerade via nedbrytning. Co-fraktioneringsmetoden exponerade deras koordinerade förändringar på komplexnivå.
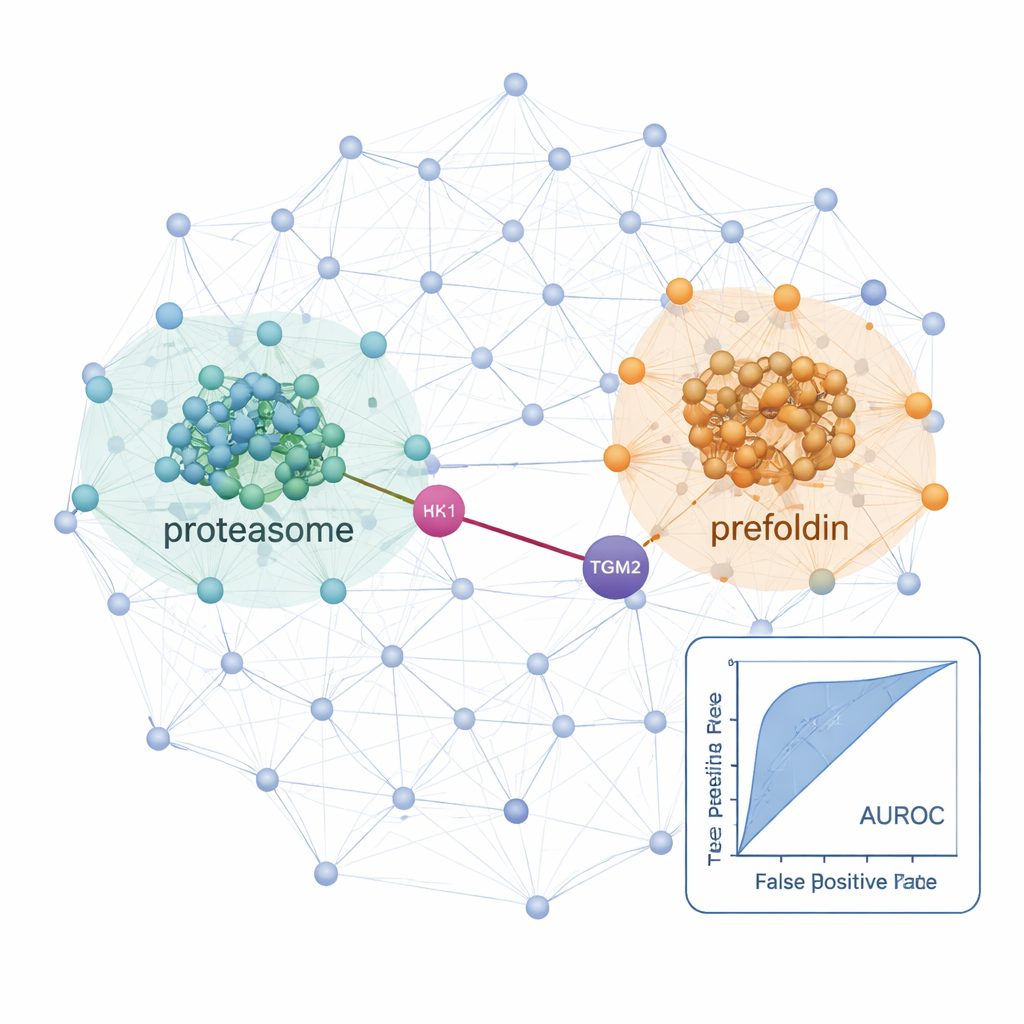
Dolda länkar som kan vägleda framtida behandlingar
Studien lyfte också fram specifika interaktioner som kan vara viktiga för hur thyreoideacancer växer och sprider sig. Ett exempel är en förutsagd koppling mellan HK1, ett enzym som påbörjar cellens huvudsakliga sockernedbrytningsväg, och TGM2, ett protein känt för att främja invasion och metastas i thyreoideatumörer. Denna HK1–TGM2-anslutning, frånvarande i befintliga interaktionsdatabaser, stöddes av strukturell modellering och verkade särskilt aktiv i den papillära karcinomlinjen, vilket antyder att metabol omprogrammering och invasivt beteende kan vara fysiskt kopplade. Sammanfattningsvis visar ProteoAutoNet hur kombinationen av robotik och maskininlärning kan förvandla långsam, expertberoende kartläggning av proteinnätverk till en mer skalbar process. För icke-specialister är huvudbudskapet att denna teknik kan avslöja både breda skiftningar i cellulärt maskineri och oväntade proteinpartnerskap som en dag kan hjälpa kliniker att bättre förutse vilka thyreoideacancerformer som blir aggressiva och föreslå nya måltavlor för terapi.
Citering: Lyu, M., Hu, P., Zhang, G. et al. ProteoAutoNet: high-throughput co-eluted protein analysis with robotics and machine learning. Nat Commun 17, 1949 (2026). https://doi.org/10.1038/s41467-026-68686-9
Nyckelord: proteininteraktioner, masspektrometri, maskininlärning i biologi, thyreoideacancer, proteasom och prefoldin