Clear Sky Science · sv
Flerlandsgenomanalys framhäver regional spridning av kolera i Afrika
Varför det spelar roll att följa bakterier över gränser
Kolera gör fortfarande tiotusentals människor sjuka och dödar många varje år i Afrika, men grundläggande frågor kvarstår om hur utbrott startar, rör sig mellan länder och återkommer gång på gång. Denna studie sammanför forskare och folkhälsoteam från sju afrikanska länder för att spåra bakterien som orsakar kolera genom att läsa dess genetiska kod. Genom att jämföra hundratals bakteriegenom visar forskarna hur nyliga koleravågor flödat över gränser, vilka typer av stammar som cirkulerar var, och hur denna kunskap kan skärpa insatserna för att stoppa framtida epidemier.
En kontinentövergripande blick på kolera
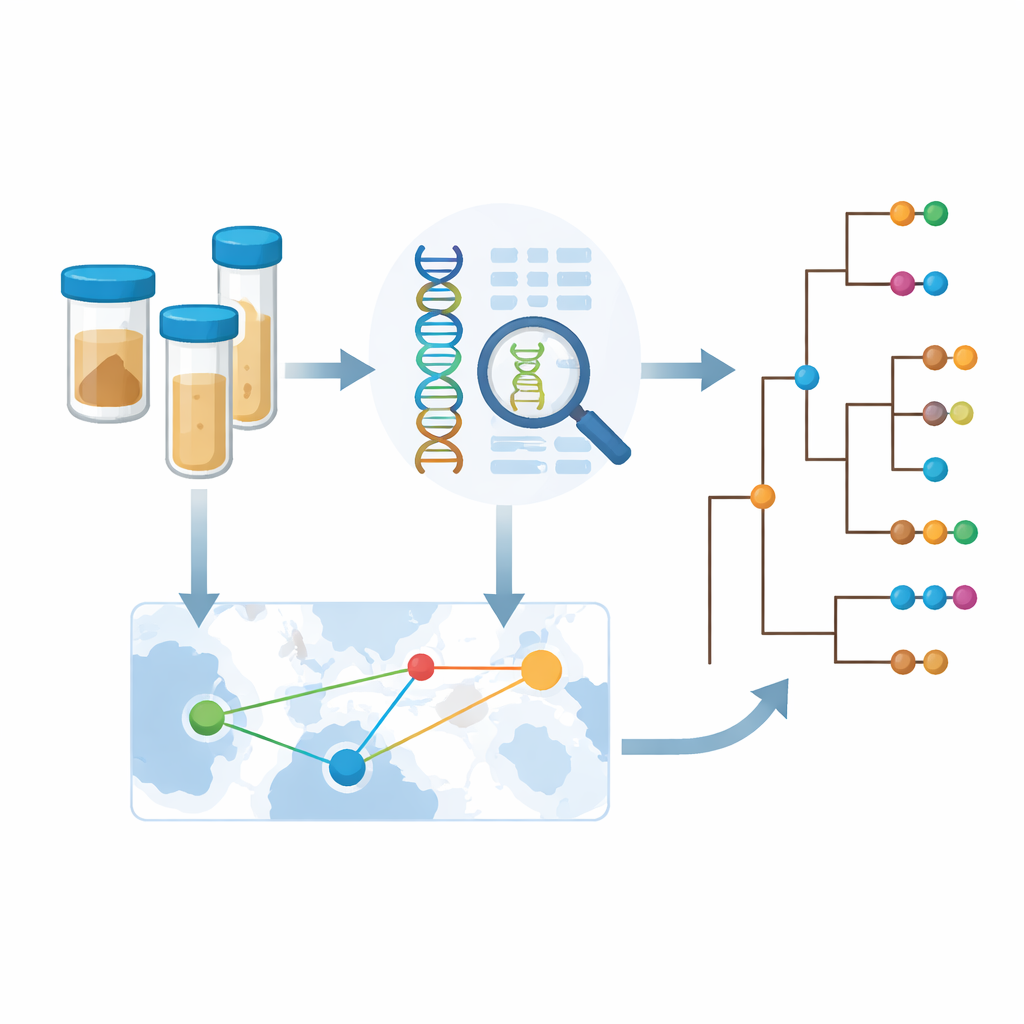
För att gå bortom spridda anmälningsfall inledde Africa Centres for Disease Control and Prevention ett samarbete kallat Cholera Genomics Consortium in Africa (CholGEN). Laboratorier i Kamerun, Demokratiska republiken Kongo, Malawi, Moçambique, Nigeria, Uganda och Zambia sekvenserade 763 högkvalitativa genom av bakterien Vibrio cholerae O1, huvudsakligen från 2019 till 2024. Detta utgör den största mängden koleragenom som någonsin genererats inom Afrika självt. Genom att placera dessa nya genom tillsammans med nästan 1 800 tidigare sekvenserade prover från Afrika och Asien kunde teamet rekonstruera hur de senaste afrikanska utbrotten passar in i den långvariga globala kolerapandemin.
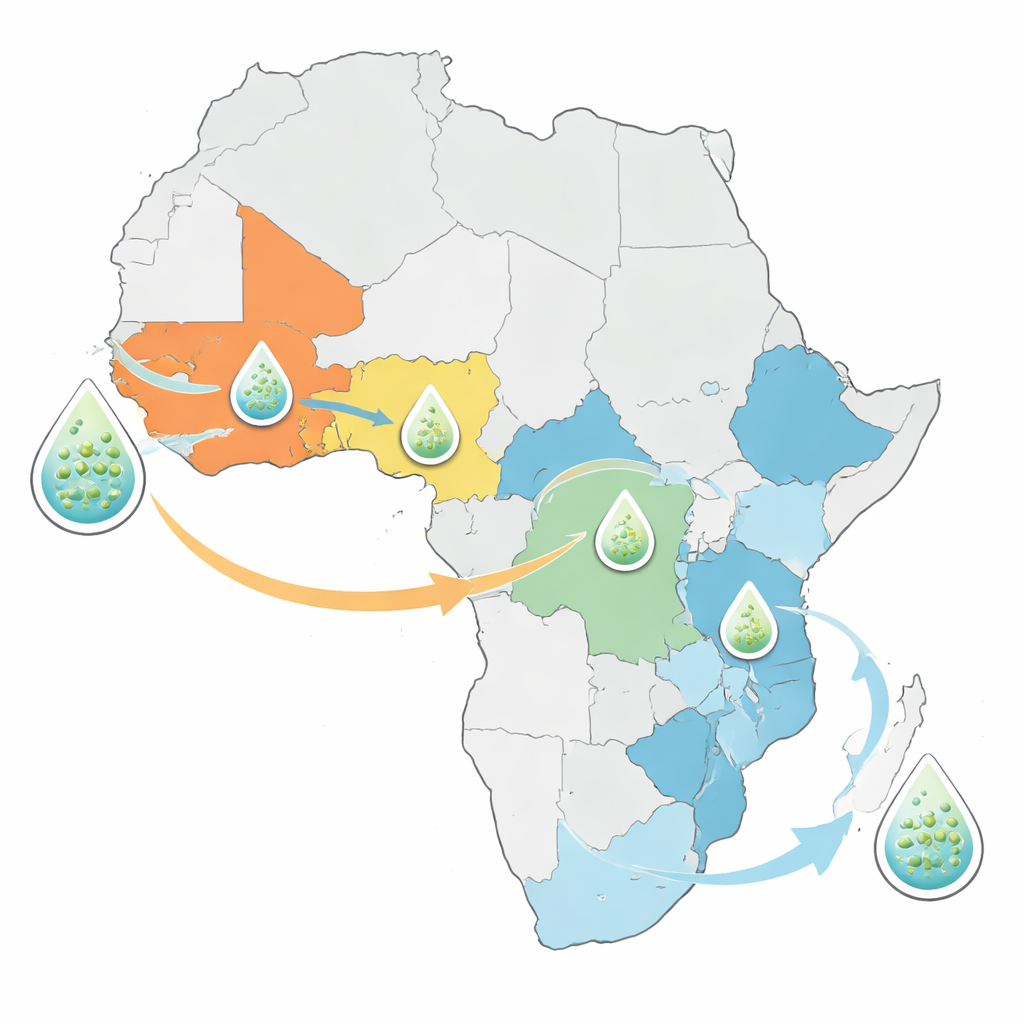
Gamla stammar, nya vägar
Analysen visade att de kolerastammar som orsakar dagens afrikanska utbrott inte utgör ett helt nytt hot. Istället härstammar alla nysekvenserade bakterier från tidigare kända introduktioner av den sjunde-pandemins koleralinje som först nådde Afrika från Asien 1970. Västra och centrala afrikanska länder som Nigeria, Kamerun och Demokratiska republiken Kongo domineras ofta av en eller två långlivade linjer som har bestått i årtionden. Östra och södra Afrika hyser däremot en blandning av flera linjer samtidigt. En linje i synnerhet, kallad AFR15, har spridit sig snabbt under senare år och kopplas till ovanligt stora utbrott i Malawi, Zambia och grannländer, liksom till epidemier i delar av Mellanöstern och Sydasien.
När utbrottens storlek inte ligger i generna
Man skulle kunna tro att AFR15:s explosiva spridning beror på stora genetiska förändringar som gör den farligare eller bättre på att undvika behandling. När forskarna jämförde mutationshastighet och mönster över flera aktiva linjer fann de dock inga påfallande skillnader. Bakterierna utvecklades i ungefär samma takt, och typerna av mutationer och vilka gener som påverkades såg mycket lika ut mellan linjerna. Övergripande profiler för antibiotikaresistens var också till största delen stabila över tid och mellan länder. Ett huvudundantag var i Uganda, där bakterierna förvärvat ett stort mobilt DNA-element kallat en plasmid som bär flera resistensgener, sannolikt importerat tillsammans med stammar kopplade till utbrott i Jemen och Libanon. Ändå fann studien inga nya gener som ensamt skulle förklara svårighetsgraden i de senaste afrikanska utbrotten.
Dolda resor avslöjade genom bättre provtagning
Eftersom bakteriegenomen bär en uppteckning över var närbesläktade stammar hittades, kunde teamet sluta sig till hur ofta kolera korsar gränser. De upptäckte många exempel på internationell spridning mellan grannländer, inklusive upprepade utbyten mellan Zambia och Demokratiska republiken Kongo. Men när de granskade mer noggrant såg de att statistiska signaler för gränsöverskridande hopp var starkast under år och i platser med intensiv provtagning. Detta tyder på att verkliga rörelser av kolera är vanligare än vad de nuvarande uppgifterna visar; många överföringstillfällen går sannolikt obemärkt förbi helt enkelt eftersom ingen sekvenserar bakterier på dessa platser eller tidpunkter. För att hantera detta utvecklade författarna ett ramverk för att uppskatta hur mycket ny information ett land får av att sekvensera ytterligare prover, i balans mellan genetisk mångfald, antal introduktioner och befintliga data.
Använda genomik för att styra smartare kontrollinsatser
Studien slutar i att för kolera i dagens Afrika spelar hur och var sjukdomen sprids större roll än någon dramatisk förändring i själva bakterien. Resultaten talar för rutinmässig, regionalt samordnad genomisk övervakning så att grannländer kan upptäcka gemensamma utbrott tidigt, spåra deras källor och rikta insatser som vaccinationskampanjer, förbättringar av vatten och sanitet samt insatser i gränsregioner mer effektivt. Genom att bygga upp sekvenseringskapacitet inom afrikanska folkhälsolaboratorier och dela data över gränser ger initiativ som CholGEN en praktisk plan för att använda modern genetik för att närma sig det ambitiösa målet att eliminera kolera som ett folkhälsoproblem till 2030.
Citering: Mboowa, G., Matteson, N.L., Tanui, C.K. et al. Multicountry genomic analysis underscores regional cholera spread in Africa. Nat Commun 17, 2539 (2026). https://doi.org/10.1038/s41467-026-68642-7
Nyckelord: kolera, genomövervakning, Afrika, gränsöverskridande överföring, antimikrobiell resistens