Clear Sky Science · sv
En kontextmedveten basavkodare för nanopore direkt-RNA-sekvensering
Varför det är viktigt att avkoda RNA-bokstäver
Varje cell i din kropp läser och omskriver ständigt meddelanden skrivna i RNA, arbetskopian av våra gener. Nya “nanopore”-maskiner kan läsa enskilda RNA-molekyler direkt, vilket lovar att avslöja hur gener slås på, hur RNA splicas och hur kemiska markeringar på RNA påverkar hälsa och sjukdom. Men det finns en hake: dessa enheter mäter i själva verket små elektriska strömmar, som sedan måste översättas—”basavkodas”—till de välkända A, C, G och U-bokstäverna. Om den översättningen är felaktig kan den biologiska berättelsen vi drar bli starkt förvrängd. Denna artikel introducerar Coral, ett nytt artificiellt intelligenssystem som gör denna översättning mycket mer träffsäker.
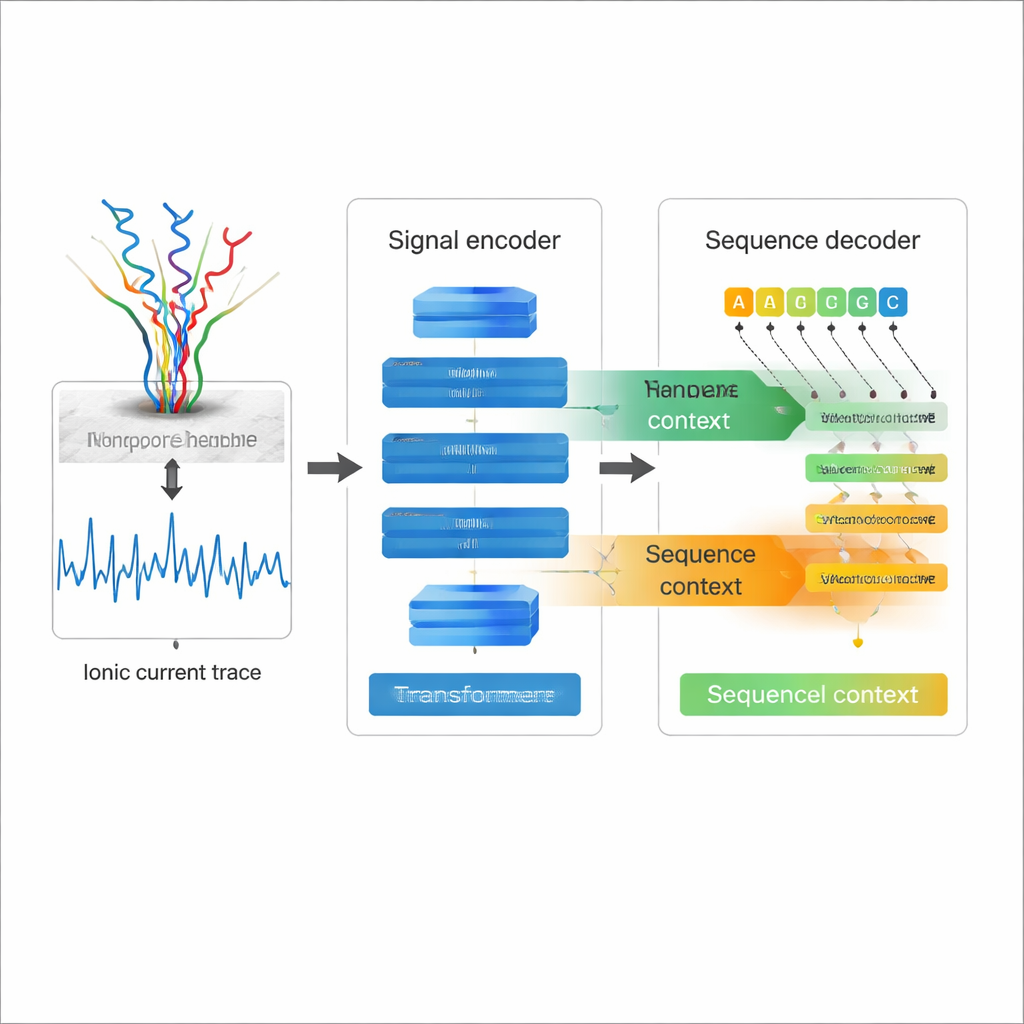
Läser elektricitet istället för bokstäver
Nanopore direkt-RNA-sekvensering fungerar genom att en enkel RNA-sträng trådas genom ett molekylärt hål—en nanopore—samtidigt som man mäter hur den elektriska strömmen förändras när varje nukleotid passerar. De där krulliga strömspåren innehåller information om RNA-sekvensen och dess kemiska modifieringar. Traditionell RNA-sekvensering konverterar istället RNA till DNA och amplifierar det, steg som kan introducera bias och utplåna många naturliga kemiska markeringar. Direkt-RNA-sekvensering undviker dessa problem, men priset har varit en relativt hög felprocent när strömspåren omsätts till sekvenser, särskilt för utmanande inslag som upprepade bassekvenser och komplexa RNA-strukturer. Bättre basavkoding är avgörande om forskare ska kunna lita på de fina detaljerna i dessa långa RNA-läsningar.
En smartare översättare som använder två typer av kontext
De flesta befintliga nanopore-basavkodare behandlar den elektriska signalen som huvudkällan till information och avkodar varje position nästan oberoende, vilket begränsar hur väl de kan utnyttja RNA-sekvensens egen struktur. Coral tar en annan väg. Den använder en Transformer-baserad encoder–decoder-arkitektur, liknande i anda moderna språkmodeller. Först smälter en encoder-nätverk byggd av konvolutioner och self-attention-lager ner den råa strömsignalen till en kompakt beskrivning av hur signalen förändras över tid. Sedan förutsäger en decoder varje ny RNA-bas steg för steg, samtidigt som den tittar bakåt på de baser den redan skrivit och åt sidan på den enkodade signalen. Två typer av attention—inom den växande RNA-sekvensen och mellan sekvens och signal—låter Coral väga både elektrisk och sekvenskontext när den avgör vilken bokstav som kommer härnäst.
Skarpare sekvenser och färre missade molekyler
Författarna testade Coral mot flera ledande basavkodare, inklusive Oxford Nanopores kommersiella verktyg, på RNA från människor och andra organismer samt på flera nanopore-kemier. Över sex arter och äldre RNA-sekvenseringskit uppnådde Coral en typisk medianläsnoggrannhet runt 97 %, klart högre än konkurrerande metoder. Med det senaste RNA-kitet översteg dess noggrannhet 99 %. Coral gav färre missmatchningar, insertioner och deletioner, och producerade längre, bättre justerade läsningar med färre sekvenser som inte kunde mappas alls. Den hanterade särskilt korta sekvenser av upprepade baser väl—mycket vanliga i verkliga data—vilket ofta är en felkälla för andra verktyg. Genom att mer pålitligt fånga längre stycken korrekt sekvens utmärkte sig Coral även vid förutsägelse av korta sekvensmönster (k‑mer) och förblev robust även när tidigare avkodningssteg innehöll små misstag.
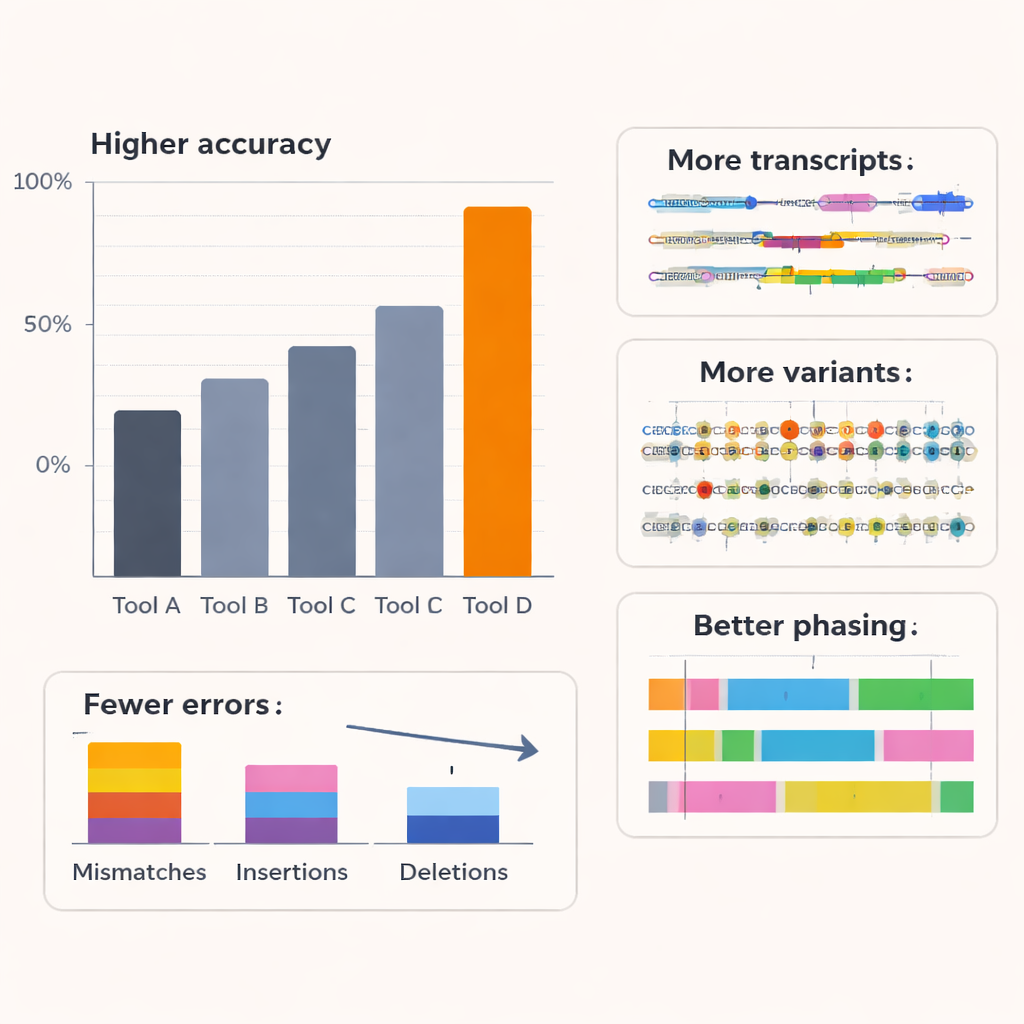
Ser mer av transkriptomets dolda detaljer
Förbättrad basavkoding är bara värdefull om den leder till bättre biologisk insikt. För att testa detta undersökte teamet hur Corals output påverkade efterföljande analyser i humana cellinjer. Genom att använda ett specialiserat verktyg för att rekonstruera fullständiga RNA-isoformer—de olika splice-versionerna av varje gen—fann de att Corals läsningar exponerade fler kända transkriptstrukturer och många ytterligare isoformer med låg abundans som andra basavkodare missade. Många Coral-specifika transkript stöddes av oberoende kortläsningsdata, vilket tyder på att de är verkliga snarare än artefakter. Coral upptäckte också fler artificiella referenstranskript med kända koncentrationer i ett spike-in-experiment och uppskattade deras abundans mer noggrant. Utöver transkriptupptäckt förbättrade Coral även upptäckten av genfusioner i en bröstcancercellinje och ökade antalet och tillförlitligheten hos gener som visade allel-specifik uttrycksnivå, där en föräldrakopia av en gen är mer aktiv än den andra.
Klarare genetiska varianter och familjelinjer
Där långa RNA-läsningar kan täcka avlägsna genetiska varianter är de kraftfulla verktyg för att bestämma vilka varianter som reser tillsammans på samma kromosomkopiera—en process som kallas haplotypfasing. Med ett välstuderat mänskligt prov med en guldstandard-variantkarta visade författarna att Corals högre kvalitet på läsningarna ledde till mer noggrann upptäckt av enkelbasförändringar och betydligt färre fasingfel: switchfel och den totala missmatchfrekvensen inom faseade block minskade med upp till omkring tre fjärdedelar jämfört med andra metoder, samtidigt som avsevärt fler varianter överhuvudtaget kunde fases. Simulationsstudier som varierade underliggande läsnoggrannhet bekräftade att när basavkodningen når ungefär 95 % noggrannhet förbättras prestanda i transkriptupptäckt, allel-specifikt uttryck och fasing kraftigt och sedan planar ut. Coral befinner sig i denna högnyttozon, vilket tyder på att den fångar det mesta av den biologiskt relevanta informationen som finns i de brusiga nanopore-signalerna.
Vad detta betyder för framtida RNA-forskning
För icke-specialister är huvudbudskapet att Coral fungerar som en mycket mer pålitlig översättare mellan nanopore-sekvenserarnas elektriska språk och RNAs genetiska språk. Genom att bättre använda kontext i både signalen och den växande sekvensen producerar det renare läsningar som avslöjar fler transkriptvarianter, hittar sällsynta fusionsgener och med större säkerhet spårar vilka varianter som härstammar från vilken förälder. Programvaran är öppen källkod, så forskare kan anpassa den till nya organismer, kemier eller till och med för att studera kemiska markeringar på RNA i sig. När nanopore-teknologin fortsätter att förbättras kommer verktyg som Coral att hjälpa till att omvandla råa strömspår till pålitliga, detaljerade kartor över RNA-världen inne i cellerna.
Citering: Xie, S., Ding, L., Yu, Y. et al. A dual context-aware basecaller for nanopore direct RNA sequencing. Nat Commun 17, 1851 (2026). https://doi.org/10.1038/s41467-026-68566-2
Nyckelord: nanopore RNA-sekvensering, basavkodning, Transformer-modell, transkriptisoformer, haplotypfasing