Clear Sky Science · sv
Low-komplexa repetitioner i RNA–RNA-interaktioner och en djupinlärningsram för duplexprediktion
Klistriga RNA-sekvenser som formar cellernas beteende
Inuti varje cell stöter RNA-molekyler ständigt ihop med varandra och bildar flyktiga partnerskap som hjälper till att styra vilka gener som är aktiva, hur proteiner produceras och hur celler utvecklas. Denna studie visar att många av dessa RNA–RNA-möten inte är slumpmässiga: de styrs av korta, enkla, mycket repetitiva sekvenser som fungerar som molekylärt kardborreband. Forskarna bygger också ett artificiellt intelligensverktyg som kan identifiera var sådana RNA-par sannolikt bildas, vilket öppnar nya sätt att utforska hur celler fungerar vid hälsa och sjukdom.
Enkla repetitioner med kraftfull effekt
RNA beskrivs ofta som en budbärare som bär genetisk information från DNA till proteiner, men det fungerar också som ett skelett, en regulator och en guide. Mycket av denna aktivitet beror på att två RNA-strängar binder till varandra. Genom att kombinera data från flera stora experimentella undersökningar i humana och musceller visar författarna att de regioner av RNA som faktiskt engagerar sig i sådant parande är starkt berikade i vad de kallar low-komplexa repetitioner. Det är sträckor byggda av korta motiv—som serier av G- och C-baser—upprepade om och om igen. Istället för att vara genomin ”skräp” visar det sig att dessa repetitiva delar utgör primära fästöra där ett RNA kan haka i många andra och bilda täta interaktionsnav över transkriptomet. 
RNA-nav för utveckling och reglering
När teamet undersökte vilka gener som bär dessa repetitionsrika kontaktställen framkom ett slående mönster: många av dem kodar för proteiner som styr utveckling och cellidentitet, såsom transkriptionsfaktorer. Även i cancercellinjer som inte aktivt differentierar var RNA kopplade till utvecklingsprogram tungt involverade i repetitionsbaserade kontakter. Författarna fördjupade sig också i specifika långa icke-kodande RNA (lncRNA), som är RNA-molekyler som inte kodar för proteiner men ofta reglerar dem. Till exempel visade mål för lncRNA TINCR och av ett annat lncRNA viktigt för motorneuronsbildning, Lhx1os, båda en överrepresentation av komplementära repetitioner. I dessa fall matchas enkla repetitioner på lncRNA av komplementära repetitioner i deras partner-RNA, vilket möjliggör stabila parningar som kan hjälpa till att justera nivåerna eller översättningen av viktiga utvecklingsgener.
Var proteiner och redigeringsenzymer går in
Dessa repetitionsdrivna RNA-kontakter verkar sällan ensamma. Författarna lade proteinbindningskartor över sina interaktionsdata och fann att många kontaktställen med repetitioner också känns igen av RNA-bindande proteiner som är involverade i translationskontroll, RNA-nedbrytning och bildandet av cytoplasmatiska granuler som P-bodies och stresskorn. Ett protein i synnerhet, STAU1, som kan utlösa nedbrytning av sina RNA-mål, binder ofta duplexer som bildas genom low-komplexa repetitioner. Nedreglering av STAU1 ledde till högre nivåer av RNA inblandade i dessa duplexer, särskilt de som bär repetitioner, vilket tyder på att repetitionsmedierad RNA-parning kan flagga transkript för kontrollerad nedbrytning. Samma repetitionsrika regioner attraherar även RNA-redigeringsenzymer såsom ADAR1, vilka kemiskt modifierar specifika baser inom dubbelsträngat RNA, vilket antyder att low-komplexa repetitioner hjälper till att positionera redigeringsställen som finjusterar RNAs beteende.
Att lära ett neuralt nätverk att läsa RNA-kontakter
Standardprogram försöker förutsäga RNA–RNA-bindning främst baserat på termodynamisk stabilitet—hur mycket energi det skulle krävas för att bilda eller bryta en duplex. Dessa modeller är användbara men missar ofta verkliga interaktioner som observeras i celler, särskilt mellan långa RNA. För att gå bortom enkla energiregler tränade författarna en djupinlärningsmodell kallad RIME som använder ”språkmodells”-liknande inbäddningar: numeriska representationer av RNA-sekvenser som kodar mönster inlärda från mycket stora samlingar av nukleinsyra-data. RIME visas par av RNA-segment och lär sig klassificera om de interagerar, med många verkliga parningar från psoralen-baserade tvärbindningsexperiment som positiva exempel och noggrant konstruerade icke-interagerande par som negativa. 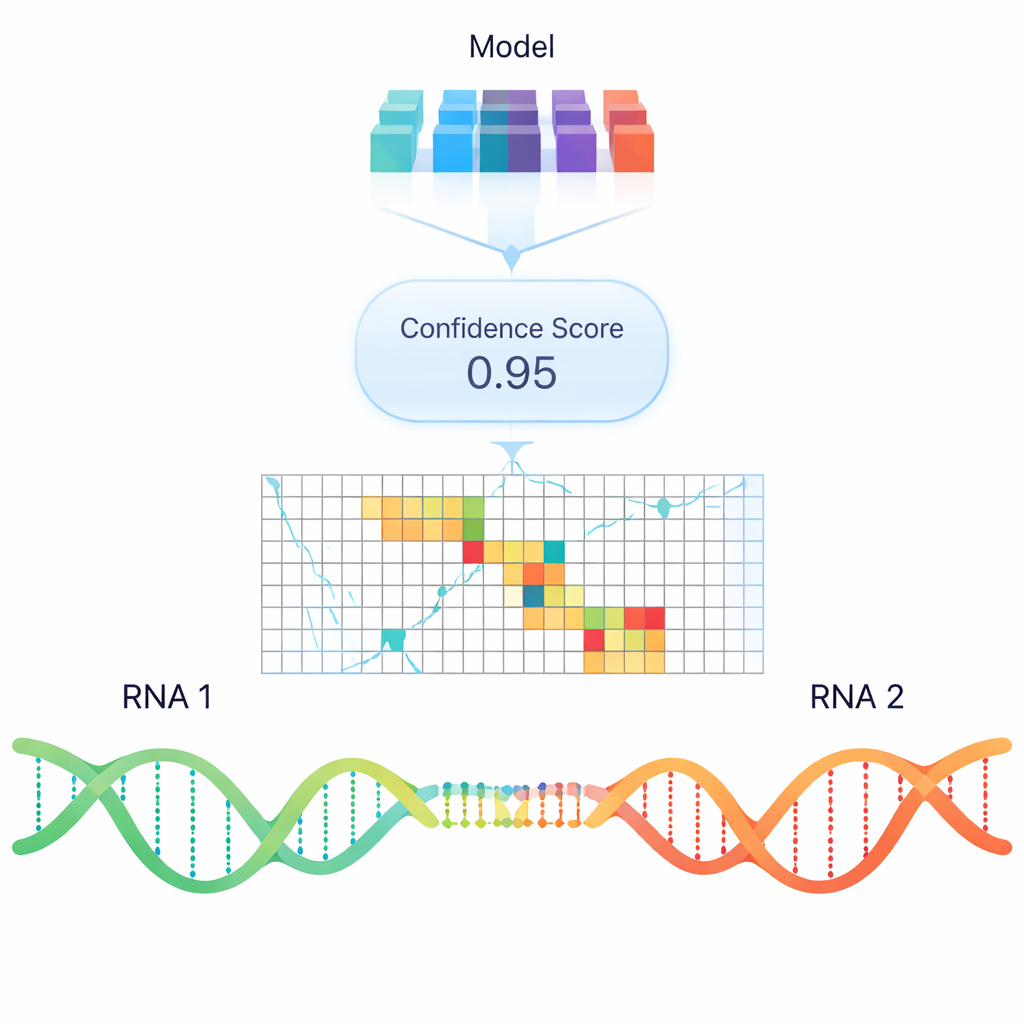
Smartare prediktioner och nya biologiska ledtrådar
När RIME jämfördes med ledande termodynamikbaserade verktyg och en annan neuralt nätverksmetod presterade den konsekvent bättre på att skilja verkliga RNA–RNA-kontakter från lockbeten, särskilt för högkonfidens experimentella interaktioner. Den förutspår inte bara om två RNA kommer att paras utan tenderar också att markera de exakta regioner som är involverade, och den lär sig naturligt att low-komplexa repetitioner är starka prediktorer för kontakt. Anmärkningsvärt nog fungerar samma modell, tränad endast på interaktioner mellan olika RNA, också bra för att förutsäga intern basparning inom en enskild RNA-molekyl, i överensstämmelse med både strukturella experiment och klassiska veckningsalgoritmer. För icke-kodande regulatorer som TINCR, NORAD och SMaRT återupptäcker RIME framgångsrikt kända funktionella interaktionsställen och föreslår ytterligare kandidatregioner.
Varför detta är viktigt
För en lekmannaläsare är huvudbudskapet att korta, repetitiva sträckor i RNA—som tidigare lätt kunnat avfärdas som värdeligt brus—fungerar som centrala kontaktytor i cellens RNA-kopplingsdiagram. De hjälper till att föra RNA samman, bjuder in regulatoriska proteiner och redigeringsenzymer och används flitigt i vägar som styr hur celler utvecklas och svarar på stress. Den nya RIME-modellen ger forskare ett kraftfullt verktyg för att skanna genom genom för dessa RNA–RNA-partnerskap, inklusive sådana som kan gå fel i neurologiska och andra sjukdomar kopplade till repeatexpansioner. I korthet visar detta arbete att förstå — och förutsäga — hur enkla RNA-repetitioner hakar i varandra kan avslöja dolda lager av genreglering.
Citering: Setti, A., Bini, G., Pellegrini, F. et al. The role of low-complexity repeats in RNA–RNA interactions and a deep learning framework for duplex prediction. Nat Commun 17, 1637 (2026). https://doi.org/10.1038/s41467-026-68356-w
Nyckelord: RNA–RNA-interaktioner, low-komplexa repetitioner, långa icke-kodande RNA, djupinlärning, genreglering