Clear Sky Science · sv
En lång väg kvar till tillförlitliga och fullständiga genom för medicinalväxter
Varför växt-DNA‑kartor spelar roll för människors hälsa
Många av dagens mest verksamma läkemedel — från cancerläkemedel som paklitaxel till smärtstillande medel som morfin och malariamedlet artemisinin — kommer från växter. För de flesta medicinalväxter saknar forskare dock fortfarande en fullständig ”instruktionsmanual” i form av deras DNA. Denna översikt förklarar hur nya genomtekniker förändrar vår förmåga att läsa dessa manualer, varför nuvarande växtgenom ofta fortfarande är ofullständiga eller felaktiga, och hur verkligt precisa genom kan öppna för bättre läkemedel, mer hållbar produktion och förbättrad bevarande av värdefulla arter.
Löftet i att läsa medicinalväxters ritningar
Under årtusenden har människor förlitat sig på örtmedicin, och modern farmakologi fortsätter att hämta i hög grad från växternas naturliga produkter. Dessa specialiserade molekyler — alkaloider, terpenoider, fenoliska föreningar och många fler — bildas genom intrikata metaboliska vägar kodade i växternas DNA. Fram till nyligen fick forskare pussla ihop dessa vägar med långsamma, arbetsintensiva metoder som isotopspårning och kloning ett gen i taget. Framväxten av prisvärd, höggenomströmmande DNA‑sekvensering förändrade landskapet. I februari 2025 hade genom för 431 medicinalväxter (över 203 arter) sekvenserats, vilket gav forskare ett systematiskt verktyg att leta efter väggenes, förstå hur värdefulla föreningar regleras och utforska hur dessa kemier utvecklats.
En boom i sekvensering, men många ofullkomliga genom
Långläsningstekniker från PacBio och Oxford Nanopore, i kombination med kortläsningsdata från Illumina och kromosomskala kartläggningsmetoder som Hi‑C, har förbättrat kvaliteten på växtgenom avsevärt. Nästan hälften av alla monteringarna för medicinalväxter publicerades först under de senaste tre åren, och de flesta nyare genom byggs nu i kromosomskala. Granskningen visar dock att kvantitet har överträffat kvalitet. Mer än hälften av genomen finns bara i en initial version, många är fortfarande på utkastnivå, och endast 11 medicinalväxter har ”telomer‑till‑telomer” (T2T) gapfria assemblage som fångar centromerer och andra repetitiva regioner fullständigt. Standardmått som N50 (ett mått på kontiguitet) och BUSCO‑poäng (ett mått på bevarade gener) ser övergripande lovande ut, men de kan dölja avgörande luckor precis där viktiga biosyntetiska gener finns.
Dolda luckor där läkemedelsgenerna borde finnas
För att testa hur användbara nuvarande genom verkligen är undersökte författarna kända, experimentellt validerade väggenes i nio välstuderade medicinalväxter. Även i vissa kromosomnivå‑assemblage saknades viktiga enzymer för föreningar som ginsenosider i ginseng eller artemisinin i Artemisia annua helt eller var endast delvis fångade. I andra fall fanns generna i den råa genomsekvensen men var frånvarande eller trunkerade i de officiella genannoteringarna, vilket gjorde dem svåra att hitta. Ett slående exempel kommer från den kumarinproducerande örten Peucedanum praeruptorum: ett äldre kromosomnivå‑genom bröt en nyckelgen och missade två andra; ett nyare T2T‑assembly återställde inte bara dessa gener utan avslöjade också att flera av dem ligger tillsammans i ett tätt packat biosyntetiskt genkluster. Den här typen av klusterkarta är precis vad forskare behöver för att konstruera växter eller mikrober som producerar läkemedel mer effektivt.
Varför växtgenom är så svåra att montera
Medicinalväxter ställer särskilda utmaningar som går bortom de flesta grödor. Deras genom har ofta höga nivåer av heterozygositet (många DNA‑skillnader mellan de två kopiorna av varje kromosom), frekvent polyploidi (flera kromosomuppsättningar) och stora andelar repetitivt DNA — egenskaper som förvirrar monteringsalgoritmer och leder till avbrott eller felaktiga sammanfogningar. Ungefär en tredjedel av de sekvenserade medicinalväxterna har genom med mer än 70 % repetitivt innehåll, och över en fjärdedel visar mycket hög heterozygositet. Att avla fram starkt inavlade linjer eller isolera haploid vävnad kan hjälpa, men det är långsamt, kostsamt eller biologiskt svårt för många arter. Nya strategier som monterar varje föräldrahaplotyp separat, och kraftfullare algoritmer anpassade för repeat‑rika, polyploida genom, börjar lätta på dessa hinder men är ännu inte rutin.
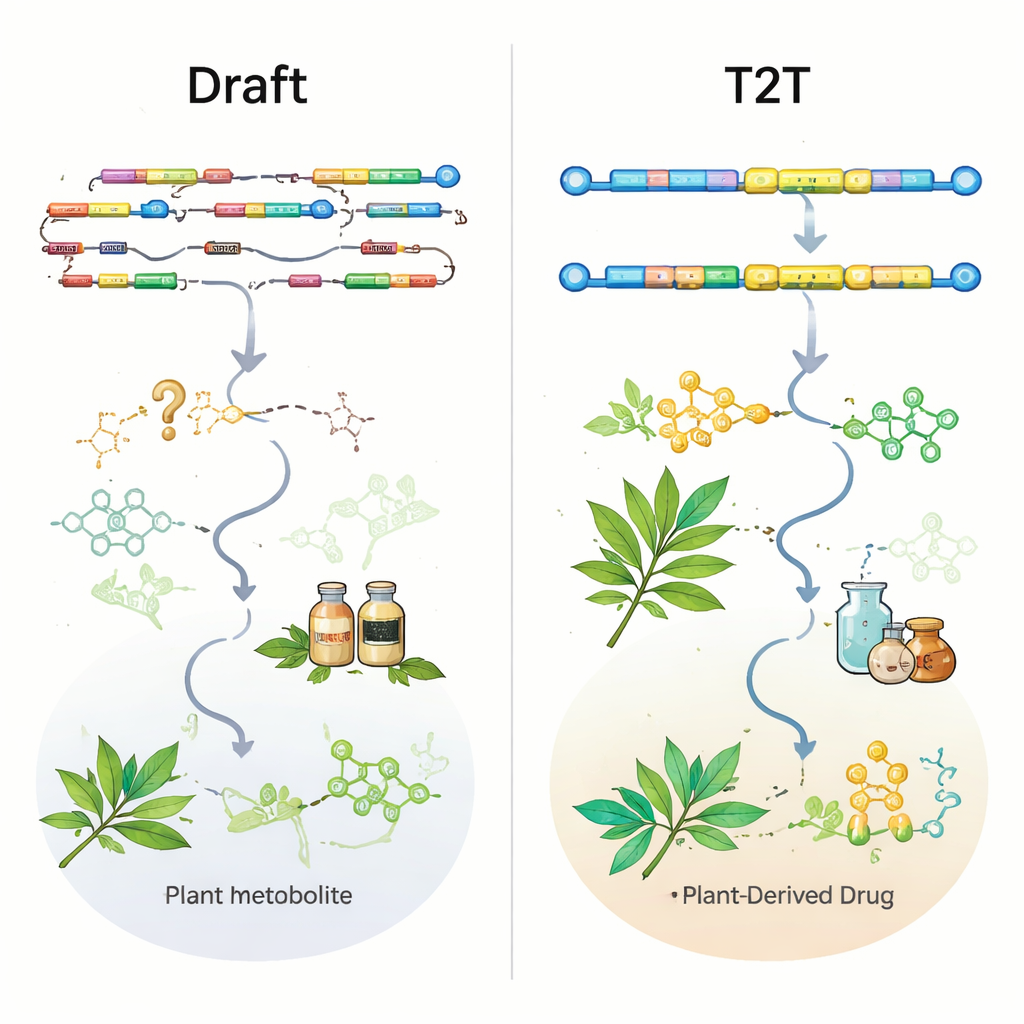
Från genom till nya läkemedel och framtida riktningar
När genom är tillräckligt bra blir de kraftfulla motorer för upptäckt. Forskare kan kombinera helgenomsdata med transkriptomik, metabolomik och syntetisk biologi för att peka ut enzymer, regulatoriska gener och biosyntetiska genkluster som styr produktionen av högvärdiga föreningar. Dessa insikter har redan möjliggjort rekonstruktion av komplexa växtvägar — såsom de för vinblastin, paklitaxel och många andra läkemedel — i jäst eller modellväxter, vilket öppnar en väg mot stabil storskalig bioproduktion. Framöver argumenterar författarna för ett skifte från ”ett grovt genom per art” till flera högkvalitativa, T2T‑ och haplotypupplösta assemblage som fångar intraspecifik mångfald, liknande pan‑genom i grödforskning. Att koppla dessa referensgenom till storskalig resekvenering, avancerad fenotypering och framväxande single‑cell‑ och rumslig transkriptomik bör belysa hur miljö, celltyp och genätverk samverkar för att forma medicinalkemi.
Vad detta betyder för patienter och planeten
Granskningens centrala budskap är att tillförlitliga, fullständiga genom för medicinalväxter inte är en lyx; de är grunden för att omvandla århundraden av örtkunskap till precisa, moderna terapier. Bättre genom hjälper forskare att hitta saknade steg i läkemedelsvägar, konstruera säkrare och mer rikliga leveranser av kritiska läkemedel och identifiera alternativa arter som kan producera samma föreningar. De kommer också att vägleda bevarande och hållbar användning av hotade medicinalväxter, varav de flesta fortfarande saknar något genomiskt resurser. Kort sagt kan slutförandet av kartläggningen av dessa genom snabba upp läkemedelsupptäckt, stabilisera leveranskedjor och bevara botanisk mångfald — allt till gagn för människors hälsa.
Citering: Cheng, LT., Wang, ZL., Zhu, QH. et al. A long road ahead to reliable and complete medicinal plant genomes. Nat Commun 16, 2150 (2025). https://doi.org/10.1038/s41467-025-57448-8
Nyckelord: genomik för medicinalväxter, biosyntetiska genkluster, telomer-till-telomer-genom, biosyntes av naturliga produkter, syntetisk biologi