Clear Sky Science · sv
Overensstämmande analys av DNA‑ och RNA‑profiler: MD Anderson IMPACT2‑studien inom precisionsonkologi
Varför denna forskning är viktig för cancerpatienter
Behandling av cancer styrs i allt högre grad av den genetiska sammansättningen i varje patients tumör. Läkare använder redan DNA‑tester för att hitta mutationer som kan riktas med specifika läkemedel, men dessa tester berättar inte hela historien om hur en tumör beter sig. Denna studie från MD Anderson Cancer Center ställer en praktisk fråga: om vi också tittar på RNA — de "arbetskopia" av gener som visar vilka gener som faktiskt är påslagna eller avstängda — kan vi då bättre förstå en patients cancer och deras överlevnadschanser?
Två informationslager: DNA och RNA
Varje cancercell bär på förändringar i sitt DNA, men DNA är till stor del en statisk ritning. RNA fångar däremot vad cellen aktivt gör vid ett givet ögonblick. I IMPACT2‑studien fick mer än 800 patienter med avancerad cancer sina tumörer genetiskt profilerade. För 253 av dem fanns både DNA‑ och RNA‑data. Forskarna jämförde vilka gener som var förändrade på DNA‑nivå (såsom mutationer eller extra kopior) med vilka gener som visade onormalt höga eller låga RNA‑nivåer, för att se hur ofta dessa två lager berättade samma historia och om den informationen var kopplad till hur länge patienterna levde.
När genförändringar och aktivitet stämmer överens
Teamet letade först efter "överensstämmande" händelser — fall där samma gen var onormal både i sitt DNA och i sitt RNA. Bland de 253 patienterna hade 50 minst en sådan träff, totalt 58 händelser över 23 gener. De flesta av dessa involverade extra eller förlorade kopior av en gen som också visade högre eller lägre RNA‑nivåer, och denna korrespondens var starkast för kända cancerrare som CDKN2A, AR, ESR1, KRAS, PIK3CA, AKT2, TP53 och CCND1. Dessa fynd stöder idén att strukturella DNA‑förändringar för vissa viktiga cancergener faktiskt översätts till ökad eller minskad genaktivitet, vilket förstärker deras betydelse som behandlingsmål.
Dolda relationer avslöjade av RNA‑signaler
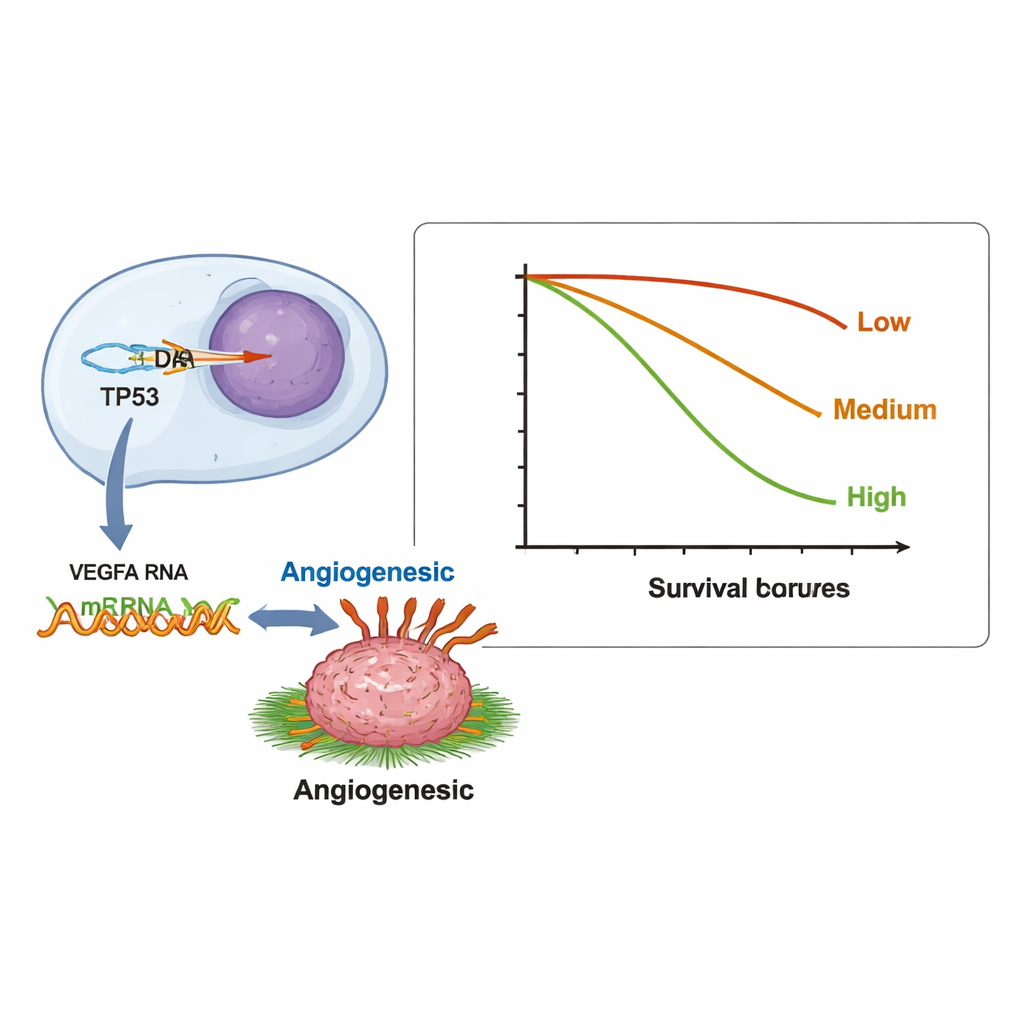
Utöver en‑till‑en‑matchningar testade forskarna mer än 12 000 genpar för att se om en DNA‑förändring i en gen konsekvent var kopplad till onormala RNA‑nivåer i en annan. De fann 123 signifikanta par. Många av dessa klustrade i ett stort tillväxt‑ och överlevnadsnätverk känt som PI3K/AKT‑vägen, ett vanligt fokus för riktade läkemedel. Ett särskilt anmärkningsvärt mönster kopplade förändringar i tumörsupressorgen TP53 till överaktiva RNA‑signaler från VEGFA, en gen som hjälper tumörer att bygga nya blodkärl. Denna relation kan bidra till att förklara varför vissa patienter vars tumörer bär TP53‑förändringar svarar på bevacizumab, ett läkemedel som blockerar blodkärlsbildning, och illustrerar hur RNA‑data kan avslöja kliniskt relevanta gen‑gen‑interaktioner som DNA ensamt kan missa.
Genaktivitetsbörda och patientöverlevnad
Forskarna undersökte också om den totala mängden onormal genaktivitet i en tumör — vad de kallar tumörtranskriptionell belastning, eller TTB — var kopplad till hur länge patienterna överlevde. De räknade hur många gener som visade förändrade RNA‑nivåer i varje patient och grupperade dem i låg (0–2 gener), intermediär (3–5) och hög (6 eller fler). Patienter i gruppen med hög TTB hade en medianöverlevnad på 6,7 månader, jämfört med 9,8 respektive 11,9 månader i de lägre grupperna. Med andra ord tenderade tumörer med många felaktigt fungerande gener på RNA‑nivå att vara mer aggressiva. Tumörer som saknade PD‑L1, en markör som ofta används för att välja patienter för immunterapi, tenderade också att ha fler gener med onormal uttrycksnivå, vilket pekar på en möjlig koppling mellan omfattande genstörning och en tumörmiljö som motstår immunangrepp.
Vad detta betyder för framtidens cancerbehandling
Denna studie visar att RNA‑profilering tillför användbar, kompletterande information till DNA‑testning hos verkliga patienter med avancerad cancer. För vissa gener överensstämmer DNA‑förändringar och RNA‑aktivitet och stärker kända behandlingsmål; i andra fall avslöjar RNA‑mönster nya relationer som kan styra läkemedelsval, såsom kopplingen mellan TP53 och VEGFA. Viktigast för patienterna var att en hög börda av onormal genaktivitet var associerad med kortare överlevnad, vilket tyder på att RNA‑baserade mått kan hjälpa läkare att bedöma hur aggressiv en tumör är och förfina prognosen. Även om RNA‑testning ännu inte rutinmässigt används för att välja terapier, stödjer dessa fynd dess potential som ett nästa steg inom precisionsonkologi, särskilt när större studier och bättre analysverktyg hjälper till att föra transkriptomprofilering in i vardaglig cancervård.
Citering: Schmidt, S.T., Baysal, M.A., Fu, S. et al. Concordance analysis of DNA and RNA profiling: The MD Anderson IMPACT2 study in precision oncology. Sig Transduct Target Ther 11, 68 (2026). https://doi.org/10.1038/s41392-026-02580-0
Nyckelord: precisionsonkologi, RNA‑profilering, DNA‑sekvensering, tumörtranskriptionell belastning, cancerbiomarkörer