Clear Sky Science · ru
Оценка качества 3D-моделей РНК с помощью глубокого обучения и промежуточных 2D-карт
Почему важно оценивать формы РНК
Внутри каждой клетки молекулы РНК сворачиваются в сложные трёхмерные формы, которые регулируют включение генов, направляют химические реакции и даже защищают от вирусов. Сегодня мощные компьютерные программы умеют предсказывать многие из этих форм, но перед учёными всё ещё стоит фундаментальная задача: когда компьютер выдаёт десятки или сотни кандидатов для одной и той же РНК, какая из моделей действительно близка к реальной структуре? В этой работе представлен RNArank — инструмент искусственного интеллекта, предназначенный для решения этой проблемы путём оценки 3D-моделей РНК, подобно инспектору качества структур, чтобы исследователи могли сосредоточиться на наиболее надёжных предсказаниях.
Новый инспектор для моделей РНК
RNArank разработан для оценки качества предложенной формы РНК без знания того, как эта модель была получена. Независимо от того, сгенерирована ли модель системой глубокого обучения, физико-обоснованным симулятором или создана человеком-экспертом, RNArank анализирует только итоговые 3D-координаты. По сути он задаёт вопрос: «Выглядит ли эта структура как реалистичная РНК?» Такая независимая оценка качества особенно важна, потому что, в отличие от мира белков, где инструменты вроде AlphaFold часто дают сразу очень надёжные ответы, предсказание РНК по-прежнему выигрывает от комбинирования разных методов и экспертного контроля — и от умного способа ранжирования полученных моделей.
Обучение ИИ распознавать хорошие РНК
Для обучения RNArank авторы собрали около 200 000 структур РНК, охватывающих широкий диапазон от явно ошибочных до почти идеальных. Эти модели были получены на основе известных экспериментальных структур с использованием различных подходов: современных предикторов глубокого обучения, молекулярно-динамических симуляций, имитирующих движение атомов, и преднамеренных искажений точных структур для создания «обманок». Для каждой модели команда рассчитывала, насколько она соответствует реальной экспериментально установленной РНК, используя уточнённую метрику точности, адаптированную для РНК, называемую lDDT_RNA. Эта оценка фокусируется на том, насколько точно воспроизводятся расстояния между парами нуклеотидов, захватывая как общую складку, так и локальные детали, не будучи чрезмерно чувствительной к длине молекулы.
Как RNArank читает и оценивает РНК
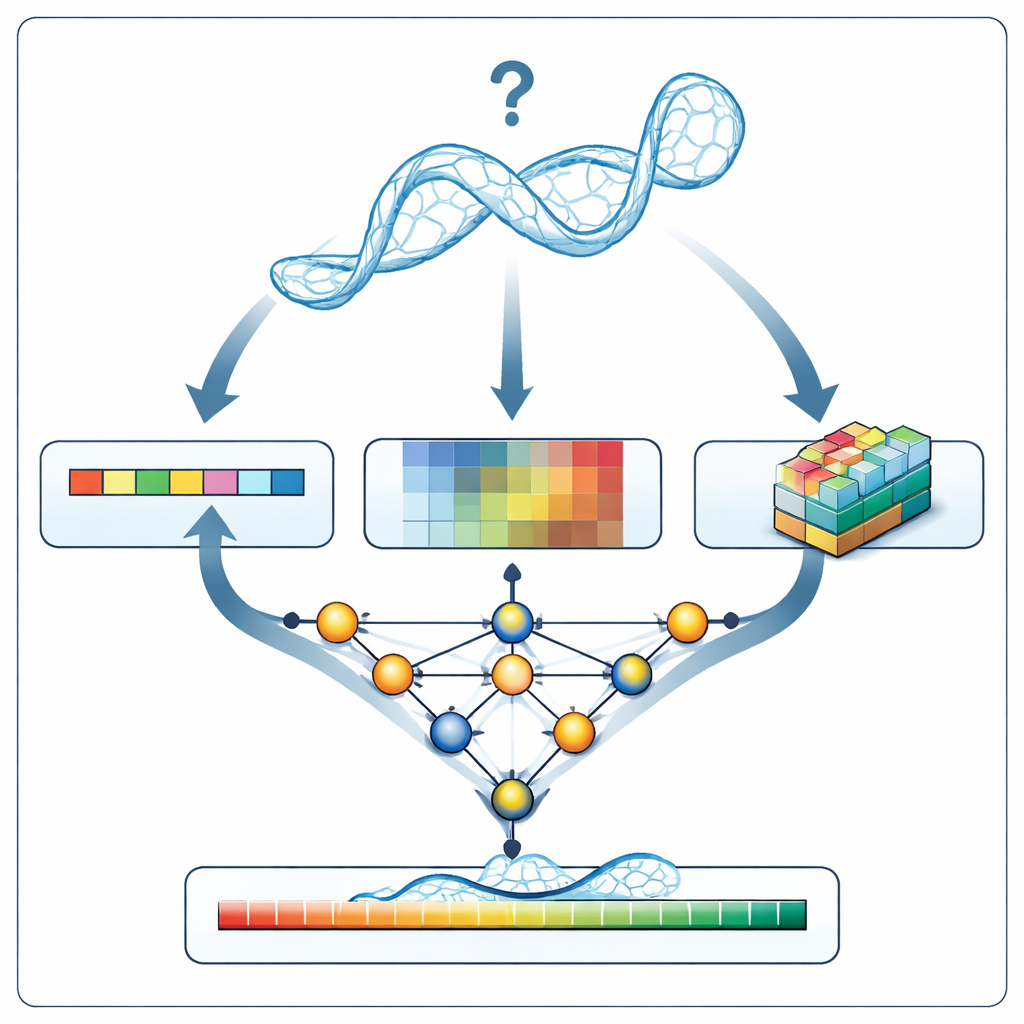
Когда RNArank анализирует новую модель РНК, он сначала переводит структуру в три вида информации: 1D-описание последовательности и геометрии каркаса вдоль цепи, 2D-описания взаимосвязей между парами нуклеотидов (их расстояния, оценённые энергии взаимодействия и возможные атомные столкновения) и 3D «воксельные» снимки — небольшие сетки, фиксирующие локальное облако атомов вокруг каждого нуклеотида. Многокомпонентная нейронная сеть объединяет эти подсказки в единую картину и затем предсказывает две промежуточные 2D-карты: какие нуклеотиды, вероятно, находятся в контакте, и насколько каждое смоделированное расстояние, вероятно, отклоняется от неизвестной истинной структуры. На основе этих карт RNArank восстанавливает как построчную по нуклеотиду оценку уверенности, так и общий балл для всей модели РНК.
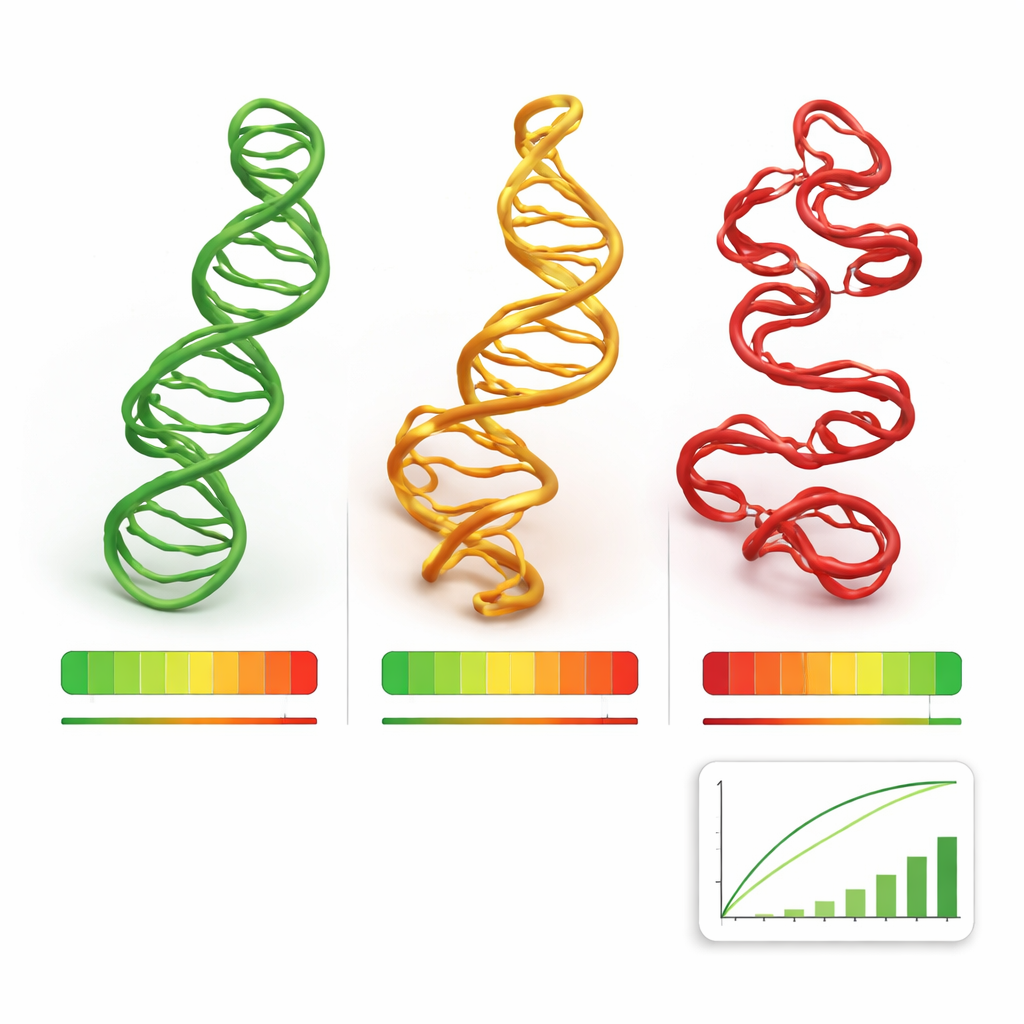
Проверка метода
Авторы протестировали RNArank на трёх требовательных наборах данных: на наборе из 24 недавно решённых РНК из Банка белковых структур (PDB) и на мишенях РНК из двух международных закрытых конкурсов предсказаний, CASP15 и CASP16, где многие команды представляют модели, не зная ответа заранее. Среди тысяч кандидатных структур оценки RNArank лучше коррелировали с истинным качеством моделей по сравнению с рядом устоявшихся энерго-ориентированных методов и другими подходами глубокого обучения. Особенно сильно он показал себя при отборе лучших или близких к лучшим моделей из пула и при выявлении частей структуры, которые, вероятно, ненадёжны. Авторы также показали, что RNArank сохраняет свои характеристики даже для РНК с последовательностями, заметно отличающимися от тех, что встречались в обучающей выборке — признак реальной обобщающей способности, а не запоминания.
Ограничения сегодня и перспективы завтра
RNArank не идеален: он по-прежнему испытывает трудности с особенно гибкими РНК, которые принимают множество конформаций, а также с РНК, меняющими форму при связывании с белками в крупных молекулярных комплексах. Тем не менее он достаточно быстр, чтобы за секунды обработать множество моделей для РНК длиной в несколько сотен нуклеотидов, и уже помогает автоматическим серверам выбирать предсказания более высокого качества в общественных тестах. Предоставляя метод-независимый, основанный только на структуре судью моделей РНК, RNArank даёт биологам более точный фильтр для преобразования сырых вычислительных результатов в надёжные структурные гипотезы, что приближает область к рутинному и достоверному предсказанию форм РНК и, в свою очередь, к более глубокому пониманию того, как работают эти универсальные молекулы.
Цитирование: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Ключевые слова: 3D-структура РНК, глубокое обучение, оценка качества модели, структурная биоинформатика, RNArank