Clear Sky Science · ru
Сравнительная пластидная геномика Hippophae выявляет филогенетические связи и предлагает кандидатные ДНК-маркеры для таксономической идентификации
Почему этот выносливый кустарник важен
Облепиха — выносливый кустарник, который процветает там, где многие другие растения не выживают: на холодных, сухих и ветреных склонах Цинхай‑Тибетского плато и за его пределами. Её ярко‑оранжевые ягоды продвигаются по всему миру как «суперфрукты», а само растение широко используют для укрепления почв и восстановления деградированных территорий. Тем не менее даже специалисты порой не в состоянии отличить близкородственные виды и подсорта только по внешнему виду. В этом исследовании задаётся простой, но важный вопрос: можно ли, прочитав «внутреннее руководство» растения — его ДНК — разобраться, кто есть кто, и при этом дать селекционерам и природоохранителям мощный инструмент для управления этим ценным ресурсом?
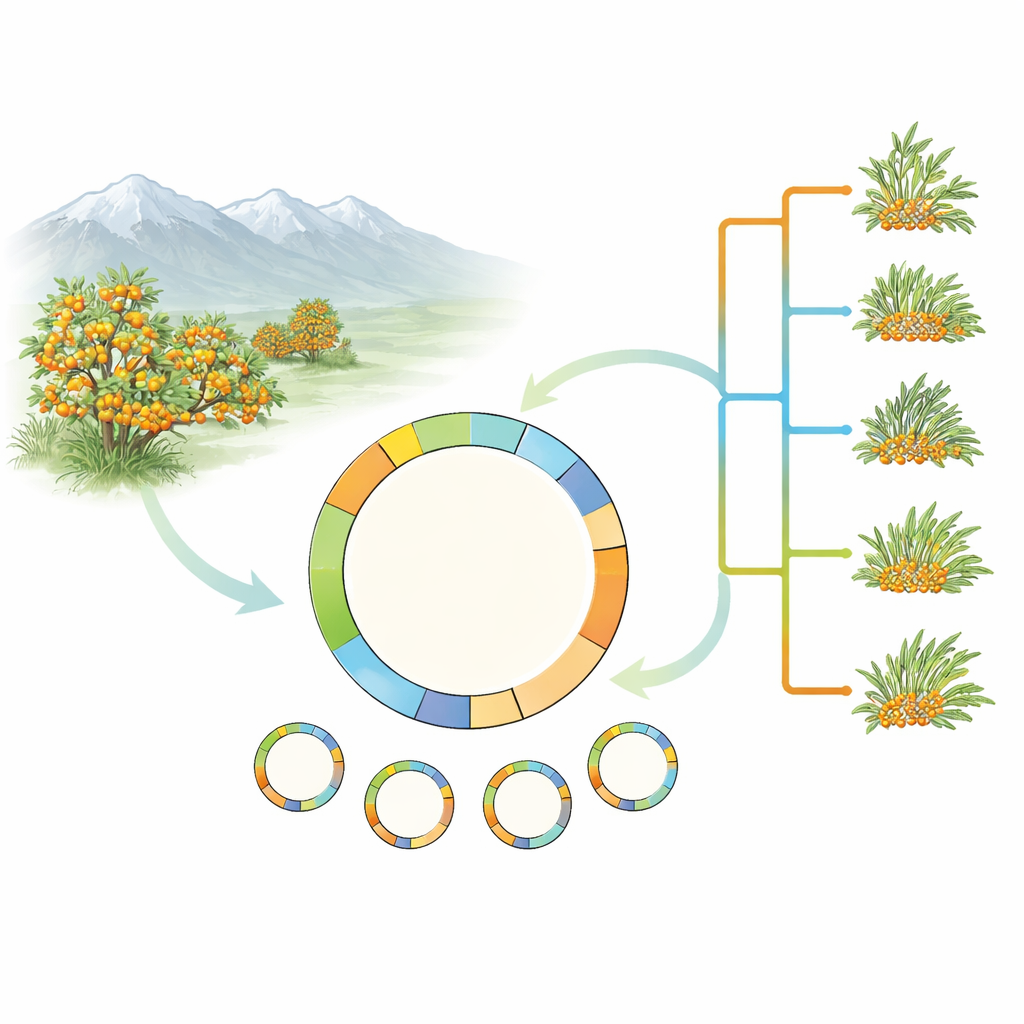
Заглядывая внутрь зелёных «двигателей» растения
Вместо того чтобы браться за всю сложность генома облепихи, исследователи сосредоточились на пластидах — крошечных зелёных структурах в клетках, которые осуществляют фотосинтез. Пластиды имеют собственную небольшую кольцевую ДНК, в основном наследуемую от материнского организма, и она оказалась чрезвычайно полезной для восстановления растительных родословных. Команда собрала и секвенировала полные пластидные геномы у 17 образцов, охватывающих пять видов облепихи и несколько форм широко распространённой Hippophae rhamnoides. Они также добавили недавно собранный пластидный геном важного культурного типа H. rhamnoides subsp. mongolica cv. Prevoskhodnaya и тщательно перепроверили ранее опубликованные записи баз данных на предмет ошибок.
Общий план с важными различиями
На первый взгляд пластидная ДНК всех образцов облепихи выглядела поразительно сходной. Каждый геном насчитывал примерно 155000–156000 «букв» и следовал той же четырёхчастной структуре, встречающейся у многих цветковых растений: два однокопийных региона, разделённые парой дублированных сегментов. Присутствовал одинаковый набор генов, расположенных в одном и том же порядке, и даже общая частота четырёх нуклеотидов едва менялась. Такая структурная стабильность указывает на то, что в ходе эволюции пластидный план у Hippophae сохранялся. В то же время при более детальном анализе — например, частоты использования определённых кодонов для кодирования той же аминокислоты — выявились тонкие, специфичные для линий закономерности, намекающие на медленное, долговременное изменение «кода» в разных ветвях рода.
Распутывая семейное древо
Используя 78 кодирующих белки генов пластидной ДНК, команда построила эволюционные деревья, которые помещают облепиху в более широкую семью розоцветных, а затем уточняют отношения внутри Hippophae. Анализы подтвердили, что облепиха как группа представляет собой единую естественную линию, и что H. rhamnoides вместе с её подсортами также образуют плотную группу. Любопытно, что один вид, H. tibetana, постоянно оказывается внутри клады H. rhamnoides в пластидном дереве, хотя предыдущие исследования по ядерной ДНК помещали его ближе к основанию рода. Это несоответствие между ядерной и пластидной историями указывает на прошлые гибридизации или другие сложные эволюционные события и подчёркивает необходимость будущих работ, объединяющих полные ядерные и пластидные наборы данных.
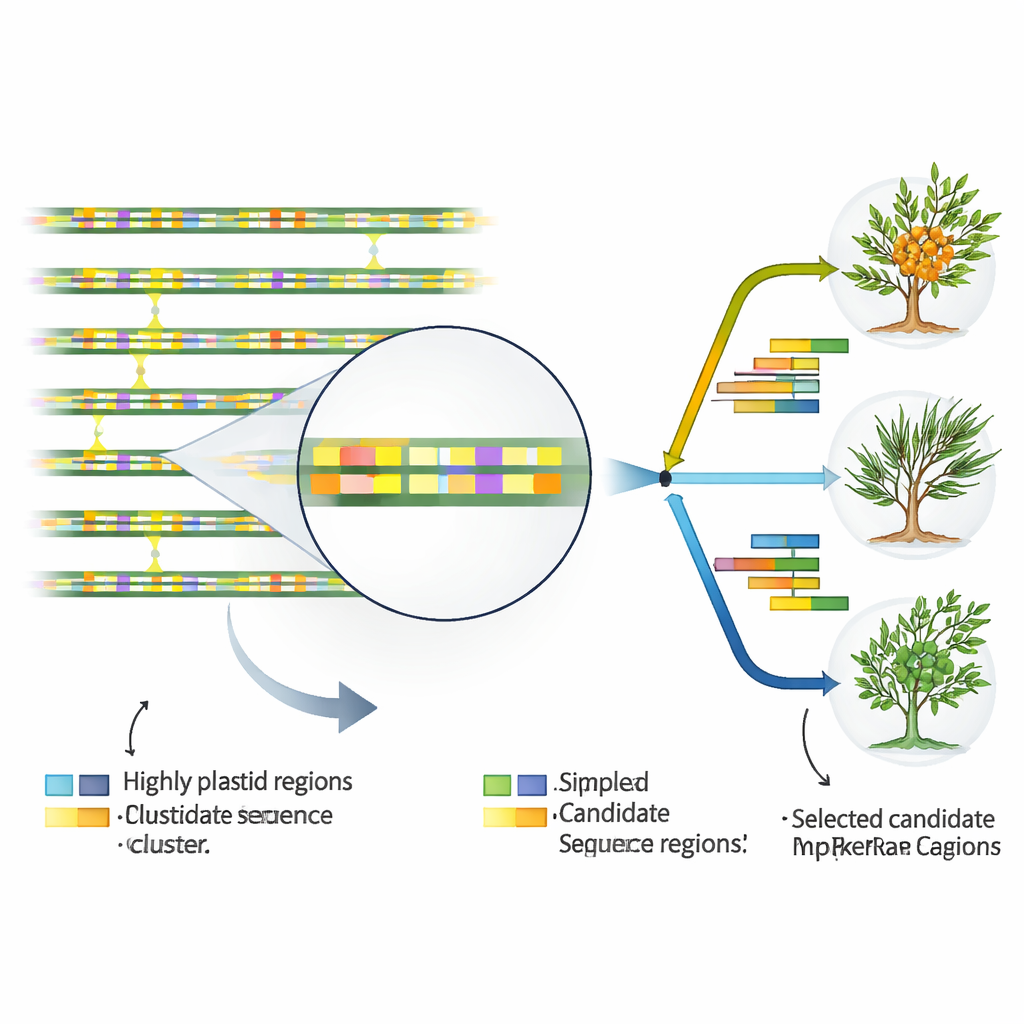
Поиск геномных «горячих точек», маркирующих идентичность
Чтобы превратить пластидную ДНК в практичные инструменты для таксономов и селекционеров, авторы искали участки последовательности, которые изменяются быстрее остального генома. Сравнив все 17 пластидных геномов, они выделили 46 особенно переменных регионов, почти все из которых находятся между генами или внутри некодирующих интронов, а не в самих телах генов. Они также выявили десятки мелких повторяющихся мотивов, известных как простые последовательные повторы (SSR), особенно богатые нуклеотидами A и T и сконцентрированные в некодирующих областях. Некоторые из этих повторов и переменных сегментов демонстрировали чёткие различия между видами и даже между подсортами H. rhamnoides. Несколько участков проявили себя как «горячие» и на уровне видов, и на уровне подсортов, что делает их перспективными кандидатами на практические ДНК‑маркеры, выявляемые простыми лабораторными тестами.
От ДНК‑паттернов к практическим применениям
Отобразив как стабильную структуру, так и мелкие, но информативные различия в пластидных геномах облепихи, это исследование предоставляет набор инструментов для надёжной ДНК‑идентификации. Предложенные маркерные регионы могут помочь отличать похожие виды, проверять происхождение коммерческих ягодных продуктов, защищать дикий генетический фонд и направлять выбор родителей в селекционных программах, ориентированных на питание, медицину и восстановление земель. Проще говоря, авторы показывают, что тщательно прочитанное хлоропластное «руководство» может раскрыть, кто есть кто в расширённой родне этого жёсткого кустарника, открывая путь к более продуманной охране природы и целевому использованию одного из наиболее выносливых плодовых растений мира.
Цитирование: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
Ключевые слова: облепиха, пластидный геном, ДНК-маркеры, растительная таксономия, генетическое разнообразие