Clear Sky Science · ru
rhinotypeR обеспечивает воспроизводимое присвоение генотипа риновируса по последовательностям VP4/2
Почему мелкие вирусы простуды всё ещё имеют значение
Большинство из нас воспринимает обычную простуду как неприятность, а не как серьёзную угрозу. Однако вирусы, вызывающие многие простуды — человеческие риновирусы — также связаны с тяжёлыми инфекциями лёгких, приступами астмы и обострениями хронических заболеваний лёгких. Чтобы отслеживать, как эти вирусы эволюционируют и распространяются, учёным необходимо разбивать их на точные генетические «типы», подобно присвоению штрих‑кодов товарам. В этой статье представлено rhinotypeR — бесплатный пакет с открытым исходным кодом, который делает такое генетическое маркирование более точным, согласованным и воспроизводимым, помогая службам общественного здравоохранения лучше следить за часто недооценяемым семейством респираторных вирусов.
Скрытое разнообразие в обычной простуде
Человеческие риновирусы чрезвычайно распространены и обнаруживаются в до 60% проб у людей с острым респираторным заболеванием. Это далеко не единый вирус: они разделены на три основные группы — A, B и C — и по крайней мере 169 признанных генетических типов. Разные типы ведут себя по‑разному: некоторые чаще связаны с тяжёлыми инфекциями у детей и с обострениями астмы, тогда как другие реже обнаруживаются при серьёзных заболеваниях. Поскольку эти типы эволюционируют независимо и имеют отличительные поверхностные особенности, учёным нужны надёжные методы их различения, чтобы проследить, как вспышки распространяются в школах, домохозяйствах и сообществах.
От разрозненных инструментов — к единому пути
До сих пор присвоение типа риновируса по его генетическому коду было трудоёмким и разрозненным процессом. Исследователи обычно ориентировались на короткий участок генома вируса, называемый регионом VP4/2, выравнивали его с известными референтными штаммами, измеряли степень различий между последовательностями и затем применяли пороговые значения, чтобы решить, к какому типу относится образец. Но эти шаги выполнялись с использованием набора различных программ, ручных правок и субъективных решений. Из‑за этого разные исследования было сложно сравнивать или воспроизводить, даже при схожих данных. rhinotypeR создан специально для того, чтобы превратить этот многошаговый, склонный к ошибкам процесс в единый скриптованный рабочий процесс, который может запускать и обмениваться им любой пользователь.
Что делает новое программное обеспечение
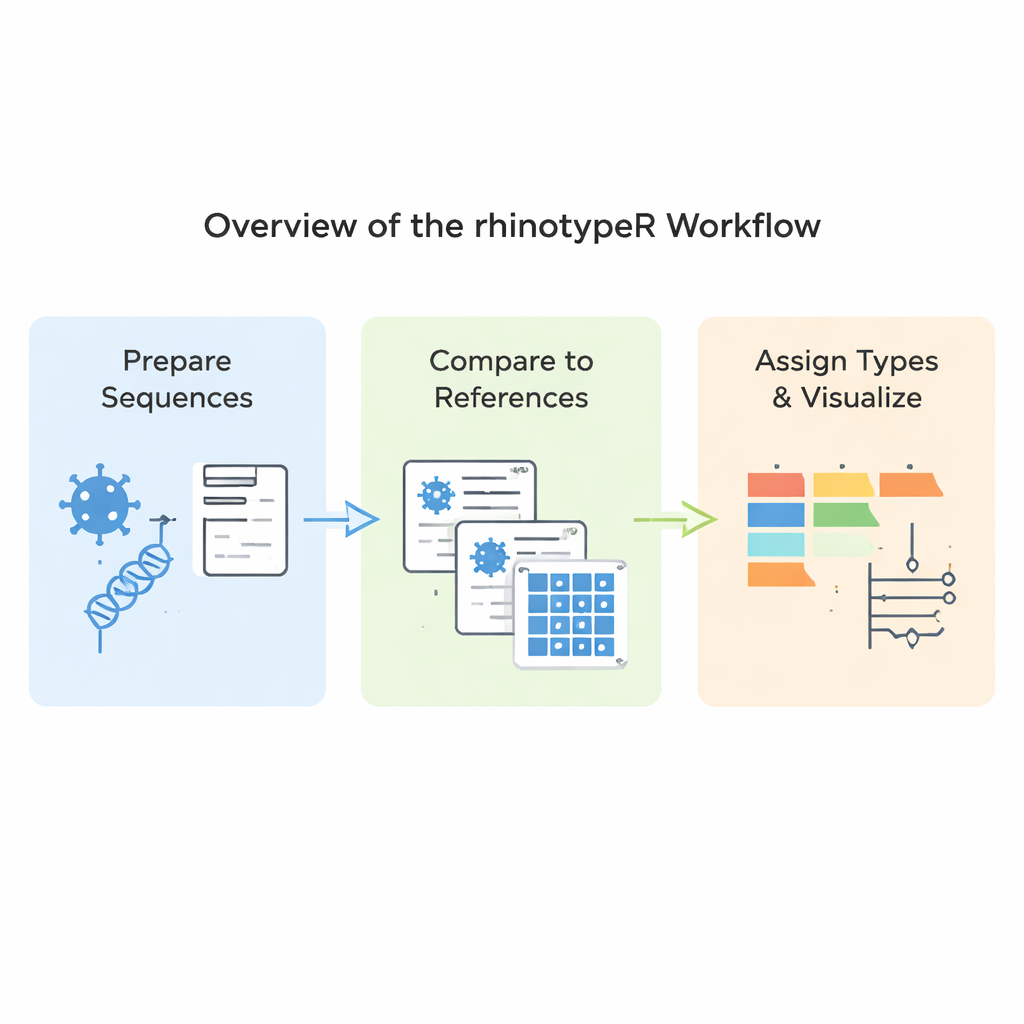
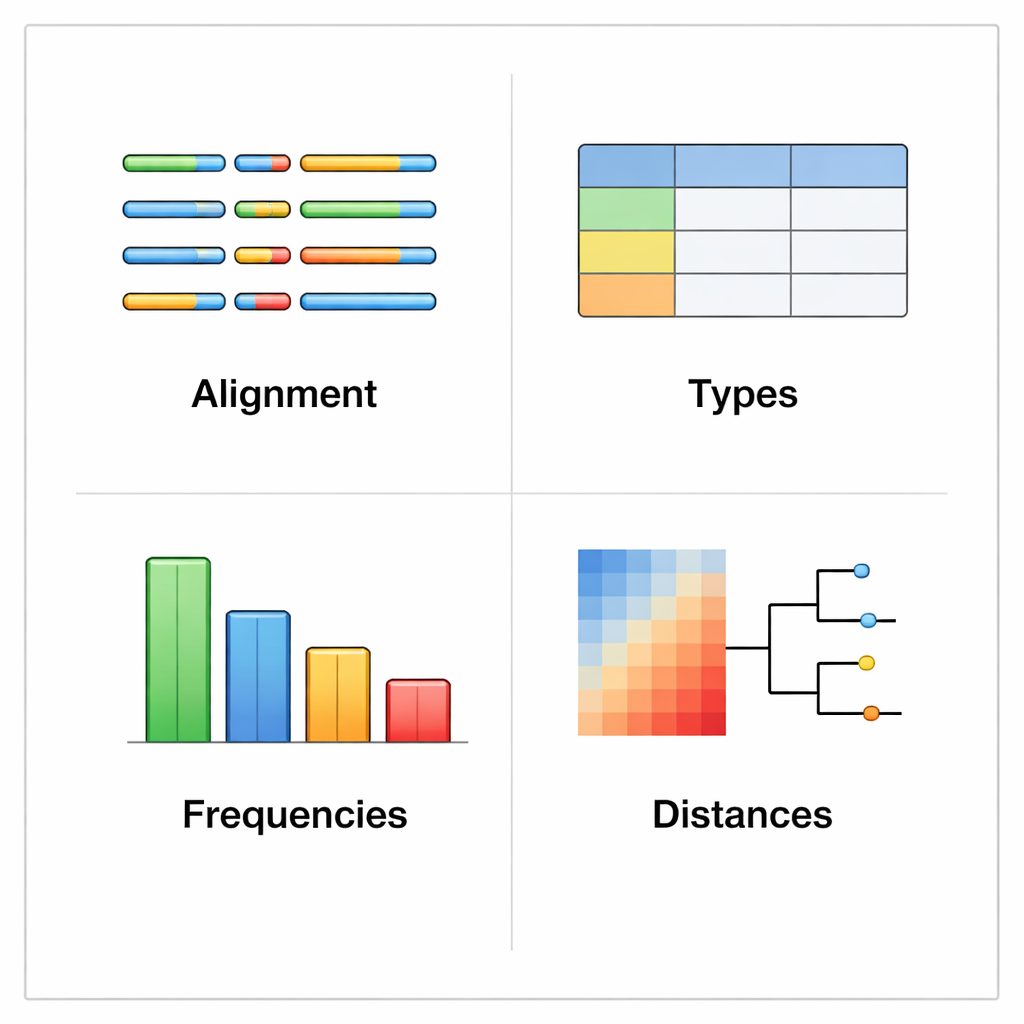
rhinotypeR работает в широко используемой среде R и Bioconductor для анализа данных. Он принимает набор последовательностей VP4/2 риновирусов и проводит их через три основных этапа: подготовка и выравнивание последовательностей, расчёт расстояний каждой последовательности до курируемого набора референтных типов и затем присвоение образца ближайшему известному типу или пометка как «неприсвоено», если он слишком отличается. Тот же инструмент может выдавать наглядные результаты, включая цветовые карты генетических различий, простые филогенетические деревья и графики, показывающие распространённость каждого типа в наборе данных. Пользователи могут выравнивать данные с помощью внешних программ при желании или позволить rhinotypeR выполнить весь процесс в R для максимальной воспроизводимости.
Проверка инструмента
Чтобы убедиться, что rhinotypeR даёт надёжные результаты, авторы сравнили его расчёты расстояний с результатами двух признанных программ, ape и MEGA X, используя одни и те же входные файлы и модели. Результаты практически полностью совпали; мелкие расхождения объяснялись обычным округлением в компьютерных вычислениях, а не реальными методологическими различиями. Команда затем запустила rhinotypeR на большой коллекции более чем 2 300 последовательностей риновирусов из нескольких предыдущих исследований, охватив более 90% известных типов. Примерно в четырёх из пяти случаев новый инструмент полностью согласовывался с ранее присвоенными метками типов. Большинство несоответствий возникали именно вблизи заранее согласованных пороговых значений, используемых для разделения типов, где ожидаемы спорные решения. Важно, что образцы, которым не удалось надёжно присвоить известный тип, не демонстрировали признаков просто низкого качества или малого количества вируса, что указывает на то, что они могут отражать действительное вирусное разнообразие.
Почему это важно для общественного здравоохранения
Для неспециалистов главная мысль в том, что rhinotypeR не переписывает принципы классификации риновирусов; он делает этот процесс более прозрачным, понятным и воспроизводимым. Объединив выравнивание, расчёт расстояний и присвоение типов в один открытый пакет — вместе с понятными визуальными сводками — он помогает исследователям и программам эпиднадзора обрабатывать тысячи образцов последовательно. Такая согласованность повышает нашу способность сравнивать исследования, выполненные в разных местах и в разное время, быстро обнаруживать необычные или вновь возникающие линии вирусов и связывать генетические паттерны с реальными эпидемиологическими трендами. В долгосрочной перспективе инструменты вроде rhinotypeR усиливают рутинный мониторинг кажущихся обычными простуд, которые у многих людей могут приводить к серьёзным заболеваниям.
Цитирование: Luka, M.M., Nanjala, R., Rashed, W.M. et al. rhinotypeR enables reproducible rhinovirus genotype assignment from VP4/2 sequences. Sci Rep 16, 6149 (2026). https://doi.org/10.1038/s41598-026-37050-8
Ключевые слова: генотипирование риновирусов, молекулярный надзор, секвенирование VP4/2, биоинформатические инструменты, респираторные вирусы