Clear Sky Science · ru
Ампликонное секвенирование с использованием Oxford Nanopore Technologies как диагностическая альтернатива для лентивирусов мелких жвачных у овец
Скрытые инфекции в повседневной жизни овец
Овцы по всему миру тихо переносят вирусы, которые могут ослаблять их здоровье, сокращать жизнь и наносить финансовый ущерб фермерам — часто без явных симптомов на протяжении многих лет. В этом исследовании рассматривается новый способ выявления таких скрытых инфекций с помощью портативной технологии секвенирования ДНК, что может стать качественным прорывом в защите благополучия животных, доходов ферм и даже продовольственной безопасности.
Медленное, дорогое заболевание, которое трудно распознать
Работа сосредоточена на лентивирусах мелких жвачных (SRLV) — группе вирусов, поражающих овец и коз. У овец они вызывают болезнь Маеди-Висна — длительную инфекцию, которая может приводить к дыхательным расстройствам, артриту, поражениям головного мозга и хроническому воспалению вымени. Многие инфицированные животные никогда не демонстрируют явных признаков, но вирус всё равно снижает удой, увеличивает смертность ягнят и вынуждает к преждевременной выбраковке. В некоторых европейских молочных стадах, включая Испанию и Грецию, примерно половина животных может быть инфицирована, что делает это одно из ключевых заболеваний в интенсивных овцеводческих хозяйствах.
Почему современные тесты пропускают многих инфицированных
Сегодня на фермах в основном полагаются на анализы крови, ищущие антитела (ELISA), или на стандартные ДНК-тесты (qPCR), чтобы определить, какие животные инфицированы и подлежат удалению из стада. Но SRLV быстро мутируют и рекомбинируют, создавая множество слегка различающихся вариантов вируса. Некоторые варианты плохо распознаются серологическими тестами, а у части инфицированных овец вообще не формируется сильный ответ антител. qPCR, которая нацелена на короткие и очень специфические участки вирусной ДНК, также может не сработать, если целевые регионы изменяются. В результате многие реально инфицированные животные дают отрицательный результат и остаются в стаде, тихо распространяя вирус.
Использование чтения ДНК в реальном времени для обнаружения вируса
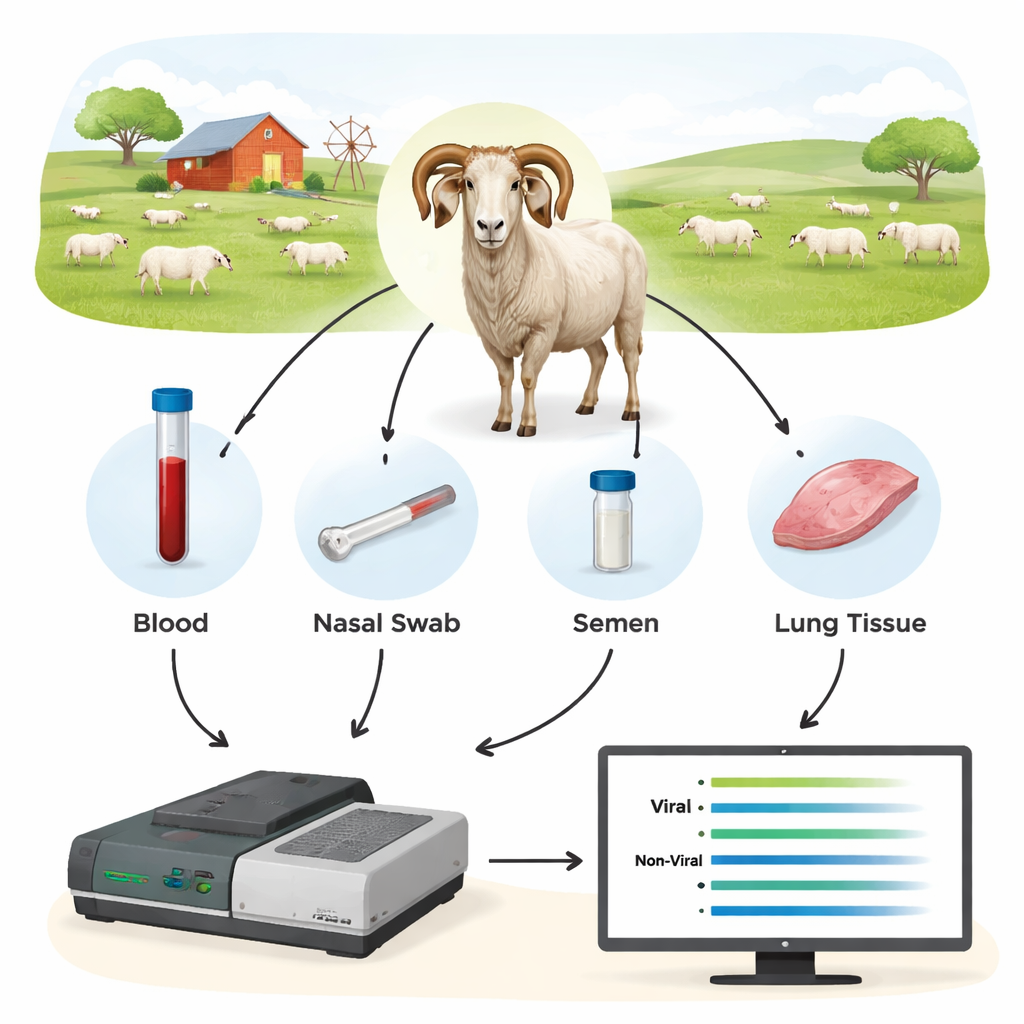
Исследователи протестировали метод третьего поколения — секвенирование Oxford Nanopore — в качестве нового диагностического инструмента. Вместо поиска одного малого фрагмента вирусной ДНК они сначала амплифицировали более длинные участки ключевых вирусных генов из образцов животных, а затем секвенировали эти фрагменты в реальном времени на устройстве Nanopore. Были собраны кровь, назальные мазки, сперма и клетки из крови и лёгких от 44 баранов и дополнительных овец, многие из которых уже проходили стандартные тесты. Сосредоточив внимание на вирусных регионах, которые относительно консервативны, но достаточно длинны, чтобы определить точный штамм, команда смогла и обнаруживать инфекцию, и идентифицировать присутствующие типы вируса.
Лучше всего подходит кровь — и она выявляет то, что пропускают другие тесты
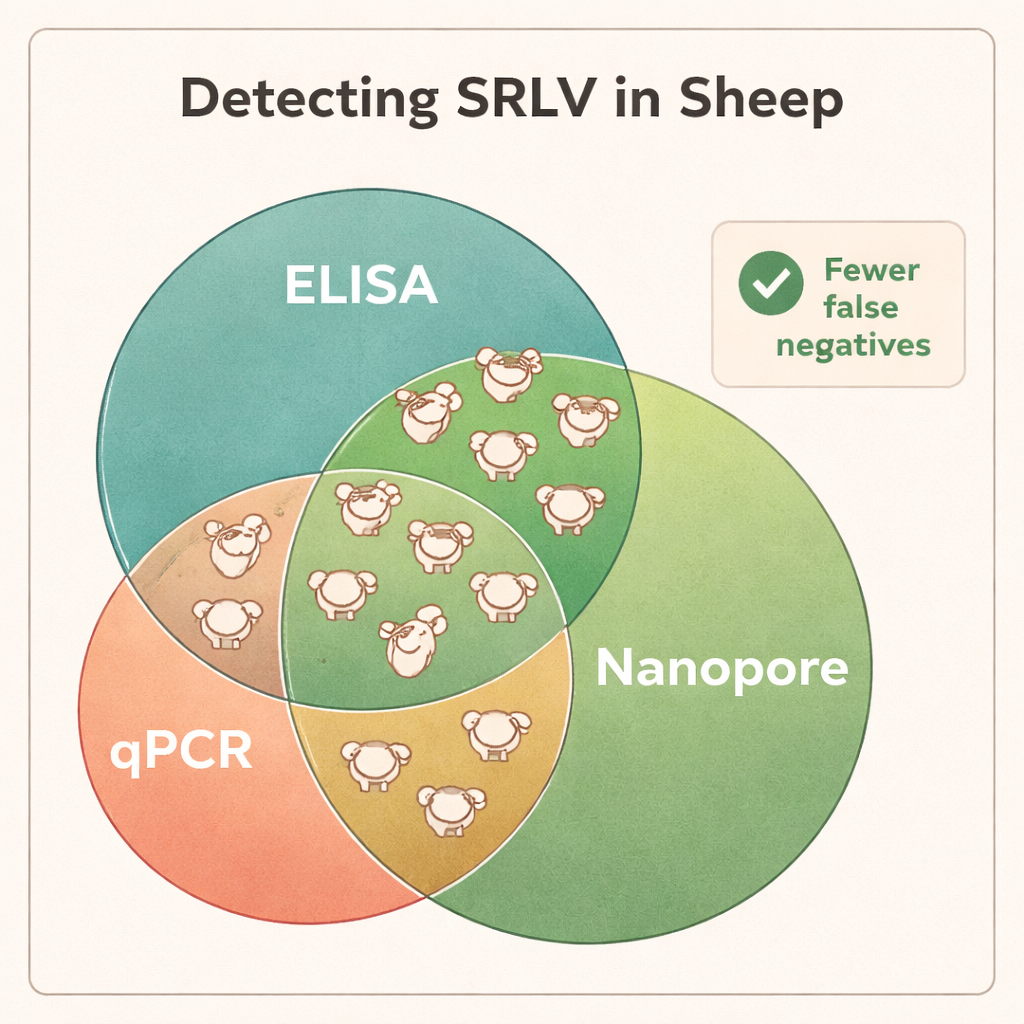
Секвенирование показало, что ДНК из цельной крови была наиболее надёжным материалом для обнаружения SRLV, хотя вирус преимущественно живёт в небольшой подгруппе лейкоцитов. Лёгочная ткань у сильно инфицированных животных давала очень большие количества вирусной ДНК, но такие образцы доступны лишь после забоя. Напротив, назальные мазки, сперма и очищенные лейкоциты содержали слишком мало вирусного материала для стабильной диагностики. При сравнении результатов Nanopore с типичными ELISA и qPCR различия оказались впечатляющими: Nanopore-секвенирование подтвердило инфекцию у всех баранов с положительным ELISA, но также показало, что многие животные с отрицательным ELISA на самом деле инфицированы. В разных стадах примерно 40–45% животных, помеченных ELISA как «отрицательные», оказались носителями вируса, а qPCR пропускал ещё большую долю. Данные секвенирования также выявили коинфекции разными типами SRLV у некоторых баранов — информацию, которую традиционные тесты тяжело получить.
От простого «да/нет» к глубоким выводам
Поскольку Nanopore читает реальные последовательности вируса, он может предоставить больше, чем простую диагностическую формулу «есть/нет». Команда использовала данные для сравнения штаммов, построения родословных вирусов, циркулирующих в стадах, и изучения тонких различий в вирусных белках, которые могут объяснить, почему некоторые животные ускользают от обнаружения стандартными наборами ELISA. Они показали, что определённые версии ключевого вирусного белка, на которые нацелены коммерческие серологические тесты, заметно отличаются между антителоположительными и антителоотрицательными животными. Со временем такая информация может помочь улучшить серологические тесты и программы разведения, направленные на отбор животных с природной устойчивостью к инфекции.
Что это значит для фермеров и здоровья животных
Для неспециалистов главное сообщение простое: читая более длинные участки вирусной ДНК напрямую, Nanopore-секвенирование может выявлять больше инфицированных овец, раньше и точнее, чем текущие рутинные тесты. Оно также показывает, какие именно штаммы вируса присутствуют в стаде. Хотя этот подход пока сложнее и дороже, чем один анализ крови, технология становится быстрее, дешевле и портативнее. Если интегрировать её в программы контроля, это может существенно сократить число «скрытых» носителей, улучшить разработку вакцин и тестов и поддержать селекцию более устойчивых животных — сделав овцеводство более устойчивым и гуманным.
Цитирование: Serrano, M., González, C., Roy, R. et al. Amplicon sequencing with Oxford nanopore technologies as a diagnostic alternative for small ruminant lentiviruses in sheep. Sci Rep 16, 6212 (2026). https://doi.org/10.1038/s41598-026-36989-y
Ключевые слова: здоровье овец, лентивирус, нанопоровое секвенирование, ветеринарная диагностика, Маеди-Висна