Clear Sky Science · ru
Интегрированный идентификатор бактерий при бактериальной инфекции крови на кристалле с использованием приближённого сопоставления k-мер
Почему важно более быстрое обнаружение микробов
Для пациентов, получающих жизненно важную трансплантацию стволовых клеток, инфекции в кровотоке могут превратить восстановление в неотложную ситуацию за считанные часы. Врачи знают, что каждая минута на счету, но современные лабораторные инструменты для выявления виновных бактерий могут работать медленно или требовать мощных вычислителей. В этом исследовании представлен крошечный энергоэффективный компьютерный чип — PC-CAM — который может быстро сканировать ДНК из образцов пациентов и в режиме реального времени отмечать опасные бактерии, потенциально прямо у постели больного.
Риск инфекции после лечения, сохраняющего кишечник
У некоторых реципиентов трансплантации развивается тяжёлое осложнение, при котором пересаженные иммунные клетки атакуют собственный кишечник пациента. Одним из перспективных методов лечения является трансплантация микробиоты кишечника, когда здоровые микробы донора вводят пациенту. Это может спасти кишечник, но иногда влечёт за собой дополнительную опасность: вредные кишечные бактерии могут проникнуть в кровоток и вызвать угрожающие жизни инфекции. Чтобы эффективно лечить такие инфекции, врачи должны быстро определить, какие виды бактерий присутствуют, тогда как традиционные тесты могут занимать часы или дни и пропускать незнакомые штаммы.
От медленной сборки геномов к быстрому анализу фрагментов ДНК
Современные секвенаторы ДНК могут считывать генетический материал прямо из образцов крови или кала почти в реальном времени. Узкое место теперь — не чтение ДНК, а её интерпретация. Классические методы сначала пытаются восстановить целые геномы из миллионов коротких фрагментов ДНК, а затем сопоставляют эти собранные геномы с референсной библиотекой — вычислительно затратный процесс. Авторы заменяют это более простой стратегией: они разбивают ДНК на короткие кусочки фиксированной длины, называемые k-мерами, и ищут эти кусочки непосредственно в базе известных бактериальных последовательностей. Вместо требовательного посимвольного совпадения их система допускает определённое число различий, что позволяет справляться с неизбежными ошибками секвенирования и естественными мутациями. 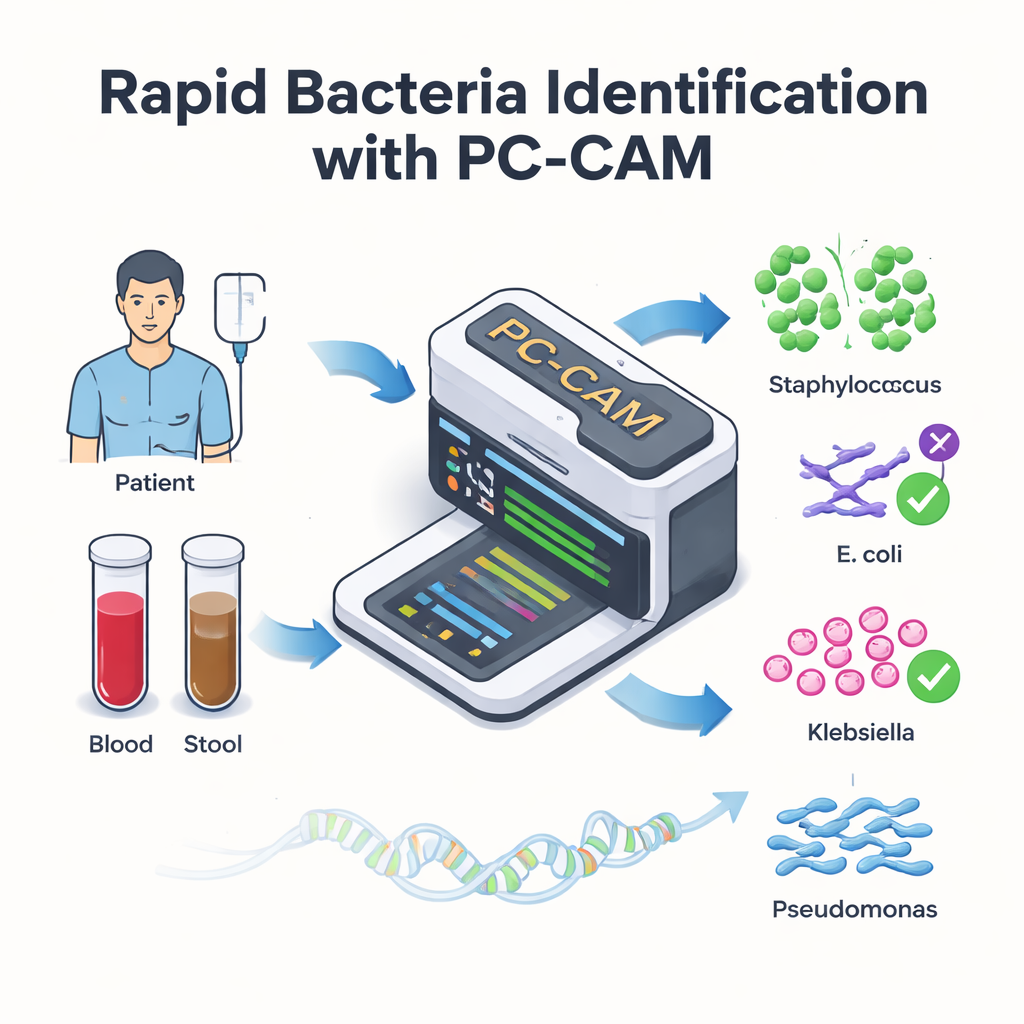
Умный чип-память, созданный для поиска ДНК
В основе PC-CAM лежит специализированный тип памяти, называемый ассоциативной (content-addressable) памятью, которая может одновременно сравнивать входные данные со всем, что в ней хранится. Исследователи спроектировали версию этой памяти для «приближённого поиска» (ACAM), которую можно настроить на принятие почти совпадающих записей вместо точных. Каждый короткий фрагмент ДНК кодируется и хранится в виде строки в этой памяти. Когда поступает новый фрагмент из образца пациента, чип активирует линию поиска по всем строкам одновременно и измеряет, как быстро разряжаются крошечные электрические сигналы. Путём регулировки двух управляющих напряжений система устанавливает порог того, сколько несовпадений она готова допустить, фактически задавая, насколько «снисходительным» должно быть совпадение. Такое сравнение на уровне аппаратуры позволяет чипу просеивать паттерны намного быстрее и с меньшим потреблением энергии, чем универсальный компьютер.
Насколько хорошо чип находит реальные бактерии
Команда протестировала PC-CAM на реальных наборах данных от пациентов, перенёсших трансплантацию микробиоты кишечника, сравнивая бактерии, обнаруженные в их крови и кале, с результатами полноформатного программного анализа геномов. Даже когда чип хранил лишь небольшой, тщательно подобранный подмножество фрагментов ДНК от каждого бактериального генома, он в основном совпадал с более вычислительно затратным методом, правильно идентифицируя ключевые патогены у нескольких пациентов. В расширенных экспериментах с моделируемыми чтениями ДНК из разных бактерий и при различных уровнях ошибок чувствительность чипа (его способность обнаруживать истинные совпадения) росла с увеличением допустимого числа различий, тогда как специфичность (способность избегать ложных срабатываний) снижалась при очень высокой терпимости к ошибкам. Авторы показывают, что простые шаги постобработки — например, требование нескольких согласующихся фрагментов или отбрасывание слабых совпадений — могут снизить число ложноположительных результатов. 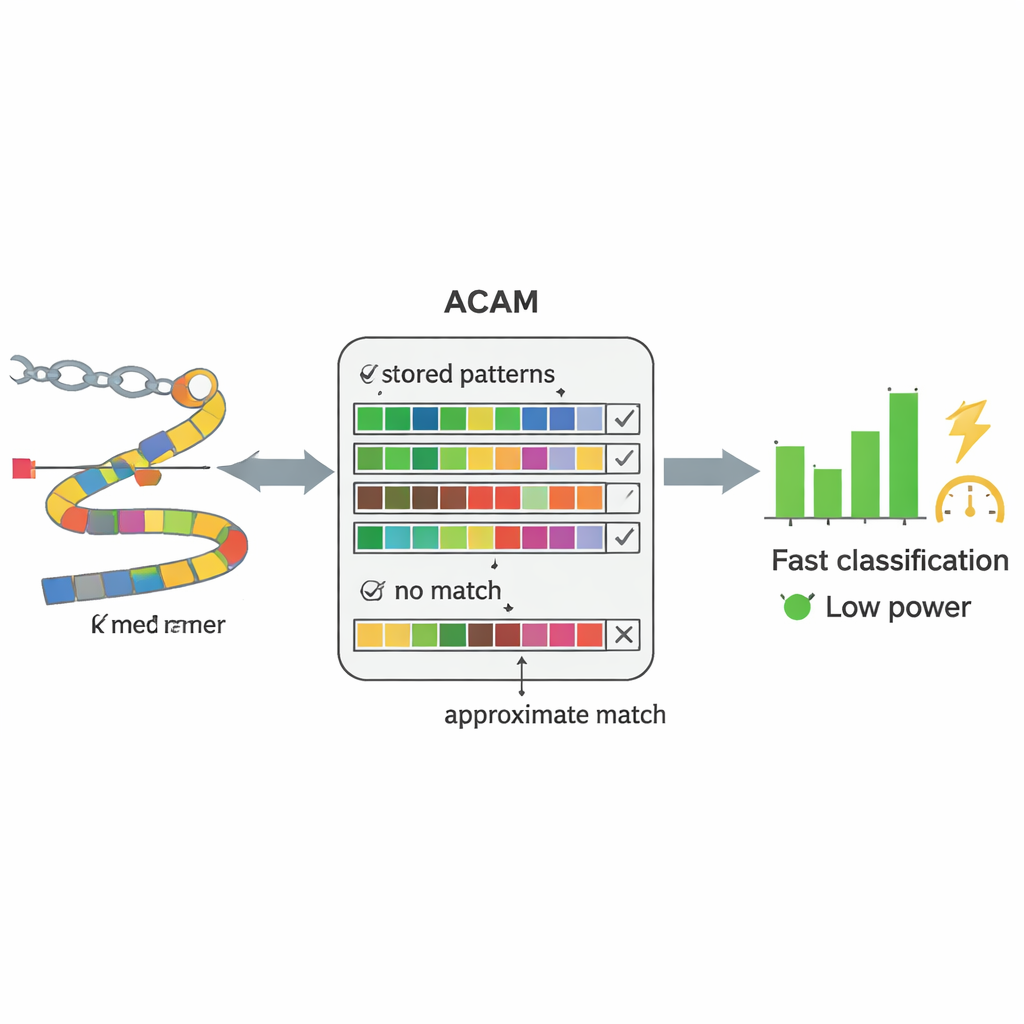
Крошечный аппарат с большой скоростью и низким энергопотреблением
PC-CAM интегрирует память ACAM с небольшим процессором RISC-V на кристалле площадью всего в несколько квадратных миллиметров, изготовленном по стандартной 65-нанометровой технологии. Измерения на реальном железе показывают, что он может классифицировать примерно 960 000 коротких чтений ДНК в секунду при потреблении около 1,27 милливатта — меньше, чем у многих цифровых наручных часов. В сравнении с ведущим программным инструментом, запущенным на мощном настольном процессоре, чип оказался примерно в 1 900 раз быстрее для такого рода задач классификации. Хотя его точность несколько снижается из-за хранения разбавленной версии каждого генома, авторы утверждают, что такая компенсация приемлема, когда приоритетом являются скорость и энергопотребление — например, в неотложной помощи или портативных устройствах.
Что это значит для пациентов и не только
Проще говоря, исследование показывает, что крошечный энергоэффективный чип может выступать в роли специализированной поисковой машины для бактериальной ДНК, мгновенно обнаруживая опасные микробы в образцах крови или кала. Хотя он не заменяет полноформатный генетический анализ в крупной лаборатории, он может дать быстрое, оперативное указание о том, какие бактерии присутствуют, помогая врачам быстрее и точнее выбирать антибиотики. Тот же подход можно расширить для мониторинга антибиотикорезистентности, проверки пищевых продуктов и воды на загрязнения или наблюдения за болезнями сельскохозяйственных культур — всё это с использованием компактного оборудования, которое переносит сложный анализ ДНК из дата-центра ближе к месту принятия решений.
Цитирование: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Ключевые слова: бактериальная инфекция крови, быстрое обнаружение патогенов, секвенирование ДНК, лаборатория-на-кремнии, микробиом