Clear Sky Science · ru
Сборка полноразмерного транскриптома и разработка маркеров SSR для Spinibarbus hollandi с использованием секвенирования PacBio SMRT
Почему скромная речная рыба имеет значение
В реках южного Китая обитает Spinibarbus hollandi — карпообразная рыба, ценимая как пищевой и декоративный объект. Рыбоводы хотели бы разводить её более эффективно, но рыба растёт медленно, поздно приходит в половую зрелость и откладывает относительно мало икры. Описанное здесь исследование использует современные методы секвенирования ДНК и РНК для создания подробного генетического «каталога» этого вида. Эта генетическая информация в конечном счёте поможет селекционерам отбирать более выносливых и быстрее растущих особей и поддержать охрану диких популяций.
Преобразование множества тканей в генетическую карту
Чтобы захватить как можно больше генетической информации, исследователи собрали шесть разных тканей — сердце, жабры, мозг, плавник, печень и половые железы — у шести взрослых самцов и самок. Из этих тканей они выделили РНК, молекулу, которая переносит копии активных генов внутри клеток. С помощью технологии PacBio SMRT, позволяющей читать очень длинные фрагменты копий РНК, они собрали первый полноразмерный транскриптом S. hollandi. Проще говоря, был создан высокоразрешающий перечень из 15 197 различных генов и 23 403 транскриптовых последовательностей, большинство из которых значительно длиннее и полнее, чем данные, получаемые старыми короткочитающими методами.
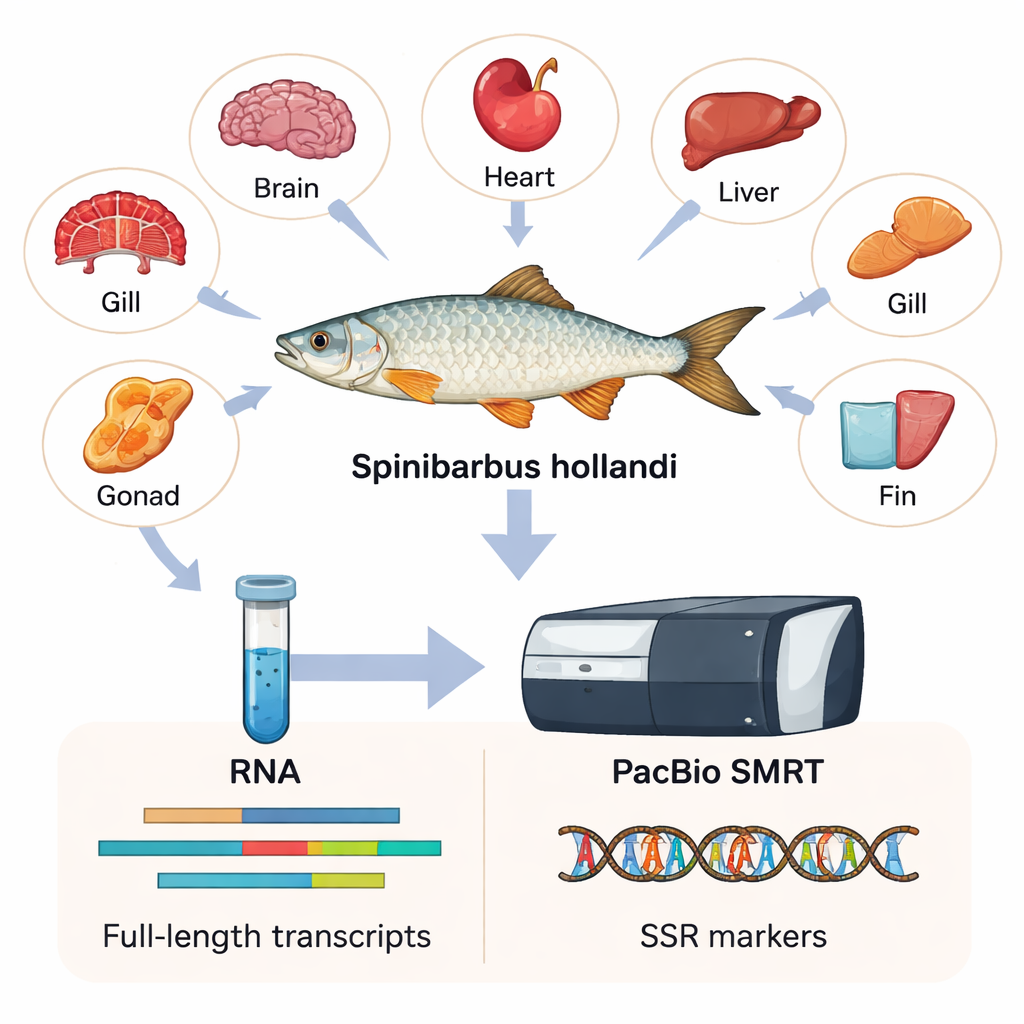
Что гены говорят о рыбе
Далее команда изучила функциональное назначение этих генов. Они сравнили каждую последовательность с крупными публичными базами данных, группирующими гены по функциям. Более 95% генов удалось сопоставить с известными записями — очень высокий показатель, указывающий на хорошее качество данных. Многие гены оказались в категориях, связанных с базовыми клеточными процессами, такими как метаболизм, передача сигналов и развитие, и в основном напоминали гены других карповых рыб. Это подтверждает биологическую состоятельность нового транскриптома и предоставляет основу для поиска генов, связанных с такими признаками, как скорость роста, устойчивость к стрессам и репродукция у S. hollandi.
Скрытые уровни контроля на уровне РНК
Помимо идентификации генов, учёные исследовали, как эти гены регулируются. Они обнаружили 373 случая альтернативного сплайсинга, когда один и тот же ген вырезается и склеивается по-разному, образуя разные РНК-сообщения. Наиболее распространённый вариант включает сохранение фрагментов РНК, которые часто удаляются у других видов, что указывает на особый способ тонкой настройки белков у этой рыбы. Также было обнаружено 2 397 длинных некодирующих РНК — молекул РНК, не кодирующих белки, но влияющих на то, когда и где включаются другие гены. В совокупности эти результаты показывают, что у S. hollandi имеется богатый набор регуляторных механизмов на уровне РНК, который может влиять на рост, половое созревание и адаптацию к локальным условиям.
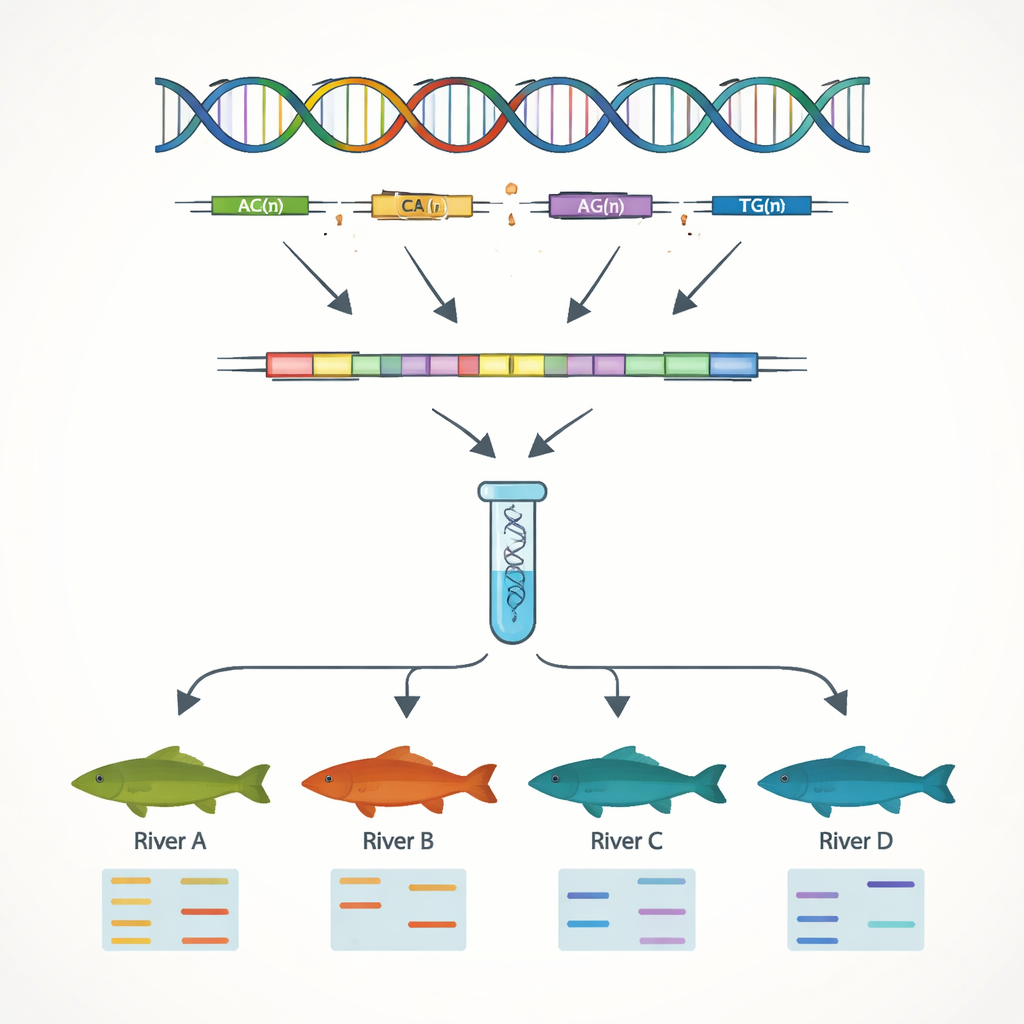
Создание ДНК-ориентиров для селекции и охраны
Одна из основных целей работы заключалась в разработке простых ДНК-маркеров, позволяющих отличать отдельных рыб и популяции. Сосредоточившись на генных последовательностях, авторы искали простые тандемные повторы — SSR (short sequence repeats) — короткие мотивы ДНК вроде «AC» или «AAT», повторяющиеся многократно подряд. Такие участки обычно варьируют между особями, что делает их полезными в качестве генетических «штрихкодов». Было выявлено 7 449 таких SSR-участков и разработано десятки коротких праймеров для их амплификации в лаборатории. Тринадцать из этих маркеров оказались высоковариабельными и надёжными при тестировании на 51 рыбе из четырёх речных бассейнов. Используя лишь эти 13 маркеров, команда чётко выявила генетические различия между популяциями из Янцзы и реки Жемчужной (Перл), что отражает горные хребты, ограничивающие естественное смешение бассейнов.
Что это означает для рыбоводов и рек
Для неспециалистов главный вывод заключается в том, что авторы создали подробный, высокого качества генетический референс для S. hollandi и набор практичных ДНК-маркеров. Этот набор инструментов поможет исследователям выявлять гены, ответственные за медленный рост или низкую плодовитость, поможет селекционерам выбирать родительские особи с желаемыми признаками и позволит природоохранцам отслеживать генетическое разнообразие между речными системами. Хотя требуется дополнительная работа, чтобы связать конкретные гены с продуктивностью в прудах или в дикой природе, это исследование закладывает молекулярную основу для превращения традиционной речной рыбы в современный вид устойчивого аквакультурного производства.
Цитирование: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Ключевые слова: Spinibarbus hollandi, транскриптом рыб, секвенирование PacBio, микросателлитные маркеры, генетика аквакультуры