Clear Sky Science · ru
ONCOPLEX: онкологически вдохновлённая модель-гиперграф, интегрирующая разнородные биологические знания для предсказания драйверных генов рака
Почему это исследование важно
Рак вызывается небольшим числом мощных генетических изменений, скрытых среди тысяч безобидных вариантов. Нахождение этих действительно опасных «драйверных» генов необходимо для лучшей диагностики и таргетной терапии, но это похоже на поиск нескольких зачинщиков в огромной, шумной толпе. В этом исследовании представлен ONCOPLEX — новая система искусственного интеллекта, которая рассматривает гены не поодиночке, а в контексте биологических путей, в которых они взаимодействуют, предлагая более точный способ выявления генов, действительно подпитывающих опухоли.
Видеть гены рака в их биологических окрестностях
Большинство современных методов просматривают геномы опухолей в поисках мутаций, которые встречаются необычно часто, или выделяют гены в простых сетях взаимодействий. Эти подходы полезны, но биология редко так проста. Гены обычно действуют группами внутри путей, контролирующих рост клеток, восстановление ДНК и многие другие процессы. ONCOPLEX принимает эту сложность, представляя гены в виде узлов и пути как большие перекрывающиеся группы, которые могут включать множество генов одновременно. Такая структура, известная как гиперграф, позволяет модели напрямую учитывать взаимоотношения между несколькими генами, не разлагая их на множество отдельных пар.
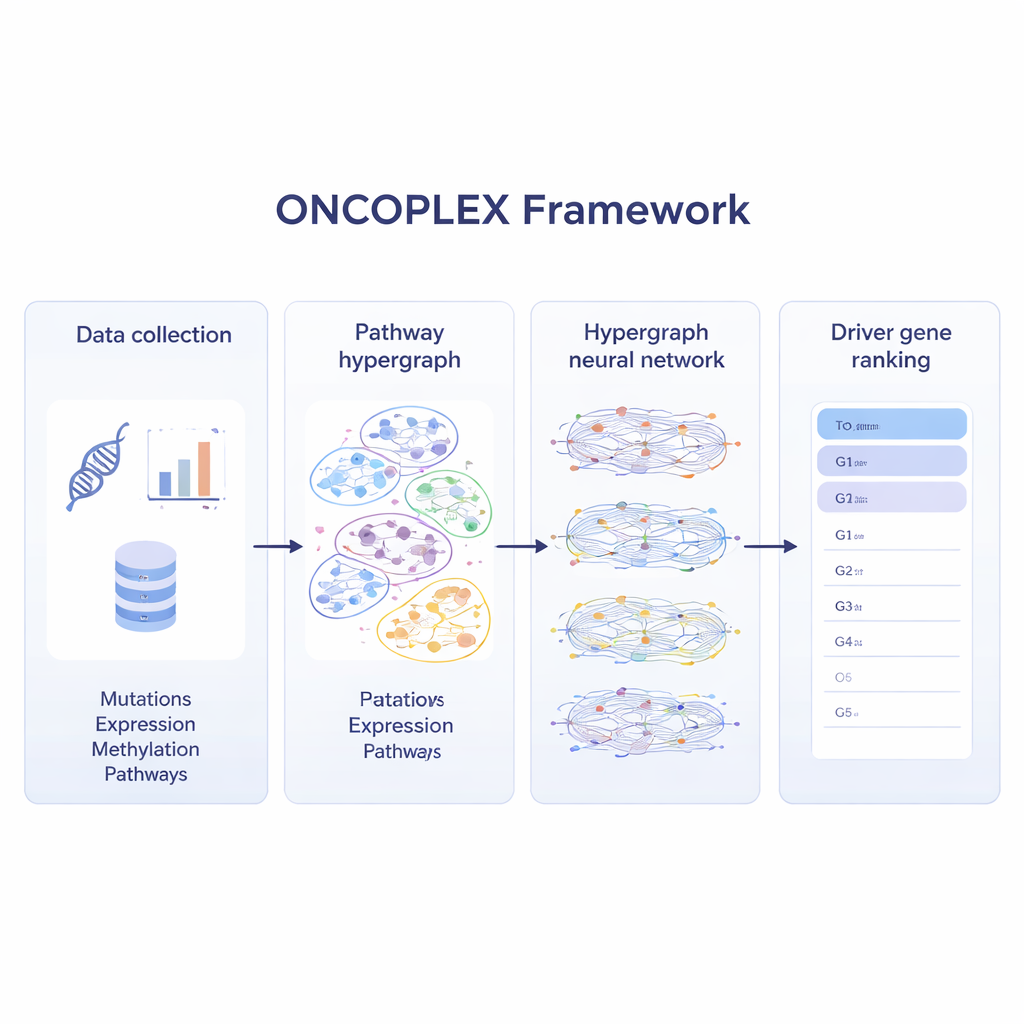
Смешение многих уровней данных о раке
Чтобы максимально использовать современные онкологические наборы данных, ONCOPLEX объединяет несколько типов информации о каждом гене. Он использует частоты мутаций, изменения активности гена, химические метки на ДНК (метилирование) и богатый набор биологических признаков, таких как эволюционная консервация и функциональные аннотации. Эти признаки прикрепляются к каждому гену в гиперграфе. Специализированная нейронная сеть затем передаёт информацию через пути, позволяя представлению каждого гена формироваться как под влиянием собственных данных, так и поведения генов, с которыми он работает. Модель обучается на уже известных драйверных генах, одновременно извлекая знания из множества немаркированных генов, которые могут быть важны, но ещё не признаны.
Превосходство существующих инструментов во многих типах рака
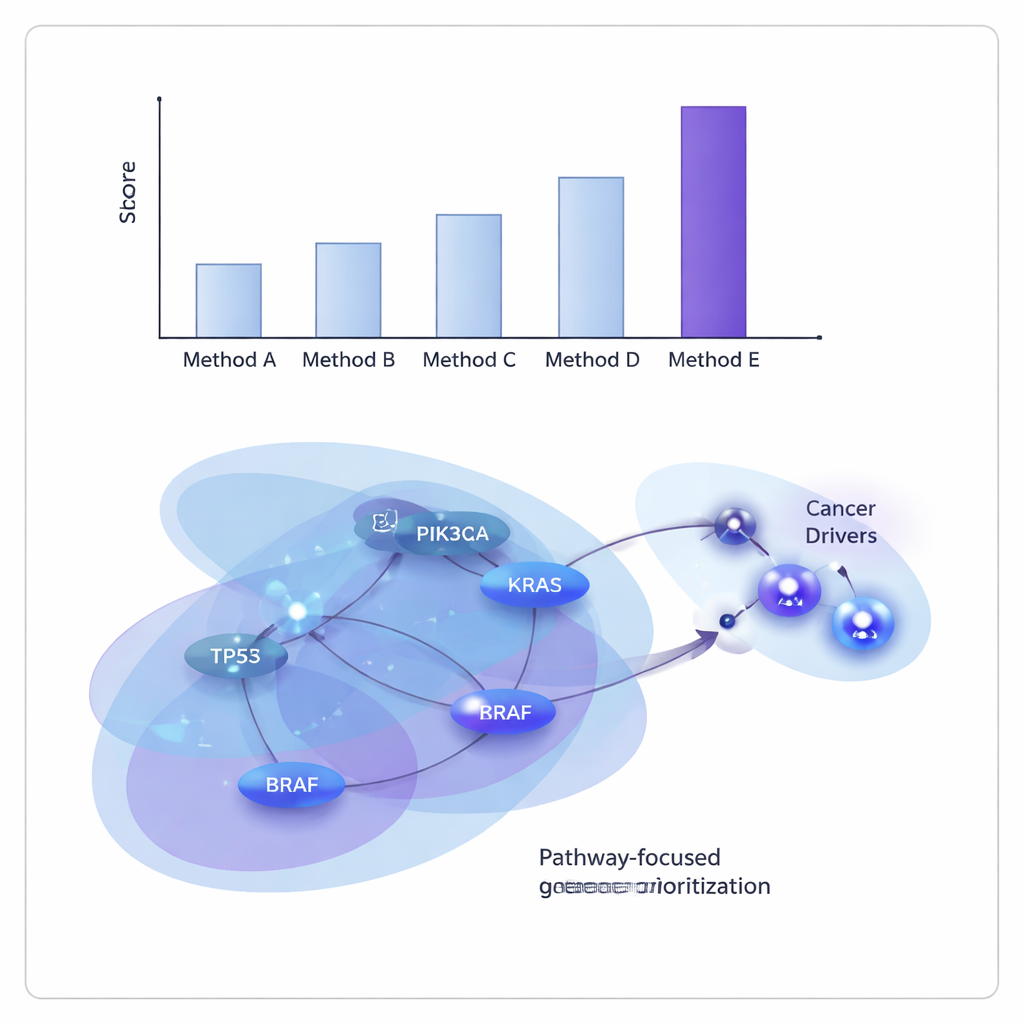
Исследователи протестировали ONCOPLEX на данных из The Cancer Genome Atlas, как объединяя множество типов опухолей, так и рассматривая 11 отдельных видов рака, включая рак молочной железы, лёгкого, печени, мочевого пузыря и головы и шеи. Они сравнили его с несколькими ведущими методами, основанными на графах и гиперграфах. Во всех случаях ONCOPLEX лучше различал известные драйверные гены и значительно более многочисленные негровые гены и ставил вероятные драйверы ближе к вершине своих списков. Его преимущество особенно заметно при анализе генов с наивысшими рангами — именно там точная идентификация наиболее ценна для последующих экспериментов и клинической трансляции.
Выявление общих и специфичных для рака виновников
Помимо сырых показателей, ранжированные списки генов ONCOPLEX восстановили многие знакомые онкогенные гены, такие как KRAS, BRAF и компоненты сигнального пути PI3K–AKT, что подтверждает, что модель захватывает устоявшуюся биологию. Она также выделила многообещающих кандидатов, которые ещё не прочно признаны драйверами в некоторых типах рака, включая гены вроде GRB2 и MAPK3 при раке молочной железы и SHC1 при раке желудка. При анализе топ‑ранжированных генов методами обогащения по путям были обнаружены сильные подписи известных онкологических путей, включая сигнальные каскады ErbB и PI3K–AKT–mTOR, а также иммуно‑связанные пути, что указывает на то, что ONCOPLEX фокусируется на клинически значимых сетях.
Сильные стороны, ограничения и дальнейшие шаги
Показывая, что более богатые биологические признаки стабильно улучшают прогнозы, ONCOPLEX демонстрирует ценность слияния множества источников данных в рамках, ориентированном на пути. В то же время исследование выявляет ограничение: поскольку многие раки разделяют большое число путей, модель иногда отдаёт предпочтение широко действующим «пан‑раковым» генам в ущерб генам, действительно специфичным для отдельного типа опухоли. Авторы предлагают, что в дальнейшем следует уточнить способы использования информации о путях, чтобы общие и специфические для рака сигналы можно было чётче разделять.
Что это значит для пациентов и клиницистов
Для неспециалистов главный вывод в том, что ONCOPLEX предлагает более биологически реалистичный способ поиска генов, которые запускают рак. Рассматривая гены в компании их соучастников — внутри путей, а не по отдельности — модель улучшает нашу способность замечать как хорошо известные, так и ранее упущенные драйверы, даже в типах рака, о которых сейчас известно мало. Такой инструмент может помочь исследователям расставить приоритеты для лабораторных исследований, направлять поиски новых лекарственных мишеней и в конечном итоге поддерживать более точные, ориентированные на пути стратегии лечения в онкологии.
Цитирование: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Ключевые слова: драйверные гены рака, нейронные сети на гиперграфах, интеграция мультиомных данных, анализ путей, персонализированная онкология