Clear Sky Science · ru
Разделение прямых и плейотропных эффектов SNP у люцерны (Medicago sativa L.) с помощью обучения причинных графов
Почему это важно для ферм и продовольствия
Люцерна — рабочая лошадка современной сельскохозяйственной практики: она кормит молочных коров и способствует восстановлению плодородия почв. В то же время селекция улучшенных сортов — растений, которые лучше переносят зиму, устойчивы к повреждениям и дают качественный корм — замедляется из‑за высокой сложности их генетики. В этом исследовании предложен новый подход, позволяющий превратить длинные запутанные списки маркеров ДНК в понятные карты причинно‑следственных связей, показывающие, какие участки генома действительно управляют важными признаками стебля, а какие лишь сопутствуют им.
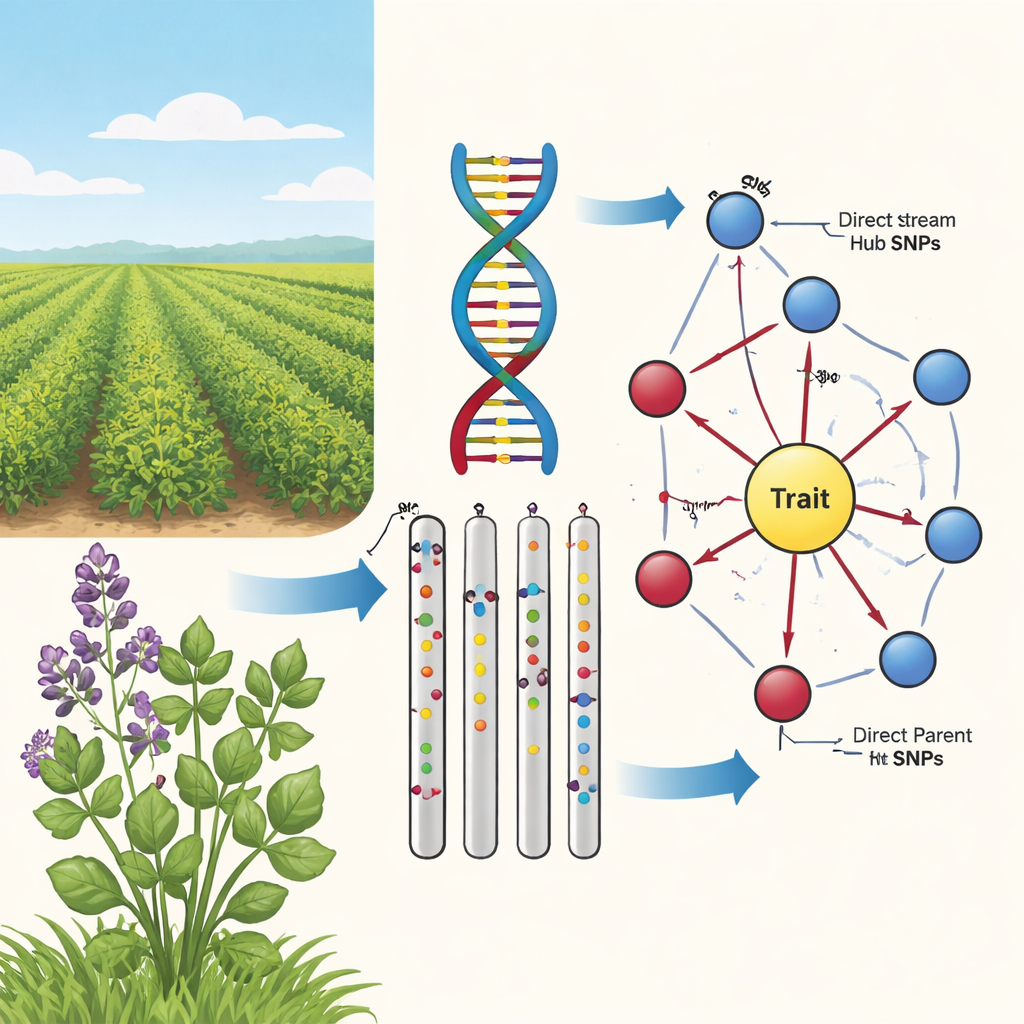
От слабых связей к причинно‑следственным отношениям
Традиционные исследования ассоциаций по всему геному ищут варианты ДНК, SNP, которые часто встречаются вместе с признаком, например цветом стебля или зимостойкостью. У люцерны ситуация особенно сложна: она тетраплоидна, большие участки ДНК наследуются совместно, а популяции генетически сильно перемешаны. Это создаёт «туман корреляций», где многие маркеры кажутся важными, но лишь немногие реально влияют на признак. Авторы утверждают, что селекционерам нужно не просто статистические связи; важно знать, какие маркеры лежат на реальных причинных путях от генотипа к наблюдаемым признакам растений.
Как работает новая схема
Исследователи разработали двухэтапную схему, объединяющую современные методы машинного обучения и идеи из теории причинных графов. Сначала они применили метод Double Machine Learning, чтобы отсеять около 2400 SNP в 500 генотипах люцерны. Этот этап устраняет влияние скрытых факторов, таких как родственные связи и география, используя главные компоненты генома в качестве прокси. В результате получается более чистая картина маркеров, которые сохраняют прямой эффект на признаки (например, цвет стебля) после учёта этих помех. В отфильтрованном сигнале заметные, стабильные пики сосредоточились в основном на хромосомах 2 и 4, а ключевые маркеры показали оценки эффекта с доверительными интервалами, ясно исключающими ноль, что указывает на реальное причинное влияние.
Преобразование маркеров в генетические дорожные карты
На втором этапе команда использовала алгоритм обучения причинных графов, известный как алгоритм PC, чтобы соединить наиболее перспективные маркеры в ориентированную сеть. В этих диаграммах узлы представляют SNP и признак, а стрелки указывают наиболее вероятное направление влияния. Отсеивая рёбра, противоречащие базовой биологии (например, признак не может изменить последовательность ДНК), и оставляя только SNP, воздействующие на признак, авторы получили компактные, биологически правдоподобные карты. Эти «подсолнухоподобные» сети показывают слоистую структуру: внутреннее кольцо из Direct Parent SNP, напрямую связанных с признаком, и внешнее кольцо Upstream Hub SNP, которые влияют на несколько родителей, но напрямую на признак не действуют.
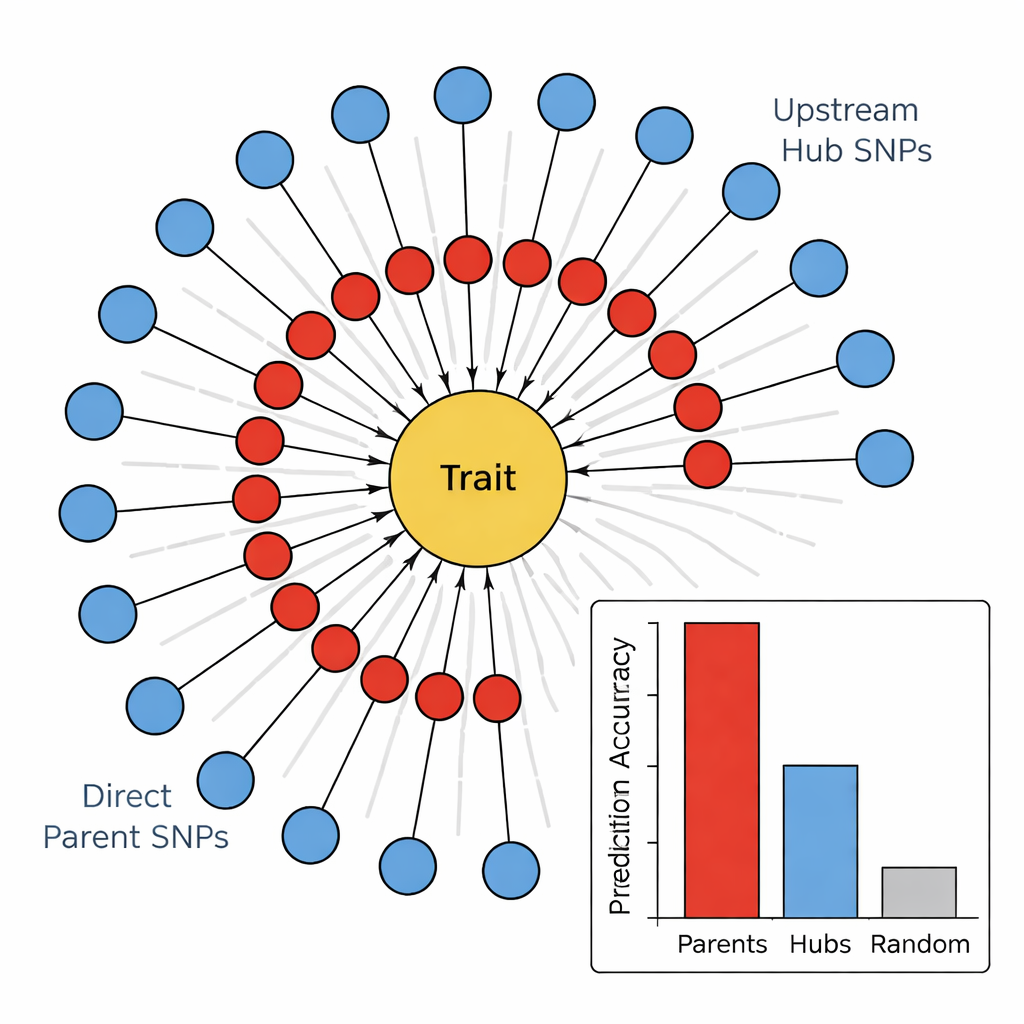
Исполнители против режиссёров в геноме
Чтобы проверить значимость этой иерархии, авторы сопоставили, насколько разные группы маркеров предсказывают четыре признака, связанные со стеблем: цвет стебля, заполнение стебля, прочность стебля и повреждения зимой. По всем признакам Direct Parent SNP последовательно оказывались лучшими предикторами, зачастую объясняя в несколько раз больше вариации, чем случайные маркеры или Upstream Hubs. Напротив, хабы демонстрировали слабую или даже отрицательную прогностическую силу, несмотря на высокую связность в сети. При соотнесении этих SNP с известными генами выявилась закономерность: Direct Parent чаще соответствовали ферментам или структурным белкам, действующим непосредственно на клеточные стенки, пигменты или процессы повреждения, тогда как Hubs чаще соответствовали факторам транскрипции и регуляторным белкам, которые широко модулируют множество путей одновременно.
Что это значит для будущей селекции люцерны
Для селекционеров и генетиков исследование предлагает способ отсеять шумные результаты ассоциаций и сфокусироваться на изменениях в ДНК, которые действительно влияют на конкретные признаки. Авторы показывают, что сочетание де‑факто очистки экранов с обучением причинных графов служит встроенной защитой от переобучения, превращая длинные списки кандидатов в небольшие, интерпретируемые сети, согласующиеся с известной биологией. На практике Direct Parent SNP становятся высокоточным маркером для отбора растений с лучшими характеристиками стебля или зимостойкостью, тогда как Upstream Hubs указывают на «главные переключатели», способные перестроить широкие стрессовые ответы, но с возможными компромиссами. Такая структурная модель генома создаёт основу для более надёжного геномного отбора в сложных культурах и для интеграции будущих слоёв данных, таких как экспрессия генов и метаболизм, в связные причинно‑следственные модели продуктивности растений.
Цитирование: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Ключевые слова: генетика люцерны, обучение причинных графов, геномный отбор, растительное селекционирование, полиплоидные культуры