Clear Sky Science · ru
Прогнозирование белков, ассоциированных с корнями, с использованием большой языковой модели для белков и гиперграфовых свёрточных сетей
Почему корни и их скрытые помощники важны
Когда мы думаем о поддержании здоровья посевов, обычно представляем листья и плоды. Но значительная часть успеха растения происходит вне поля зрения — в почве. Там специальные белки, ассоциированные с корнями, помогают растениям поглощать воду и питательные вещества и справляться со стрессами, такими как засуха или бедная почва. Отыскать эти ключевые белки только лабораторными методами — медленно и дорого. В этом исследовании представлена мощная компьютерная модель под названием Hypergraph-Root, которая может быстро просматривать последовательности белков и предсказывать, какие из них, вероятно, связаны с корнями, предлагая более быстрый путь к выносливым культурам и лучшим урожаям.
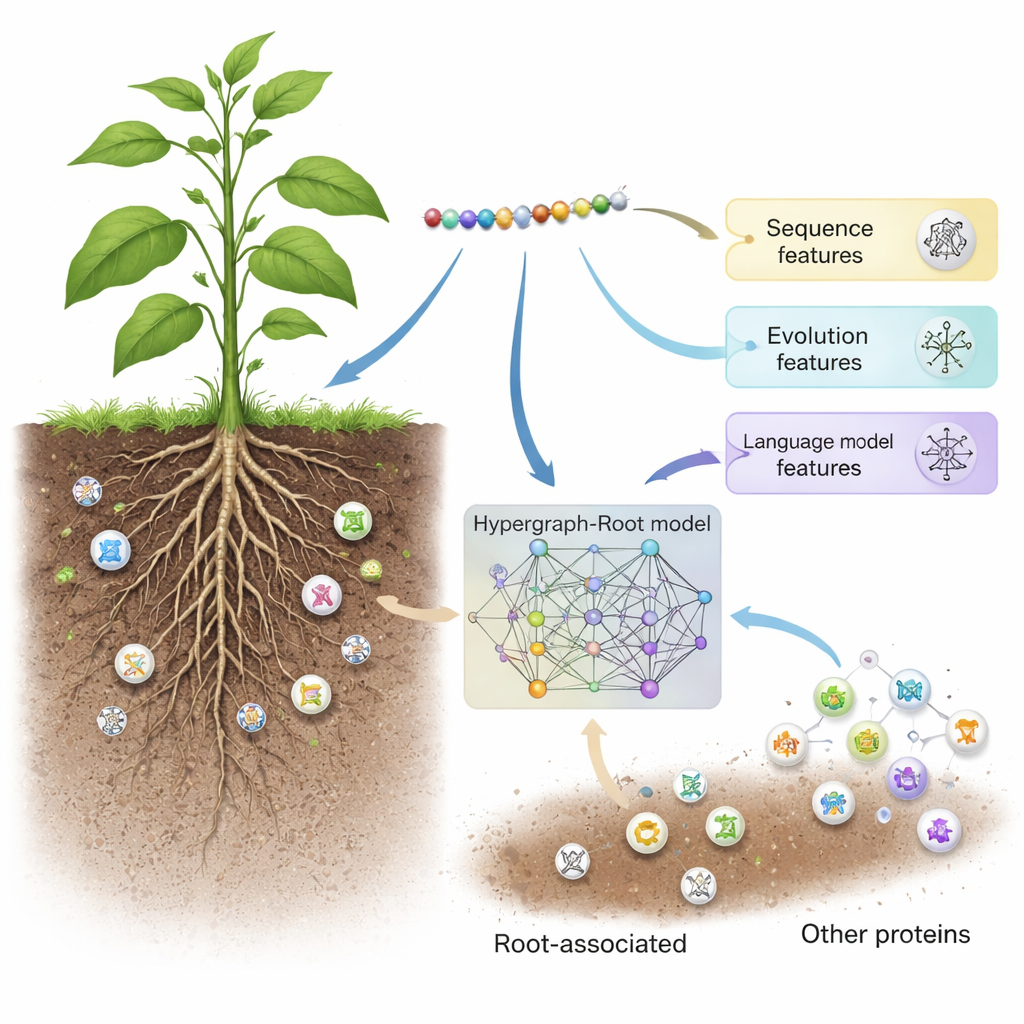
Скрытые труженики в почве
Корни растений выполняют не только функцию закрепления в почве. Они постоянно ощущают окружающую среду, поглощают минералы и взаимодействуют с почвенными микроорганизмами. Белки, ассоциированные с корнями, играют ключевую роль во всём этом: они формируют рост корней, их ответ на жару, засуху или дефицит питательных веществ, а также взаимодействие с полезными микробами. Поскольку эти белки сильно влияют на урожайность и устойчивость, они представляют интерес для фермеров и селекционеров, даже если те не видят их напрямую. Тем не менее многие такие белки остаются неизвестными, во многом потому, что традиционные методы — такие как протеомика и исследования уровня экспрессии генов — требуют дорогостоящего оборудования, сложного анализа и кропотливых экспериментов.
Преобразование последовательностей белков в подсказки
Белки состоят из цепочек аминокислот, и закономерности в этих цепочках часто указывают, где в растении функционирует белок и какова его роль. Предыдущие компьютерные модели пытались использовать эти закономерности для обнаружения белков, ассоциированных с корнями, но их точность обычно не превышала 80 процентов. Одна из проблем в том, что они рассматривали связи между аминокислотами довольно упрощённо, обычно как попарные. Другая — полагались на ограниченные типы признаков, извлекаемых из последовательностей. Авторы предположили, что более богатые представления каждого белка в сочетании с более умными способами моделирования отношений между аминокислотами могут выявить более тонкие паттерны, связанные с корневыми функциями.
Подсмотрено у языков и сетей
Hypergraph-Root начинает с трёх взаимодополняющих описаний каждого белка. Он использует традиционные схемы оценки последовательностей (BLOSUM62 и матрицы позиционно-специфических оценок), которые отражают, как аминокислоты в ходе эволюции обычно замещают друг друга. Затем добавляется третье, более современное представление от языковой модели для белков ProtT5 — программного обеспечения, обученного на миллионах последовательностей белков, подобно тому как модель предсказания текста обучается на человеческом языке. ProtT5 даёт богатое числовое «встраивание» для каждой аминокислоты, кодирующее подсказки о структуре и функции. Вместе эти три взгляда формируют подробный отпечаток каждого белка в исследовании.
Картирование сложных связей внутри белков
Чтобы выйти за рамки простых попарных сравнений, исследователи предсказали, насколько близки аминокислоты в 3D‑структуре белка, и использовали эту информацию для построения гиперграфа — сети, в которой одна связь может объединять более чем две аминокислоты одновременно. Специализированная нейронная сеть, гиперграфовая свёрточная сеть, обрабатывает эту структуразнную сеть и превращает отпечатки белков в более высокоуровневые признаки. Модуль мультиголовного внимания затем обучается выделять те участки белка, которые несут наиболее полезные сигналы для решения, ассоциирован ли белок с корнями. Наконец, стандартный классификатор преобразует эти сжатые признаки в вероятностную оценку: связан с корнями или нет. В ходе многочисленных тренировочных прогонов и на сбалансированных и несбалансированных тестовых наборах Hypergraph-Root достиг точности свыше 83 процентов и площади под ROC‑кривой (AUC) около 0,9, явно превосходя предыдущие модели.
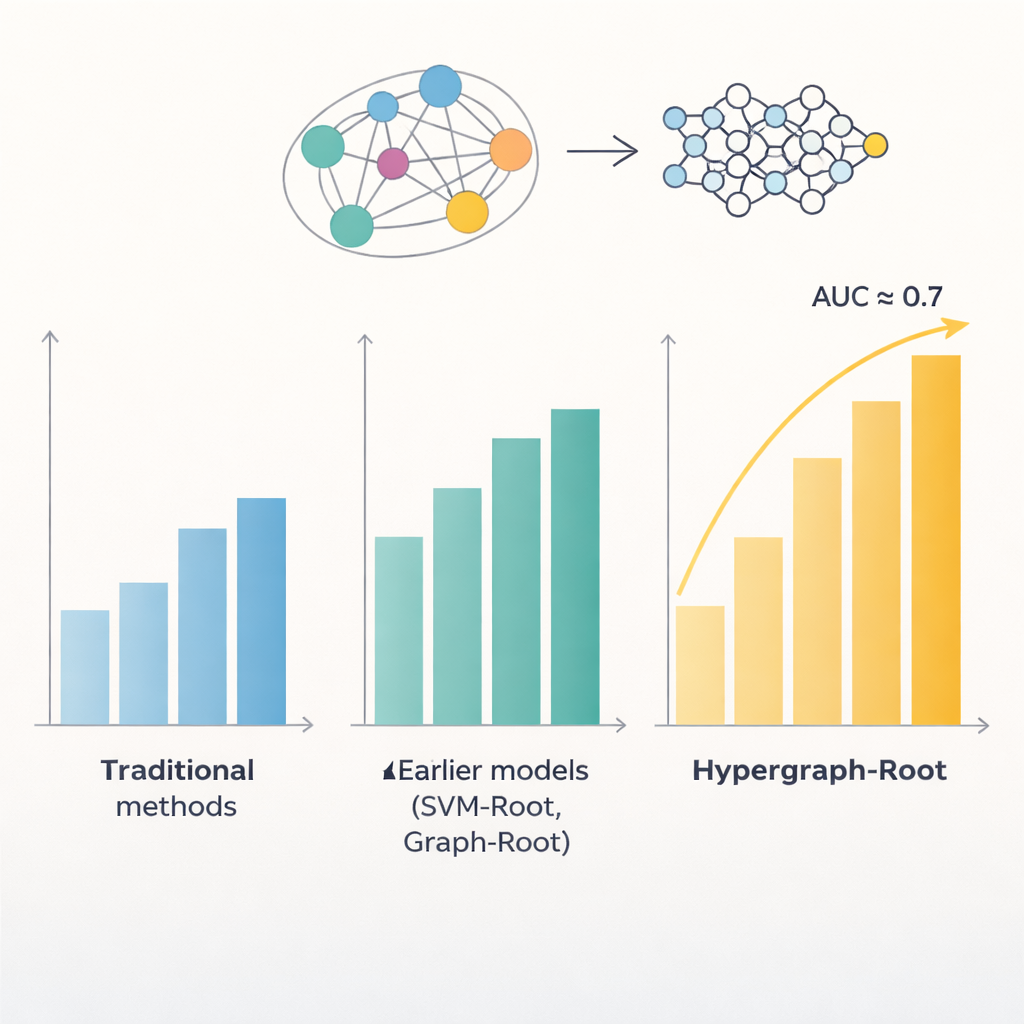
Что показывает модель и почему это важно
Помимо абсолютной точности, модель дала представление о том, какая информация важнее всего. Признаки из языковой модели ProtT5 внесли больший вклад, чем традиционные последовательностные и эволюционные признаки, что указывает на то, что большие предобученные модели способны захватывать тонкие биологические сигналы, которые старые методы упускают. Гиперграфовый компонент также оказался значимым: удаление его или замена более простой графовой моделью снижала качество. Когда исследователи применили Hypergraph-Root к белкам, ранее не маркированным как связанные с корнями, он выделил несколько кандидатов, чьи известные функции — например транспорт через мембраны и метки белков в корнях — сильно указывают на их роль в корневой биологии. Эти кандидаты теперь дают экспериментальным биологам сжатые списки для лабораторной проверки.
От умных предсказаний к более крепким культурам
Проще говоря, Hypergraph-Root похож на опытного библиотекаря по растительной биологии: зная лишь «буквы» белка, он оценивает, вероятно ли этот белок действует в корнях. Комбинируя выводы языковой модели, эволюционную историю и сложные структурные отношения, он значительно улучшает инструменты предыдущего поколения. Хотя он не заменяет эксперименты, он может сократить тысячи вариантов до управляемого числа, экономя время и деньги. В долгосрочной перспективе такие модели могут ускорить открытие белков, ассоциированных с корнями, которые помогут культурам выживать в условиях жары, засухи или бедных почв — важный шаг к более устойчивому сельскому хозяйству в меняющемся климате.
Цитирование: Chen, L., Xun, X. & Zhou, B. Root-associated protein prediction using a protein large language model and hypergraph convolutional networks. Sci Rep 16, 4876 (2026). https://doi.org/10.1038/s41598-026-35110-7
Ключевые слова: белки, ассоциированные с корнями, биоинформатика растений, глубокое обучение, языковые модели для белков, устойчивость сельхозкультур