Clear Sky Science · ru
Сборка беспробельного генома от теломера до теломера Opsariichthys evolans (Cypriniformes: Cyprinidae)
Речная рыба с собственной геномной историей
Стремительные горные ручьи на юго-востоке Китая и на Тайване населяет небольшая яркая рыба Opsariichthys evolans. За пределами региона она малоизвестна, но выполняет важную экологическую роль и сама по себе представляет природное произведение искусства: у неё яркие полосы и эффектная брачная окраска. В течение более ста лет учёные спорили о её классификации и месте в родословном дереве пресноводных рыб. Это исследование даёт ключ к разгадке: первую полную, лишённую разрывов сборку генома O. evolans, прочитанную от одного конца хромосомы до другого.
Почему эта рыба важна
O. evolans обитает в чистых быстрых потоках, где она способствует равновесию пищевых цепей и служит чувствительным индикатором качества воды. В брачный период у самцов появляются яркие боковые полосы и зернистые бугорки на голове и вокруг глаз, а также тёмно-черновато-пурпурный нос. Эти заметные признаки в сочетании с предпочтением быстрых вод делают вид идеальным объектом для изучения адаптаций животных к окружающей среде. Одновременно антропогенные изменения — загрязнение, фрагментация среды и инвазивные виды — сокращают численность, поэтому понимание биологии вида важно для его охраны.
Длительная путаница в названии
Десятилетиями биологи спорили, относится ли O. evolans к роду Opsariichthys или к Zacco. Ранние таксономы описывали вид как Zacco evolans, опираясь в основном на внешние признаки — форму плавников и полосы на теле. Позднейшие более детальные исследования показали, что узор полос и брачные бугорки у него отличаются от аналогичных у похожего Zacco platypus. Исследования митохондриальной ДНК указывали, что O. evolans лучше вписывается в Opsariichthys, но данные по ядерным генам иногда намекали на более близкую связь с Zacco. Без полного генома эволюционная картина оставалась расплывчатой, и споры о его месте в родословной продолжались.

Чтение каждой буквы генома
Чтобы разрешить эти вопросы, исследователи поймали дикого самца в реке провинции Аньхой, Китай, и аккуратно сохранили девять различных тканей. Затем они объединили несколько передовых технологий секвенирования ДНК, каждая из которых имеет свои преимущества, чтобы прочитать генетический код животного. Короткие высокоточныe фрагменты помогали «полировать» последовательность, тогда как длинные и сверхдлинные прочтения от платформ PacBio и Oxford Nanopore позволяли покрывать сложные участки и сшивать хромосомы от конца до конца. Технология Hi-C, фиксирующая трёхмерную организацию ДНК в клетке, использовалась для сборки фрагментов в полноразмерные хромосомы. В результате получен беспробельный геном от теломера до теломера примерно 0,89 миллиарда пар оснований, аккуратно организованный в 39 хромосом, по одной непрерывной молекуле ДНК на каждую.
Что показывает геном
Готовая сборка прошла строгую проверку качества, охватив более 99% ожидаемых консервативных генов и тесно выровнявшись с известными последовательностями у родственных рыб. Почти половину генома составляют повторы, многие из которых — «прыгающие гены», способные перемещаться и перестраивать геном в ходе эволюции. Команда идентифицировала почти 30 000 кодирующих белки генов и тысячи некодирующих РНК, большинство из которых удалось связать с известными функциями с помощью крупных биологических баз данных. Сравнение этого нового генома с геномами двух близких родственников — Opsariichthys bidens и Zacco platypus — показало, что общая структура хромосом очень схожа, подтверждая тесные эволюционные связи. В рамках этой структуры они выделили кандидатные гены и сигнальные пути, вероятно связанные с окраской полос тела и адаптациями к жизни в быстром течении, что даёт подсказки о том, как сформировались характерный внешний вид и образ жизни вида.
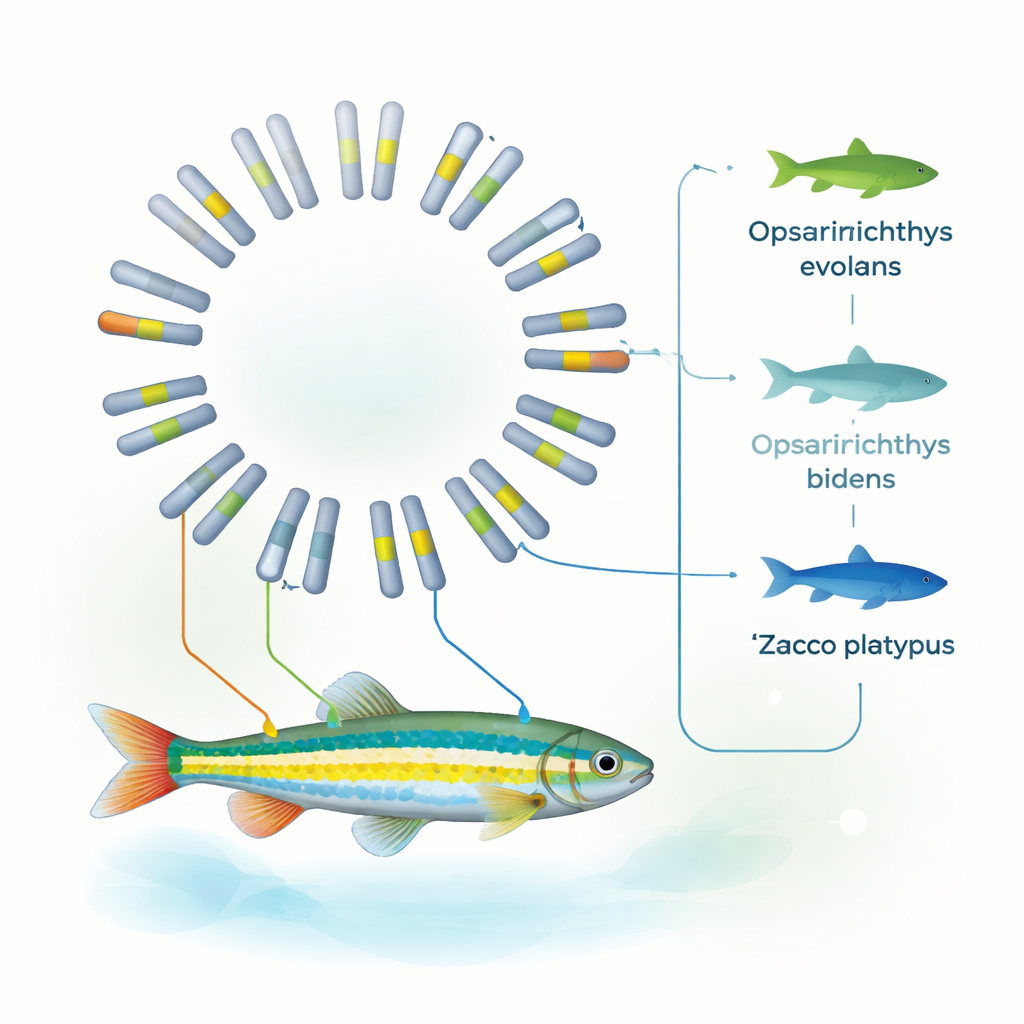
Прояснение его места в родословной рыб
Используя семейства генов, общие для десяти различных видов рыб, команда реконструировала подробное эволюционное дерево. Их анализ указывает на то, что O. evolans отделился от Z. platypus примерно 8–19 миллионов лет назад и что структура его генома особенно близка к O. bidens. Вкупе с предыдущими митохондриальными данными эти наблюдения поддерживают отнесение O. evolans к роду Opsariichthys, а не к Zacco. Иными словами, теперь полный геном подтверждает то, что указывали тщательные наблюдения за полосами, цветом рыла и брачными структурами: внешность может вводить в заблуждение, но когда морфология и полный геном сходятся, таксономические границы становятся гораздо яснее.
Почему полный геном меняет правила игры
Для неспециалистов достижение похоже на переход от размытых порванных карт к чёткому атласу высокого разрешения для вида. С полным, лишённым разрывов геномом учёные теперь могут проследить происхождение яркой окраски O. evolans, её обтекаемую форму, приспособленную к жизни в быстром течении, и отношения с другими азиатскими гольянами с беспрецедентной точностью. Этот ресурс поможет уточнить классификацию рыб, направлять усилия по охране уязвимых речных экосистем и углубить наше понимание того, как небольшие различия в ДНК порождают богатое разнообразие пресноводных рыб.
Цитирование: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Ключевые слова: сборка генома, пресноводная рыба, от теломера до теломера, эволюция рыб, сравнительная геномика