Clear Sky Science · ru
SMART: пространственная мультиомика с агрегацией через графовые нейронные сети и метрическое обучение
Видеть ткани как карты соседств
Наши тела состоят из оживлённых клеточных соседств, где гены, белки и упаковка ДНК работают вместе в точных локализациях. Новые микроскопы и секвенирующие методы теперь могут считывать многие из этих молекулярных пластов прямо в тонких срезах ткани, но преобразовать этот поток многослойных пространственных данных в понятные картины организации органов — большая вычислительная задача. В этом исследовании представлен SMART, вычислительный метод, который помогает учёным объединять эти сложные сигналы в детализированные карты того, где располагаются разные клеточные сообщества и как они организованы.
Почему картирование клеточных соседств сложно
Современные методы «пространственной мультиомики» могут одновременно измерять несколько типов молекулярной информации — например, РНК, белки на поверхности клетки и доступность хроматина — при этом сохраняя точное положение каждой измеренной точки в срезе ткани. Каждый тип, или «омик», даёт свой взгляд на поведение клетки, но данные шумны, имеют высокую размерность и не выравниваются друг с другом естественным образом. К тому же клетки одного типа не всегда сгруппированы вместе; они могут появляться разбросанными островками по органу. Существующие программные инструменты часто либо игнорируют пространственную компоновку, либо слишком упрощают взаимосвязи между омиками, либо испытывают сложности с масштабированием на очень большие наборы данных, которые дают новые приборы.
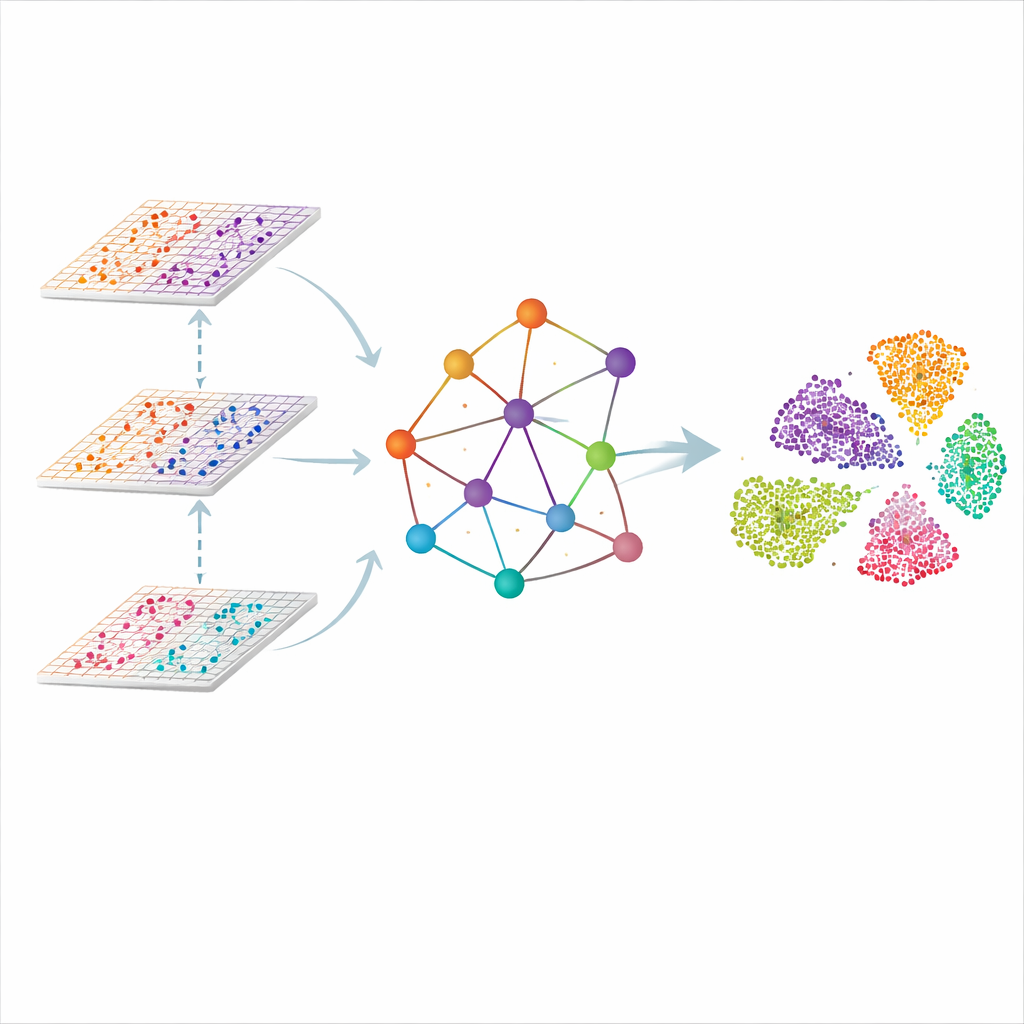
Граф ткани, а не просто список клеток
SMART решает задачу, рассматривая каждую измерительную точку в ткани как узел в сети. Близкие точки связываются, формируя пространственный граф, а молекулярные считывания из каждого омиса сначала сжимаются в меньший набор согласованных признаков, которые фиксируют общие шаблоны вместо отдельных генов. Специальный вид нейронной сети для графов затем передаёт информацию по этим связям, позволяя каждой точке «слушать» соседей, при этом отслеживая вклад каждого омиса. В результате получается общее низкоразмерное представление, в котором похожие регионы ткани — например, отдельные слои мозга или зоны лимфоузла — естественно группируются вместе.
Обучение модели тому, что должно быть похожим
Простого следования за физическими соседями недостаточно, потому что клетки одного типа могут располагаться далеко друг от друга. SMART добавляет второй компонент из систем распознавания лиц: метрическое обучение с использованием триплетов. Для каждой точки метод автоматически находит другую точку с очень похожими молекулярными паттернами («положительную») и одну, которая явно отличается («отрицательную»). Затем он настраивает внутреннее представление так, чтобы положительные точки сближались, а отрицательные отдалялись, даже если они находятся далеко на срезе ткани. Эта «перетягивание» происходит одновременно со стадией восстановления, которая заставляет SMART сохранять ключевые детали каждого омисного слоя, уравновешивая пространственную непрерывность молекулярной специфичностью.
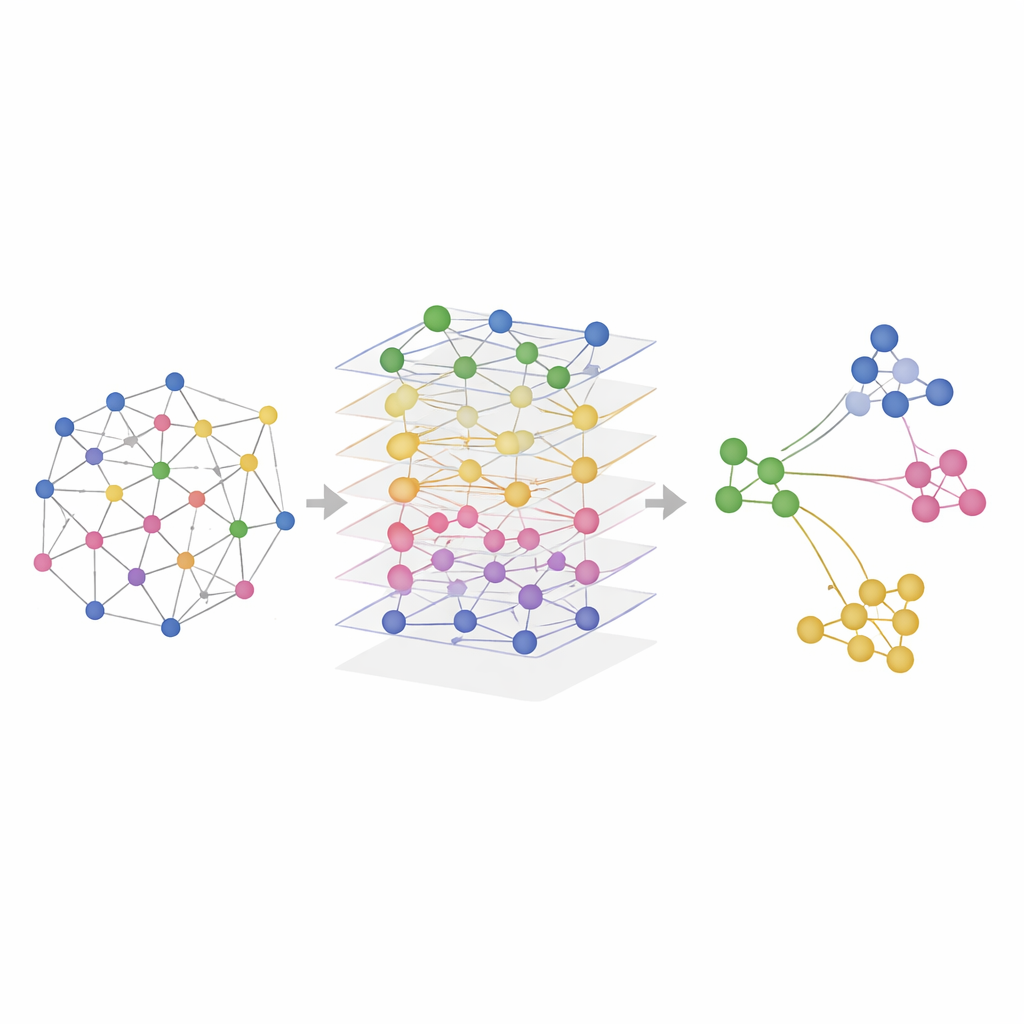
Тестирование SMART на реальных тканях
Исследователи проверяли SMART как на смоделированных данных, так и на реальных экспериментах, которые измеряли комбинации РНК, белков и доступности хроматина в мозге и селезёнке мышей, а также в человеческих лимфоузлах и миндалинах. В контролируемых симуляциях, где были известны истинные пространственные регионы, SMART точнее всего восстанавливал эталонные шаблоны и сохранял отношения, присутствующие в каждом омисном слое. На реальных наборах данных SMART последовательно выявлял тонкие анатомические структуры — такие как конкретные участки мозга или иммунные зоны в лимфоидных органах — более отчётливо, чем конкурирующие методы, при этом поддерживая низкие вычислительные затраты. Связанная версия, называемая SMART‑MS, расширяет те же идеи на несколько срезов ткани, выравнивая срезы одного органа и корректируя технические различия между экспериментами.
Быстрые карты для следующей волны пространственной биологии
Проще говоря, SMART — это движок для создания карт следующего поколения молекулярных атласов. Комбинируя сетевое моделирование пространственной компоновки ткани с встроенным представлением того, что следует считать «похожим», он превращает огромные, шумные наборы пространственных мультиомических измерений в согласованные карты соседств органов. Это позволяет исследователям быстрее находить, где располагаются определённые типы клеток и микроокружения, как они меняются при развитии или болезни и как новые экспериментальные технологии сочетаются друг с другом. По мере того как объём и сложность пространственных данных будут расти, инструменты вроде SMART и SMART‑MS станут ключом к превращению сырых измерений в биологическое понимание.
Цитирование: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Ключевые слова: пространственная мультиомика, графовые нейронные сети, микроокружение ткани, интеграция данных, биология одиночных клеток