Clear Sky Science · ru
Использование предсказуемой кинетики связывания в DNA-PAINT для удаления шума в суперразрешающих изображениях
Более чёткие взгляды на микромир
Современные микроскопы теперь способны «видеть» отдельные молекулы внутри клеток, но такие изображения часто усеяны вводящими в заблуждение пятнами фона. В этом исследовании предложен способ очистки таких изображений с использованием того, как фрагменты ДНК естественно связываются и расцепляются во времени. В результате получаются более чёткие изображения молекулярной машинерии в клетках — это важно как для базовой биологии, так и для разработки лекарств.
Как мерцание раскрывает скрытые детали
Один мощный метод визуализации, называемый DNA-PAINT, превращает случайное связывание коротких ДНК-цепочек в инструмент суперразрешающей микроскопии. Одна ДНК-цепочка прикреплена к белку, который изучают; соответствующая цепочка с флуоресцентным красителем плавает в растворе. Когда плавающая цепочка кратковременно связывается со своей парой, возникает крошечная вспышка света. Записывая множество таких мерцаний и точно определяя их положения, исследователи могут восстановить местоположение белков с нанометровой точностью — гораздо лучше, чем при обычной световой микроскопии.
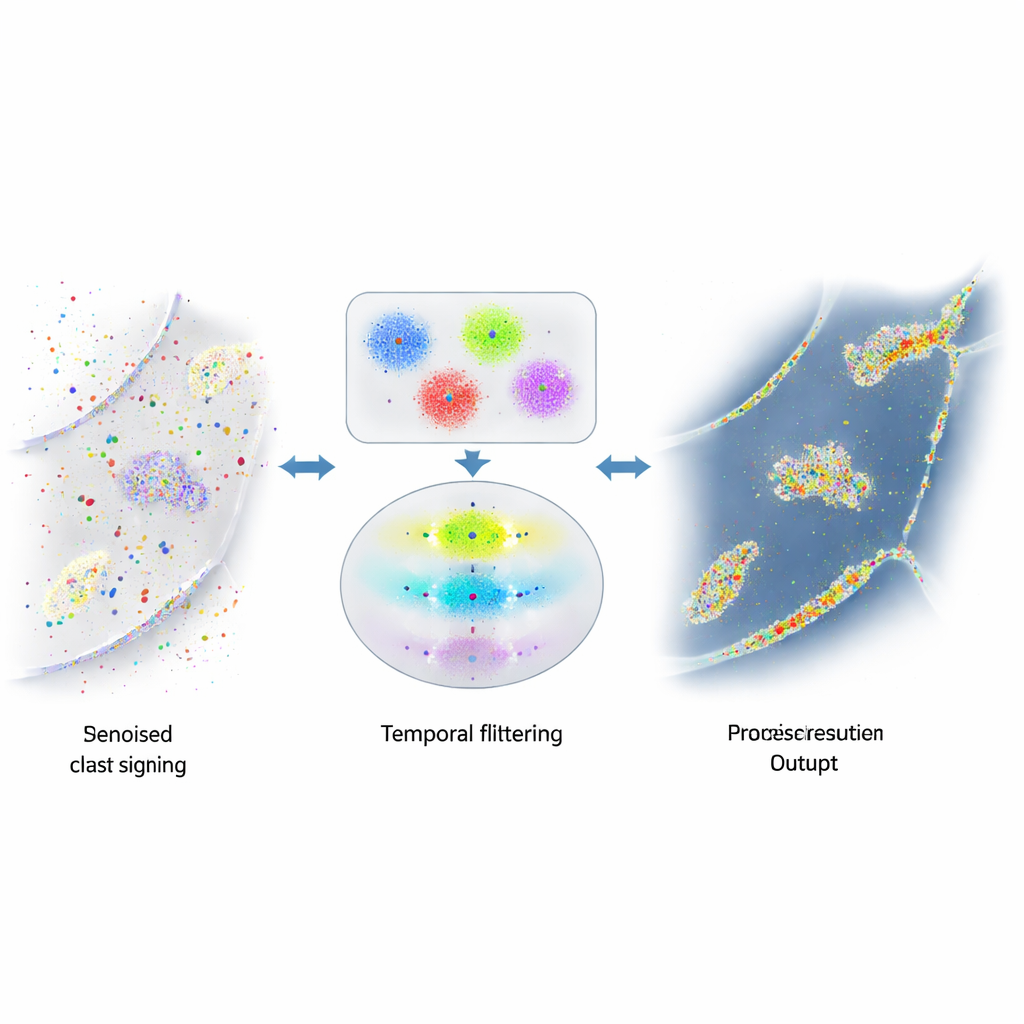
Когда полезные сигналы тонут в шуме
Сила DNA-PAINT — большое число свободно движущихся флуоресцентных цепочек — одновременно порождает проблему. Эти цепочки иногда прикрепляются не там, где нужно, например к случайным поверхностям в клетке или к обильной ДНК в ядре. Такие случайные вспышки внешне неотличимы от настоящих и засоряют итоговое изображение ложными точками и скоплениями. Ранние попытки уменьшить этот шум были направлены на изменение химии, чтобы сделать нежелательное связывание реже, или на грубые правила для отсечения очевидных выбросов. Тем не менее значительная доля вводящего в заблуждение сигнала оставалась, что ограничивало надежность измерений числа белков или их пространственных соотношений.
Использование времени, чтобы отличить правду от обмана
Авторы заметили, что реальные ДНК-пары в DNA-PAINT подчиняются простому временному правилу: паузы между подлинными событиями связывания следуют предсказуемому экспоненциальному распределению. В отличие от этого, случайные прикрепления такого порядка не имеют. Они разработали многоэтапный алгоритм, который сначала группирует близкие по положению мерцания в небольшие кластеры, используя сочетание алгоритмов на основе плотности и k-средних, чтобы разбивать сложные формы на единицы размера локализации. Для каждого кластера они затем строят «временную трассу» событий связывания, аккуратно объединяя быстрое включение-выключение в рамках одного и того же связывания в единичные события. Наконец, применяется статистический тест, который проверяет, соответствуют ли интервалы между событиями в каждом кластере ожидаемому экспоненциальному поведению. Кластеры, прошедшие проверку, рассматриваются как реальные; те, что не проходят — отбрасываются как шум.
Проверка метода в живых клетках
Для испытания подхода команда визуализировала белок клеточной адгезии E-кадгерин в яйцевых камерах плодовой мушки, где одни клетки продуцировали помеченный белок, а соседние — нет. Это создало соседние области, богатые подлинным сигналом, и области, которые должны были содержать лишь фон. Настраивая минимальное число событий связывания, которое кластер должен показать перед проверкой, они нашли параметры, удалявшие более 90% ложных кластеров при сохранении более 98% настоящих на границах клеток. В очищенных изображениях тонкие структурные элементы, такие как трубчатые структуры и везикулы, стали гораздо более различимы. Та же стратегия сработала и в других системах, включая митохондрии и микротрубочки, а также для белков с более расплывчатым, аморфным распределением, где пространственная информация сама по себе не даёт подсказки, что является реальным сигналом.
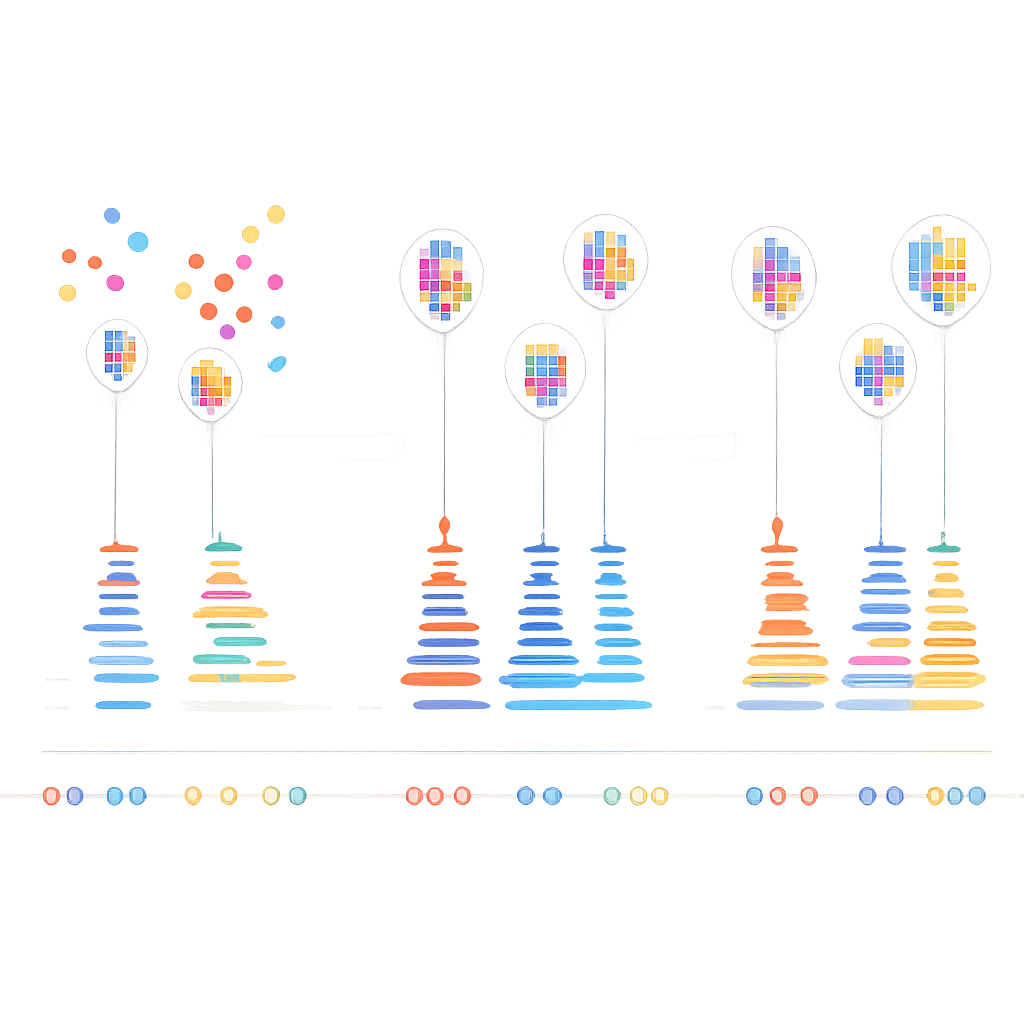
Более чёткие молекулярные карты для будущих исследований
Слушая «ритм» связывания ДНК, а не только фиксируя места мерцаний, этот метод надёжно удаляет вводящий в заблуждение фон из данных DNA-PAINT. Для неспециалистов ключевой результат прост: более чёткие и более достоверные молекулярные карты внутри клеток. Это упрощает подсчёт числа молекул белка, оценку того, насколько близко расположены разные белки, и построение более точных представлений внутренней жизни клетки. По мере развития ДНК-основанной визуализации такие интеллектуальные методы удаления шума станут необходимыми для превращения сырых зернистых изображений в надёжные биологические выводы.
Цитирование: Sirinakis, G., Allgeyer, E.S., Richens, J.H. et al. Utilizing the predictable binding kinetics of DNA-PAINT to denoise super-resolution images. Nat Commun 17, 2397 (2026). https://doi.org/10.1038/s41467-026-69304-4
Ключевые слова: DNA-PAINT, суперразрешающая микроскопия, удаление шума изображения, одномолекулярная визуализация, картирование белков