Clear Sky Science · ru
Экспериментально информированная модель полимера раскрывает высокоразрешающую организацию геномных локусов
Как сворачивание ДНК формирует клеточную идентичность
Каждая клетка вашего тела по существу несёт одну и ту же ДНК, но клетки мозга, кожи и стволовые клетки ведут себя совершенно по‑разному. Одна из ключевых причин — то, как эта ДНК свернута и упакована в ядре. В этом исследовании предложен новый способ «увидеть» это сворачивание с впечатляющей детализацией, связывающий физическое расположение ДНК с тем, включены ли важные гены или выключены. Сочетая эксперименты с физически обоснованными компьютерными симуляциями, авторы выявляют скрытые сгустки генетического материала, которые, по‑видимому, выступают в роли базовых строительных блоков организации генома.
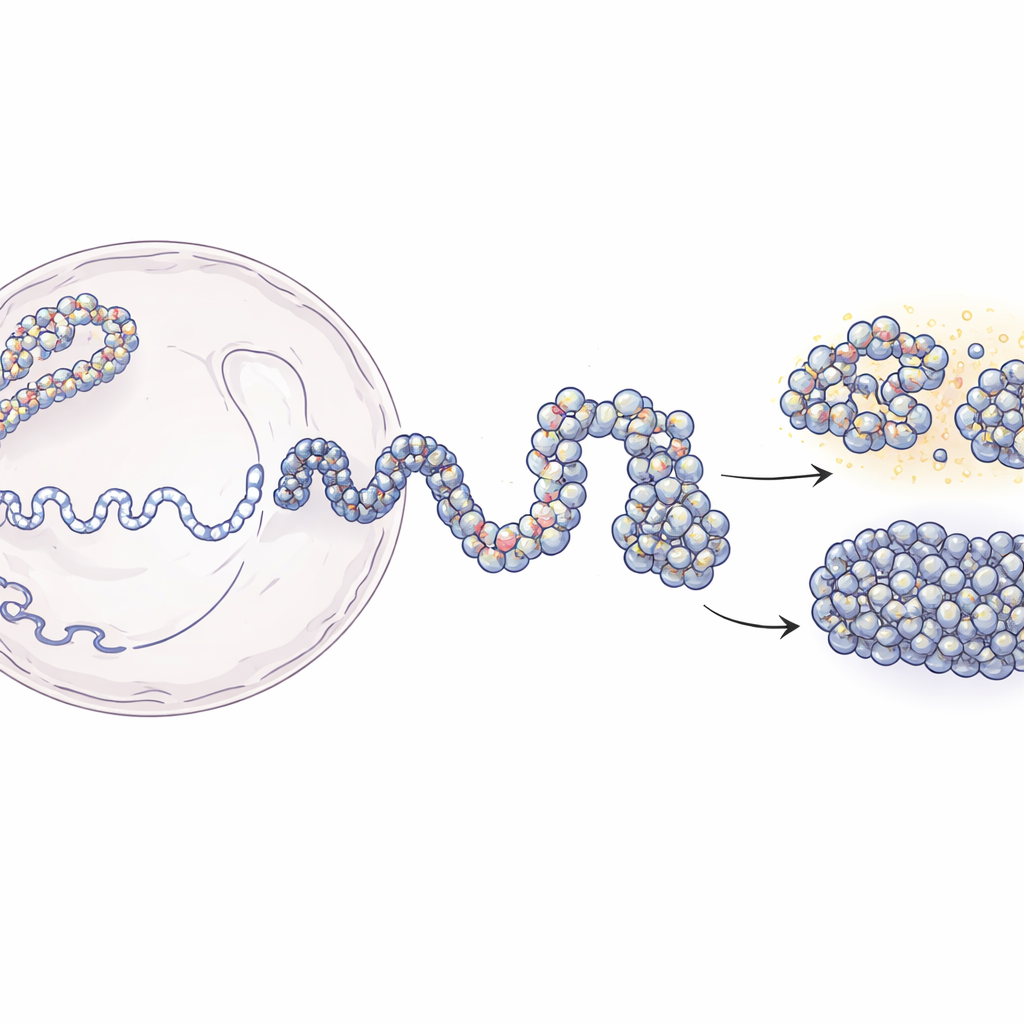
От длинных нитей ДНК к 3D‑картам генома
Внутри ядра ДНК намотана на белковые катушки — нуклеосомы, формируя структуру «бусы на нити», известную как хроматин. Современные методы, такие как Hi‑C и Micro‑C, показывают, какие участки ДНК находятся рядом в трёхмерном пространстве, но обычно дают размытые, усреднённые по популяции снимки. С другой стороны, эксперименты, локализующие отдельные нуклеосомы, дают чёткие локальные данные, но мало показывают о крупной структуре. Эта работа заполняет этот разрыв. Авторы начинают с карт контактов низкого разрешения, которые сообщают, как часто удалённые сегменты ДНК соприкасаются, а затем комбинируют их с экспериментальными картами позиций нуклеосом. Используя принципы полимерной физики, они строят смоделированные 3D‑ансамбли хроматина, согласующиеся с данными экспериментов и при этом разрешающие структуры до нескольких десятков букв ДНК.
Двухэтапная стратегия восстановления хроматина
Подход к моделированию разворачивается в двух основных стадиях. Сначала команда использует данные Hi‑C для генерации множества возможных крупномасштабных форм участка ДНК длиной 200 000 букв, рассматривая хроматин как гибкую цепь, где сегменты по 5 000 букв мягко направляются на установление или избегание контактов, наблюдаемых в экспериментах. Эти грубые структуры захватывают общие схемы сворачивания, которые создают белки в клетке. На втором этапе каждая крупная «шарика» заменяется значительно более тонкой цепочкой, состоящей из отдельных нуклеосом и коротких звеньев ДНК между ними. Позиции нуклеосом определяются методом картирования на основе фермента (MNase‑seq), который показывает, где они обычно располагаются вдоль генома. Затем тонкомасштабные цепочки позволяют сворачиваться, при этом сохраняя общую архитектуру. Когда исследователи «размывают» свои высокоразрешающие модели обратно до экспериментального разрешения, они с высокой точностью воспроизводят контактные карты Hi‑C и Micro‑C.
Открытие «пузырьков» нуклеосом как структурных единиц
При приближении к смоделированным структурам выявился поразительный рисунок: нуклеосомы располагались неравномерно, а собирались в неправильные кластеры, которые авторы называют пузыриками нуклеосом. Эти пузырики напоминают комковатые структуры, ранее наблюдавшиеся в изображениях реальных клеток при сверхразрешающей микроскопии. Проанализировав тысячи смоделированных снимков, команда показала, что пузырики вытянуты, а не сферичны, и обычно содержат несколько плотно упакованных нуклеосом. Существенно, что контакты внутри этих пузыриков тесно соответствуют блокам доменоподобных взаимодействий, наблюдаемым в экспериментальных данных, что указывает на то, что пузырики — не случайные образования, а фундаментальные 3D‑единицы организации хроматина. Симуляции даже предсказывают дополнительные тонкие границы доменов, которые трудно обнаружить экспериментально, предполагая, что физическая модель может выявлять мелкомасштабные особенности, скрытые в шумных данных.
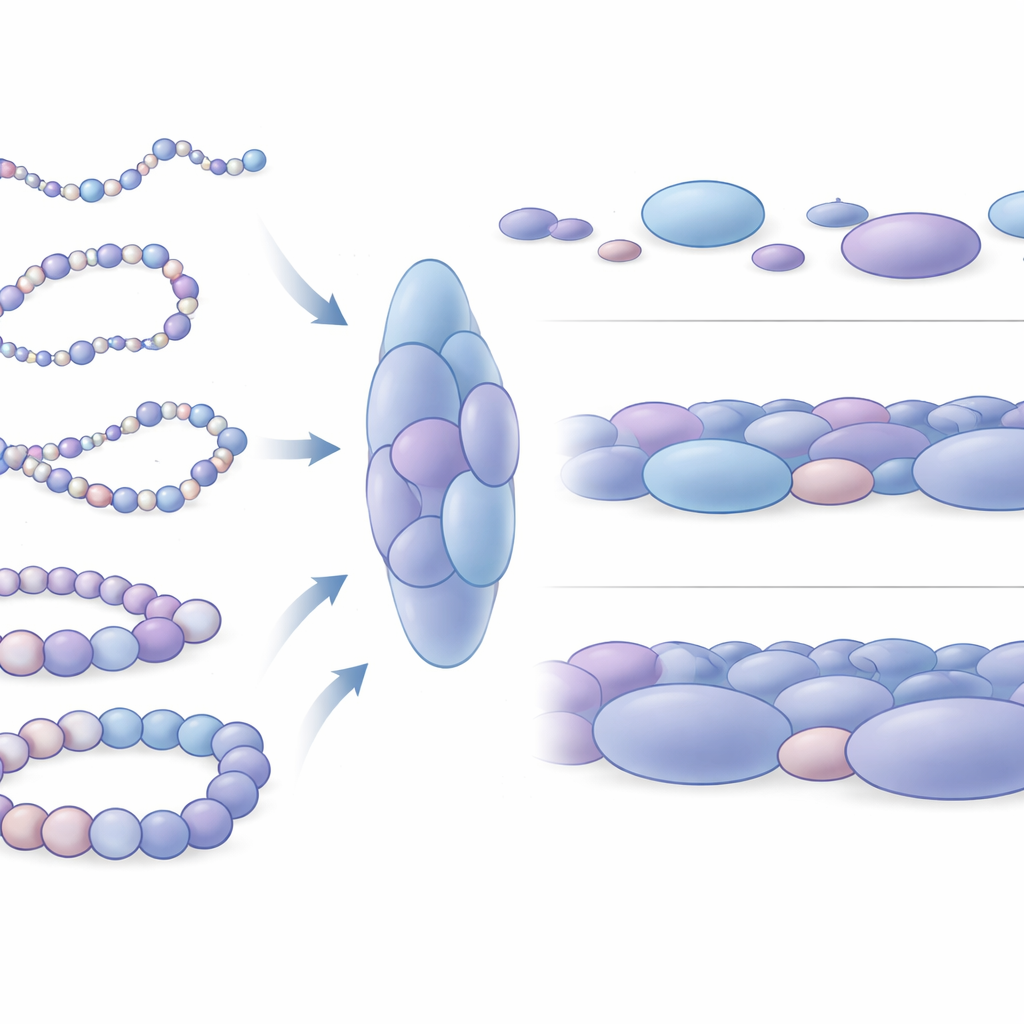
Как различия в упаковке отражают активность генов
Далее исследователи выяснили, как пузырики отличаются вокруг активных генов по сравнению с неактивными. Они сосредоточились на четырёх хорошо изученных участках человеческой ДНК, включая два гена, поддерживающие стволовые клетки в гибком, недифференцированном состоянии (Nanog и Lin28A), и два гена развития (HoxB4 и HoxA13), выключенные в тех же клетках. Вокруг неактивных генов пузырики в среднем были крупнее и плотнее упакованы: нуклеосомы формировали более закрытые локальные структуры. Напротив, пузырики рядом с активными генами были меньше, несколько рыхлее и более разнообразны. В более широком масштабе ДНК вокруг активных генов испытывала больше различных форм и была механически более гибкой, тогда как области вокруг молчащих генов вели себя как жёсткие участки хроматина. Эта механическая разница, вероятно, влияет на то, насколько легко удалённые регуляторные элементы ДНК могут встречаться и взаимодействовать с переключателями генов.
Почему это важно для понимания регуляции генов
В целом полученная картина такова: геном построен из динамичных кластеров нуклеосом, размер, форма и расстояния между которыми помогают определять, доступны ли близлежащие гены или заперты. Новая модель объединяет данные контактных карт, карты нуклеосом и физические принципы в единую схему, объясняющую, как гены стволовых клеток остаются гибкими и интерактивными, тогда как гены развития оказываются изолированы в более жёстких, компактных округах. Для неспециалиста ключевая идея в том, что активность генов определяется не только последовательностью ДНК; она также зависит от того, как эта ДНК свернута в трёхмерные структуры. Выявление пузыриков нуклеосом как базовых строительных блоков этого сворачивания даёт мощный путь для связи микроскопической архитектуры генома с крупномасштабными процессами, такими как развитие, клеточная идентичность и заболевания.
Цитирование: Mittal, R., Heermann, D.W. & Bhattacherjee, A. An experimentally-informed polymer model reveals high resolution organization of genomic loci. Nat Commun 17, 2338 (2026). https://doi.org/10.1038/s41467-026-68928-w
Ключевые слова: сворачивание хроматина, кластеры нуклеосом, 3D-организация генома, регуляция генов, полимерное моделирование