Clear Sky Science · ru
Атлас абсолютной квантификации малых некодирующих РНК в различных тканях млекопитающих и клеточных линиях
Почему важны крошечные молекулы РНК
Внутри каждой клетки множество маленьких молекул РНК участвуют в решении того, какие гены включаются, а какие выключаются. Эти малые некодирующие РНК действуют как регуляторы уровня активности генетических программ, формируя развитие, функцию органов и процессы, связанные с болезнями. Несмотря на мощные технологии секвенирования, ученым трудно точно определить, сколько таких молекул присутствует в разных клетках и тканях. В этом исследовании предложен более точный способ их подсчёта и создан подробный атлас, показывающий истинную их распространённость в разных тканях млекопитающих и в распространённых лабораторных клеточных линиях.
Более прозрачный способ подсчёта малых РНК
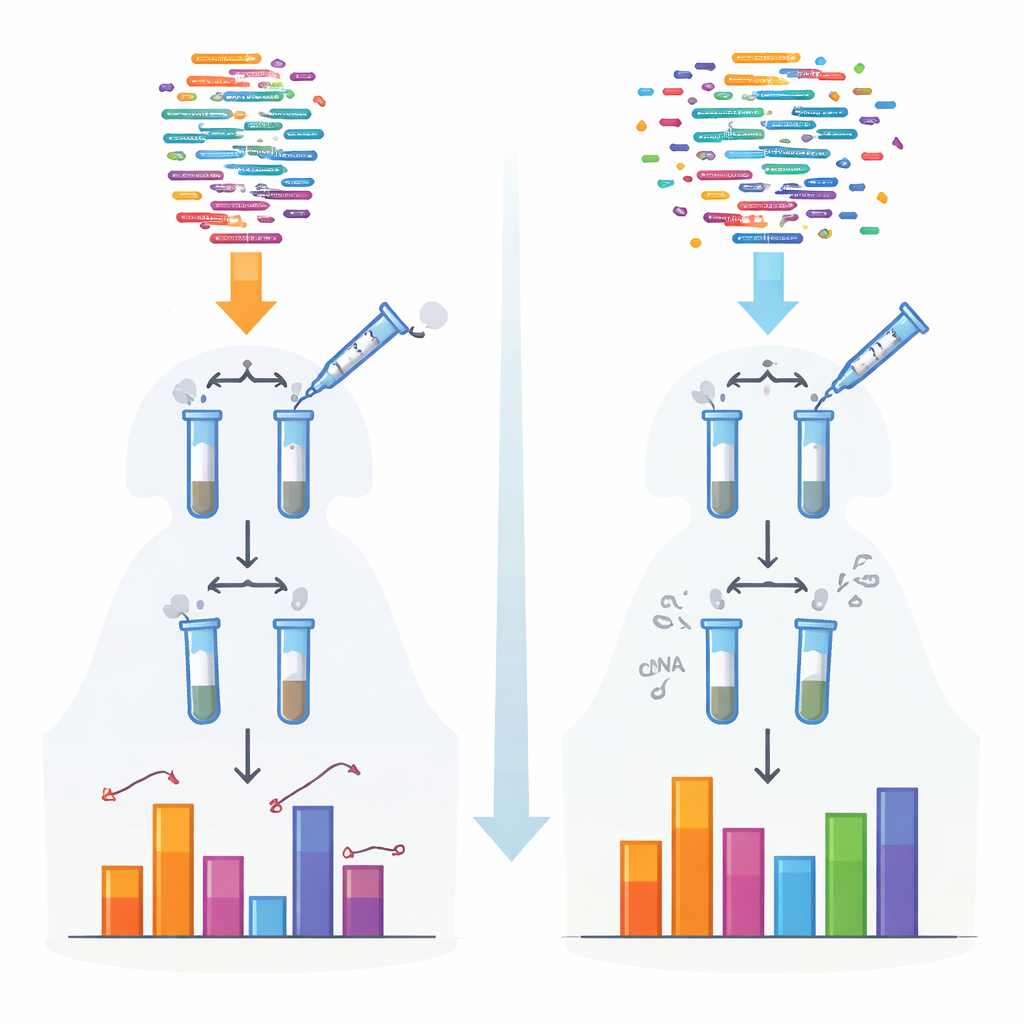
Традиционные методы секвенирования малых РНК опираются на ферменты, которые присоединяют адаптеры перед считыванием молекул. Эти ферменты имеют предпочтение к определённым формам и химическим окончаниям, поэтому одни РНК захватываются эффективно, а другие пропускаются или недооцениваются. Такое смещение особенно сильно влияет на отдельные классы, например piRNA и растительные малые РНК, которые несут защитные химические «шапки» на концах. Авторы разработали новый протокол, названный 4NBoost, который переработал адаптеры и условия реакции, чтобы выровнять эти предпочтения, а также ввёл встроенные молекулярные штрих‑коды для различения истинных молекул и копий, появившихся в ходе амплификации.
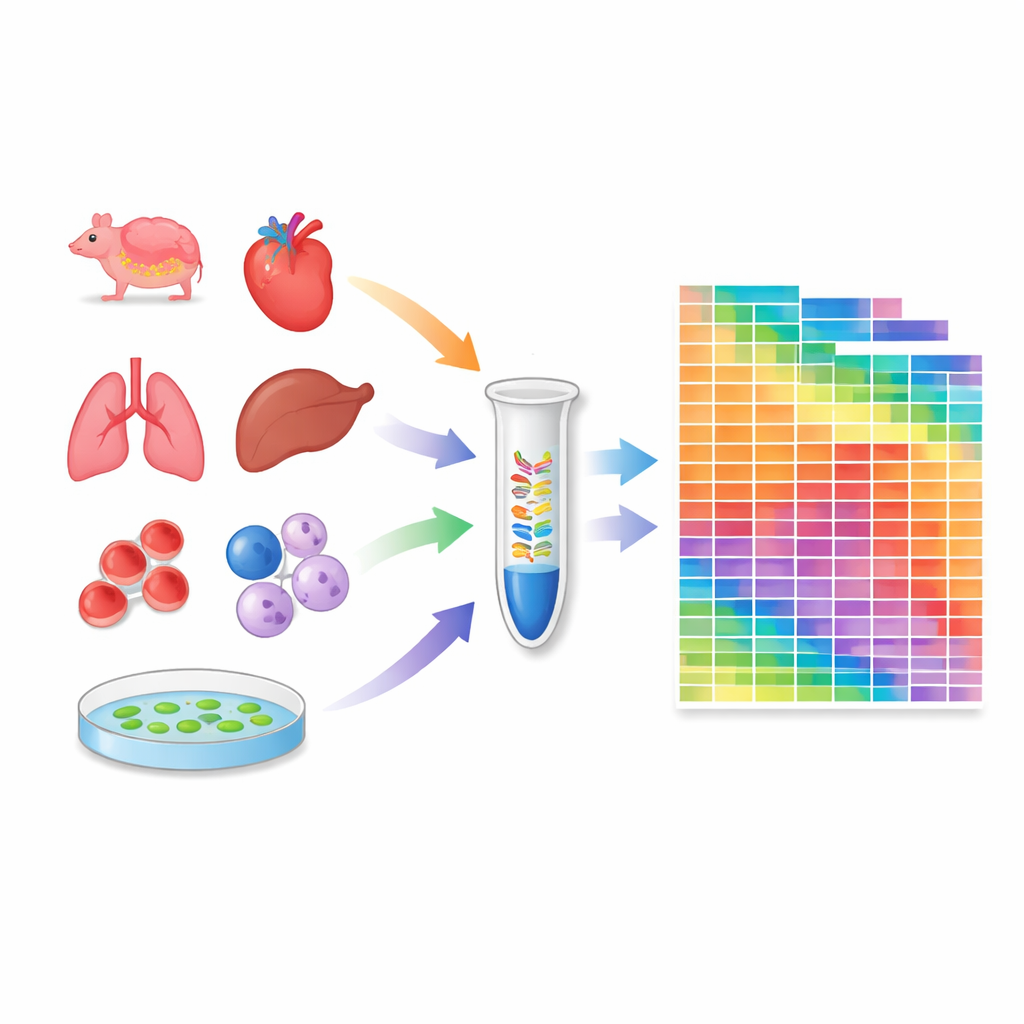
Преобразование протокола в измерительный инструмент
Чтобы превратить 4NBoost из относительного в абсолютный метод измерения, команда добавила точно сконструированные синтетические «спайк‑ины» РНК с известными концентрациями, охватывающими очень широкий диапазон. Сравнивая, сколько раз секвенсор считал каждый спайк‑ин с тем, сколько было добавлено изначально, они построили стандартные кривые, переводящие число чтений в абсолютное число молекул. Испытания с различными смесями спайк‑инов и добавленными контрольными РНК показали, что 4NBoost способен точно отслеживать концентрации на нескольких порядках величины, включая РНК с трудноучитываемыми химическими модификациями. Даже при исходном материале всего в один нанограмм общей РНК метод надёжно отражал ландшафт малых РНК.
Построение атласа по тканям и клеточным линиям
Вооружившись откалиброванным протоколом, исследователи профилировали 259 образцов: 20 тканей мыши, 18 тканей крабоедкой макаки, 24 широко используемые человеческие и мышиные клеточные линии и несколько тканей модельного растения Arabidopsis. Для каждого образца они оценивали абсолютное число молекул тысяч микроРНК и piRNA. Это показало, какие виды микроРНК присутствуют в каждой среде и как их суммарные количества варьируют между тканями и видами. Некоторые клеточные линии и органы обладают особенно богатым репертуаром микроРНК, тогда как в других, например в клетках крови, доминируют несколько высокообильных видов. Атлас также выявил существенные различия между тканями мыши и макаки, подчёркивая, что регуляция с помощью малых РНК может быть специфичной для вида.
Коррекция старых данных и пересмотр общих предположений
При сопоставлении нового атласа с популярными базами данных малых РНК, созданными традиционными методами, обнаружились заметные несоответствия. Некоторые важные семейства микроРНК — такие как miR‑19 и miR‑29 — оказались значительно более распространёнными, чем считалось ранее, в то время как другие — например широко изучаемые семейства let‑7 и miR‑10 — часто были переоценены. В работе также пересмотрели, какая «цепь» прекурсорного шпилькового молекулы реально используется в клетках, обнаружив случаи, где текущие аннотации указывают неправильную основную нить. Чтобы исправить множество существующих смещённых наборов данных, авторы обучили модель машинного обучения, которая изучает, как традиционные измерения отклоняются от 4NBoost, а затем математически корректирует их, чтобы лучше отражать истинную абундантность.
Публичный ресурс для изучения малых РНК
Все измерения 4NBoost и модель коррекции доступны бесплатно через онлайн‑платформу SmRNAQuant. Исследователи могут просматривать или скачивать абсолютные уровни малых РНК для конкретных тканей, клеточных линий или микроРНК, а также загружать свои данные, подготовленные с помощью стандартного набора, чтобы получить скорректированные значения с учётом смещения. Для неспециалистов главный вывод таков: точный подсчёт важен — крошечные различия в числе копий малых РНК могут означать разницу между активной генетической регуляцией и её отсутствием. Предоставляя более надёжные числа и способ исправлять старые данные, эта работа закладывает прочную количественную основу для понимания того, как малые РНК формируют нормальную биологию и болезни.
Цитирование: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
Ключевые слова: квантификация микроРНК, малые некодирующие РНК, смещение при секвенировании РНК, атлас тканевой экспрессии, машинное обучение для коррекции