Clear Sky Science · ru
Автоматизированная картография продвижения вилки репликации ДНК в человеческих клетках с помощью ForkML
Почему важно отслеживать скорость копирования ДНК
Каждый раз при делении человеческой клетки ей нужно быстро и точно скопировать более трёх миллиардов букв ДНК. Если этот процесс замедляется или останавливается, это может повредить геном и способствовать возникновению рака и нарушений развития. Однако до сих пор учёным не хватало простого способа увидеть, с какой скоростью отдельные «машины» копирования движутся по конкретным участкам человеческой ДНК. В этой статье представлен ForkML — новый метод, который с помощью нанопорового секвенирования и машинного обучения автоматизирует эту задачу в беспрецедентном масштабе.
Наблюдение за «машинами» копирования клетки в реальном времени
ДНК дублируется крошечными молекулярными комплексами, называемыми репликационными вилками, которые движутся по двойной спирали и синтезируют новые цепи. ForkML позволяет исследователям косвенно наблюдать за этими вилками: в вновь синтезируемую ДНК вводят безвредную химическую метку BrdU в течение двух очень коротких вспышек, разделённых фиксированным интервалом времени. Поскольку BrdU можно обнаружить в отдельных молекулах ДНК с помощью нанопоровых секвенаторов, учёные видят на каждой цепи две меченые «полосы», где вилка прошла во время двух импульсов. Измеряя расстояние между полосами и деля на известный интервал времени, они вычисляют, с какой скоростью каждая вилка двигалась в этой области генома. 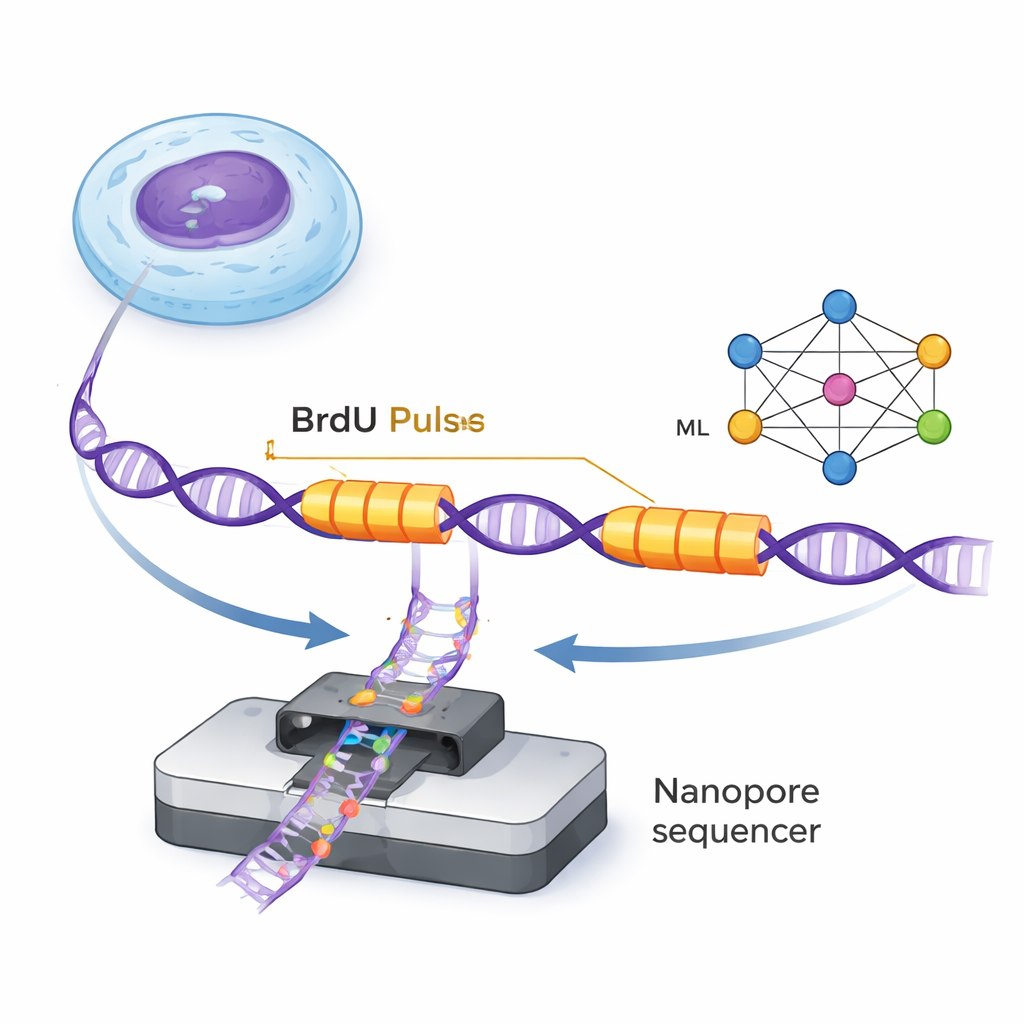
Обучение компьютера распознавать химические следы
В ранних работах на дрожжах авторы могли обнаруживать эти треки BrdU простыми правилами, но в человеческих клетках сигналы слабее и сложнее. Эксперты-человеки всё ещё могут распознать характерный паттерн — резкий подъём BrdU в начале импульса, за которым следует плавное снижение при вымывании — но вручную просматривать миллионы фрагментов ДНК невозможно. ForkML решает эту проблему: нейронная сеть, форма машинного обучения, обучается на тысячах вручную аннотированных примеров. Модель учится классифицировать каждый участок ДНК как фон или как вилку, движущуюся влево или вправо, и точно определять начало каждого импульса BrdU. Это позволяет полностью автоматизировать картирование тысяч индивидуальных скоростей вилок в рамках одного запуска секвенирования.
Измерение стресса и различий по всему геному
Применив ForkML к клеточной линии рака толстой кишки человека, команда получила более 2000 измерений скорости вилки в одном эксперименте и обнаружила, что типичная вилка движется примерно со скоростью 1,2 килобазы в минуту, что согласуется с прежними, менее масштабными методами. При обработке клеток препаратами, известными своим эффектом замедления репликации ДНК, ForkML чётко зафиксировал замедление, доказав свою чувствительность к репликационному стрессу. Поскольку каждая вилка возвращается к позиции в референсном геноме, авторы смогли соотнести скорость с другими характеристиками: временем репликации в клеточном цикле, степенью упаковки ДНК и активностью транскрипции в регионе. 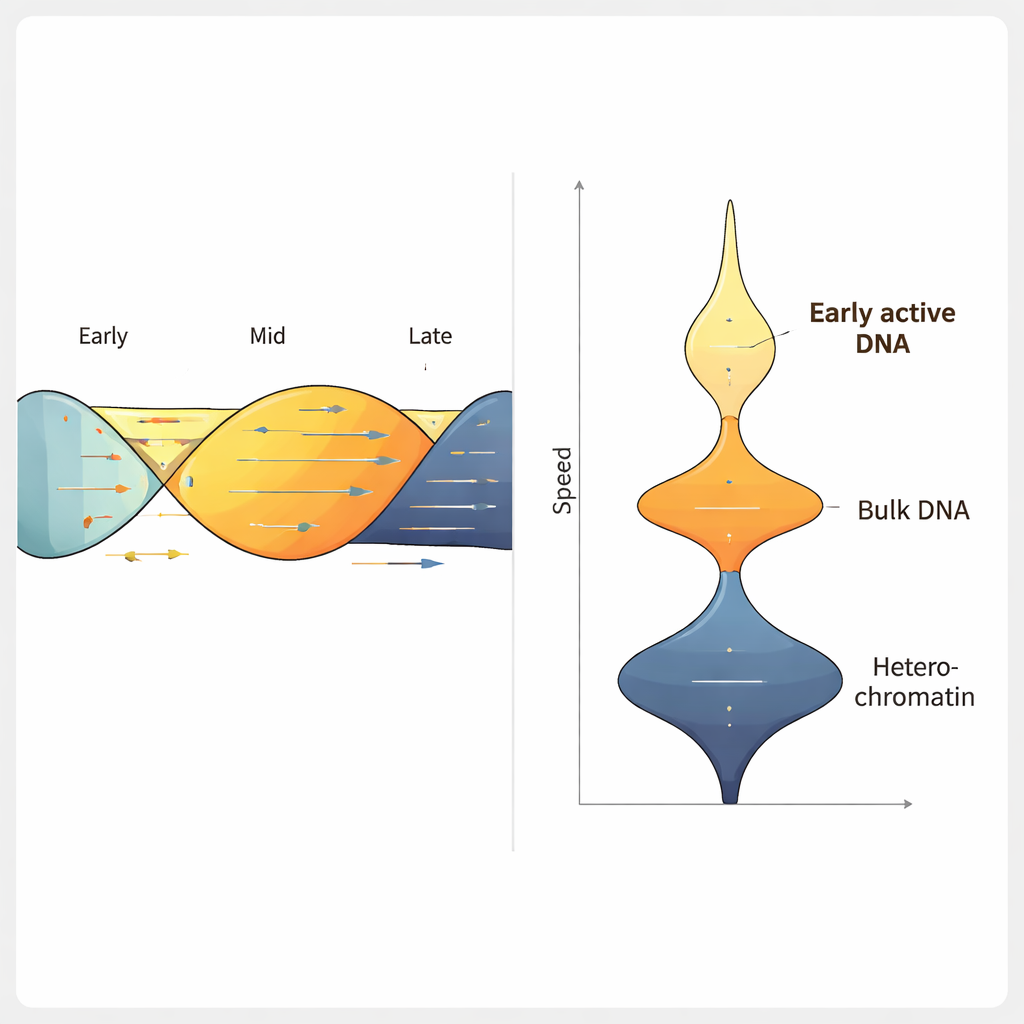
Выявление мест начала копирования и различий между цепями
Помимо скорости, ForkML также определяет, где начинается и где заканчивается репликация, обнаруживая точки, где вилки расходятся или сходятся на одной молекуле. Картируя более 20 000 таких сайтов инициации, авторы подтверждают, что человеческие клетки используют смешанную стратегию: часть репликации начинается в хорошо определённых зонах инициации, но большинство стартов распределено по геному. Сочетая направление вилки с тем, какая цепь ДНК была прочитана секвенатором, ForkML также различает скорости синтеза лидирующей и отстающей цепей — то, чего нельзя получить традиционными фибровыми методами. Испытания на шести различных человеческих клеточных линиях — как нормальных, так и опухолевых — показали, что одинаковые простые условия маркировки BrdU работают широко и дают надёжные оценки скорости в каждом случае.
Цифровое обновление классического метода
Для неспециалистов ForkML можно рассматривать как современную цифровую версию классического метода анализа ДНК-фибр: используется аналогичная схема меток, но ручную микроскопию заменяют длинночитовым секвенированием и машинным обучением. Это даёт гораздо большую пропускную способность, прямое привязывание каждого измерения к позиции в геноме и более подробную информацию о том, где и с какой скоростью копируется ДНК. Поскольку протокол прост, совместим с существующим нанопоровым оборудованием и адаптируем к другим организмам, ForkML имеет все предпосылки стать стандартным инструментом для изучения репликации ДНК. В практическом плане он предлагает исследователям мощный способ связать локальную скорость копирования ДНК — нормальную или при стрессе — с активностью генов, состоянием хроматина и изменениями в геноме, связанными с заболеваниями.
Цитирование: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
Ключевые слова: Репликация ДНК, скорость репликационной вилки, нанопоровое секвенирование, метка BrdU, машинное обучение в геномике