Clear Sky Science · ru
Высокоскоростная слепая микроскопия со структурированным освещением через несупервизируемое разворачивание алгоритма
Более четкие фильмы о жизни внутри клетки
Современная биология во многом зависит от наблюдения живых клеток в действии, но многие ключевые структуры слишком малы и слишком быстры, чтобы обычный микроскоп мог снять их отчетливо. В этой статье представлен новый способ превращать размытые, быстро снятые изображения в четкие, сверхдетализированные фильмы в реальном времени, без необходимости идеально настроенного оборудования. Метод, названный развёрнутой слепой микроскопией со структурированным освещением (UBSIM), обещает сделать передовую высокоскоростную визуализацию клеток более доступной для обычных лабораторий.
Почему обычные микроскопы не справляются
Традиционные световые микроскопы ограничены дифракцией — фундаментальным свойством света, которое размывает мелкие детали размером меньше нескольких сотен нанометров. Микроскопия со структурированным освещением (SIM) решает это, подсвечивая образец узорчатым светом и используя возникающие интерференции, чтобы извлечь дополнительную детальность, примерно удваивая разрешение. Однако классический SIM требует точно известных шаблонов подсветки и тщательной калибровки, что может быть дорого и хрупко. Новый вариант — слепой SIM — ослабляет требования к оборудованию, позволяя использовать случайные узоры и восстанавливая одновременно и образец, и освещение по самим данным. Минус в том, что процесс восстановления медленный и итеративный — от секунд до минут на кадр, что слишком медленно для живых динамических фильмов.
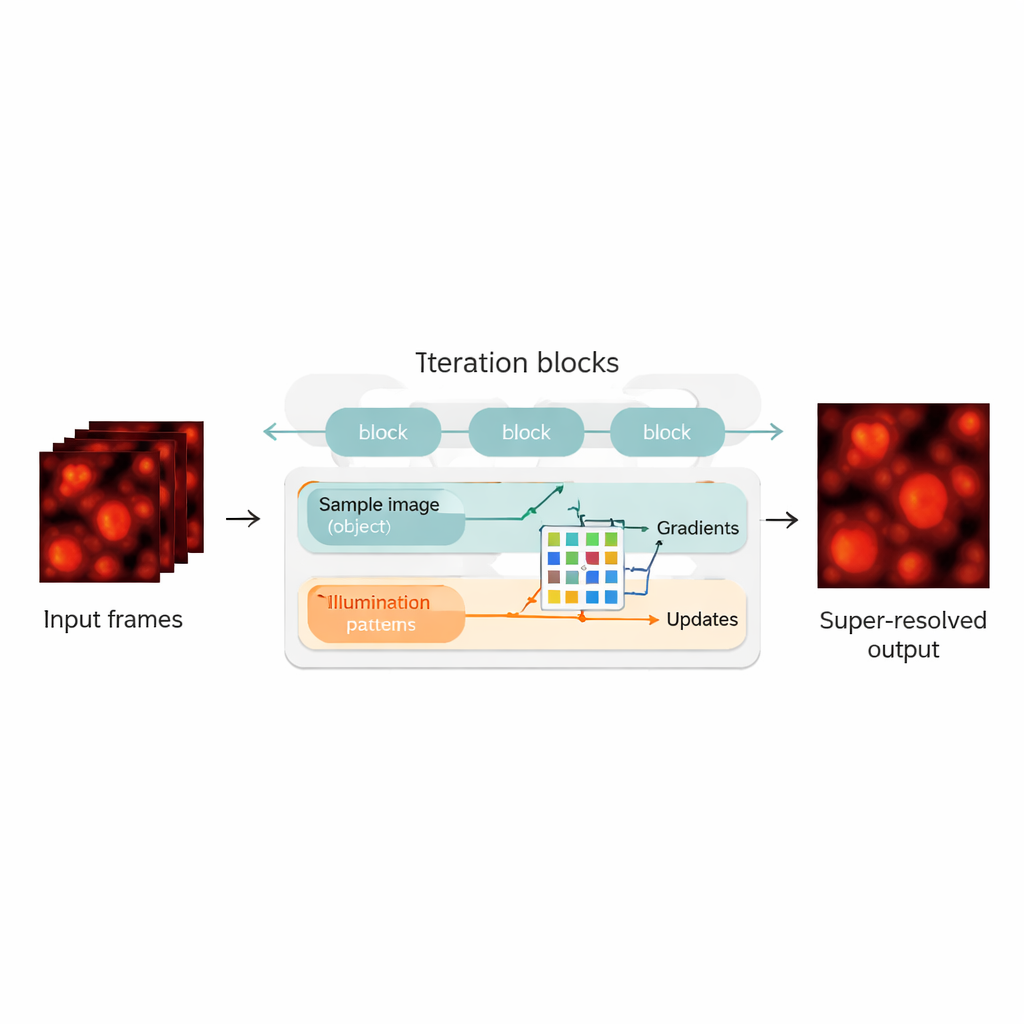
Сочетание физики и нейросетей
Авторы преодолевают этот разрыв, перерабатывая задачу восстановления слепого SIM как гибрид физической модели и нейронной сети. Они «разворачивают» исходный итеративный алгоритм — каждая итерация становится слоем в нейросети, формируя цепочку блоков обновления. Внутри каждого блока метод оценивает, насколько текущее предположение об образце и подсветке объясняет измеренные изображения, вычисляет градиенты (направления улучшения), а затем передаёт эти данные в компактную сверточную нейросеть. Эта сеть учится выполнять более умные шаги коррекции, выполняя роль автоматически настраиваемого ускорителя для исходного алгоритма. Важный момент: UBSIM обучается в несупервизируемом режиме — вместо необходимости в идеальных эталонных изображениях как опоре, требуется только физическая модель прохождения света через микроскоп. Это снижает риск того, что сеть «надумывает» правдоподобные, но неверные структуры.
Быстро, точно и с меньшим числом домыслов
Для проверки UBSIM команда сначала использовала смоделированные микроскопические изображения, где истинная структура известна. Они показали, что UBSIM восстанавливает примерно вдвое лучшее разрешение по сравнению с обычными широкополосными изображениями, сопоставимое со стандартным слепым SIM, но работает на две–три порядковые величины быстрее — изображение 256×256 можно реконструировать примерно за 10 миллисекунд вместо секунд. Метрики качества изображения, включая ошибку, сходство и отношение сигнал/шум, заметно улучшились по сравнению с обычными изображениями. UBSIM также оказался более надежным, чем популярные сети глубокого обучения для сверхразрешения при столкновении с незнакомыми данными. В то время как стандартные сети, обученные на одном типе структур, имели тенденцию «внедрять» эти шаблоны в новые образцы — внося тонкие, но вводящие в заблуждение артефакты — UBSIM сохранял согласованную достоверность, поскольку опирается на физику изображения, а не только на визуальные примеры.
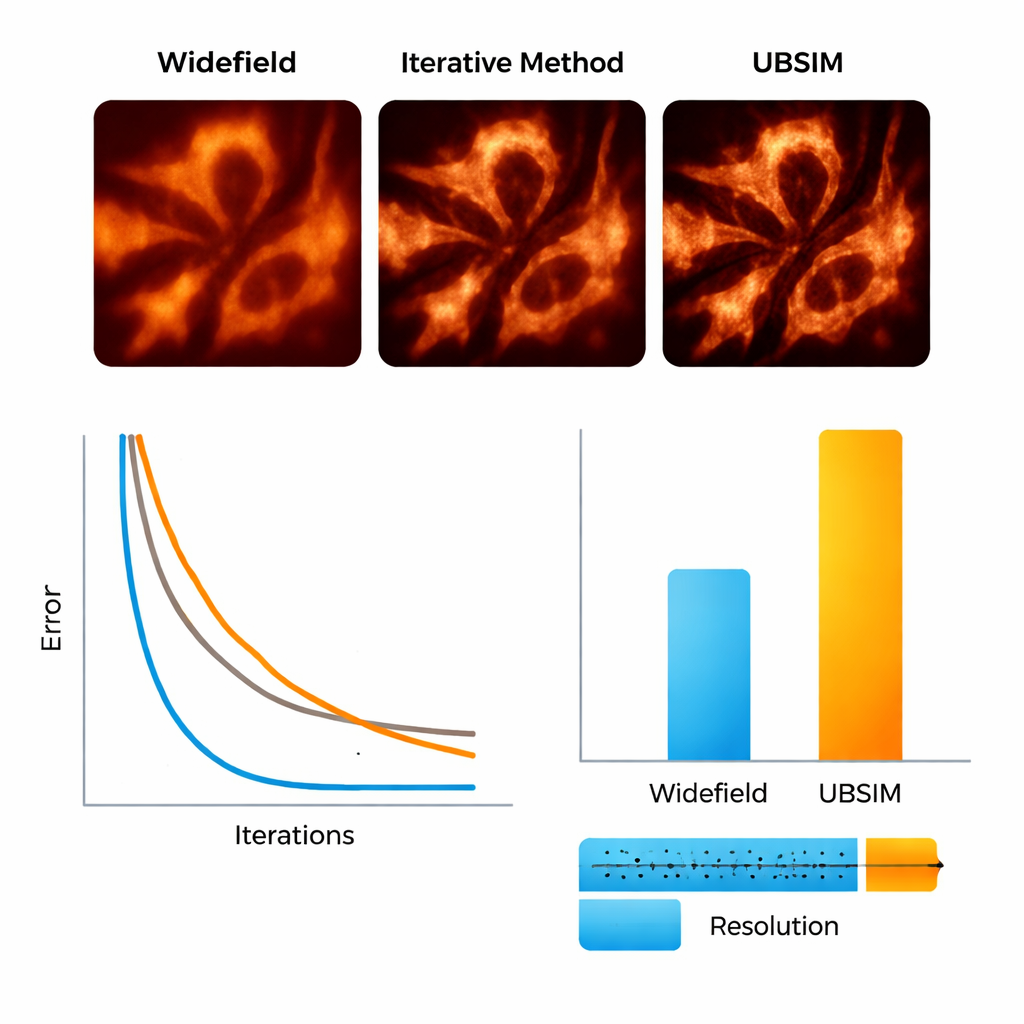
Наблюдение за скелетом и мембранами клетки в движении
Далее исследователи перешли к реальным биологическим образцам. С помощью гибкой установки, проецирующей случайные спекл‑узоры на живые клетки, они снимали актиновые филаменты — белковый «скелет» внутри клетки — и эндоплазматический ретикулум (ЭР), разветвленную сеть мембран, участвующую в синтезе белков и реакции на стресс. С UBSIM актиновые волокна, в обычных изображениях выглядевшие как размытые полосы, превратились в четко разделённые нити: разрешение улучшилось примерно с 300 нанометров до ~150 нанометров. Самое впечатляющее — UBSIM обеспечил сверхразрешение в режиме видео: при съёмке исходных данных до 100 кадров в секунду и реконструкции до 50 сверхразрешённых кадров в секунду команда могла наблюдать, как трубочки ЭР растут, коллапсируют и реорганизуются в реальном времени. Эти динамические процессы, происходящие за доли секунды — несколько секунд, обычно трудно визуализировать с достаточной детализацией.
Что это значит для будущей визуализации клеток
Для неспециалистов ключевой вывод таков: UBSIM делает гораздо более практичным наблюдение за движением крошечных клеточных структур в реальном времени с ясностью, превышающей обычные пределы световой микроскопии — и всё это без требования идеальной калибровки оборудования или огромных обучающих наборов данных. Комбинируя надёжность физических моделей с быстродействием современных нейросетей, подход превращает стопки шумных, узорно подсвеченных снимков в достоверные, ультра‑чёткие фильмы достаточно быстро для рутинных экспериментов. По мере дальнейшей доработки метода и сочетания с улучшенными стратегиями подсветки он может помочь исследователям изучать, как органеллы вроде ЭР реагируют на стресс, как клеточный «скелет» реорганизуется при движении или делении и как заболевания изменяют клеточную архитектуру на наноуровне.
Цитирование: Burns, Z., Zhao, J., Sahan, A.Z. et al. High-speed blind structured illumination microscopy via unsupervised algorithm unrolling. Nat Commun 17, 1967 (2026). https://doi.org/10.1038/s41467-026-68693-w
Ключевые слова: сверхразрешающая микроскопия, структурированное освещение, глубокое обучение, съемка живых клеток, динамика эндоплазматического ретикулума