Clear Sky Science · ru
Модель языкового уровня генома уменьшает артефакты химер в прямом РНК-секвенировании nanopore
Почему важно очищать РНК-риды
Клетки постоянно считывают генетические инструкции, записанные в РНК, а новые технологии секвенирования позволяют исследователям наблюдать этот процесс с беспрецедентной точностью. Один из самых мощных инструментов — nanopore прямое РНК-секвенирование — может считывать целые молекулы РНК за один проход, но при этом вносит сбои, которые создают впечатление, будто гены ломаются и сшиваются иначе, чем в реальной жизни. В этом исследовании представлен DeepChopper — программный инструмент, действующий как языковая модель для генома, который исправляет такие ошибки, чтобы учёным можно было доверять данным РНК.
Когда секвенатор придумывает фальшивые слияния генов
Современные nanopore-устройства протягивают отдельные РНК-цепочки через крошечные поры и считывают их последовательность напрямую. Это даёт большие преимущества по сравнению со старыми методами: сохраняются химические модификации и можно получить полные транскрипты в одном риде. Но процесс также требует коротких вспомогательных фрагментов — адаптеров, которые присоединяют к молекулам РНК при подготовке библиотеки. Иногда две или более молекул РНК случайно соединяются этими адаптерами, образуя кажущиеся химерными гибридные молекулы, похожие на слияния разных генов. Стандартные инструменты анализа могут ошибочно принять такие технические остатки за реальные биологические события — например, за хромосомные фьюжны, связанные с раком, или необычные варианты сплайсинга, — что приводит к вводящим в заблуждение выводам.
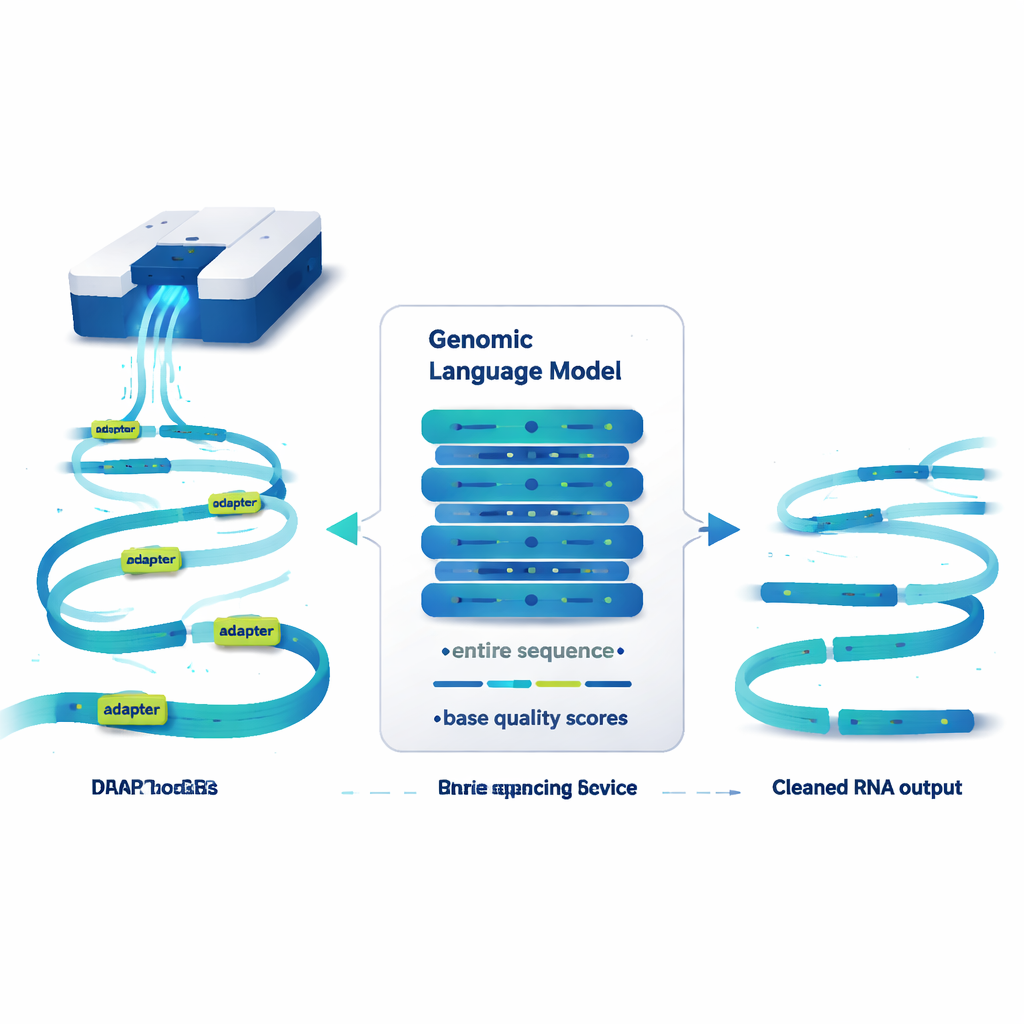
Языковая модель, которая «читает» геномы, а не предложения
DeepChopper рассматривает генетические последовательности немного как текст и применяет идеи из больших языковых моделей к ним. Вместо слов он читает рид РНК по одному символу и учитывает оценку качества для каждого символа, показывающую надёжность считывания. Построенный на компактной архитектуре HyenaDNA, он может просматривать до 32 000 нуклеотидов за раз — достаточно, чтобы охватить практически любую человеческую РНК-молекулу. Для каждой позиции DeepChopper оценивает, является ли нуклеотид частью истинного биологического сегмента или частью адаптера. Затем этап уточнения сглаживает эти прогнозы, чтобы адаптеры отмечались как непрерывные блоки, а не разрозненные отдельные точки.
Вырезая плохие соединения без потери данных
После того как DeepChopper находит адаптеры внутри рида, он делает важное: вместо удаления всего рида он «разрубает» его в местах адаптеров и сохраняет настоящие фрагменты. Таким образом искусственное слияние двух РНК можно разделить обратно на исходные части. В тестах на миллионах nanopore-ридов из нескольких линий человеческих раковых клеток и стволовых клеток DeepChopper значительно превзошёл существующие инструменты для обрезки адаптеров, которые изначально не были разработаны для прямого РНК-формата. На синтетических наборах данных он распознавал адаптеры с точностью и полнотой более 99% и эффективно масштабировался до наборов с более чем 20 миллионами ридов с использованием графических процессоров.
Отделение реальных слияний генов от иллюзий секвенирования
Авторы затем проверили, может ли DeepChopper отличать подлинные биологические события от артефактов в реальных онкологических данных. Сравнивая прямые РНК-риды с сопоставимыми наборами, полученными независимыми методами (например, прямым секвенированием кДНК на платформах Oxford Nanopore и PacBio), они маркировали, какие кажущиеся химеры подтверждаются другими технологиями, а какие — нет. DeepChopper уменьшил количество неподтверждённых химерных выравниваний на 62–91%, значительно обогатив долю событий, подтверждённых другими методами. Он также сократил число подозрительных вызовов слияний генов почти на 90%, особенно тех, что вовлекали рибосомальные гены и оказались частыми артефактами. При этом истинные события слияний, подтверждённые короткочтениями РНК-секвенирования, сохранялись.
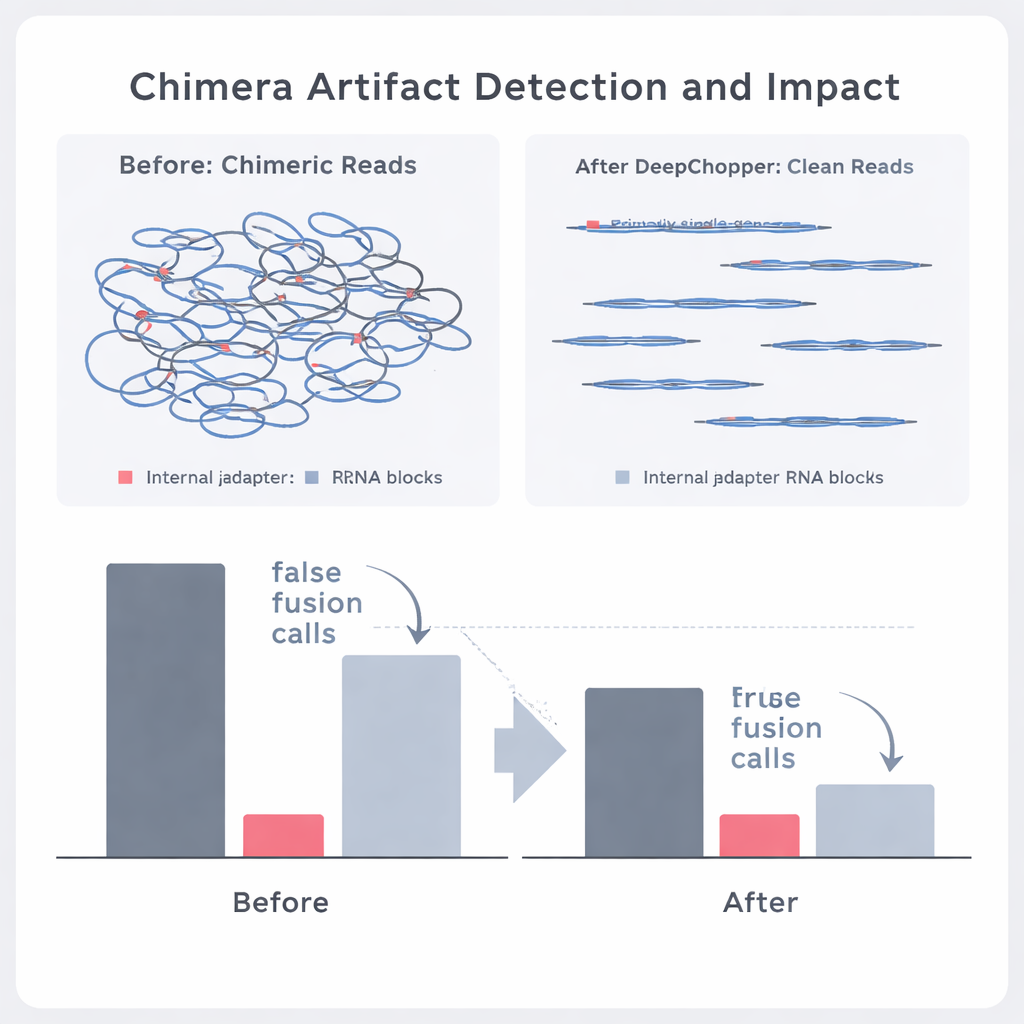
Лучшая химия помогает — но артефакты остаются
Oxford Nanopore недавно выпустила обновлённый набор для секвенирования (RNA004), частично рассчитанный на снижение технических артефактов. DeepChopper был применён «из коробки» к данным этой новой химии и по-прежнему обнаружил, что небольшая, но важная доля ридов содержит внутренние адаптеры и химерные соединения. Даже без дополнительного дообучения модель сократила число артефактных химер примерно на одну пятую; после тонкой настройки на новых данных её работа улучшилась, при этом настоящие сигналы оставались нетронутыми. Во всех химиях и типах клеток исправление этих артефактов позволило последующим инструментам обнаруживать значительно больше полноразмерных и альтернативных транскриптов, давая более ясную картину РНК-ландшафта клетки.
Что это значит для будущих исследований РНК
Для неспециалистов основной вывод таков: не каждое неожиданное соединение РНК, о котором сообщает секвенатор, является реальной биологией — часть из них вызвана ошибками, вносимыми самой технологией. DeepChopper действует как высококвалифицированный редактор для nanopore-данных РНК: он обнаруживает характерные последовательности адаптеров, соединяющие несвязанные молекулы, и вырезает их с точностью до одного нуклеотида. В результате получаются более чистые и надёжные карты того, какие молекулы РНК присутствуют в клетке и как они собраны. По мере того как лаборатории всё больше полагаются на секвенирование длинных ридов для изучения рака, заболеваний мозга и других сложных состояний, такие инструменты, как DeepChopper, станут необходимыми для преобразования шумных исходных ридов в достоверные биологические выводы.
Цитирование: Li, Y., Wang, TY., Guo, Q. et al. Genomic language model mitigates chimera artifacts in nanopore direct RNA sequencing. Nat Commun 17, 1864 (2026). https://doi.org/10.1038/s41467-026-68571-5
Ключевые слова: нанопоровое РНК-секвенирование, химерные риды, артефакты слияния генов, геномная языковая модель, DeepChopper