Clear Sky Science · pt
Expansão global ao longo de cinco décadas de Staphylococcus argenteus ST2250 molda a dinâmica da resistência antimicrobiana
Por que um microrganismo pouco conhecido importa
A maioria das pessoas já ouviu falar de “MRSA”, o Staphylococcus aureus resistente a drogas que assombra hospitais e manchetes. Muito menos conhecem seu parente próximo, Staphylococcus argenteus. Este estudo mostra que uma família particular de S. argenteus, chamada ST2250, se espalhou discretamente pelo mundo nas últimas 5 décadas enquanto acumulava um conjunto de genes de resistência a antibióticos. Compreender como isso ocorreu ajuda médicos e autoridades de saúde pública a se prepararem para a próxima onda de infecções de difícil tratamento.
Um novo agente problemático na família staph
S. argenteus só foi reconhecido como espécie própria em 2015, após anos sendo confundido em laboratório com S. aureus. Ainda assim, pode causar muitos dos mesmos problemas: intoxicação alimentar, infecções de pele e tecidos moles, infecções sanguíneas, doenças ósseas e articulares, além de infecções em animais e em produtos alimentares. Como testes rotineiros frequentemente o rotulam como S. aureus, seu impacto real provavelmente foi subestimado. Os autores reuniram 379 genomas de alta qualidade de S. argenteus de 28 países em seis continentes, majoritariamente de pacientes humanos, mas também de alimentos, animais e do ambiente, para analisar globalmente como essa espécie está evoluindo.
Um clone dominante circula pelo globo
Quando a equipe comparou o DNA de todos esses isolados, descobriu que S. argenteus é composto por várias linhagens distintas, cada uma correspondendo a um “tipo de sequência” genético específico. Uma delas, ST2250, dominou o conjunto de dados, representando mais da metade de todos os genomas. ST2250 foi encontrada em múltiplos continentes e em muitos tipos de amostras, desde pacientes hospitalizados até alimentos. Usando uma árvore evolutiva calibrada no tempo, os pesquisadores estimaram que o ancestral comum das cepas ST2250 atuais surgiu por volta de 1967. Desde então, seu tamanho efetivo de população — um indicador de quantas infecções e transmissões bem-sucedidas ocorrem — cresceu por décadas, atingindo o pico ao redor de 2012 antes de mostrar sinais de declínio recente.
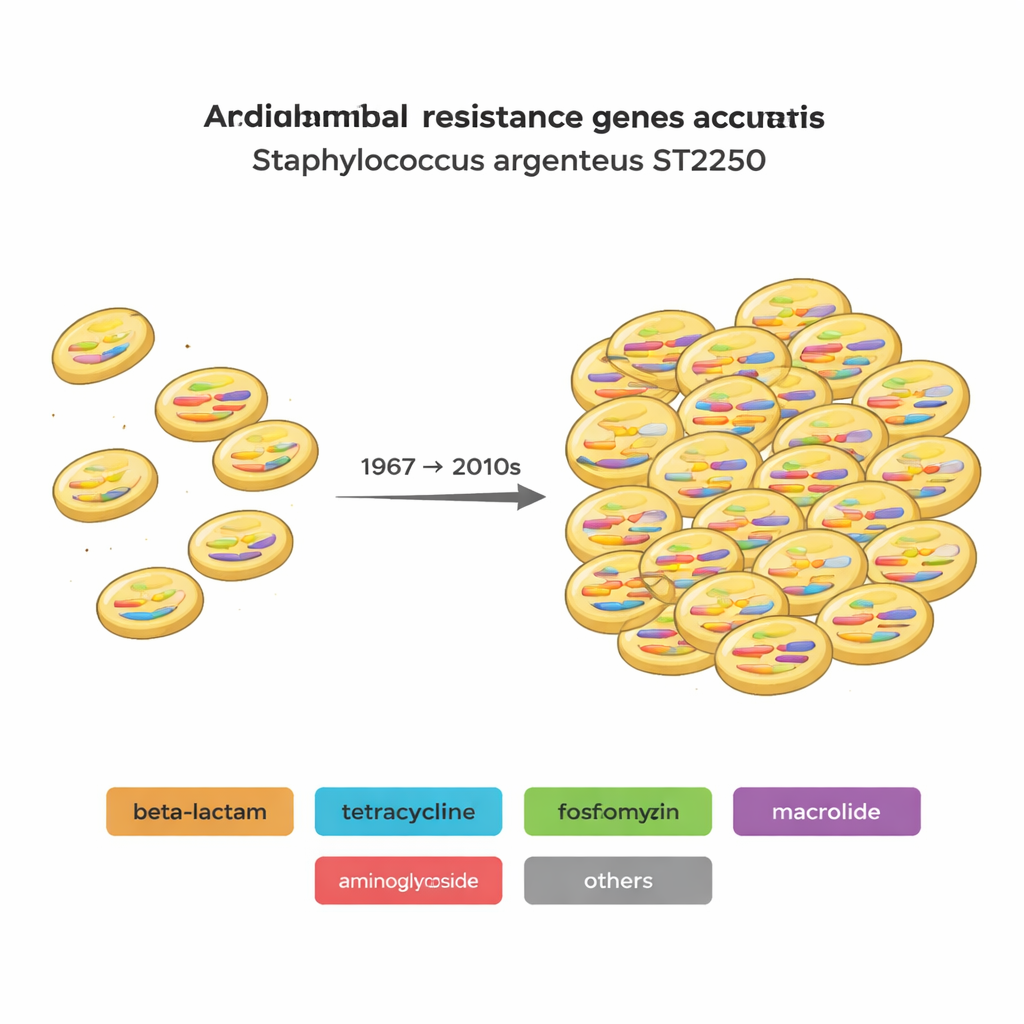
Carregada com ferramentas de resistência e virulência
O estudo catalogou genes que ajudam S. argenteus a causar doença (genes de virulência) e a resistir a antibióticos (genes de resistência antimicrobiana, ou RAM). Cada genoma carregava dezenas de genes de virulência, e as cepas ST2250 tinham apenas um pouco menos desses genes do que outras linhagens, sugerindo potencial semelhante de causar doença. A diferença maior residia na resistência. No conjunto de genomas, os autores identificaram 29 genes distintos de RAM cobrindo 12 classes de antibióticos e desinfetantes. As cepas ST2250 tipicamente carregavam mais genes de resistência que outros tipos e frequentemente compartilhavam as mesmas combinações. Muitas cepas ST2250 também apresentavam fosB, um gene que protege contra a fosfomicina, um antibiótico “antigo” que voltou a ser usado contra infecções staph difíceis. A parente próxima ST1850 também carregava fosB, sugerindo que esse gene pode ter estado presente no ancestral comum delas.
Como os traços de resistência viajam juntos
Os pesquisadores procuraram genes de resistência que tendem a aparecer juntos na mesma cepa com mais frequência do que o acaso esperaria. Encontraram pares fortes, como genes de resistência à tetraciclina (tetL) com resistência a aminoglicosídeos (aph(3')-IIIa), e resistência ao trimetoprim (dfrG) com resistência à meticilina (mecA). Esses aglomerados provavelmente refletem eventos passados em que vários genes foram adquiridos ao mesmo tempo em elementos de DNA móvel, como plasmídeos, e então transmitidos conforme as linhagens bacterianas se espalharam. De fato, a equipe detectou dezenas de tipos de “replicons” plasmidiais e mostrou que alguns plasmídeos coocorrem fortemente com genes de resistência específicos. Dentro de ST2250, surgiram duas sublinhagens principais: uma na Ásia e outra na Europa, cada uma marcada por seu próprio pacote característico de resistência e, na Europa, pela cassete de resistência à meticilina conhecida como SCCmec.
O que isso significa para o futuro
Para não especialistas, a mensagem principal é que S. argenteus não é uma curiosidade inofensiva, mas um membro em ascensão da família staph resistente a medicamentos. Ao longo de cerca de cinco décadas, uma única linhagem bem-sucedida, ST2250, espalhou-se amplamente e acumulou uma combinação rica de genes de resistência, criando condições em que cepas multirresistentes podem emergir com facilidade. Embora haja indícios iniciais de que o crescimento de ST2250 possa estar desacelerando, outras linhagens com seus próprios traços de resistência aguardam nos bastidores. Os autores defendem que a detecção mais precisa de S. argenteus, amostragens mais amplas além dos hospitais e vigilância genética próxima serão essenciais para impedir que esse patógeno silencioso se torne a próxima grande ameaça staph.
Citação: Costa, L.R.M., Marmion, M., Buiatte, A.B.G. et al. Five-decade global expansion of Staphylococcus argenteus ST2250 shapes antimicrobial resistance dynamics. npj Antimicrob Resist 4, 14 (2026). https://doi.org/10.1038/s44259-026-00188-6
Palavras-chave: Staphylococcus argenteus, resistência antimicrobiana, epidemiologia genômica, clone ST2250, bactérias resistentes a medicamentos