Clear Sky Science · pt
Paisagem genômica da resistência antimicrobiana na Índia: achados de um estudo de vigilância multiespécie
Por que os supermicróbios na Índia interessam a todos nós
Os “supermicróbios” resistentes a antibióticos são uma preocupação global crescente, mas ainda sabemos surpreendentemente pouco sobre como esses germes evoluem e se espalham em muitas regiões do mundo. Este estudo examina de perto bactérias perigosas de hospitais na Índia e lê seu DNA completo para entender como elas driblam nossas drogas mais potentes. Os resultados não apenas revelam o que torna esses microrganismos tão difíceis de eliminar, como também testam se métodos rápidos baseados em DNA podem substituir de forma confiável os testes laboratoriais mais lentos — uma questão que pode influenciar o tratamento de infecções em qualquer lugar.
Uma investigação mais próxima das infecções hospitalares
Pesquisadores coletaram 266 amostras bacterianas de pacientes gravemente doentes em grandes hospitais do norte e do oeste da Índia entre 2022 e 2024. A maioria das amostras veio de sangue, mas também havia material de urina e de infecções pulmonares, e a maior parte foi obtida em unidades de terapia intensiva, onde os pacientes são mais vulneráveis. A equipe concentrou-se em microrganismos problemáticos bem conhecidos — como Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, Staphylococcus aureus resistente à meticilina (MRSA) e Enterococcus resistente à vancomicina (VRE). Para cada amostra, os médicos já haviam realizado testes padrão de suscetibilidade a antibióticos, que expõem as bactérias aos fármacos em laboratório para ver quais remédios ainda funcionam. Em seguida, os cientistas sequenciaram os genomas das bactérias para mapear o conjunto completo de genes de resistência e compararam o que o DNA “previu” com o que realmente ocorreu nos tubos de ensaio.
Quando genes e tubos de ensaio discordam
Ao confrontar previsões genéticas com resultados laboratoriais para 56 antibióticos diferentes, o estudo realizou mais de 5.000 comparações. Na maioria dos casos, o método baseado em DNA e os testes tradicionais concordaram, mas quase 600 divergências chamaram atenção. O tipo de erro mais comum foi a ferramenta genômica prever que uma bactéria seria resistente quando o teste de laboratório indicou que ainda era tratável. Isso ocorreu com frequência para drogas como minociclina, colistina e gentamicina, especialmente em E. coli. O erro oposto — em que o laboratório detectou resistência mas os genes não a explicaram claramente — foi menos frequente porém mais preocupante, porque implica o risco de resistência não identificada. Essas discrepâncias “muito graves” apareceram de forma notável em bactérias intestinais chamadas enterococos, particularmente para antibióticos do tipo penicilina e para a combinação trimetoprim‑sulfametoxazol.
Arsenal oculto dentro do DNA bacteriano
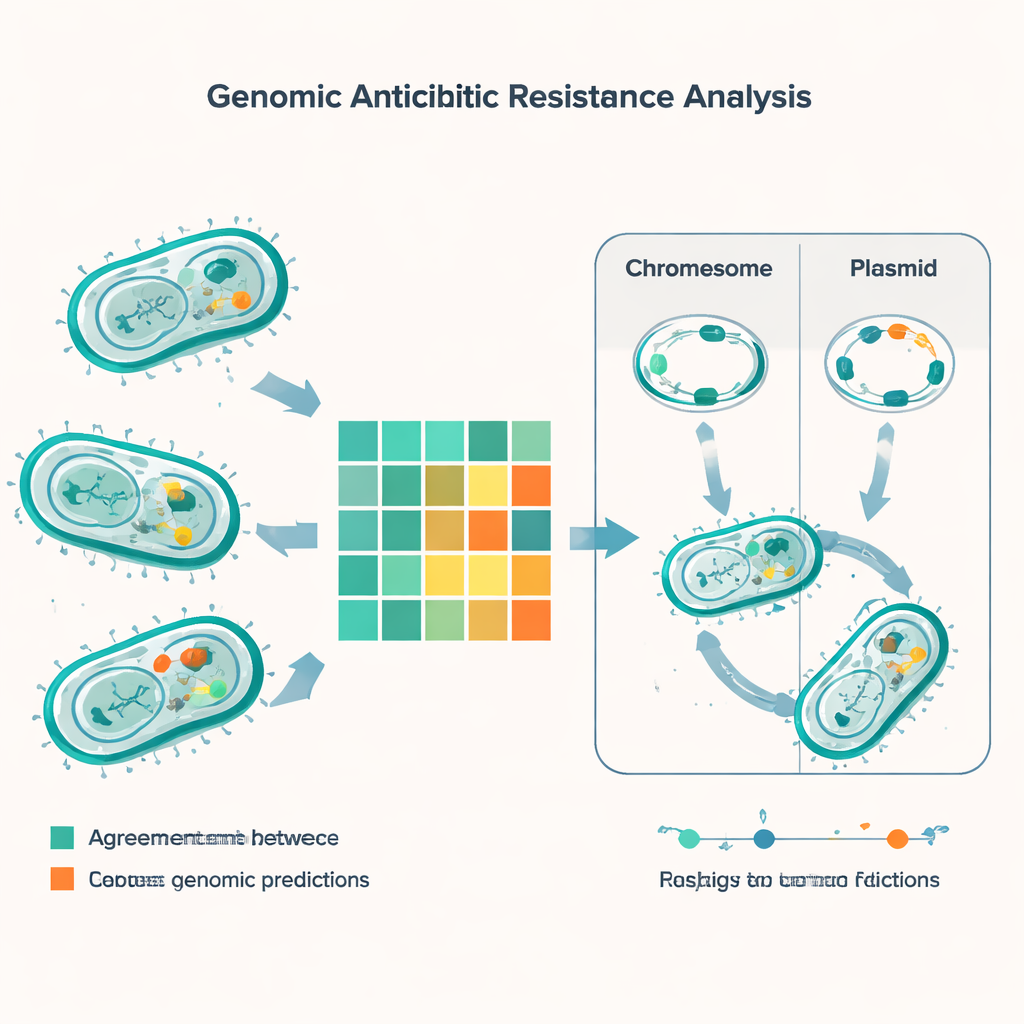
O levantamento genômico revelou um arsenal denso de genes de resistência entre as principais espécies. Cada um dos patógenos Gram‑negativos comuns carregava ao menos um gene beta‑lactamase, capaz de degradar penicilinas e drogas relacionadas, e muitas cepas apresentavam vários desses genes simultaneamente. Vilões notórios como carbapenemases do tipo NDM — que neutralizam antibióticos de último recurso — eram disseminados em E. coli, Klebsiella, Acinetobacter e Pseudomonas. O estudo também encontrou genes que ajudam as bactérias a sobreviver a poderosos antibióticos “peptídicos” como a colistina, além do clássico gene mecA, que torna o MRSA resistente à meticilina, e clusters de resistência à vancomicina em enterococos. Ao comparar perfis de DNA chamados tipos de sequência, a equipe associou alguns desses genes de resistência a linhagens bacterianas de alto risco conhecidas por já se espalharem na Índia e no mundo.
Compartilhamento de genes via DNA móvel
Uma parte crucial da história não está apenas em quais genes as bactérias carregam, mas onde esses genes residem. Muitos genes de resistência estão em pequenos círculos de DNA chamados plasmídeos, que as bactérias podem trocar como cartas colecionáveis. Usando software especializado, os pesquisadores previram cerca de 1.400 plasmídeos nas amostras, com diversidade especialmente alta em E. coli e Klebsiella. Nessas espécies, uma grande parcela dos genes de resistência — incluindo várias beta‑lactamases críticas — era plasmidial, tornando‑os mais fáceis de transferir entre cepas e até entre espécies. Outros traços de resistência estavam incorporados nos cromossomos bacterianos, o que significa que podem persistir mesmo se os plasmídeos forem perdidos. A equipe também catalogou elementos genéticos móveis — segmentos curtos de DNA que podem saltar de lugar e carregar genes de resistência consigo — destacando mais uma via para disseminação rápida.
O que isso significa para tratamentos futuros
Para não especialistas, a mensagem central é que ler o DNA bacteriano pode ajudar muito na luta contra os supermicróbios, mas a tecnologia ainda não é perfeita. As ferramentas genômicas tenderam a “superestimar” resistência, o que é mais seguro do que deixar passar uma cepa perigosa, mas pode levar os médicos a usar drogas mais fortes do que o necessário. Ao mesmo tempo, um número menor de casos mostrou que os testes laboratoriais detectaram resistência que os catálogos genéticos atuais não conseguiram explicar totalmente, ressaltando lacunas importantes em nosso conhecimento. Ao construir um mapa detalhado de genes de resistência, plasmídeos e elementos móveis em hospitais indianos, este estudo cria uma base para diagnósticos baseados em DNA melhores e mais rápidos e para um uso de antibióticos mais informado — não apenas na Índia, mas em qualquer cenário onde os supermicróbios ameacem a medicina moderna.
Citação: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Palavras-chave: resistência antimicrobiana, sequenciamento genômico, infecções hospitalares, bactérias multirresistentes, resistência mediada por plasmídeo