Clear Sky Science · pt
Análise da expressão gênica do hospedeiro na detecção da etiologia bacteriana e viral em crianças hospitalizadas com suspeita de infecção grave
Por que esta pesquisa importa para crianças com infecções graves
Quando uma criança chega ao hospital com febre alta e aspecto muito doente, os médicos precisam decidir rapidamente se a causa é uma infecção bacteriana, que geralmente requer antibiótico, ou uma infecção viral, que frequentemente se resolve sozinha. Os testes disponíveis hoje estão longe de ser perfeitos, e muitas crianças recebem antibióticos “por precaução”. Este estudo investigou se ler os sinais do próprio corpo no sangue — especificamente, padrões de atividade gênica — pode distinguir com mais precisão infecções bacterianas de virais em crianças com suspeita de doença grave.
Olhando para o sistema de alarme do corpo em vez do microrganismo
Os testes tradicionais tentam encontrar o microrganismo diretamente, por exemplo cultivando bactérias a partir do sangue ou detectando material genético viral por PCR. Essas abordagens podem ser lentas, podem não identificar o verdadeiro causador e frequentemente detectam vírus “coadjuvantes” sem importância clínica, especialmente em crianças pequenas que costumam portar vírus respiratórios. Os pesquisadores, em vez disso, focaram na resposta do hospedeiro: quais genes nas células sanguíneas da criança são ativados ou desativados durante a infecção. Como o sistema imune reage de maneira diferente a bactérias e vírus, o padrão de genes ativos pode funcionar como uma impressão digital do tipo de infecção, mesmo quando é difícil encontrar ou interpretar o microrganismo.
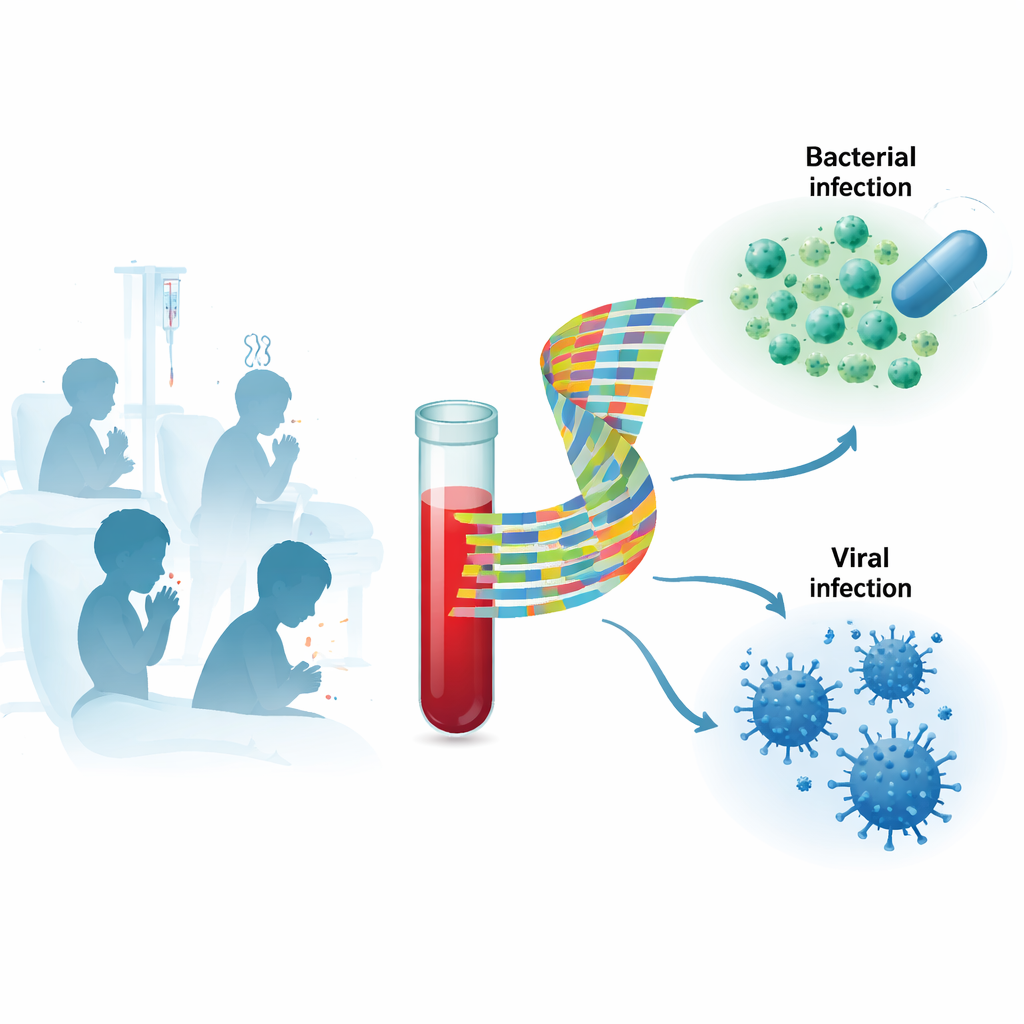
Estudando uma mistura real de crianças doentes
A equipe recrutou 268 crianças de 4 semanas a 16 anos na Finlândia. A maioria estava hospitalizada com suspeita de infecção grave; um grupo menor tinha infecções virais confirmadas e mais leves tratadas em ambulatório, e alguns eram controles saudáveis. Os médicos coletaram dados clínicos detalhados, exames laboratoriais padrão como proteína C-reativa e procalcitonina, e swabs nasais para vírus respiratórios. Amostras de sangue foram usadas para medir a atividade de milhares de genes por sequenciamento de RNA. A doença de cada criança foi cuidadosamente classificada como bacteriana, viral, mista bacteriana–viral, indeterminada ou não infecciosa, e depois também agrupada de forma mais simples como “bacteriana” ou “viral” para as análises principais.
Encontrando um sinal simples de dois genes
Quando os cientistas analisaram amplamente a atividade gênica no sangue de todas as crianças, observaram que as amostras se agrupavam em vários clusters, mas esses clusters não correspondiam de forma clara aos rótulos “bacteriana” versus “viral”. Crianças saudáveis eram nitidamente diferentes daquelas com infecções bacterianas definidas, enquanto os padrões gênicos em infecções virais definidas eram mais variados. Para lidar com essa complexidade, os pesquisadores dividiram os pacientes em dois conjuntos: um grupo de descoberta com crianças com infecções respiratórias e um grupo de validação com outros tipos de infecções, como renais ou cutâneas. No grupo de descoberta, procuraram combinações muito pequenas de genes que pudessem distinguir melhor doença bacteriana de viral e depois testaram o desempenho dessas mesmas combinações no grupo de validação.
Identificaram um par de genes particularmente promissor, chamados TSPO e SECISBP2. Em conjunto, os níveis de atividade desses dois genes conseguiam separar infecções bacterianas (incluindo mistas bacteriana–viral) de infecções puramente virais com alta acurácia. Medido pela área sob a curva ROC, esse sinal de dois genes atingiu 0,93 no conjunto de descoberta e 0,81 no conjunto de validação; em ambos os grupos combinados foi 0,87, com sensibilidade em torno de 77% e especificidade em torno de 87%. Em outras palavras, o sinal identificou corretamente a maioria dos casos bacterianos enquanto raramente rotulava infecções virais como bacterianas. Também teve desempenho superior a marcadores sanguíneos amplamente usados, como proteína C-reativa e procalcitonina, nesta população do estudo.

O que esses dois genes podem estar fazendo
TSPO está envolvido em como as mitocôndrias — as usinas de energia da célula — lidam com estresse e ajudam a controlar a inflamação. Trabalhos anteriores associaram maior atividade de TSPO a infecções bacterianas mais graves e sepse, e experimentos sugerem que estimular células imunes com componentes bacterianos pode aumentar TSPO e favorecer a liberação de moléculas inflamatórias que ajudam a matar microrganismos. Neste estudo, TSPO tendia a estar mais ativo em infecções bacterianas e menos ativo em infecções virais. SECISBP2, por sua vez, ajuda o corpo a produzir proteínas que contêm selênio e que possuem funções antioxidantes, imunes e antivirais. Sabe-se que o selênio apoia células imunes e reduz a gravidade de algumas doenças virais. Aqui, a atividade de SECISBP2 foi geralmente mais alta em infecções virais, coerente com a ideia de que o organismo aumenta as defesas relacionadas ao selênio ao combater vírus.
O que isso pode significar para o cuidado futuro
Os autores enfatizam que suas descobertas são iniciais, mas animadoras. Um teste simples que leia apenas esses dois genes a partir de uma pequena amostra de sangue poderia, no futuro, ajudar equipes de emergência a decidir com mais confiança se uma criança muito doente precisa de antibióticos. Como o sinal de dois genes funcionou não só em infecções pulmonares, mas também em outras infecções graves, pode ser útil em uma ampla gama de casos do mundo real, incluindo aqueles em que microrganismos bacterianos e virais são detectados juntos. Contudo, o estudo foi realizado em um único país e se apoiou nas melhores, porém imperfeitas, definições disponíveis de doença bacteriana versus viral. Serão necessários estudos maiores em hospitais diversos e versões rápidas e adequadas para a clínica antes que isso possa orientar decisões cotidianas. Ainda assim, este trabalho mostra que a própria atividade gênica do hospedeiro pode conter a chave para uso mais inteligente de antibióticos e melhor cuidado de crianças com infecções graves.
Citação: Piri, R., Valta, M., Lempainen, J. et al. Host gene expression analysis in the detection of bacterial and viral etiology in children hospitalized with a suspected severe infection. Commun Med 6, 204 (2026). https://doi.org/10.1038/s43856-025-01370-z
Palavras-chave: infecções pediátricas, expressão gênica, bacteriana versus viral, uso racional de antibióticos, diagnósticos da resposta do hospedeiro