Clear Sky Science · pt
Previsão e interpretação das respostas a medicamentos específicas por tipo celular no regime de poucos dados usando priors indutivos
Por que esta pesquisa importa para os medicamentos do futuro
Quando um novo medicamento é testado, uma das maiores incógnitas é com que intensidade ele afetará os muitos tipos de células do nosso corpo. Um composto que ajuda um tipo celular pode ter pouco efeito em outro ou até causar dano. Gerar essas informações experimentalmente para milhares de medicamentos e inúmeros tipos celulares é lento e caro demais. Este artigo apresenta uma abordagem computacional, chamada PrePR-CT, que aprende a prever como tipos celulares individuais respondem a medicamentos, mesmo quando há apenas dados limitados disponíveis. O trabalho aponta caminhos para formas mais rápidas, baratas e precisas de explorar potenciais fármacos in silico antes de investir em caros estudos de laboratório e clínicos.
Olhando dentro das células em vez de apenas nos medicamentos
Triagens tradicionais de medicamentos frequentemente tratam as células como se fossem todas iguais e se concentram principalmente em médias globais. Na realidade, células imunes, hepáticas e cancerígenas podem reagir de maneiras muito diferentes ao mesmo composto. Os autores argumentam que, para prever essas diferenças, um modelo precisa entender a fiação interna de cada tipo celular: quais genes tendem a ser ativos em conjunto e como esses padrões definem a identidade da célula. Eles constroem “mapas” por tipo celular examinando quais genes em células não perturbadas (controle) sobem e descem em conjunto. Cada mapa é representado como uma rede, onde nós correspondem a genes e links refletem co-atividades fortes. Essas redes servem como conhecimento prévio sobre como um dado tipo celular é organizado antes de qualquer droga ser adicionada.
Um motor de aprendizado sensível a redes
PrePR-CT combina três ingredientes: a rede de atividade gênica de um tipo celular, a expressão gênica basal desse tipo celular e uma descrição compacta da estrutura química do medicamento. O modelo usa uma classe de redes neurais projetadas para grafos para digerir a rede gênica da célula e extrair um resumo que captura seus padrões característicos. Em paralelo, converte cada droga em uma assinatura numérica derivada de sua estrutura molecular. Essas peças são alimentadas em um módulo preditivo que aprende, a partir dos experimentos disponíveis, como um dado medicamento deslocará a distribuição de atividade gênica nesse tipo celular. Em vez de produzir um único número por gene, o método estima tanto a mudança média quanto quão variável é a resposta entre células individuais, o que é crucial para entender efeitos sutis e intensos igualmente.
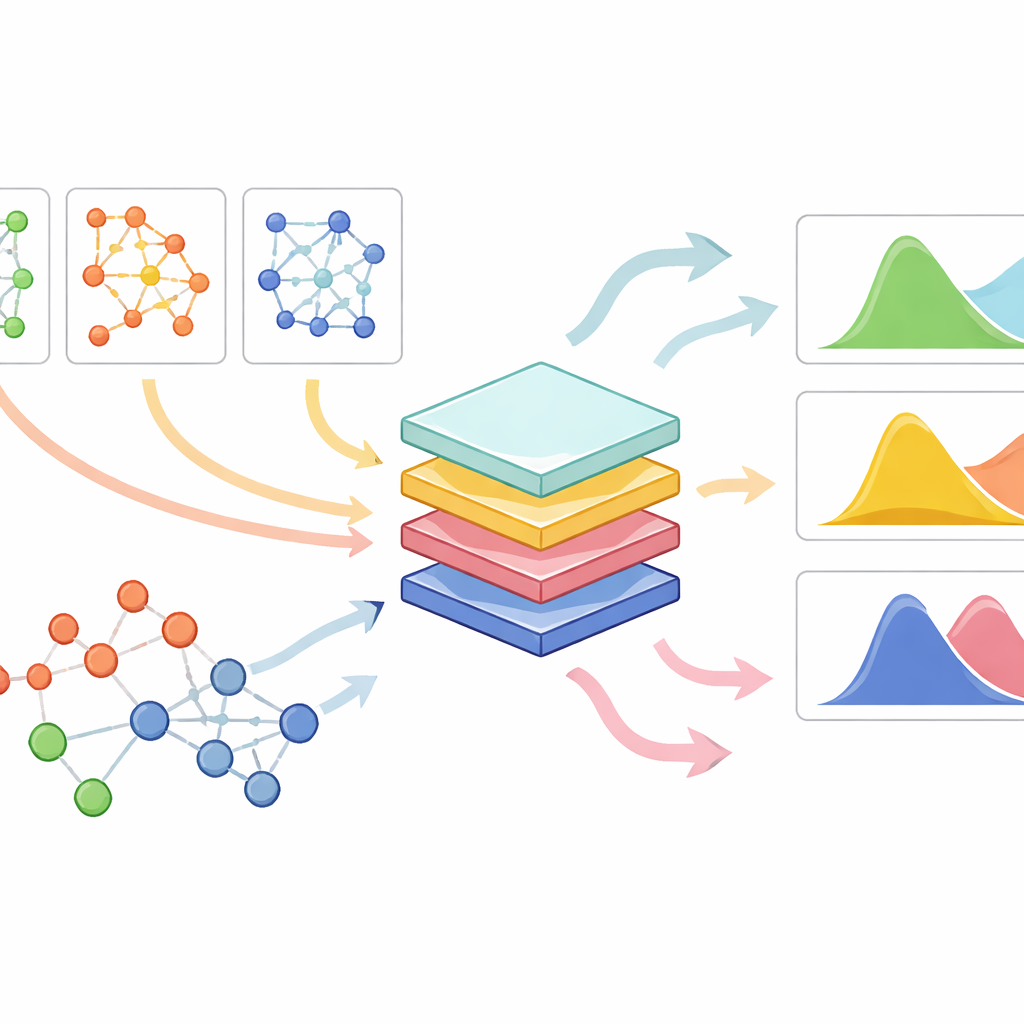
Funciona em muitos tipos celulares, medicamentos e com conjuntos de dados pequenos
Os pesquisadores testaram o PrePR-CT em uma ampla coleção de conjuntos de dados, incluindo células sanguíneas humanas expostas a sinais imunes, várias linhas celulares de câncer tratadas com diversos compostos, células hepáticas de camundongo expostas a um poluente e triagens de medicamentos em larga escala de recursos públicos. Em cenários desafiadores onde um tipo celular inteiro foi deixado de fora durante o treinamento, o modelo ainda conseguiu prever como esse novo tipo celular responderia a um medicamento conhecido, muitas vezes com precisão superior à de modelos generativos anteriores. Da mesma forma, quando um medicamento novo, mas um tipo celular familiar, foi excluído, o método antecipou seu impacto usando apenas sua assinatura química. Importante, o modelo permaneceu eficaz quando treinado com números relativamente pequenos de células, uma situação em que muitas abordagens de aprendizado profundo apresentam dificuldades.
De caixa-preta a pistas sobre mecanismo
Além da predição bruta, os autores queriam saber se seu modelo poderia oferecer insights sobre quais genes e vias impulsionam a resposta de uma célula. A arquitetura baseada em grafos inclui um mecanismo de atenção que destaca genes que o modelo considera especialmente influentes em cada tipo celular. Muitos desses genes de “alta atenção” não eram os suspeitos usuais sinalizados pela análise padrão de expressão diferencial, ainda assim eles se agruparam em vias relacionadas ao sistema imune, coerentes com a biologia dos medicamentos testados. Quando os pesquisadores deliberadamente prejudicaram esses genes influentes na entrada do modelo, a qualidade da predição caiu, especialmente para os genes mais responsivos, sugerindo que as pontuações de atenção apontam para participantes mecanísticos significativos em vez de ruído.
O que isso significa para desenhar medicamentos melhores
Em termos simples, este trabalho mostra que dar aos modelos de inteligência artificial uma visão estruturada de como cada tipo celular é conectado—sua rede gênica interna—melhora muito sua capacidade de prever como os medicamentos irão remodelar essas células, mesmo quando há apenas dados modestos disponíveis. PrePR-CT não substitui experimentos, mas pode ajudar a reduzir quais compostos e tipos celulares valem ser testados e indicar por que certas células reagem como reagem. À medida que os conjuntos de dados crescem e recursos celulares adicionais são incorporados, tais abordagens podem se tornar ferramentas-chave para adaptar terapias a tecidos ou tipos celulares de pacientes específicos, reduzindo tentativa e erro no laboratório e aproximando medicamentos mais precisos da realidade.
Citação: Alsulami, R., Lehmann, R., Khan, S.A. et al. Predicting and interpreting cell-type-specific drug responses in the small-data regime using inductive priors. Nat Mach Intell 8, 461–473 (2026). https://doi.org/10.1038/s42256-026-01202-2
Palavras-chave: previsão de resposta a medicamentos, transcritômica de célula única, redes neurais gráficas, descoberta de medicamentos, especificidade por tipo celular