Clear Sky Science · pt
Relatório de Reutilização: Avaliando o desempenho de um modelo base de meta-aprendizagem na predição da atividade antibacteriana de produtos naturais
Procurando Novos Antibióticos, Mais Rápido
A resistência a antibióticos está aumentando, mas descobrir novos fármacos é um processo dolorosamente lento e frequentemente depende de tentativa e erro no laboratório. Este estudo investiga se um tipo poderoso de inteligência artificial, originalmente treinado em grandes coleções de dados sobre fármacos, pode ser rapidamente adaptado para prever quais compostos naturais derivados de plantas podem combater bactérias — usando apenas pequenas quantidades de novos dados experimentais. Se eficazes, essas ferramentas poderiam ajudar cientistas a concentrar o tempo de bancada nos candidatos mais promissores e acelerar a busca pela próxima geração de antibióticos.
Por que os Compostos Vegetais Importam
Muitos dos nossos melhores antibióticos começaram como produtos naturais de plantas e microrganismos. Essas moléculas podem impedir o crescimento bacteriano, mas encontrar novas na natureza é como procurar agulhas num palheiro. Pesquisadores precisam testar muitos compostos contra várias cepas bacterianas, e cada ensaio é caro. Pior ainda, grandes conjuntos de dados cuidadosamente rotulados — que os métodos modernos de aprendizado profundo exigem para um bom desempenho — são raros nessa área. Isso torna a descoberta de antibióticos um campo ideal para testar “modelos base”: sistemas de IA grandes e de uso geral que podem ser ajustados para tarefas específicas com apenas alguns exemplos novos.
Um Modelo Base Aprende sobre Agentes que Matam Germes
A equipe concentrou-se em um modelo base chamado ActFound, originalmente treinado para prever quão fortemente diferentes produtos químicos afetam alvos biológicos, usando conjuntos de dados extensos de recursos como as bases ChEMBL e BindingDB. Em vez de prever um único número para cada composto, o ActFound aprende comparando pares de compostos dentro do mesmo experimento e estimando qual é mais ativo. Esse aprendizado “por pares”, combinado com uma estratégia de treinamento conhecida como meta-aprendizagem, foi projetado para ajudar o modelo a se adaptar rapidamente a novas tarefas de predição quando apenas um pequeno número de exemplos rotulados está disponível — exatamente a situação em muitos ensaios de antibióticos.
Testando o Modelo em Dados Reais de Produtos Vegetais
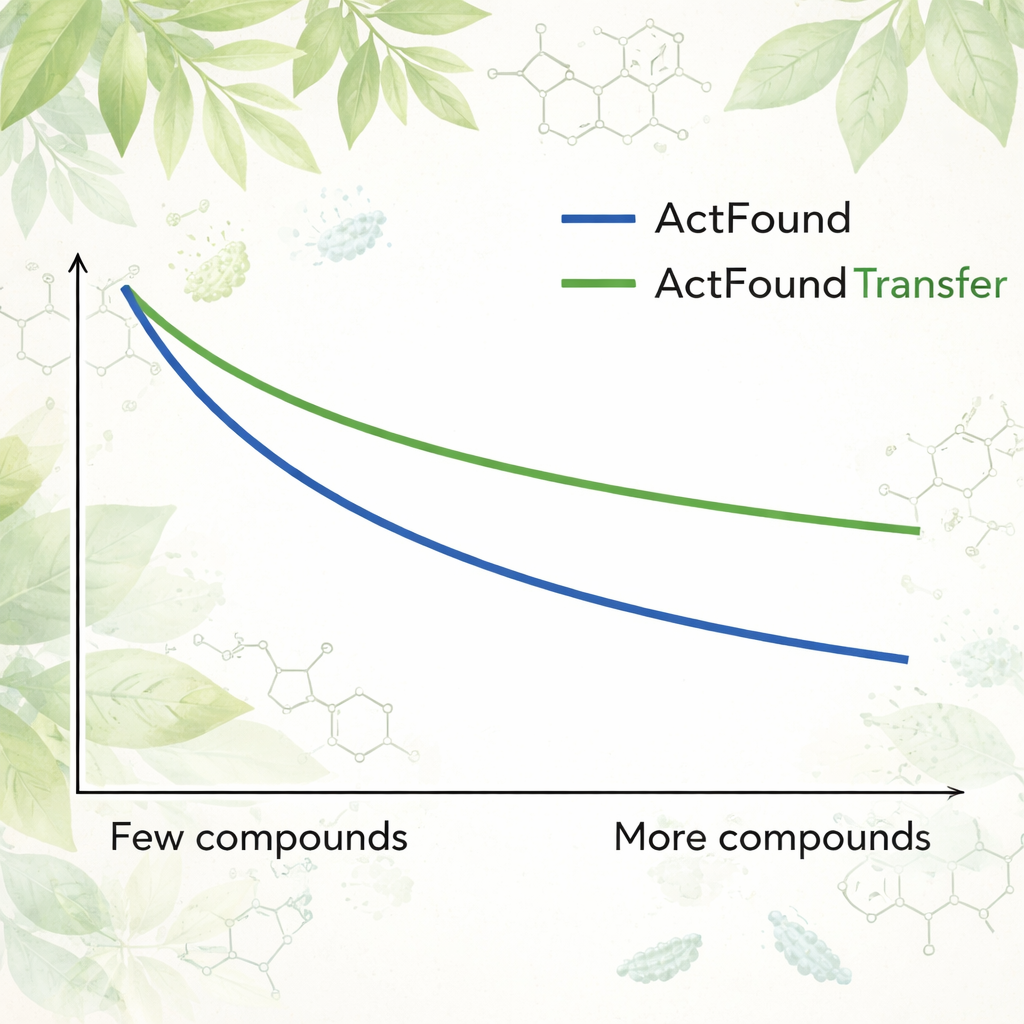
Para avaliar quão reutilizável o ActFound realmente é, os autores o ajustaram em um conjunto de dados curado de produtos naturais derivados de plantas testados quanto à capacidade de inibir o crescimento de várias bactérias. Cada cepa bacteriana foi tratada como sua própria tarefa, e o modelo foi adaptado usando apenas de 8 a 128 compostos por cepa, ou porcentagens fixas dos dados disponíveis. Eles também compararam o ActFound com modelos mais simples de meta-aprendizagem e de transferência de aprendizado que não usam comparações por pares. Nesses testes, o ActFound não alcançou a precisão obtida em trabalhos anteriores com outros tipos de dados de fármacos. No entanto, quando havia pouquíssimos dados — aproximadamente apenas alguns compostos por cepa — o ActFound e sua variante de transferência de aprendizado geralmente igualaram ou superaram métodos alternativos.
Quando a Semelhança Ajuda — e Quando Atrapalha
O ActFound parte do princípio de que moléculas semelhantes se comportam de forma semelhante, o que funciona bem quando os conjuntos de dados são organizados em torno de grupos de químicos relacionados. O conjunto de produtos naturais, contudo, era quimicamente diverso e frequentemente carecia de “famílias” de compostos intimamente relacionadas. Essa diversidade, embora valiosa cientificamente, comprometeu a estratégia de aprendizado por pares: quando os compostos dentro de um experimento são muito diferentes entre si, o modelo tem dificuldade em aprender comparações estáveis. Os autores também descobriram que um diagnóstico simples, proposto no artigo original do ActFound para prever antecipadamente quão bem o modelo se sairia em uma nova tarefa, não se manteve para esses dados de produtos naturais, destacando uma limitação importante ao transitar para novos espaços químicos.
O Que Isso Significa para a Descoberta de Medicamentos
Para não especialistas, a conclusão é que modelos base como o ActFound são ferramentas promissoras para descoberta de fármacos quando os dados são escassos, mas não são soluções milagrosas. Neste estudo, o ActFound e sua versão de transferência de aprendizado frequentemente tiveram desempenho igual ou superior ao de métodos concorrentes quando apenas alguns compostos vegetais estavam disponíveis para treinamento, embora tenham encontrado dificuldades nesse conjunto altamente diverso de produtos naturais. O trabalho sugere que esses modelos de IA são mais úteis quando os dados incluem muitos compostos quimicamente semelhantes — como em estudos focados em relações estrutura–atividade —, mas continuam menos confiáveis para prever o comportamento de tipos inteiramente novos de moléculas. Em outras palavras, a IA pode ajudar a estreitar a busca, mas a parte mais difícil de explorar territórios químicos verdadeiramente novos ainda está por vir.
Citação: Butt, C.M., Walker, A.S. Reusability Report: Evaluating the performance of a meta-learning foundation model on predicting the antibacterial activity of natural products. Nat Mach Intell 8, 270–275 (2026). https://doi.org/10.1038/s42256-026-01187-y
Palavras-chave: descoberta de antibióticos, produtos naturais, aprendizado profundo, meta-aprendizagem, triagem de medicamentos