Clear Sky Science · pt
Mineração de enzimas baseada em inferência de ortólogos para diversificação do esqueleto anticâncer evodiamina
Transformando químicos de plantas em medicamentos melhores
Muitos dos medicamentos atuais começaram sua existência como compostos defensivos em plantas. Essas moléculas naturais frequentemente exibem efeitos potentes contra câncer, infecções ou dor, mas raramente são “drogas perfeitas”. Químicos gostariam de ajustar suas estruturas de forma precisa para torná‑las mais seguras e eficazes, porém essas moléculas costumam ser tão complexas que mesmo pequenas mudanças são difíceis. Este estudo mostra como cientistas podem recorrer a enzimas vegetais como miniferramentas moleculares para realizar alterações direcionadas em um composto anticâncer chamado evodiamina, abrindo potencialmente novas vias para terapias aprimoradas.
Por que essa molécula de planta importa
A evodiamina é um composto natural encontrado nos frutos de uma árvore usada na medicina tradicional chinesa. Pertence a uma família de moléculas em anel que já fundamentam fármacos importantes para câncer, pressão alta e infecções. A própria evodiamina mostrou propriedades anticâncer, anti‑inflamatórias, analgésicas e antimicrobianas, e algumas de suas versões modificadas parecem especialmente promissoras como candidatos antitumorais multitarget. O desafio é como acrescentar novas “alças” químicas, como grupos contendo oxigênio, em pontos muito específicos desse arcabouço lotado sem usar reagentes agressivos ou sínteses com múltiplas etapas.
Deixar as enzimas fazerem a química difícil
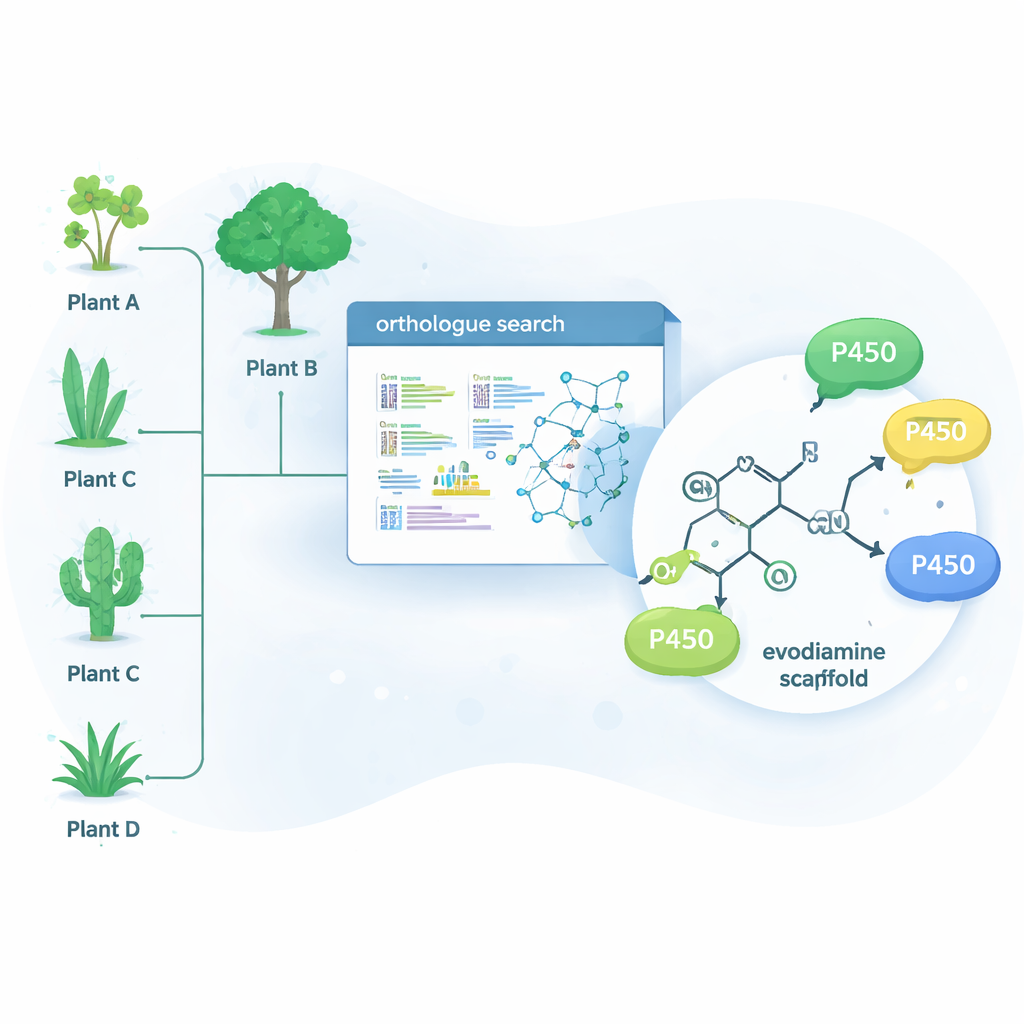
A natureza já resolveu muitos desses problemas químicos difíceis usando enzimas — proteínas que catalisam reações específicas. Uma grande família de enzimas, chamada citocromos P450, é excepcional em inserir oxigênio em ligações carbono–hidrogênio normalmente pouco reativas. Esse único passo pode mudar dramaticamente como uma molécula se comporta no organismo e também criar um ponto de partida para modificações químicas posteriores. Em vez de buscar apenas em plantas que naturalmente produzem evodiamina, os pesquisadores usaram uma ferramenta de bioinformática chamada OrthoFinder para vasculhar dados genéticos de 15 plantas produtoras de alcaloides. Eles procuraram P450s que fossem “ortólogos” próximos de enzimas conhecidas por modificar alcaloides, partindo do raciocínio de que parentes dessas enzimas também poderiam ajustar finamente moléculas relacionadas com caráter farmacológico.
Encontrando novas enzimas em plantas inesperadas
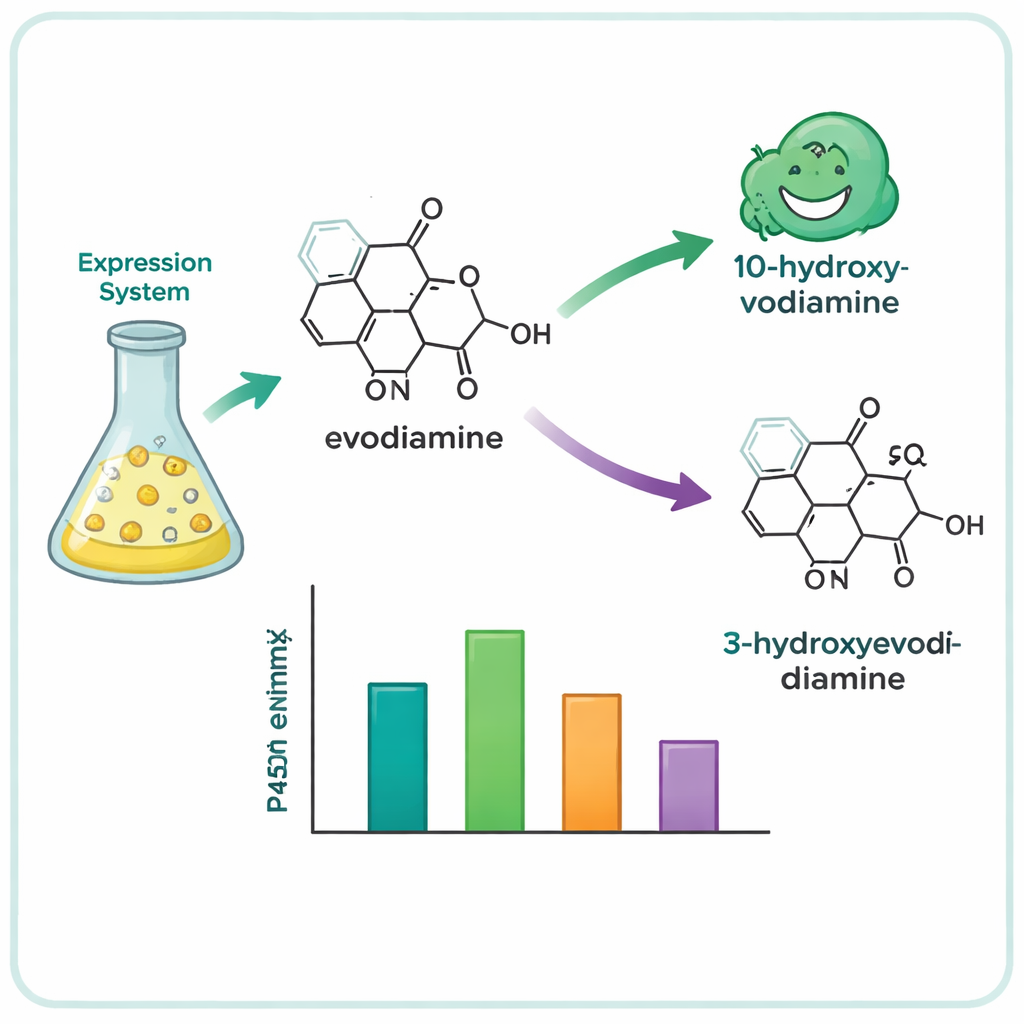
A partir de centenas de genes candidatos, a equipe reduziu a lista para 15 P450s promissores e os expressou em células de levedura, que serviram como fábricas enzimáticas em miniatura. Em seguida, alimentaram essas leveduras com uma coleção de moléculas vegetais complexas e analisaram quais foram quimicamente alteradas. Quatro enzimas — três da árvore Camptotheca acuminata e uma do arbusto Tabernaemontana elegans — agiram sobre a evodiamina, mesmo que nenhuma dessas plantas seja conhecida por produzi‑la. Essas enzimas inseriram seletivamente um átomo de oxigênio em uma de duas posições no sistema de anéis da evodiamina, gerando dois produtos principais: 10‑hidroxi‑evodiamina e 3‑hidroxi‑evodiamina. Versões oxigenadas desse tipo são mais fáceis de transformar posteriormente em candidatos medicamentosos solúveis em água ou mais potentes, usando química mais suave do que as rotas sintéticas tradicionais.
Espiando o kit de ferramentas molecular
Para entender por que essas enzimas intimamente relacionadas se comportaram de forma diferente, os pesquisadores construíram modelos tridimensionais da enzima mais ativa e de seus parentes usando ferramentas modernas de predição de estrutura proteica. Em seguida, usaram análise de docking computacional para ver como a evodiamina poderia se acomodar dentro dos bolsos ativos das enzimas, perto do centro do P450 que contém ferro, onde a reação ocorre. Os modelos destacaram vários aminoácidos volumosos e hidrofóbicos — em especial resíduos de fenilalanina — posicionados próximos aos anéis aromáticos da evodiamina. Ao mutar cuidadosamente essas posições, a equipe demonstrou que mudar o tamanho e a forma desse bolso poderia enfraquecer a atividade, alterar o encaixe do substrato ou mesmo trocar o sítio de oxigenação favorecido de um anel da molécula para outro. Em um caso, uma única mutação inverteu a preferência da enzima de produzir o produto 10‑hidroxi para produzir o 3‑hidroxi.
O que isso significa para futuros medicamentos
Para não especialistas, a conclusão principal é que os autores demonstraram um roteiro prático para descobrir e ajustar enzimas vegetais capazes de realizar edições precisas e “cirúrgicas” em moléculas complexas com caráter farmacológico. Ao combinar mineração genética em larga escala com ensaios enzimáticos e modelagem estrutural, eles descobriram um conjunto de biocatalisadores que podem remodelar seletivamente o arcabouço da evodiamina em posições de difícil acesso pela química padrão. Isso não apenas oferece uma maneira mais limpa e sustentável de produzir versões avançadas da evodiamina — como candidatos anticâncer solúveis em água — mas também mostra que enzimas úteis podem ser encontradas em plantas que nunca produzem o composto alvo. A mesma estratégia agora pode ser aplicada a muitos outros produtos naturais, acelerando o desenho da próxima geração de medicamentos derivados de plantas.
Citação: Kwan, B.D., Kim, T., Nguyen, H.H. et al. Orthologue inference-based enzyme mining for diversification of the anti-cancer evodiamine scaffold. Commun Chem 9, 73 (2026). https://doi.org/10.1038/s42004-025-01876-6
Palavras-chave: evodiamina, enzimas de plantas, citocromo P450, biocatálise, descoberta de fármacos