Clear Sky Science · pt
Otimizando a precisão do CRISPR em embriões de camundongo via direcionamento dominante por união de extremos mediada por micro-homologia
Por que produzir camundongos editados com maior precisão é importante
Ferramentas de edição genética como o CRISPR tornaram notavelmente fácil criar camundongos que modelam doenças humanas, mas há um problema oculto: as alterações genéticas na primeira geração de animais costumam ser confusas e mistas. Isso torna os experimentos mais lentos, menos confiáveis e demanda mais animais. Este estudo introduz uma forma de orientar os cortes do CRISPR em embriões de camundongo para resultados altamente previsíveis, de modo que a maioria dos camundongos fundadores nasça com a mesma mutação bem definida — trazendo biologia mais limpa e uma ética melhor para a pesquisa em edição gênica.
O desafio dos reparos de DNA desordenados
Quando o CRISPR corta o DNA, a célula precisa remendar a quebra usando seus próprios sistemas de reparo. A via mais comum, chamada união de extremidades não homóloga (non-homologous end joining), é rápida mas imprecisa, produzindo um emaranhado de pequenas inserções e deleções no sítio de corte. Outra via, a união de extremidades mediada por micro-homologia (microhomology-mediated end joining), tende a deletar trechos de DNA de forma estereotipada usando pequenas sequências correspondentes como guias. Ambas são muito mais eficientes do que a via precisa, porém mais lenta, de reparo por homologia. Em experimentos padrão com CRISPR, os cientistas se concentram principalmente em quão eficientemente uma RNA guia corta e em quantos sítios fora do alvo ela atinge, e prestam muito menos atenção a qual via de reparo será favorecida ou a qual mutação exata resultará. O desfecho é que muitos camundongos fundadores carregam um mosaico de mutações diferentes em células distintas, obrigando os pesquisadores a cruzar para a geração seguinte antes de poderem trabalhar com um genótipo limpo e uniforme.
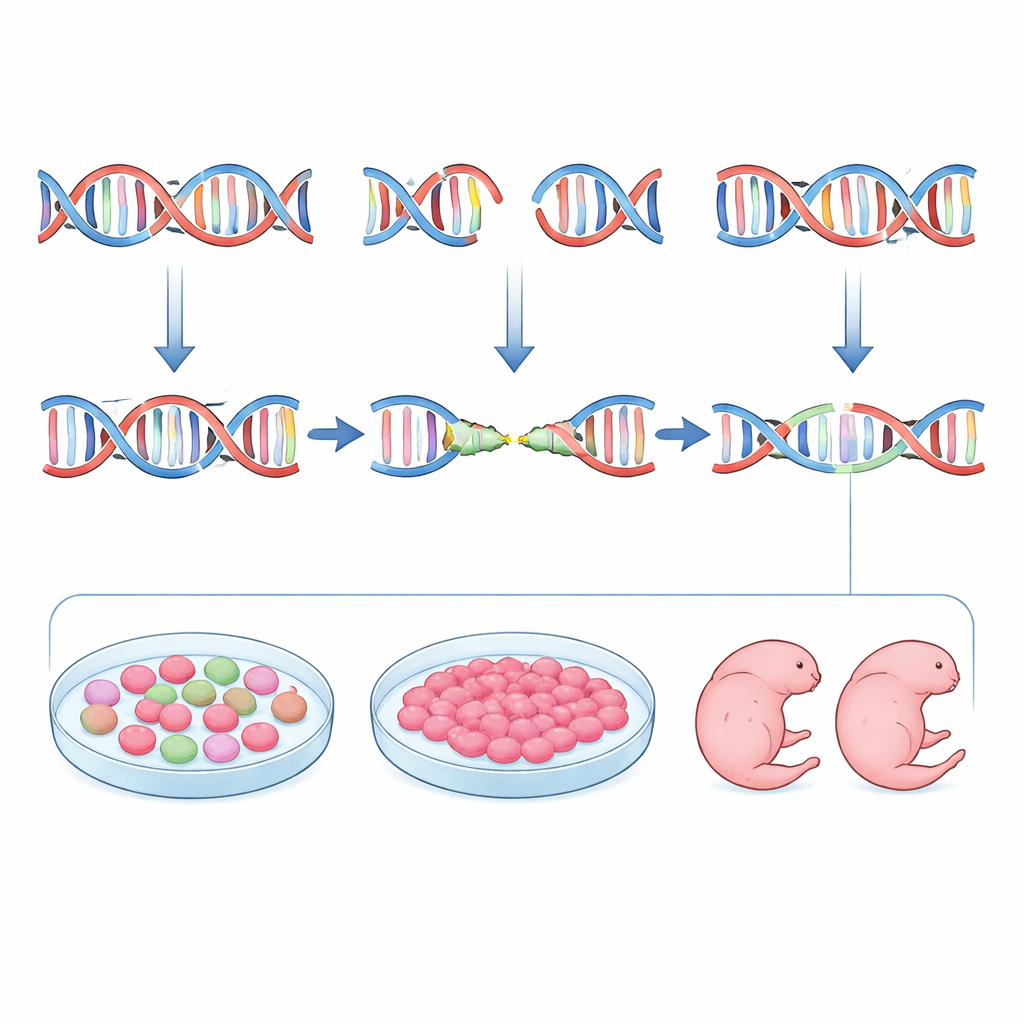
Uma forma mais inteligente de escolher guias do CRISPR
Os autores propuseram inverter esse cenário projetando guias não apenas para força e segurança, mas também para previsibilidade. Eles começaram com o inDelphi, uma ferramenta de aprendizado de máquina treinada em grandes conjuntos de dados de mutações induzidas por CRISPR em células cultivadas. O inDelphi não se limita a dizer com que frequência um sítio será editado; ele prevê o cardápio completo de possíveis inserções e deleções e com que frequência cada uma aparecerá, com atenção especial a eventos dirigidos por micro-homologia. A equipe varreu o gene da tirosinase (Tyr) do camundongo, cuja perda de função torna os animais albinos, e selecionou RNAs guias previstos para favorecer deleções mediadas por micro-homologia fortes e repetíveis, mantendo baixos os riscos fora do alvo. Em seguida editaram embriões de camundongo e mediram as mutações resultantes por sequenciamento profundo. No geral, o genótipo preferido pelo inDelphi para cada guia apareceu em frequências semelhantes às previstas nos embriões, e guias com características de micro-homologia mais fortes de fato produziram padrões de mutação mais uniformes.
Usando células-tronco como palco de ensaio
No entanto, a predição sozinha não foi suficiente. Quando a equipe comparou as previsões do inDelphi com os padrões reais de edição, encontrou apenas concordância moderada. Para reduzir essa lacuna, introduziram um passo intermediário prático: testar cada guia em células-tronco embrionárias de camundongo que compartilham muitas características com embriões muito precoces. Após transfectar essas células com os componentes do CRISPR, eles separaram as células editadas e sequenciaram os sítios alvo. Os padrões de mutação nas células-tronco corresponderam aos observados nos embriões muito mais de perto do que o modelo computacional. Guias que produziram uma única deleção dominante em células-tronco tipicamente fizeram o mesmo em blastocistos e embriões em estágios posteriores. Ao combinar o ranqueamento do inDelphi com esse “ensaio geral” em células-tronco, os pesquisadores puderam escolher de forma confiável guias que direcionam o reparo mediado por micro-homologia e minimizam a diversidade de alelos mutantes.
Da cor dos olhos a membros ausentes
Os autores testaram seu fluxo de trabalho em animais vivos. Para o gene Tyr, eles escolheram três guias representando precisão prevista alta, média e baixa e transferiram embriões editados para mães adotivas. No dia 11.5 do desenvolvimento, examinaram a pigmentação ocular e sequenciaram cada embrião individualmente. O guia que favorecia fortemente a micro-homologia produziu embriões majoritariamente albinos e que carregavam uma pequena deleção dominante, frequentemente em ambas as cópias do gene, com muito pouca variação. Um guia menos otimizado gerou uma mistura de perda de pigmento e pigmentação parcial ligada a um conjunto mais complexo de mutações. Em seguida aplicaram a mesma abordagem ao gene Fgf10, cuja perda de função resulta em embriões sem membros. Selecionando um guia previsto — e confirmado em células-tronco — para gerar uma deleção específica de quatro bases com alta probabilidade de interromper o gene, eles geraram embriões no dia 15.5 que eram uniformemente desprovidos de membros e carregavam um conjunto fortemente enriquecido das deleções esperadas. Em ambos os genes, os mesmos poucos tipos de mutação dominaram nas previsões do inDelphi, nas células-tronco, nos embriões iniciais e nos embriões em estágios posteriores.
Genética mais limpa com menos animais
Em termos práticos, o estudo oferece um novo modelo para projetar experimentos com CRISPR em camundongos. Em vez de passar diretamente de um guia desenhado por computador para a edição de embriões, os autores defendem um pipeline integrado: usar o inDelphi e ferramentas de análise de off-target para escolher guias que provavelmente favoreçam deleções mediadas por micro-homologia e frameshifts, testar esses guias em células-tronco embrionárias para confirmar eficiência e uniformidade das mutações, e avançar para o trabalho com embriões apenas com os melhores desempenhos. Essa estratégia gera camundongos fundadores cujas células compartilham em grande parte a mesma mutação bem caracterizada, tornando-os imediatamente úteis para modelar doenças humanas — especialmente aquelas causadas por alterações recorrentes do tipo deleção — ao mesmo tempo que reduz o número de animais que precisam ser cruzados e triados. O resultado é uma genética mais precisa e reprodutível e um caminho mais ético para modelos de doenças mais robustos.
Citação: Lkhagvadorj, K., Okamura, E., Taki, T. et al. Optimizing CRISPR precision in mouse embryos via microhomology-mediated end joining-dominant targeting. Commun Biol 9, 371 (2026). https://doi.org/10.1038/s42003-026-09771-z
Palavras-chave: CRISPR, modelos de camundongo, edição do genoma, reparo de DNA, modelagem de doenças