Clear Sky Science · pt
Patch aromático em fatores de transcrição do tipo WhiB facilita a interação com o fator sigma primário em Mycobacterium tuberculosis
Como as bactérias detectam perigo
Mycobacterium tuberculosis, o microrganismo que causa a tuberculose, sobrevive dentro do corpo humano reprogramando rapidamente quais genes são ativados ou desativados quando as condições mudam, por exemplo, durante exposição a antibióticos ou ataque imunológico. Este estudo revela uma pequena característica estrutural — um “patch aromático” — em uma família de proteínas bacterianas que as ajuda a se agarrar à principal maquinaria de alternância de genes da célula. Entender esse aperto microscópico explica como a tuberculose e bactérias relacionadas se adaptam e pode apontar para novas formas de enfraquecer esse patógeno.
Uma família especial de proteínas reguladoras bacterianas
O trabalho centra-se nas proteínas do tipo WhiB (Wbl), um grupo encontrado apenas em actinobactérias e seus vírus, incluindo Mycobacterium tuberculosis. Essas proteínas carregam um pequeno cluster ferro–enxofre, um cofator à base de metal que lhes permite detectar mudanças em oxigênio e outros estresses. Sabe-se que proteínas Wbl controlam processos-chave, como divisão celular, respostas ao estresse oxidativo e nutricional, e resistência a antibióticos. No entanto, a maioria delas carece das formas clássicas usadas por muitos reguladores para se ligar diretamente ao DNA, o que deixou uma questão em aberto por muito tempo: como elas realmente controlam a atividade gênica?
Agarre à principal máquina leitora de genes
Trabalhos anteriores mostraram que várias proteínas Wbl ativam genes ligando-se a uma região conservada, chamada região 4, do fator sigma primário. O fator sigma é a parte da RNA polimerase — a enzima que lê o DNA — que reconhece onde começar a copiar genes. Em Mycobacterium tuberculosis, esse fator sigma usa a mesma região 4 para recrutar muitos reguladores diferentes. Os autores combinaram cristalografia de raios X, ensaios bioquímicos de puxada (pull-down) e calorimetria para mostrar que, essencialmente, todas as proteínas Wbl testadas desse bacilo (com um caso especial) se prendem exatamente ao mesmo ponto da região 4 do sigma e o fazem com ligação muito forte.
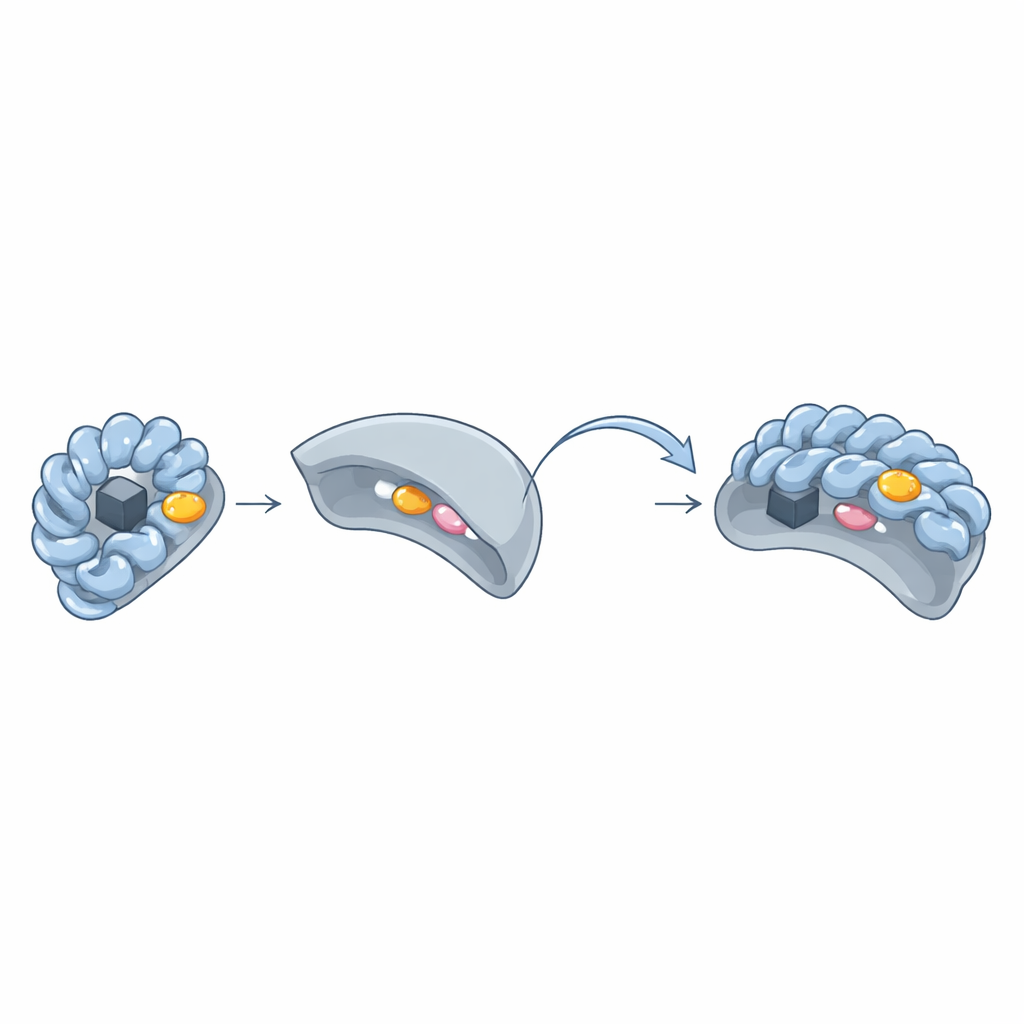
O bloqueio e a chave escondidos: o “patch aromático”
Ao comparar estruturas tridimensionais de pares Wbl–sigma, a equipe descobriu um aglomerado recorrente de aminoácidos volumosos em anel — triptofano, fenilalanina, tirosina ou histidina — formando um “patch aromático” na superfície das proteínas Wbl. Esse patch fica ao redor do cluster ferro–enxofre e pressiona diretamente contra dois aminoácidos-chave na região 4 do sigma. Quando os pesquisadores substituíram esses resíduos do patch aromático por outros mais simples, as proteínas Wbl deixaram de formar complexos estáveis com o sigma, e seus clusters ferro–enxofre frequentemente tornaram-se instáveis. Mesmo em variantes de Wbl que pareciam incomuns — como WhiB6 ou WhiB5 —, resíduos alternativos ou cadeias laterais aromáticas próximas compensaram para preservar o mesmo estilo de interação.
Um projeto compartilhado entre bactérias e seus vírus
Para avaliar quão difundida é essa característica, os autores analisaram 995 sequências de proteínas Wbl de muitas espécies de actinobactérias e de seus vírus infectantes (actinobacteriófagos). Eles agruparam essas proteínas em 29 subfamílias e descobriram que cinco ramos principais, representados por cinco proteínas Wbl de Mycobacterium tuberculosis, correspondem a cerca de 80% de todas as sequências. Modelagem estrutural com AlphaFold revelou que quase todas as Wbls — mais de 98% — carregam ao menos dois resíduos aromáticos em posições correspondentes ao patch aromático, e quase todas têm pelo menos um nos pontos centrais mais críticos. Experimentos com várias proteínas Wbl codificadas por fagos confirmaram que essas versões virais também se ligam à mesma região do sigma de maneira dependente do patch, indicando que o mesmo projeto molecular é reutilizado entre bactérias e seus fagos.
Uma disputa evolutiva pelo controle
A árvore filogenética construída a partir dessas 995 sequências mostra proteínas Wbl de fagos e bactérias entrelaçadas, com sinais claros de transferência horizontal de genes em ambas as direções. Alguns Wbls virais estão na base de ramos bacterianos importantes, sugerindo que fagos podem ter doado esses reguladores a bactérias ancestrais, que então os adaptaram às suas necessidades. Outros Wbls virais aparecem inseridos em aglomerados predominantemente bacterianos, indicando transferências de genes posteriores de volta para os fagos. Como as proteínas Wbl controlam rigidamente respostas ao estresse, desenvolvimento celular e resistência a drogas por meio de seus patches aromáticos de ligação ao sigma, essas trocas recíprocas provavelmente moldaram como tanto bactérias quanto seus vírus manipulam a maquinaria de transcrição do hospedeiro.
O que isso significa para a tuberculose e além
Em termos simples, este estudo mostra que muitos reguladores de actinobactérias compartilham um ponto adesivo minúsculo, porém crucial — o patch aromático — que lhes permite acoplar-se à mesma parte da máquina leitora de genes e ajustar quais genes estão ativos sob estresse. Em Mycobacterium tuberculosis, esse mecanismo de acoplamento compartilhado ajuda a coordenar respostas que sustentam persistência, virulência e resistência a antibióticos. Ao revelar como essa interface microscópica funciona e quão amplamente ela é conservada, o trabalho destaca um ponto fraco potencial que, algum dia, pode ser alvo para interromper a capacidade do patógeno de se adaptar e sobreviver dentro do hospedeiro.
Citação: Guiza Beltran, D., Wan, T., Seravalli, J. et al. Aromatic patch in whiB-like transcription factors facilitates primary sigma factor interaction in mycobacterium tuberculosis. Commun Biol 9, 424 (2026). https://doi.org/10.1038/s42003-026-09698-5
Palavras-chave: Mycobacterium tuberculosis, fatores de transcrição, fator sigma, proteínas ferro-enxofre, evolução de bacteriófagos