Clear Sky Science · pt
DANST possibilita a desconvolução por tipo celular em transcriptômica espacial usando redes neurais adversariais profundas de domínio
Vendo as Células em Seus Vizinhos
Tecidos humanos são cidades densas de muitos tipos celulares diferentes, cada um desempenhando seu papel. Novas tecnologias de “transcriptômica espacial” conseguem medir quais genes estão ativos ao longo de uma fatia de tecido, mas cada medida frequentemente mistura sinais de várias células vizinhas. Este artigo apresenta o DANST, um método computacional inteligente que separa essas misturas. Ao nos dizer quais tipos celulares estão presentes e onde, em órgãos e tumores, ele ajuda cientistas a entender melhor como os tecidos são organizados, como as doenças se espalham e onde os tratamentos podem ser mais bem direcionados. 
O Desafio de Desembaralhar Multidões Celulares
Ferramentas modernas de leitura gênica podem ou examinar células individuais com muita precisão ou capturar a disposição completa de um tecido, mas raramente ambos ao mesmo tempo. Tecnologias espaciais populares registram a atividade gênica em “spots” relativamente grandes que podem cobrir várias células. O resultado é como ouvir um coro sem conseguir dizer quem canta quais notas. Para entender isso, os pesquisadores precisam de métodos de “desconvolução” que estimem quanto cada tipo celular contribui para cada spot. Muitas abordagens existentes usam dados de célula única como referência, mas têm dificuldades porque os dois tipos de dados são coletados por experimentos diferentes e não combinam perfeitamente em qualidade, ruído ou resolução.
Construindo uma Ponte Entre Mundos de Dados
O DANST enfrenta esse descompasso criando uma ponte entre dados de célula única e dados espaciais. Primeiro, ele usa os perfis detalhados de célula única para simular muitos spots artificiais mistos com proporções de tipos celulares conhecidas. Ao mesmo tempo, agrupa os spots espaciais reais de acordo com sua localização no tecido e seus padrões gênicos, e usa as distâncias a esses grupos para atribuir a cada spot simulado uma posição “pseudo”. Essa etapa cria um mapa vinculado onde spots artificiais e reais compartilham um quadro espacial comum, permitindo que o método aprenda como sinais mistos devem parecer em bairros específicos do tecido. 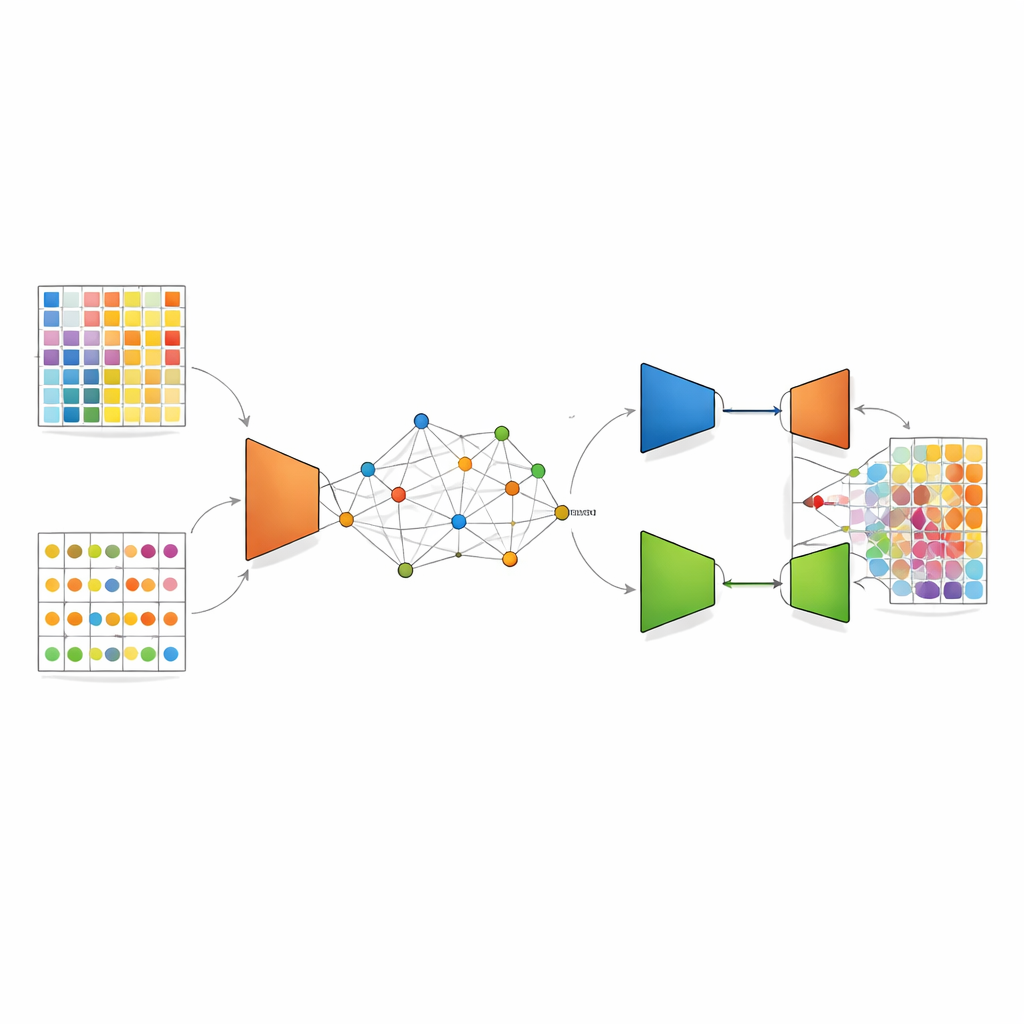
Limpeza de Sinais e Alinhamento de Domínios
Com esse mapa conjunto em vigor, o DANST aplica um tipo de aprendizado profundo chamado autoencoder variacional. Essa rede comprime padrões gênicos de spots reais e simulados em uma representação interna refinada e então tenta reconstruí-los, efetivamente reduzindo ruído e enfatizando recursos importantes. Sobre isso, os autores adicionam um componente adversarial: uma segunda rede tenta identificar se um padrão refinado veio de dados espaciais reais ou simulados, enquanto o extrator de características aprende a enganá‑la. Esse “puxão de guerra” empurra o modelo na direção de características que funcionam bem para ambas as fontes de dados, de modo que o conhecimento obtido a partir de spots simulados com frações de tipos celulares conhecidas possa ser transferido com confiança para spots de tecido reais cuja composição é desconhecida.
Testes em Corações, Cérebros e Tumores
A equipe testou o DANST tanto em benchmarks artificiais quanto em amostras biológicas reais de camundongos e humanos. Em comparação com vários métodos líderes, o DANST recuperou com maior precisão as proporções de tipos celulares em conjuntos de dados sintéticos e manteve essa vantagem em tecidos e plataformas muito diferentes. Em um conjunto de dados do cérebro de camundongo, ele reconstruiu claramente a organização em camadas do córtex e correspondeu a regiões anatômicas definidas por especialistas. Em uma fatia distinta de cérebro de camundongo, capturou padrões finos em áreas como o hipocampo. Mais notavelmente, em tecido de câncer de mama humano, o DANST mapeou como diversas células imunes, células de suporte e células luminais sensíveis a hormônios estão organizadas dentro e ao redor das regiões tumorais. Esses mapas se alinharam com a biologia conhecida e sugeriram características clinicamente relevantes, como dependência hormonal e potencial pior prognóstico onde certas células imunes eram escassas.
O Que Isso Significa para a Biologia e a Medicina
Para um não especialista, o DANST pode ser visto como um intérprete poderoso que transforma sinais borrados e sobrepostos em uma imagem clara de quais células vivem onde em um tecido. Ao separar tipos celulares no espaço de forma confiável, ele dá aos pesquisadores uma visão mais nítida de como órgãos saudáveis são organizados e como a doença reconfigura essa organização. No câncer, isso pode revelar como células tumorais e células imunes interagem em regiões específicas, o que pode orientar terapias direcionadas e ajudar a prever desfechos dos pacientes. À medida que mais conjuntos de dados espaciais e de célula única se tornarem disponíveis, ferramentas como o DANST tendem a se tornar essenciais para decodificar os bairros celulares que sustentam saúde e doença.
Citação: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Palavras-chave: transcriptômica espacial, desconvolução de tipos celulares, aprendizado profundo, microambiente tumoral, sequenciamento de RNA de célula única