Clear Sky Science · pt
Avaliação da qualidade de modelos 3D de RNA usando aprendizado profundo e mapas 2D intermediários
Por que avaliar formas de RNA importa
Dentro de cada célula, moléculas de RNA se torcem e dobram em formas tridimensionais intrincadas que ajudam a controlar quais genes são ativados, orientar reações químicas e até defender contra vírus. Hoje, programas de computador poderosos podem prever muitas dessas formas, mas os cientistas ainda enfrentam um problema básico: quando o computador produz dezenas ou centenas de formas candidatas para o mesmo RNA, qual delas está realmente próxima da realidade? Este artigo apresenta o RNArank, uma ferramenta de inteligência artificial projetada para enfrentar essa questão classificando modelos 3D de RNA, como um inspetor de qualidade estrutural, para que os pesquisadores possam focar nas previsões mais confiáveis.
Um novo inspetor para modelos de RNA
O RNArank foi desenvolvido para julgar a qualidade de uma forma proposta de RNA sem precisar saber como essa forma foi gerada. Seja o modelo originado por um sistema de aprendizado profundo, uma simulação baseada em física ou um especialista humano, o RNArank observa apenas as coordenadas 3D finais. Em seguida, pergunta, na prática: “Esta estrutura parece um RNA realista?” Esse tipo de avaliação independente é essencial porque, ao contrário do mundo das proteínas — onde ferramentas como o AlphaFold frequentemente entregam respostas altamente confiáveis prontas para uso — a predição de RNA ainda se beneficia da combinação de múltiplos métodos e da percepção humana — e de um modo inteligente de ordenar os modelos resultantes.
Ensinando à IA como é um bom RNA
Para treinar o RNArank, os autores reuniram cerca de 200.000 estruturas de RNA, cobrindo um amplo espectro entre claramente erradas e quase perfeitas. Essas estruturas foram geradas a partir de estruturas experimentais conhecidas usando uma grande variedade de abordagens, incluindo preditores modernos por aprendizado profundo, simulações de dinâmica molecular que imitam o movimento atômico e distorções deliberadas de estruturas precisas para criar “enganos” (decoys). Para cada modelo, a equipe calculou quão bem ele correspondia ao RNA real, determinado experimentalmente, usando uma métrica refinada de acurácia adaptada para RNA chamada lDDT_RNA. Essa pontuação foca em quão bem as distâncias entre pares de nucleotídeos são reproduzidas, capturando tanto o dobramento global quanto detalhes locais sem ser excessivamente sensível ao comprimento da molécula.
Como o RNArank lê e pontua um RNA
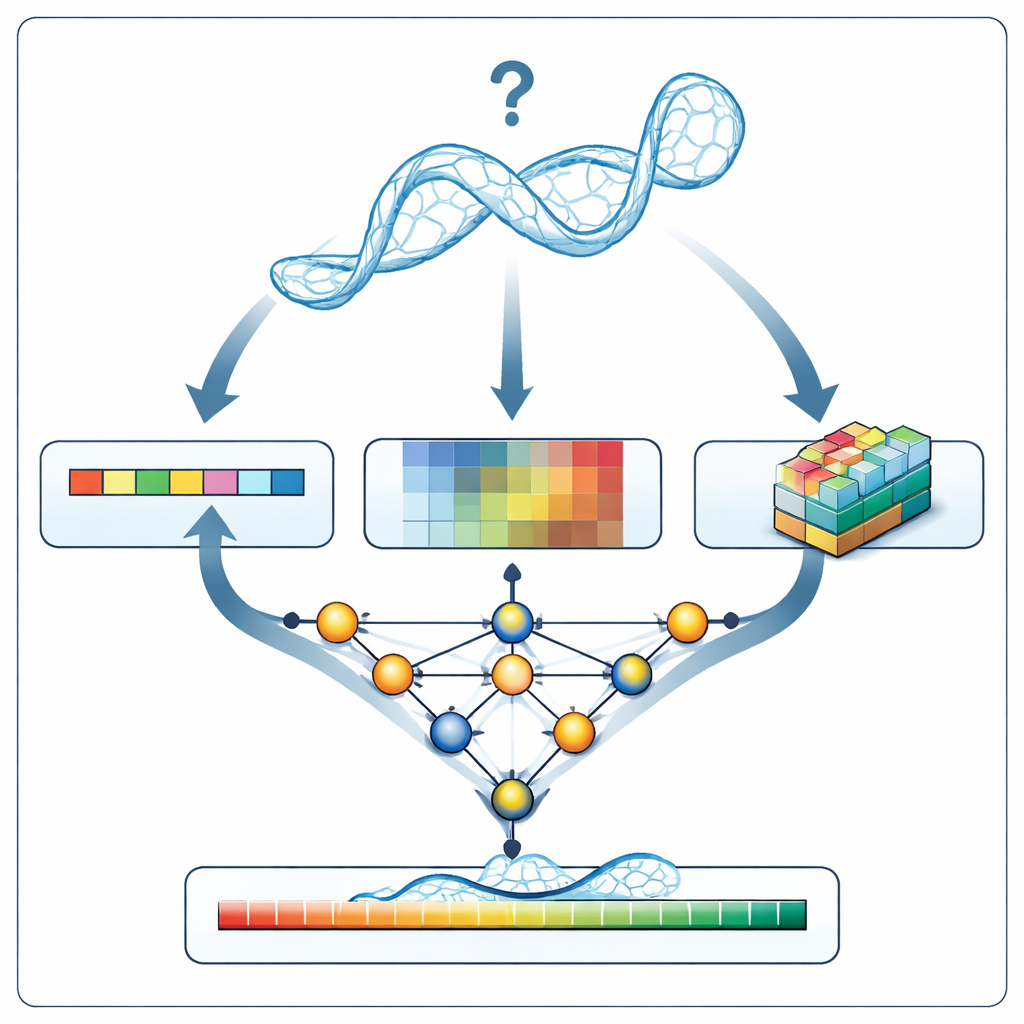
Quando o RNArank examina um novo modelo de RNA, ele primeiro traduz a estrutura em três tipos de informação: uma descrição 1D da sequência e da geometria da espinha dorsal ao longo da cadeia; descrições 2D de como cada par de nucleotídeos se relaciona (suas distâncias, energias de interação estimadas e possíveis colisões atômicas); e instantâneos 3D em “voxels”, pequenas grades que capturam a nuvem local de átomos ao redor de cada nucleotídeo. Uma rede neural multipartida entrelaça essas pistas em um quadro unificado e então prevê dois mapas 2D intermediários: quais nucleotídeos provavelmente estão em contato e quão distante cada distância modelada provavelmente divergirá da estrutura verdadeira desconhecida. A partir desses mapas, o RNArank reconstrói tanto uma pontuação de confiança por nucleotídeo quanto uma pontuação geral para todo o modelo de RNA.
Testando o método
A equipe avaliou o RNArank em três conjuntos de dados exigentes: um conjunto de 24 RNAs recém-resolvidos do Protein Data Bank e os alvos de RNA de dois concursos internacionais de predição às cegas, CASP15 e CASP16, onde muitos grupos submetem modelos sem conhecer as respostas antecipadamente. Ao longo de milhares de estruturas candidatas, as pontuações do RNArank acompanharam a qualidade real do modelo mais de perto do que vários métodos estabelecidos baseados em energia e outras abordagens de aprendizado profundo. Ele foi especialmente eficaz em identificar os melhores ou quase melhores modelos dentro de um conjunto e em apontar quais partes de uma estrutura provavelmente eram pouco confiáveis. Os autores também demonstraram que o RNArank manteve seu desempenho mesmo em RNAs claramente diferentes em sequência daqueles vistos durante o treinamento, um indicativo de generalização genuína em vez de memorização.
Limites hoje e perspectivas futuras
O RNArank não é perfeito: ele ainda encontra dificuldades com RNAs especialmente flexíveis que adotam muitas conformações, e com RNAs que mudam de forma quando associados a proteínas dentro de grandes máquinas moleculares. Porém, é rápido o suficiente para processar muitos modelos de RNAs de algumas centenas de nucleotídeos em apenas segundos, e já ajuda servidores automatizados a escolher previsões de maior qualidade em testes comunitários. Ao fornecer um juiz independente do método e baseado apenas na estrutura dos modelos de RNA, o RNArank dá aos biólogos um filtro mais afiado para transformar saídas brutas de computador em hipóteses estruturais confiáveis, aproximando o campo de previsões de formas de RNA rotineiras e confiáveis e, por consequência, de insights mais profundos sobre como essas moléculas versáteis funcionam.
Citação: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Palavras-chave: Estrutura 3D de RNA, aprendizado profundo, avaliação da qualidade de modelos, bioinformática estrutural, RNArank