Clear Sky Science · pt
MHC1-TIP possibilita perfilamento multimodal do imunopeptidoma em tubo único e revela heterogeneidade intratumoral na apresentação de antígenos
Espiando os documentos de identidade do câncer
Cada célula carrega pequenas “carteirinhas de identificação” moleculares em sua superfície que ajudam o sistema imune a decidir se aquela célula é saudável ou perigosa. No câncer, essas carteirinhas — fragmentos curtos de proteínas chamados antígenos — podem revelar o que torna uma célula tumoral anormal e marcá‑la para destruição por células imunes. Este estudo apresenta um novo método de bancada, MHC1-TIP, que torna muito mais fácil e barato ler essas carteirinhas a partir de quantidades muito pequenas de tecido de pacientes, abrindo caminho para imunoterapias contra o câncer mais precisas.
Por que os sinais na superfície celular importam
Nosso sistema imunológico inspeciona constantemente as células verificando os antígenos exibidos em moléculas especiais chamadas MHC classe I. Células tumorais frequentemente mostram antígenos incomuns que, em princípio, podem ser reconhecidos por células T e alvos de terapias como vacinas personalizadas. No entanto, medir quais antígenos estão presentes em amostras reais de pacientes tem sido tecnicamente desafiador. Métodos tradicionais exigem um grande número de células, muitos passos de processamento e anticorpos caros, o que os torna pouco adequados para biópsias minúsculas ou amostras clínicas escassas. Ao mesmo tempo, tumores não são uniformes: regiões distintas podem expressar proteínas diferentes, levantando a possibilidade de que a apresentação de antígenos também varie de lugar para lugar dentro de um mesmo tumor.
Um atalho em um tubo para antígenos do câncer
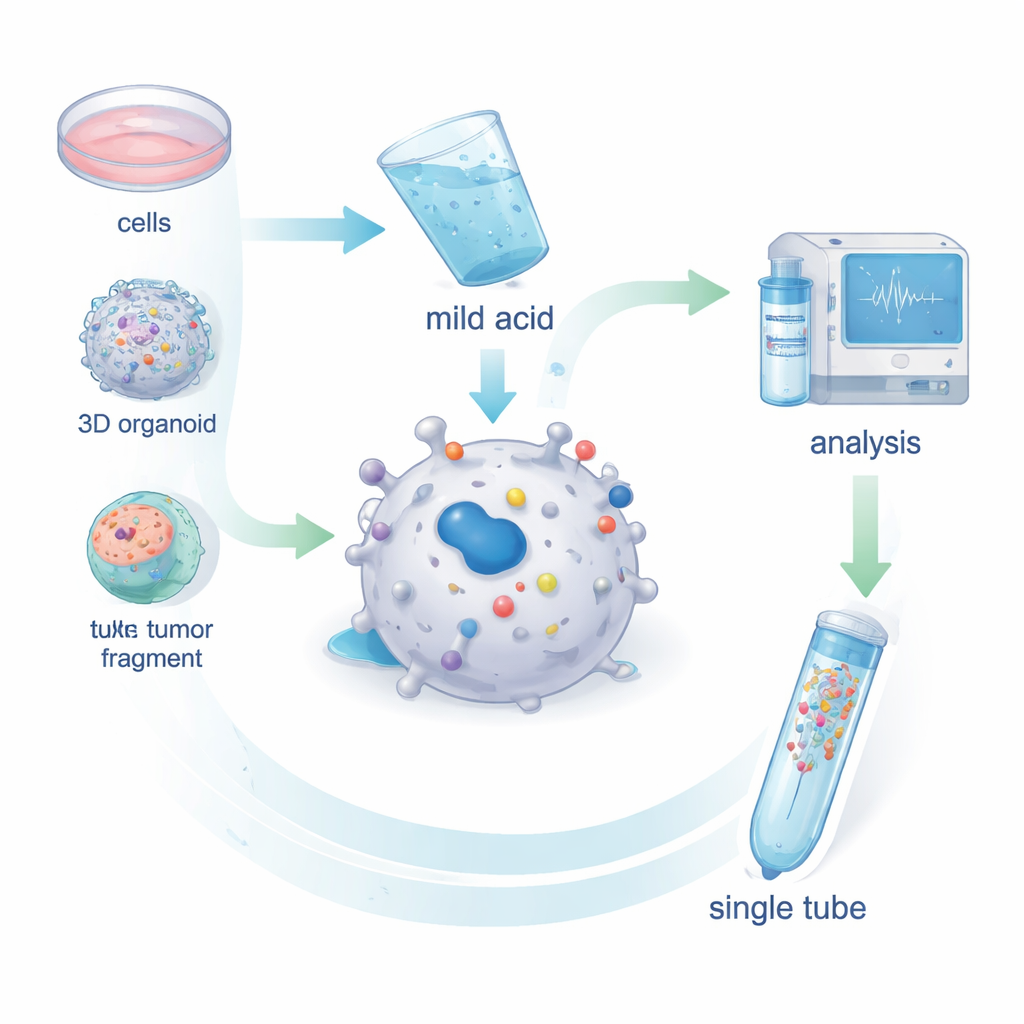
Os pesquisadores desenvolveram o MHC1-TIP (MHC‑I 1‑Tube Immunopeptidomics) como uma forma simplificada de coletar antígenos de células vivas. Em vez de romper as células e pescar as moléculas MHC com anticorpos, eles lavam brevemente células intactas — ou pequenos fragmentos tumorais — com uma solução ácida suave. Esse tratamento delicado faz com que os antígenos encaixados no sulco do MHC se desprendam sem matar as células. Os peptídeos liberados então passam por um pequeno filtro que remove detritos maiores e ficam retidos em uma coluna diminuta dentro de um único tubo. De lá, vão diretamente para um espectrômetro de massas, que identifica as sequências peptídicas. Testes em células de melanoma mostraram que essa etapa de ácido leve remove quase todos os complexos MHC–antígeno de superfície e que os peptídeos recuperados se assemelham a antígenos realmente ligados ao MHC em termos de comprimento e padrões de sequência.
Mais dados com menos amostra
O MHC1-TIP foi projetado para funcionar com pouquíssimas células e ainda fornecer muitos antígenos identificáveis. Ao combinar o novo fluxo de trabalho com um modo moderno de espectrometria de massas chamado aquisição independente de dados, a equipe detectou centenas de antígenos a partir de apenas 100.000 células e milhares a partir de alguns milhões — profundidade similar ao método padrão com anticorpos do campo, mas com menos material e menor custo. O método também funcionou em organoides derivados de pacientes, que são mini‑tumores 3D cultivados em laboratório, e em fragmentos tumorais ex vivo minúsculos menores que um milímetro cúbico. Importante: como a lavagem ácida mantém as células em grande parte intactas, o material remanescente pode ser usado para perfilagem protéica em escala completa a partir da mesma amostra, permitindo comparação direta entre quanto de uma dada proteína está presente e quanto dela é realmente apresentado como antígeno.
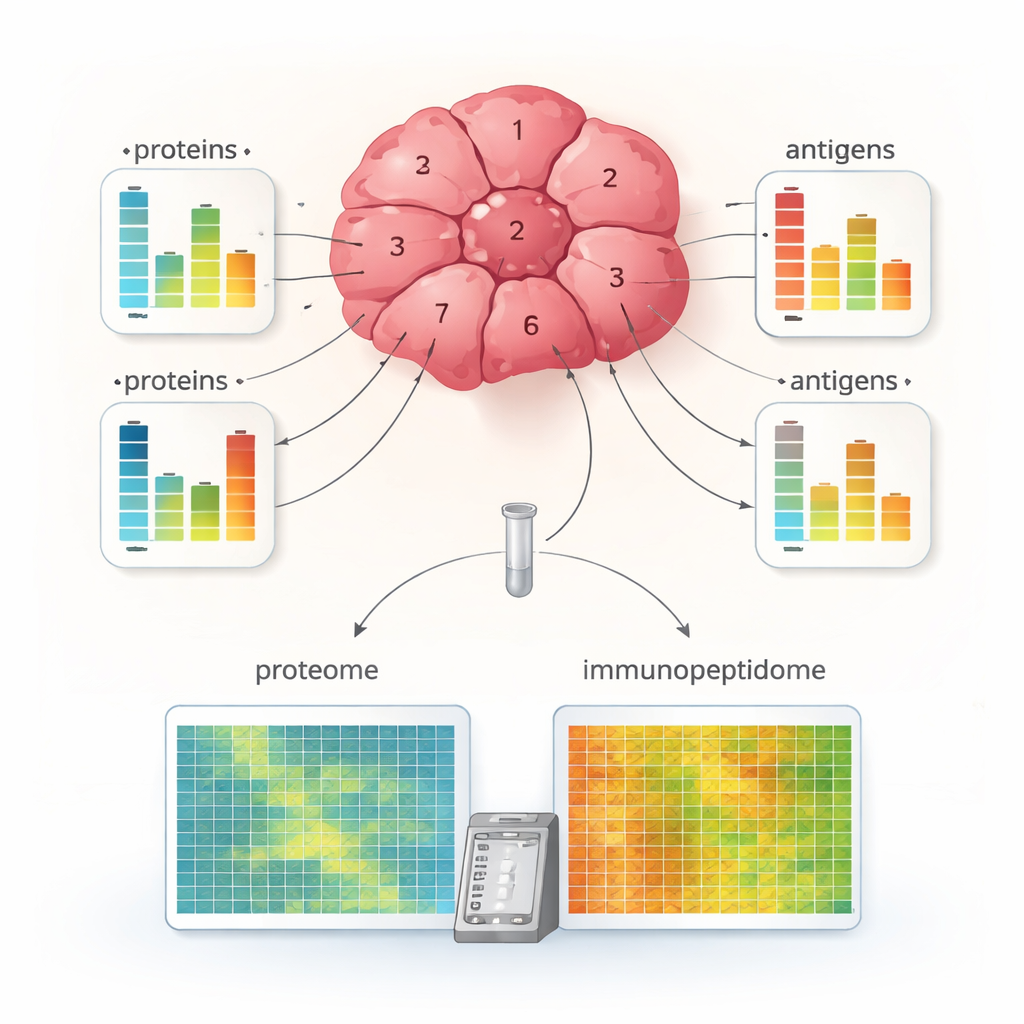
Diferenças ocultas dentro de um único tumor
Aplicar o MHC1-TIP a múltiplos pequenos fragmentos retirados de regiões diferentes de um tumor de carcinoma de células renais revelou uma diversidade interna marcante. Alguns fragmentos mostraram apresentação rica de antígenos, enquanto outros exibiram muito poucos antígenos, mesmo que seu conteúdo protéico geral pudesse ser semelhante. Para muitas proteínas, as mudanças nos níveis de antígenos não corresponderam às mudanças na abundância da proteína, sugerindo que o processamento de antígenos e o carregamento nas moléculas MHC são regulados independentemente de quanto da proteína parental está presente. A equipe também combinou os dados de antígenos com marcadores de células imunes e da maquinaria MHC, identificando regiões tumorais “quentes” imune, com alta exibição de antígenos e sinais de células T ativas, e “frias” imune, com menos antígenos e menos indicação de ataque imune. Esse nível de detalhe raramente foi possível a partir de pedaços de tecido tão pequenos.
O que isso significa para o cuidado futuro do câncer
Para um leigo, a mensagem principal é que medir apenas quais proteínas um tumor produz não é suficiente para saber o que o sistema imune realmente consegue ver. O novo método MHC1-TIP oferece uma maneira prática de ler a verdadeira exibição de antígenos a partir de amostras clinicamente realistas muito pequenas, ao mesmo tempo em que mede o panorama protéico mais amplo. A descoberta de que a apresentação de antígenos pode variar muito entre diferentes partes de um mesmo tumor, e nem sempre acompanha os níveis protéicos, alerta contra escolher alvos para vacinas ou células T baseando‑se somente na expressão génica ou protéica. No futuro, abordagens como o MHC1-TIP poderão ajudar a desenhar imunoterapias personalizadas mais eficazes ao focar em antígenos que são genuinamente exibidos na superfície e apresentados de forma mais consistente por todo o tumor.
Citação: Bathini, M., Bocaniciu, D., Johnson, F.D. et al. MHC1-TIP enables single-tube multimodal immunopeptidome profiling and uncovers intratumoral heterogeneity in antigen presentation. Commun Biol 9, 296 (2026). https://doi.org/10.1038/s42003-026-09570-6
Palavras-chave: apresentação de antígenos, imunopeptidômica, imunoterapia do câncer, heterogeneidade tumoral, espectrometria de massas