Clear Sky Science · pt
Células-tronco de glioblastoma mostram organização espacial correlacionada transcriptionalmente
Por que os padrões celulares no câncer cerebral importam
O glioblastoma é um dos cânceres cerebrais mais agressivos, e a sobrevida praticamente não melhorou nas últimas décadas. Muitos laboratórios estudam um tipo especial de célula tumoral chamado célula-tronco de glioblastoma, capaz de regenerar o tumor após o tratamento. Neste estudo, os pesquisadores fizeram uma pergunta aparentemente simples, mas com grande impacto: a forma como essas células se organizam em uma placa — padrões visíveis em um microscópio comum — pode revelar quais genes estão ativos nelas e, potencialmente, acelerar a busca por novas terapias?
Imagens que guardam mais do que aparentam
Para explorar essa ideia, a equipe reuniu cerca de 17.000 imagens de time-lapse obtidas por microscópio a partir de 15 linhagens de células-tronco de glioblastoma derivadas de pacientes, cultivadas em placas plásticas planas. Essas imagens, feitas com microscopia de contraste de fase padrão, são semelhantes às que muitos laboratórios de biologia já geram diariamente. À primeira vista, as fotos mostram apenas células preenchendo progressivamente a placa. Mas uma inspeção cuidadosa revelou diferenças marcantes na organização: algumas formaram longos filetes alinhados de células apontando em direções semelhantes, enquanto outras cresceram em aglomerados mais arredondados com orientações mais aleatórias ou camadas sobrepostas. Esses padrões visuais sugeriam que as “personalidades” internas das células podem se refletir no comportamento coletivo.

Traduzindo texturas em biologia
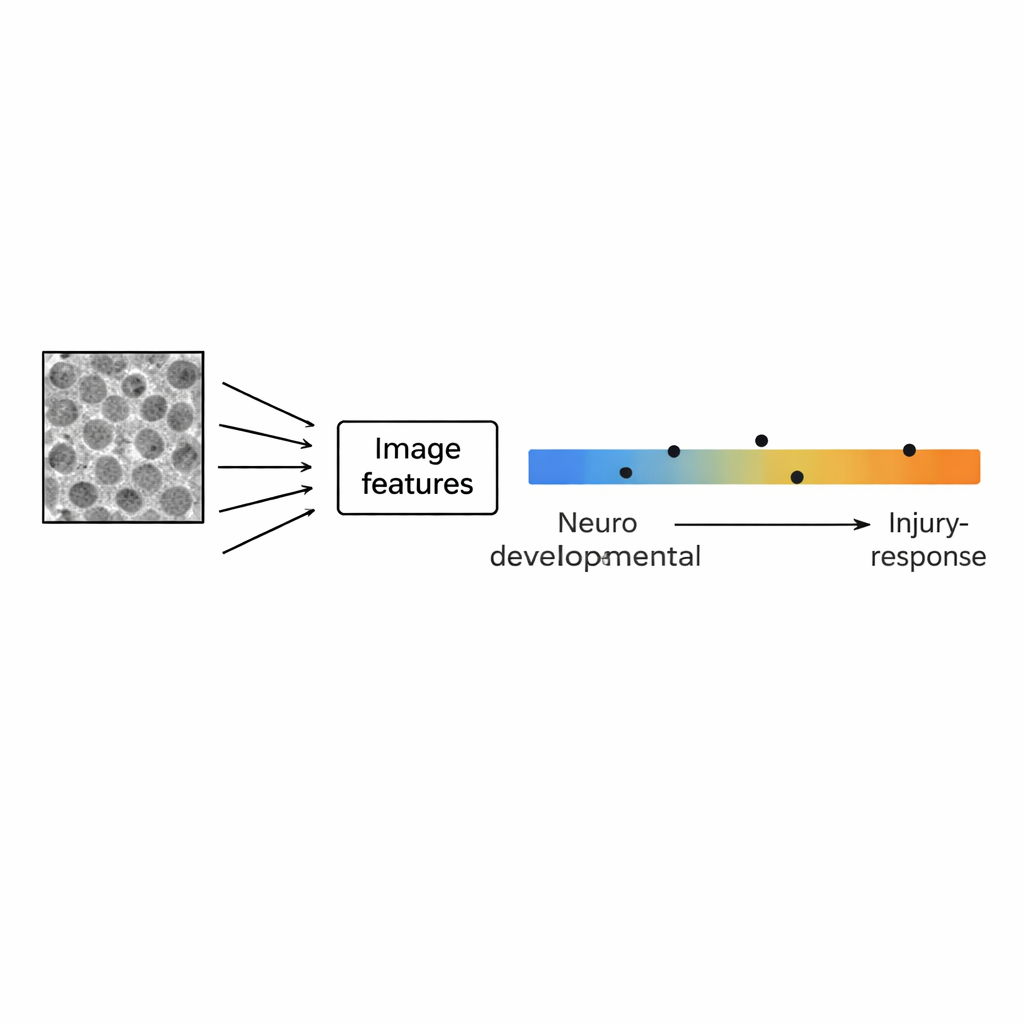
Em vez de focar em células individuais, os pesquisadores trataram cada imagem como um padrão global. Usando software de código aberto, converteram cada foto em 29 características numéricas que descrevem textura e estrutura — como a granulosidade em diferentes escalas, a frequência com que pixels vizinhos são semelhantes e a intensidade do contraste em várias direções. Em seguida, compararam essas impressões digitais baseadas em imagem com perfis de atividade gênica das mesmas linhagens, usando um conjunto de 111 assinaturas gênicas que capturam o desenvolvimento cerebral, tipos celulares normais do cérebro e estados relacionados à inflamação. Uma técnica estatística chamada análise de componentes principais revelou que o eixo principal de variação nos padrões de imagem acompanhava um gradiente biológico conhecido: em uma extremidade, as células expressavam genes ligados ao desenvolvimento cerebral normal (neurônios, células-tronco, células gliais de suporte); na outra, expressavam genes associados a lesão, inflamação e um comportamento mais agressivo, “mesenquimal”.
Padrões que persistem enquanto as culturas crescem
Um desafio na interpretação de imagens celulares é que as culturas mudam dramaticamente à medida que passam de esparsas a densamente compactadas. Os autores abordaram isso agrupando as imagens em nove níveis de densidade celular e reanalisando cada nível separadamente. De forma notável, a conexão entre padrão espacial e atividade gênica se manteve em todos os estágios de crescimento: tanto em placas mal semeadas quanto quase confluentes, imagens de linhagens mais “semelhantes ao desenvolvimento” tendiam a mostrar texturas mais suaves e uniformes, enquanto as de linhagens com resposta a lesão exibiam estruturas mais irregulares e heterogêneas. Contudo, as características de imagem específicas que carregavam o sinal mudaram com a densidade — por exemplo, medidas que capturam granulosidade em pequena escala foram mais informativas em baixas densidades, enquanto características que descrevem simetria e homogeneidade tornaram-se mais importantes à medida que as células se aglomeravam. Isso sugere que a biologia subjacente restringe como os padrões evoluem ao longo do tempo, mesmo quando a aparência física muda.
De instantâneos de microscópio a previsões moleculares
Para testar se apenas as imagens poderiam prever a posição de uma linhagem ao longo do gradiente desenvolvimento–lesão, a equipe treinou modelos estatísticos simples que usaram apenas as 29 características de imagem como entrada e escores baseados em expressão gênica como “gabarito”. Um modelo que selecionou automaticamente a combinação mais informativa de características reproduziu com precisão o gradiente para as 15 linhagens originais e mostrou concordância promissora em quatro linhagens de teste adicionais. As características de imagem mais úteis incluíram descritores de textura e medidas de tamanho de estruturas, ecoando os achados das análises de padrão. Importante, esse modelo funcionou com imagens padrão sem marcação — sem corantes fluorescentes ou microscópios especializados — apontando para uma rota prática de transformar a imagem rotineira em uma leitura rápida e barata do estado celular.
O que isso significa para pesquisas futuras sobre câncer cerebral
Para não especialistas, a conclusão principal é que a aparência e a organização das células cancerosas como uma comunidade podem servir de janela para os genes que estão sendo utilizados. Em células-tronco de glioblastoma, imagens simples em campo claro capturam informação suficiente para distinguir células que se assemelham ao cérebro em desenvolvimento normal daquelas deslocadas para um estado conduzido por lesão e inflamação, frequentemente associado a uma doença mais agressiva. No futuro, esse tipo de “impressão digital” baseada em imagem poderia ajudar cientistas a triagem rápida de drogas ou alterações genéticas observando como elas deslocam as células ao longo desse gradiente, sem precisar sequenciar RNA a cada vez. Mais amplamente, o trabalho sugere que a arquitetura de culturas celulares vivas não é apenas visualmente interessante — ela codifica informação biologicamente significativa que pode ser decodificada com as ferramentas adequadas.
Citação: Ayyadhury, S., Sachamitr, P., Kushida, M.M. et al. Glioblastoma stem cells show transcriptionally correlated spatial organization. Commun Biol 9, 208 (2026). https://doi.org/10.1038/s42003-026-09566-2
Palavras-chave: células-tronco de glioblastoma, imagem celular, organização espacial, expressão gênica, triagem de alto rendimento