Clear Sky Science · pt
A próxima camada: ampliando modelos de base com aprendizado que preserva estrutura e é guiado por atenção para consciência do contexto local a global na patologia computacional
Ensinando computadores a ler lâminas de câncer
Quando um patologista examina uma biópsia de câncer ao microscópio, ele não observa apenas células isoladas — analisa padrões, vizinhanças e como tumor, células imunes e tecido normal estão dispostos em conjunto. Os sistemas de inteligência artificial para patologia digital atuais são muito bons em detectar detalhes em pequenos fragmentos de imagem, mas frequentemente perdem essa visão mais ampla. Este estudo apresenta o EAGLE-Net, uma nova abordagem de IA que ajuda computadores a enxergar lâminas de câncer de forma mais parecida com especialistas humanos, prestando atenção tanto aos detalhes locais quanto à disposição geral do tecido na lâmina.

Por que a disposição do tecido tumoral importa
Um tumor é mais do que um amontoado de células cancerosas. Ele vive em um bairro ativo cheio de vasos sanguíneos, células imunes, tecido conjuntivo e áreas de cicatrização ou morte celular. Como esses elementos se organizam — suas distâncias, limites e misturas — pode indicar quão agressivo é o câncer e como o paciente pode responder ao tratamento. Sistemas convencionais de IA em patologia geralmente dividem uma imagem de lâmina inteira em milhares de pequenos azulejos e os analisam quase isoladamente. Depois, tentam inferir o diagnóstico ou desfecho do paciente agregando informação de todos os azulejos. Essa estratégia muitas vezes ignora como os azulejos se relacionam espacialmente, o que pode enfraquecer as previsões e fazer com que os mapas de atenção da IA fiquem dispersos ou difíceis de interpretar.
Uma nova forma de captar a imagem maior
O EAGLE-Net foi projetado para preencher essa lacuna entre detalhe local e estrutura global. Ele parte de “modelos de base” poderosos que já sabem extrair características visuais ricas de pequenos fragmentos de lâmina. Sobre isso, adiciona um novo módulo que codifica de onde cada fragmento veio na lâmina, preservando a geometria real do tecido em vez de comprimí-la em uma grade distorcida. Usando filtros em múltiplas escalas, o EAGLE-Net aprende padrões que vão desde mudanças microscópicas ao nível celular até estruturas de tecido mais amplas como bordas tumorais e estroma circundante. Em seguida, usa um mecanismo de atenção — essencialmente uma forma de atribuir pontuações de importância — para focar em fragmentos e vizinhanças que são mais relevantes para prever diagnóstico ou sobrevida.
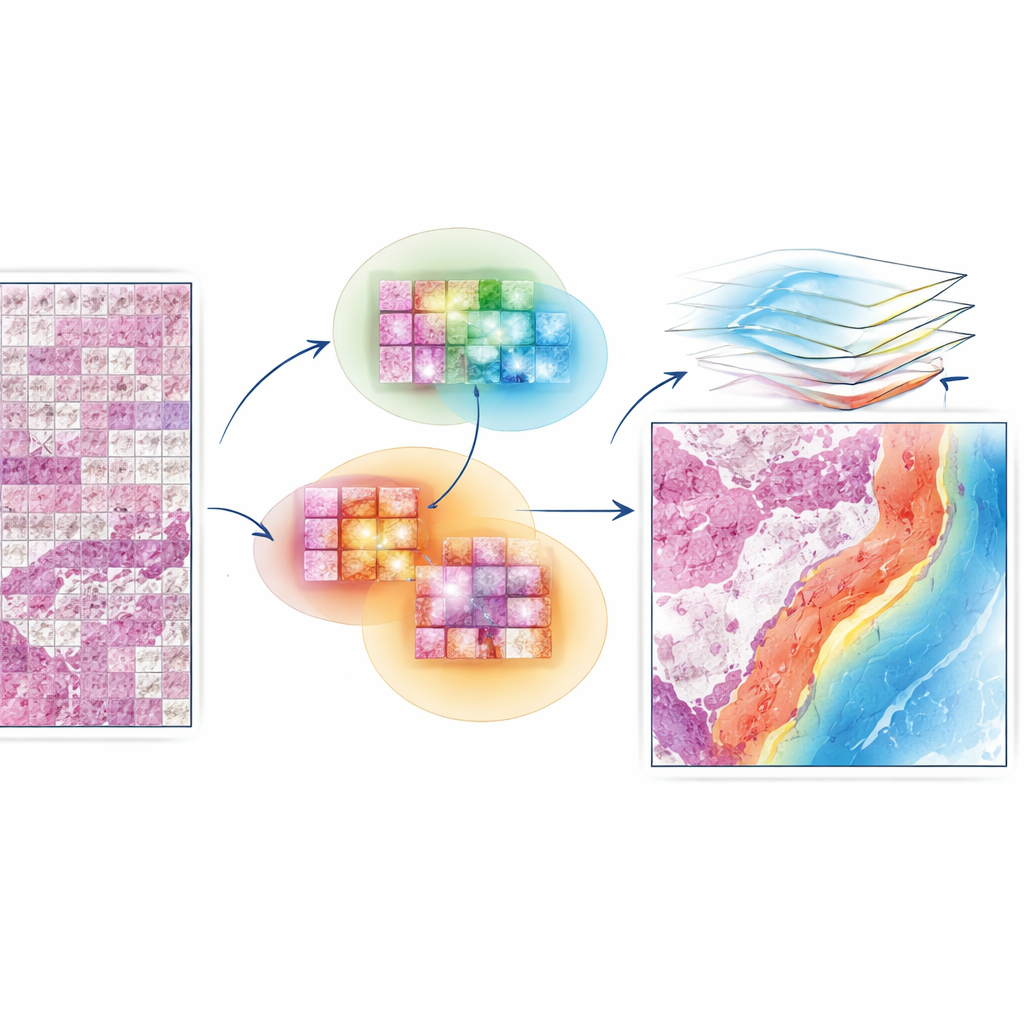
Deixando o modelo aprender com vizinhanças, não apenas pontos
Uma inovação chave do EAGLE-Net é como ele ensina a rede a valorizar não apenas os azulejos mais importantes, mas também seus vizinhos próximos. Durante o treinamento, o método identifica repetidamente os azulejos que o modelo considera mais informativos e então o encoraja a considerar azulejos circundantes dentro de um pequeno raio como parte da mesma região significativa. Esse aprendizado “consciente da vizinhança” conduz o modelo a formar regiões de atenção suaves e contínuas que se alinham com a forma como patologistas observam frentes tumorais, aglomerados imunes e outros microambientes. Ao mesmo tempo, um termo adicional no processo de treino empurra o modelo a ignorar planos de fundo ou áreas vazias, reduzindo o risco de destaques falsos em artefatos isolados ou espaços em branco.
Comprovando seu valor em muitos tipos de câncer
Os pesquisadores testaram o EAGLE-Net em quase 15.000 imagens de lâminas inteiras cobrindo 10 tipos diferentes de câncer, incluindo tumores de pulmão, rim, estômago, útero, tireoide, colorretal e próstata. Eles avaliaram duas tarefas principais: prever quanto tempo os pacientes viveriam e classificar tipos ou graus tumorais. Em grande parte das coortes, o EAGLE-Net igualou ou superou vários métodos baseados em atenção de ponta, frequentemente melhorando as pontuações de predição de sobrevida e a acurácia de classificação por alguns pontos percentuais, o que é relevante em escala populacional. Ele também teve desempenho forte quando combinado com três modelos de base muito diferentes, mostrando que seu desenho é flexível e não está ligado a um único extrator de características.
Vendo o raciocínio interno do modelo
Além da acurácia bruta, a equipe examinou cuidadosamente onde o EAGLE-Net “olhava” nas lâminas. Em comparação com outros métodos, seus mapas de atenção formaram regiões mais suaves e coerentes que acompanharam limites tumorais e captaram bordas invasivas, bolsões necróticos e aglomerados de células imunes. Comparações quantitativas com máscaras tumorais desenhadas por especialistas mostraram que as regiões destacadas pelo EAGLE-Net se sobrepunham melhor ao tumor verdadeiro, fizeram menos marcações falsas em tecido normal e reproduziram com mais fidelidade formas tumorais complexas. O modelo também dedicou uma parcela maior de sua atenção a compartimentos de tumor, necrose e imunes, e menos a pulmão normal ou vasos sanguíneos, espelhando o que um patologista priorizaria ao julgar o prognóstico.
O que isso significa para o cuidado do câncer no futuro
Em termos práticos, o EAGLE-Net demonstra que adicionar consciência espacial e raciocínio por vizinhança sobre IA de patologia existente pode melhorar tanto o desempenho quanto a interpretabilidade. Em vez de tratar uma lâmina como um conjunto desconectado de azulejos, o método aprende a reconhecer nichos biologicamente significativos — bordas tumorais, regiões ricas em imunes e padrões de invasão — que importam para os desfechos dos pacientes. Como funciona com vários modelos de base diferentes e não requer rotulagem por pixel intensiva em mão de obra, o EAGLE-Net poderia ser amplamente aplicado a grandes arquivos de lâminas digitais. Com validação adicional e integração em fluxos de trabalho clínicos, esses sistemas podem ajudar patologistas a estratificar pacientes com mais precisão, descobrir novos biomarcadores baseados em tecido e, em última análise, orientar tratamentos de câncer mais personalizados.
Citação: Waqas, M., Bandyopadhyay, R., Showkatian, E. et al. The next layer: augmenting foundation models with structure-preserving and attention-guided learning for local patches to global context awareness in computational pathology. npj Precis. Onc. 10, 109 (2026). https://doi.org/10.1038/s41698-026-01312-5
Palavras-chave: patologia computacional, prognóstico do câncer, IA em patologia digital, microambiente tumoral, EAGLE-Net