Clear Sky Science · pt
Traduzindo assinaturas transcriptômicas espaciais em carcinoma adenoescamoso para biomarcadores prognósticos em adenocarcinoma de pulmão: uma abordagem de baixo para cima
Sinais de alerta ocultos dentro dos tumores pulmonares
O câncer de pulmão continua sendo um dos mais letais, em parte porque os tumores são misturas de muitos tipos diferentes de células. Algumas dessas células podem, discretamente, impulsionar a doença para se tornar mais agressiva ou resistir ao tratamento, mas são tão raras ou tão integradas que não aparecem em testes laboratoriais convencionais. Este estudo mostra como “mapas” ultra-detalhados da atividade gênica dentro dos tumores podem revelar esses agentes problemáticos ocultos e transformá‑los em marcadores simples de laboratório que ajudam a prever o prognóstico de pacientes com câncer de pulmão.
Analisando mais de perto um tumor raro e misto
Os pesquisadores se concentraram em um câncer de pulmão raro chamado carcinoma adenoescamoso, que combina dois tipos principais de câncer de pulmão não pequenas células em uma única massa: o adenocarcinoma, com aparência glandular, e o carcinoma escamoso, de aspecto mais achatado e semelhante à pele. Como ambos os componentes crescem lado a lado no mesmo tumor, esse câncer é um modelo ideal para estudar como células tumorais podem mudar de identidade conforme se tornam mais malignas. Usando um método de imagem chamado transcriptômica espacial, a equipe mediu quais genes estavam ativados em milhares de células individuais preservando suas posições exatas em cortes finos de tecido tumoral. Ao mesmo tempo, usaram colorações padrão para dois marcadores diagnósticos comuns, TTF‑1 (para adenocarcinoma) e p40 (para células escamosas), para ancorar seus mapas de alta tecnologia na prática rotineira da patologia. 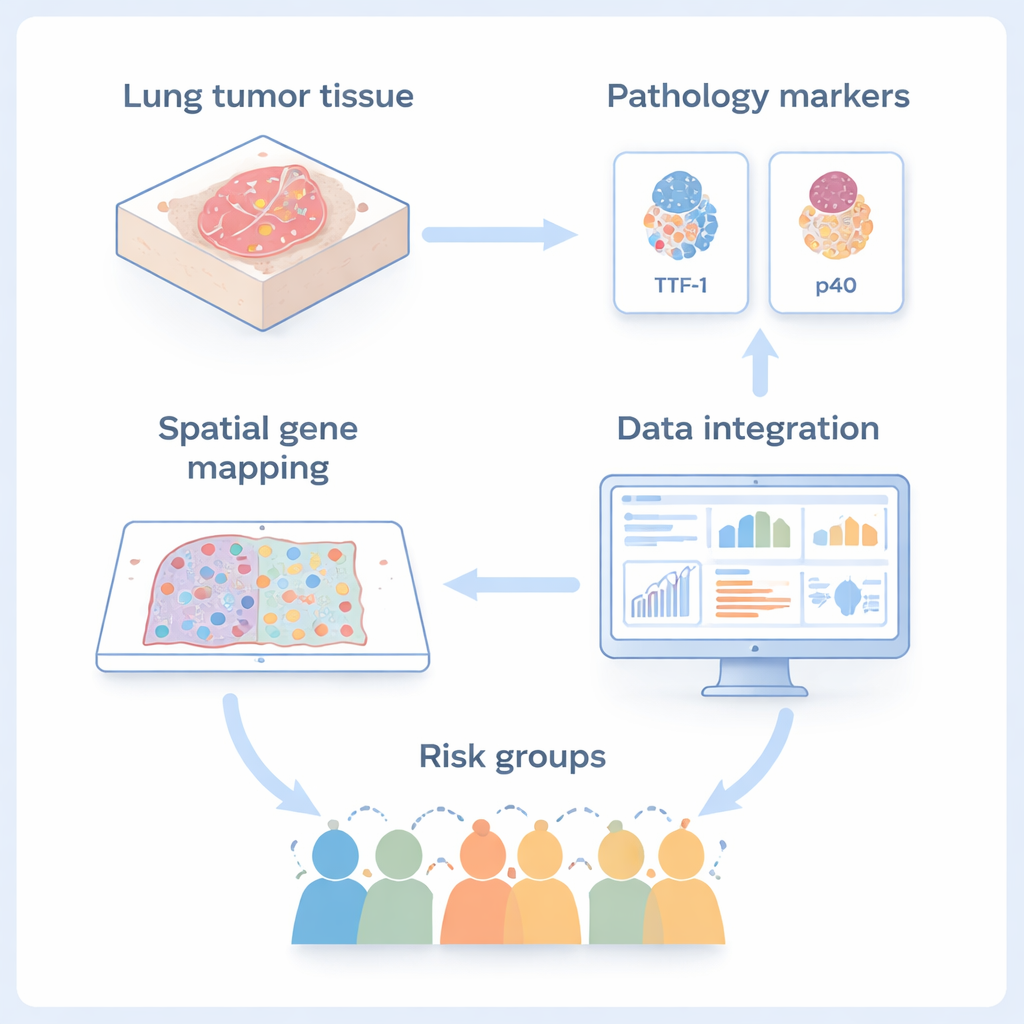
Codificando as células tumorais por cor para achar as diferentes
Apenas agrupar células por seus padrões gênicos não foi suficiente, porque células pulmonares normais e tumorais às vezes podem parecer semelhantes na leitura gênica. Para afinar a visão, a equipe usou um truque de visualização que chamam de RGB‑UMAP. Nessa abordagem, o padrão geral de atividade gênica de cada célula é compactado em três números e traduzido em uma cor vermelho‑verde‑azul. Células que se comportam de forma semelhante aparecem em cores semelhantes quando projetadas de volta na imagem do tecido. Isso permitiu aos cientistas identificar bolsões de células normais escondidas entre células tumorais e removê‑las da análise, garantindo que estudavam verdadeiras células cancerosas e não acompanhantes saudáveis.
Encontrando um estado celular híbrido e um portão chave para açúcar
Após filtrar as células normais, os pesquisadores buscaram genes fortemente e consistentemente ativos apenas nas células tumorais. Entre esses, descobriram um grupo de células tumorais que eram negativas tanto para TTF‑1 quanto para p40, mas apresentavam um padrão gênico misto, compartilhando características de adenocarcinoma e carcinoma escamoso. Um gene sobressaiu nesse grupo híbrido: SLC2A1, que codifica a proteína conhecida como GLUT1. GLUT1 atua como um portão que permite a entrada de glicose, o combustível da célula, a partir da corrente sanguínea. Em vários tumores, SLC2A1 era abundante em áreas escamosas e nas zonas negativas para TTF‑1/p40, mas quase ausente no tecido pulmonar normal. A equipe confirmou esse padrão em múltiplas amostras de pacientes, sugerindo que altos níveis de SLC2A1 marcam uma subpopulação de células cancerosas de aspecto escamoso e metabolicamente ativa.
Dos mapas microscópicos aos desfechos dos pacientes
Para testar se essa descoberta microscópica tem impacto em pacientes reais, os cientistas recorreram a grandes conjuntos de dados já existentes, nos quais a atividade gênica em nível de tumor inteiro (média sobre amostras tumorais), alterações de DNA e desfechos clínicos estavam disponíveis para centenas de pessoas com adenocarcinoma de pulmão. Quando agruparam esses pacientes pelos níveis de SLC2A1 em seus tumores, aqueles com SLC2A1 mais alto apresentaram mais alterações gênicas tipicamente observadas em cânceres escamosos, uma assinatura mais forte de metabolismo voltado ao consumo de açúcar e sobrevida significativamente pior. Essa associação manteve‑se mesmo após ajustar por fatores como idade, estágio, histórico de tabagismo e sexo, e foi confirmada em um conjunto de dados público independente. Em contraste, em tumores puramente escamosos, os níveis de SLC2A1 não separaram claramente os pacientes por desfecho, ressaltando que o marcador é especialmente informativo dentro do adenocarcinoma. 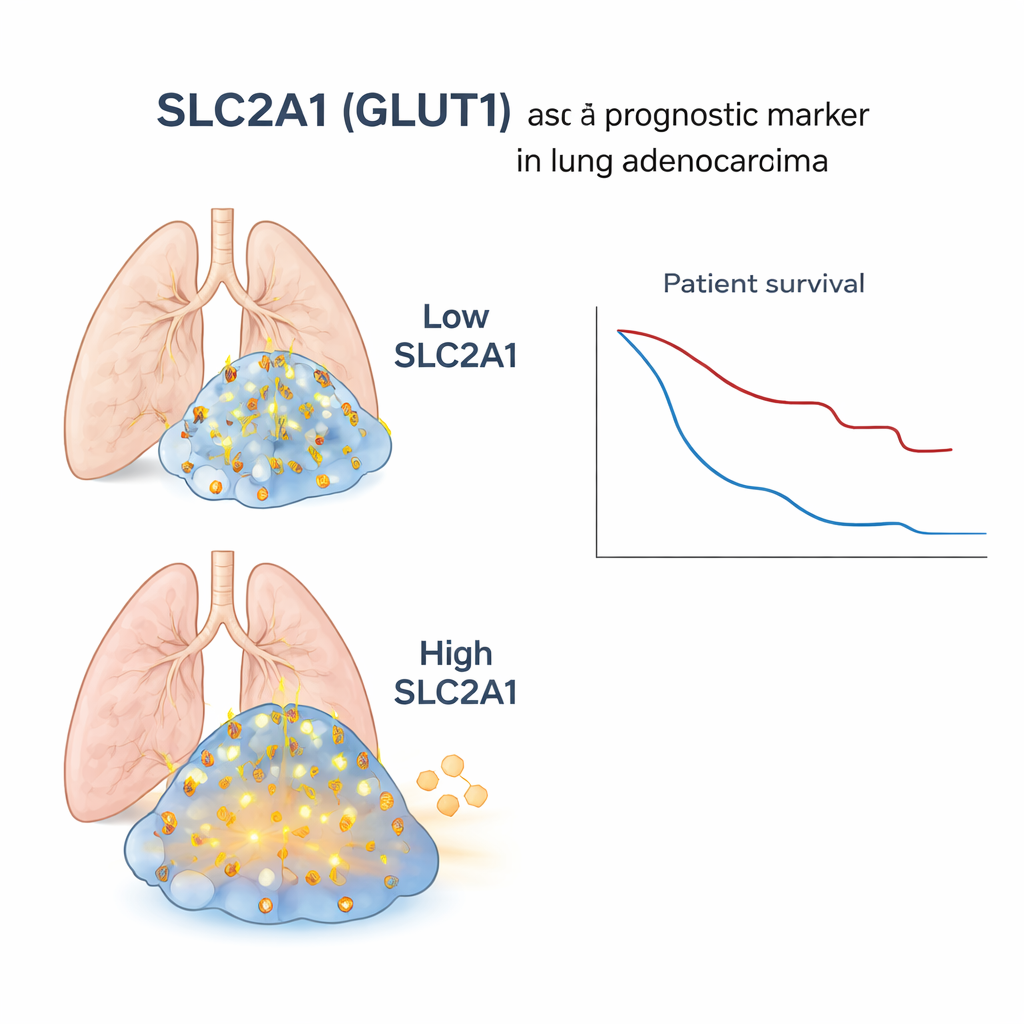
O que isso significa para pacientes com adenocarcinoma de pulmão
Para um público não especialista, a mensagem principal é que, dentro do que parece ser um único tipo de câncer de pulmão ao microscópio, pode haver bolsões ocultos de células que se comportam mais como outro tipo, mais agressivo. Ao usar mapeamento gênico de alta resolução, os pesquisadores identificaram SLC2A1 como um sinal simples e mensurável dessas células escamoso‑semelhantes e ávidas por combustível que se escondem dentro de adenocarcinomas. Níveis elevados desse gene em amostras de rotina sinalizam pacientes cujos tumores têm mais probabilidade de se comportar de forma agressiva e que podem precisar de monitoramento mais próximo ou de estratégias terapêuticas diferentes. Mais amplamente, o estudo apresenta um caminho “de baixo para cima” — das células individuais em um corte de tecido para testes em tumor inteiro — que poderia ser aplicado a outros cânceres para revelar estados celulares perigosos que métodos rotineiros atualmente deixam passar.
Citação: Hatakeyama, K., Kawata, T., Muramatsu, K. et al. Translating spatial transcriptomic signatures in adenosquamous carcinoma into bulk prognostic biomarkers in lung adenocarcinoma: a bottom-up approach. npj Precis. Onc. 10, 77 (2026). https://doi.org/10.1038/s41698-026-01297-1
Palavras-chave: adenocarcinoma de pulmão, transcriptômica espacial, carcinoma adenoescamoso, SLC2A1 GLUT1, biomarcadores de câncer